Clear Sky Science · fr
HMI-LUSC : un jeu de données d’imagerie hyperspectrale histologique pour le carcinome épidermoïde du poumon
Voir le cancer en de nouvelles couleurs
Le cancer du poumon demeure l’une des maladies les plus meurtrières au monde, en partie parce qu’identifier chaque cellule cancéreuse sur une lame de microscope est difficile et long. Les pathologistes s’appuient généralement sur des tissus colorés en rose et violet observés au microscope, une méthode qui capture la structure mais manque d’indices chimiques subtils. Cet article présente HMI‑LUSC, la première collection accessible publiquement d’images microscopiques de carcinome épidermoïde pulmonaire acquises non pas en trois couleurs, mais en des dizaines de bandes spectrales étroites, offrant aux ordinateurs et aux cliniciens une vision beaucoup plus riche de ce qui distingue les cellules tumorales de leurs voisines saines.
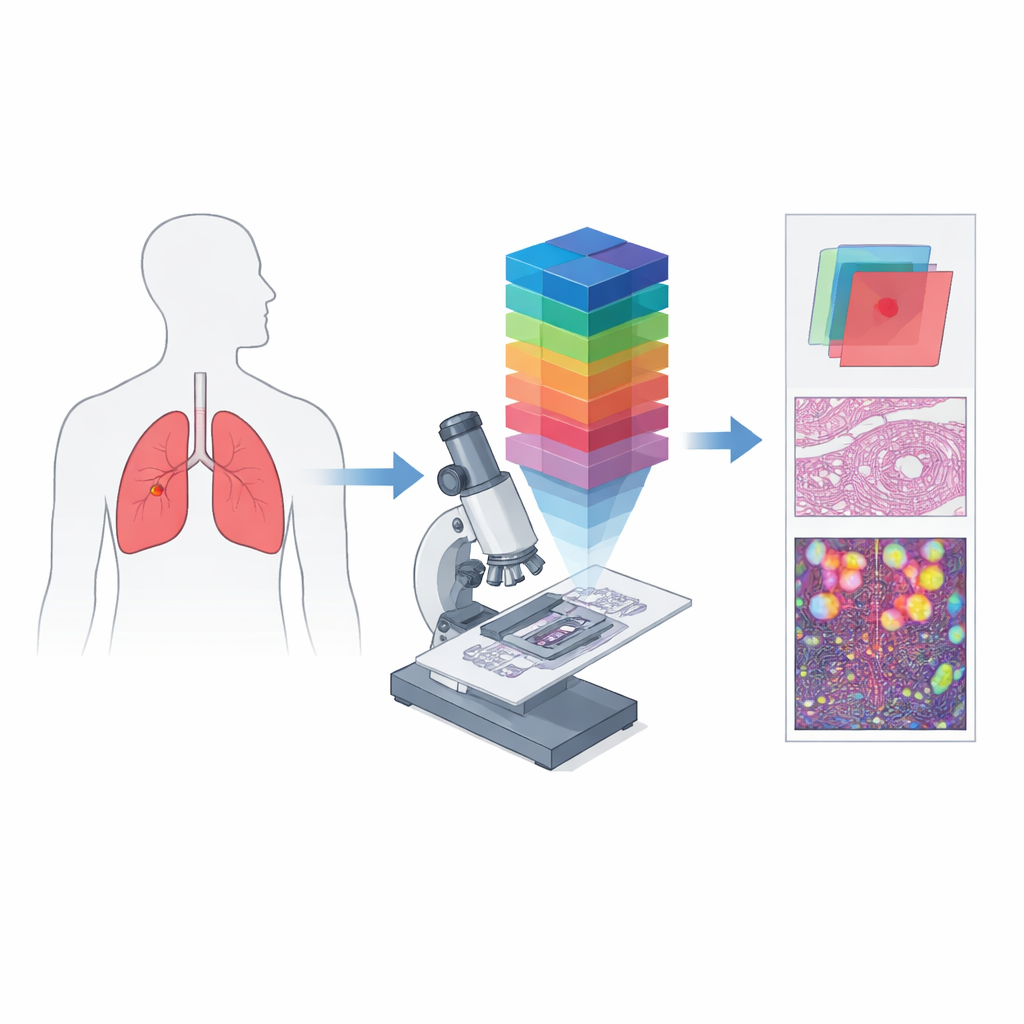
Des simples photos en couleurs aux empreintes spectrales
La pathologie numérique conventionnelle fonctionne un peu comme un appareil photo de téléphone : elle enregistre des canaux rouge, vert et bleu pour approcher ce que l’œil voit. L’imagerie hyperspectrale va plusieurs étapes plus loin en décomposant la lumière en de nombreuses longueurs d’onde rapprochées, produisant un « cube de données » tridimensionnel dans lequel chaque petit point de tissu possède son propre spectre de couleurs détaillé. Lorsqu’on associe ce principe à un microscope, on obtient l’imagerie microscopique hyperspectrale, capable de capturer à la fois la fine structure et une riche information spectrale au niveau des cellules individuelles. Ces données peuvent révéler des différences dans la façon dont les tissus absorbent et réfléchissent la lumière, invisibles sur des images standard, créant des « signatures » spectrales uniques pour les régions cancéreuses et non cancéreuses.
Construire une nouvelle bibliothèque pour l’étude du cancer du poumon
Les auteurs ont créé HMI‑LUSC pour combler une lacune évidente : avant ce travail, il n’existait pas de jeu de données hyperspectral public pour les lames de cancer du poumon, ce qui rendait difficile le test et la comparaison des méthodes diagnostiques informatisées. Ils ont collecté des tissus de dix patients opérés pour une tumeur pulmonaire, préparé des lames standard colorées à l’hématoxyline‑éosine, et les ont numérisées à haute résolution. Des pathologistes expérimentés ont marqué les zones tumorales et normales, et des régions représentatives ont été réimaginées avec un microscope hyperspectral construit sur mesure. Chaque image obtenue couvre un petit patch de tissu mais s’étend sur 61 longueurs d’onde entre 450 et 750 nanomètres, à une résolution de 3088 par 2064 pixels. Pour chaque région, le jeu de données inclut le cube spectral brut, un rendu RVB conventionnel et des masques qui délimitent la présence de tissu tumoral.
Transformer des contours grossiers en cartes au niveau cellulaire
Si les annotations au niveau de la lame sont utiles, l’entraînement des algorithmes modernes exige souvent des informations au niveau des cellules individuelles. Tracer manuellement chaque cellule est impraticable, l’équipe a donc conçu un flux de travail semi‑automatique. D’abord, les pixels ont été groupés en clusters selon leur similarité spectrale en utilisant une méthode standard de vision par ordinateur. Ensuite, les pathologistes ont inspecté ces clusters superposés à l’image tissulaire et les ont attribués à quatre catégories : cellules tumorales, cellules non tumorales, tissus non cellulaires tels que le stroma ou le sang, et fond vide. Un second pathologiste a révisé et ajusté ces résultats, les désaccords étant résolus par consensus. Le résultat est un ensemble de masques détaillés au pixel près qui capturent les mélanges subtils de types cellulaires et les zones frontalières ambiguës, fournissant un matériau d’apprentissage beaucoup plus riche pour les systèmes d’apprentissage automatique.
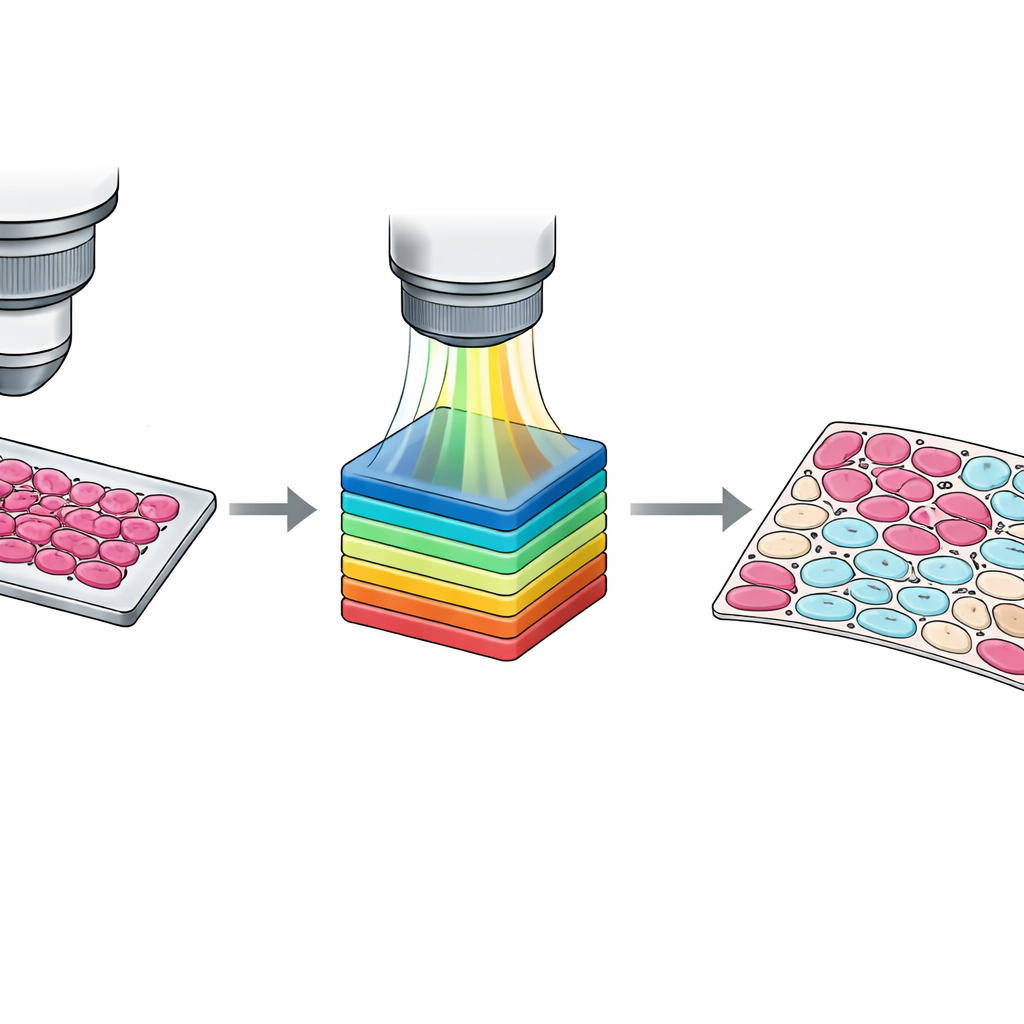
Garantir des données nettes et fiables
Pour rendre le jeu de données digne de confiance, les auteurs ont testés à fond leur système d’imagerie. Ils ont vérifié que le microscope peut résoudre des motifs fins jusqu’à environ un micron — suffisamment petit pour distinguer des cellules individuelles — et que le bruit d’image est faible sur la plupart des longueurs d’onde. Ils ont également comparé le spectre mesuré d’une source lumineuse standard avec des courbes de référence et avec une caméra hyperspectrale commerciale, trouvant un excellent accord. Enfin, ils ont démontré l’utilité des données en exécutant des modèles informatiques de référence, depuis des méthodes classiques d’apprentissage automatique jusqu’à de simples réseaux profonds, pour segmenter les régions tumorales. Même sans optimisation poussée, ces modèles ont atteint une précision solide, montrant que le jeu de données se prête bien comme référence pour les méthodes futures.
Ce que cela signifie pour les soins futurs du cancer du poumon
HMI‑LUSC ne remplace pas de vastes collections de lames standard, ni n’est encore un outil clinique autonome. Il offre plutôt aux chercheurs une fenêtre soigneusement organisée sur la façon dont les cellules tumorales pulmonaires diffèrent des tissus voisins à travers de nombreuses longueurs d’onde de la lumière. En rendant ces données, annotations et code accessibles, les auteurs fournissent un banc d’essai commun pour développer et comparer des algorithmes exploitant l’information spectrale, des classifieurs simples aux réseaux neuronaux avancés. À long terme, ce travail pourrait aider les ordinateurs à assister les pathologistes pour repérer les tumeurs plus précisément et plus rapidement, et révéler des motifs spectraux liés au type de tumeur ou à la réponse au traitement que les images ordinaires ne montrent pas.
Citation: Yan, Z., Huang, H., Guo, Y. et al. HMI-LUSC: A Histological Hyperspectral Imaging Dataset for Lung Squamous Cell Carcinoma. Sci Data 13, 415 (2026). https://doi.org/10.1038/s41597-026-06766-7
Mots-clés: imagerie hyperspectrale, cancer du poumon, pathologie numérique, segmentation de tumeur, jeu de données d’imagerie médicale