Clear Sky Science · fr
Profil métabolomique et transcriptomique de deux espèces étroitement apparentées du genre Oldenlandia
Pourquoi ces modestes herbes comptent
Deux petites plantes adventices utilisées dans la médecine traditionnelle asiatique, Oldenlandia diffusa et Oldenlandia corymbosa, sont largement employées pour des problèmes allant de l’inflammation aux maladies du foie et au cancer. Pourtant, malgré leur longue histoire dans les remèdes à base de plantes et leur mélange fréquent sur le marché, nous savons encore étonnamment peu sur ce qui les distingue réellement à l’intérieur : quels ingrédients chimiques elles produisent, dans quelles parties de la plante, et quels gènes contrôlent ces ingrédients. Cette étude ouvre ce monde caché en fournissant une cartographie détaillée à la fois des molécules et de l’activité génique dans différents tissus des deux espèces.
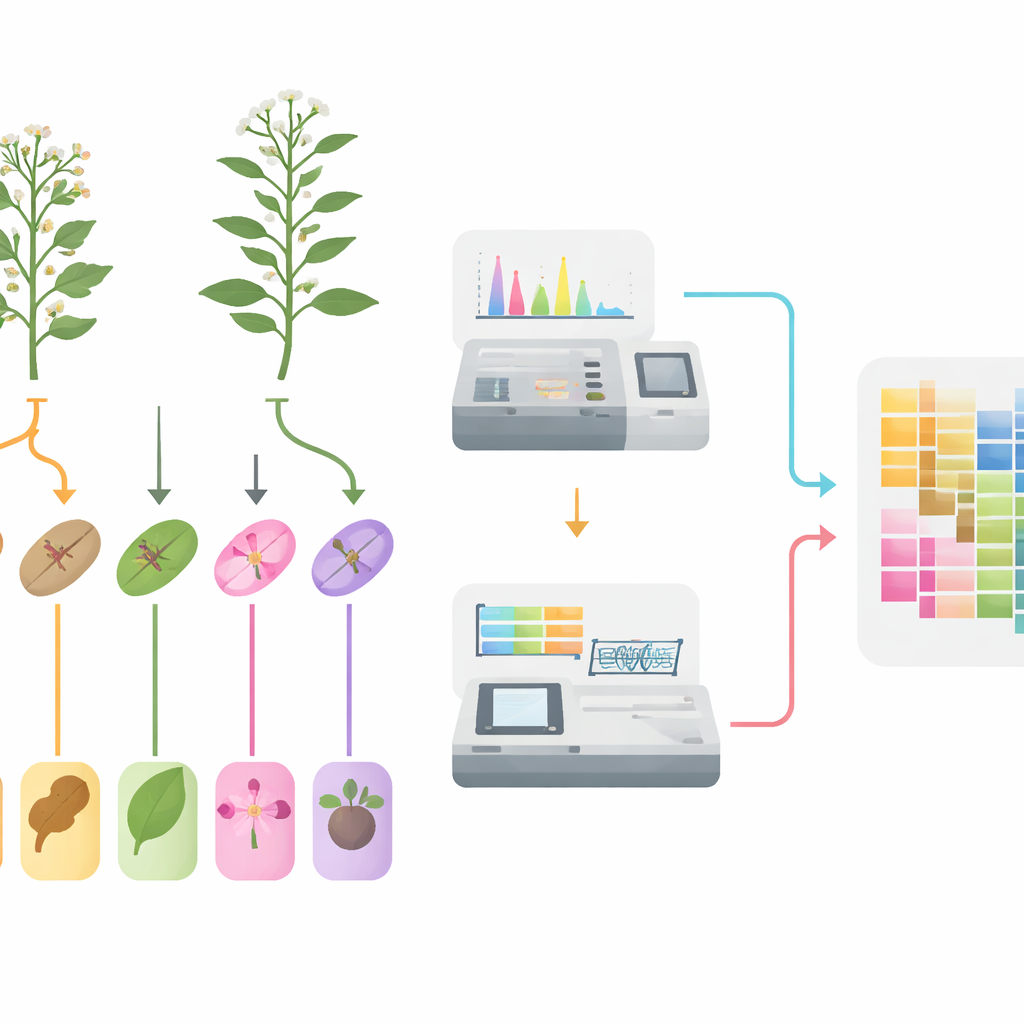
Du champ aux échantillons congelés
Les chercheurs ont commencé par cultiver les deux espèces côte à côte dans les mêmes conditions de champ afin d’éviter tout biais environnemental. Pendant la floraison, ils ont séparé avec soin cinq tissus : racines, tiges, feuilles, fleurs et fruits, prélevés sur plusieurs plantes de chaque espèce. Pour obtenir une image fiable de la variation naturelle, ils ont poolé du matériel provenant de nombreux individus et créé six réplications biologiques pour chaque type de tissu. Chaque échantillon de tissu a ensuite été divisé en deux : une partie pour mesurer les petites molécules, et une partie pour déterminer quels gènes étaient activés.
Inventorier des milliers de composés végétaux
Pour cataloguer la composition chimique des plantes, l’équipe a utilisé une approche sensible basée sur la spectrométrie de masse capable de suivre un très grand nombre de métabolites végétaux connus en une seule analyse. Sur 60 échantillons, ils ont détecté 1 342 petites molécules distinctes, dominées par des groupes déjà soupçonnés d’être importants en médecine : près d’un quart étaient des flavonoïdes, suivis par des acides phénoliques, des alcaloïdes et des terpénoïdes. Des analyses statistiques ont montré que les échantillons tissulaires se regroupaient nettement par type, et les contrôles de qualité ont confirmé la stabilité et la reproductibilité des mesures. La comparaison d’un même tissu entre les deux espèces a révélé de nombreuses molécules beaucoup plus abondantes dans l’une que dans l’autre, en particulier dans des voies liées aux pigments de couleur, aux composés de défense et à d’autres métabolites spécialisés des plantes.
Lire le mode d’emploi des plantes
En parallèle, les scientifiques ont extrait l’ARN des mêmes tissus pour voir quels gènes étaient actifs, capturant ainsi les instructions internes des plantes au moment de l’échantillonnage. Le séquençage à haut débit a généré plus de 500 gigabases de données de haute qualité et conduit à l’identification de 37 644 gènes chez Oldenlandia diffusa et de 20 825 gènes chez Oldenlandia corymbosa. Là encore, les échantillons d’un même tissu se regroupaient, soulignant la fiabilité des données. En comparant les tissus, l’équipe a trouvé des milliers de gènes se comportant différemment entre les racines et les parties aériennes, ou entre tiges, feuilles, fleurs et fruits. Beaucoup de ces gènes sont impliqués dans la capture d’énergie, le métabolisme de base et des enzymes qui modifient les composés végétaux — exactement les types d’activités qui déterminent où les composés médicinaux sont synthétisés et stockés.
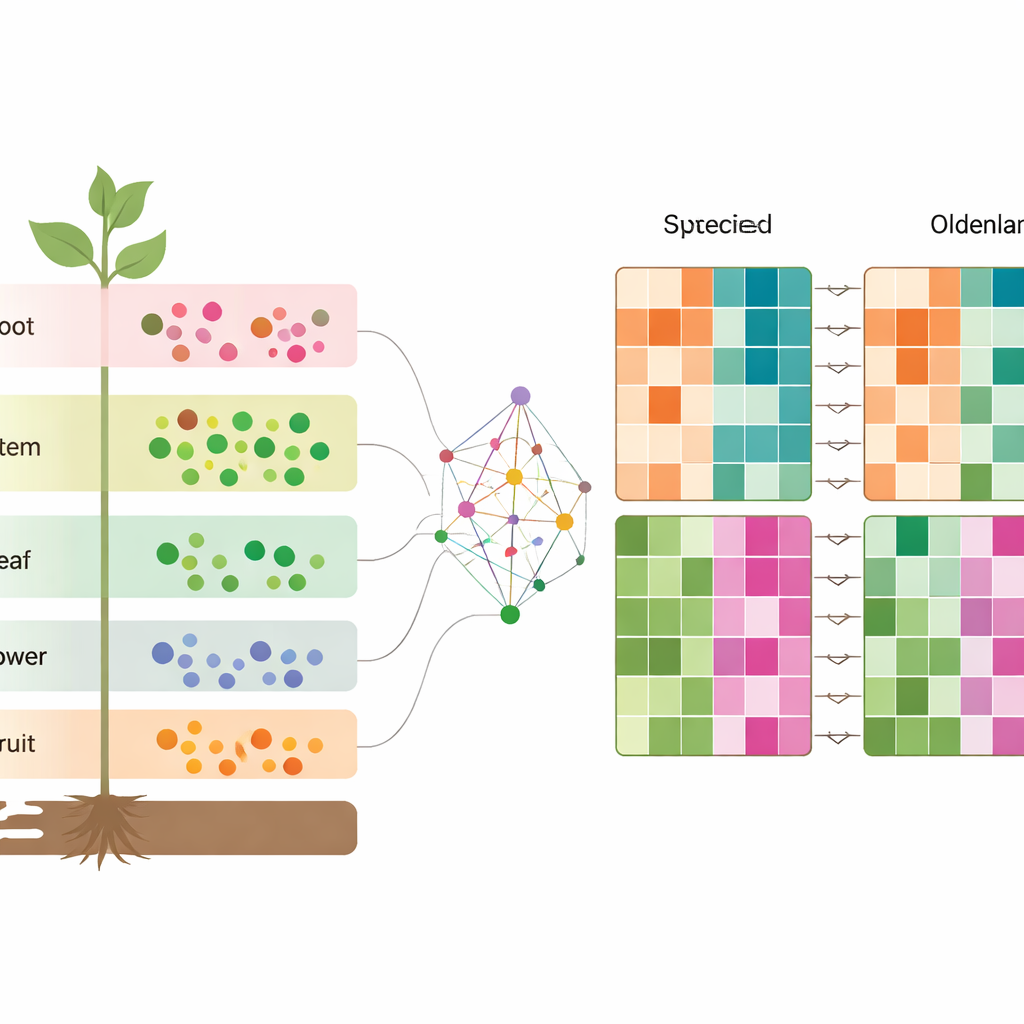
Zoom sur les différences entre les deux espèces
Pour comprendre ce qui sépare réellement les espèces, les auteurs ont apparié les gènes d’O. diffusa et d’O. corymbosa qui sont des homologues directs, puis ont comparé leur activité dans chaque tissu. Ils ont découvert des milliers de gènes up‑ ou down‑régulés dans une espèce par rapport à l’autre dans les racines, tiges, feuilles, fleurs et fruits. Ces gènes appartiennent à des voies qui fabriquent et transforment des composés clés, notamment des terpénoïdes, des phénylpropanoïdes et divers composés azotés. Associées aux données métabolitiques, ces observations révèlent une image à plusieurs niveaux : chaque tissu possède son propre profil chimique et génétique, et ces profils varient de façon caractéristique entre les deux herbes étroitement apparentées.
Ce que cela signifie pour la médecine et la recherche future
Pour le non‑spécialiste, la conclusion principale est que ces deux plantes médicinales ressemblantes ne sont pas interchangeables. Sous leur apparence similaire, leurs racines, tiges, feuilles, fleurs et fruits diffèrent tant par les quantités de petites molécules importantes que par l’activité des gènes qui synthétisent ces molécules. En publiant cet important jeu de données largement validé, l’étude fournit une atlas de référence que d’autres chercheurs pourront exploiter pour identifier quels ingrédients peuvent être responsables d’effets de santé spécifiques, et quels gènes pourraient être ciblés pour sélectionner ou modifier des plantes aux propriétés plus cohérentes et plus puissantes. En fin de compte, ce type de cartographie approfondie peut aider à transformer des mélanges traditionnels d’herbes en médicaments mieux compris et plus précisément utilisés.
Citation: Chen, P., Huang, Z., Wen, Y. et al. Metabolomic and Transcriptomic Profiling of Two Closely Related Species within the Genus Oldenlandia. Sci Data 13, 378 (2026). https://doi.org/10.1038/s41597-026-06745-y
Mots-clés: Oldenlandia, plantes médicinales, métabolomique, transcriptomique, métabolites secondaires des plantes