Clear Sky Science · fr
Jeu de données métagénomiques avec résolution en profondeur des couches de surface et du maximum de chlorophylle dans l’ouest de l’océan Pacifique
Pourquoi la vie microscopique océanique compte
Les eaux bleues et limpides du Pacifique ouvert peuvent sembler vides, mais elles regorgent de vie microscopique qui gère discrètement une grande partie de la chimie de notre planète. Ces microbes planctoniques aident à déplacer le carbone, l’azote et d’autres éléments dans l’océan, influençant tout, des pêcheries au climat. Cette étude ne se contente pas de décrire quelques nouvelles espèces : elle fournit un vaste jeu de données ouvert qui capture qui sont ces microbes et ce qu’ils peuvent faire à différentes profondeurs dans une région éloignée de l’ouest du Pacifique. Ces informations deviennent une ressource partagée pour les scientifiques cherchant à comprendre et prévoir comment l’océan réagira à un climat en mutation.
Regarder dans une couche verte cachée
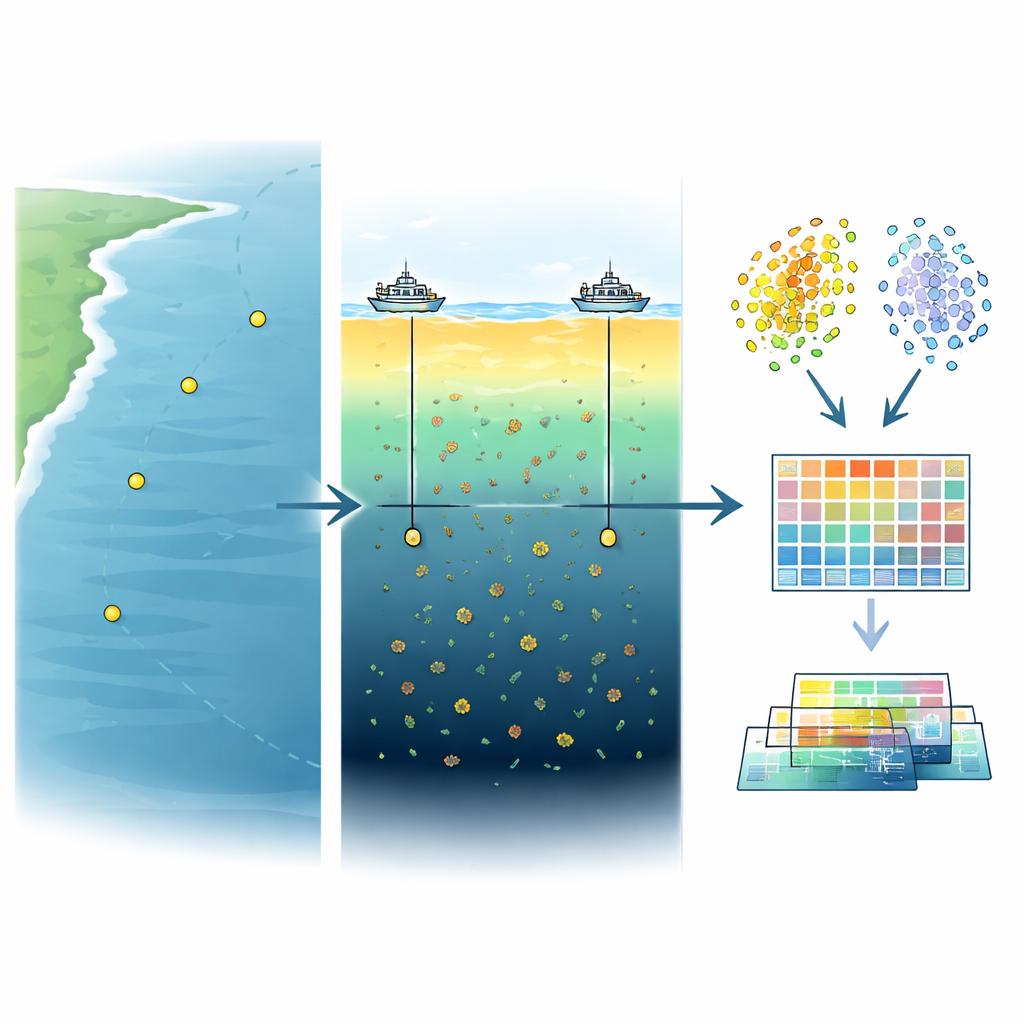
Les chercheurs se sont concentrés sur deux couches superposées de la mer : la surface éclairée par le soleil, où la lumière est la plus intense, et une bande un peu plus profonde appelée maximum de chlorophylle profond. Dans cette couche verte cachée, généralement située entre 75 et 100 mètres, les plantes microscopiques et autres minuscules organismes atteignent souvent leur abondance maximale même si la lumière est plus faible. En échantillonnant ces deux couches à quatre stations réparties sur environ 800 kilomètres de l’ouest du Pacifique, l’équipe a pu comparer comment les communautés microbiennes varient avec la profondeur et la distance. Cette région est particulièrement importante car elle est sensible aux variations de température et de nutriments entraînées par le climat et la circulation océanique.
Transformer l’eau de mer en ADN numérique
Pour capturer ces communautés, l’équipe a filtré environ 75 litres d’eau de mer par échantillon pour collecter les microbes, a congelé les filtres, puis a extrait leur ADN en conditions de laboratoire strictement contrôlées afin d’éviter toute contamination. Ils ont ensuite utilisé un séquençage ADN à haut débit pour lire des milliards de petits fragments de matériel génétique à partir de huit échantillons (quatre de surface, quatre profonds). Après nettoyage et contrôle de la qualité des données, ils ont assemblé numériquement les fragments en séquences d’ADN plus longues et les ont analysées à la recherche de gènes. Le résultat final est une vaste collection d’environ 5,26 millions de gènes non redondants — un catalogue énorme montrant les capacités potentielles de ces microbes marins.
Qui vit où dans la colonne d’eau
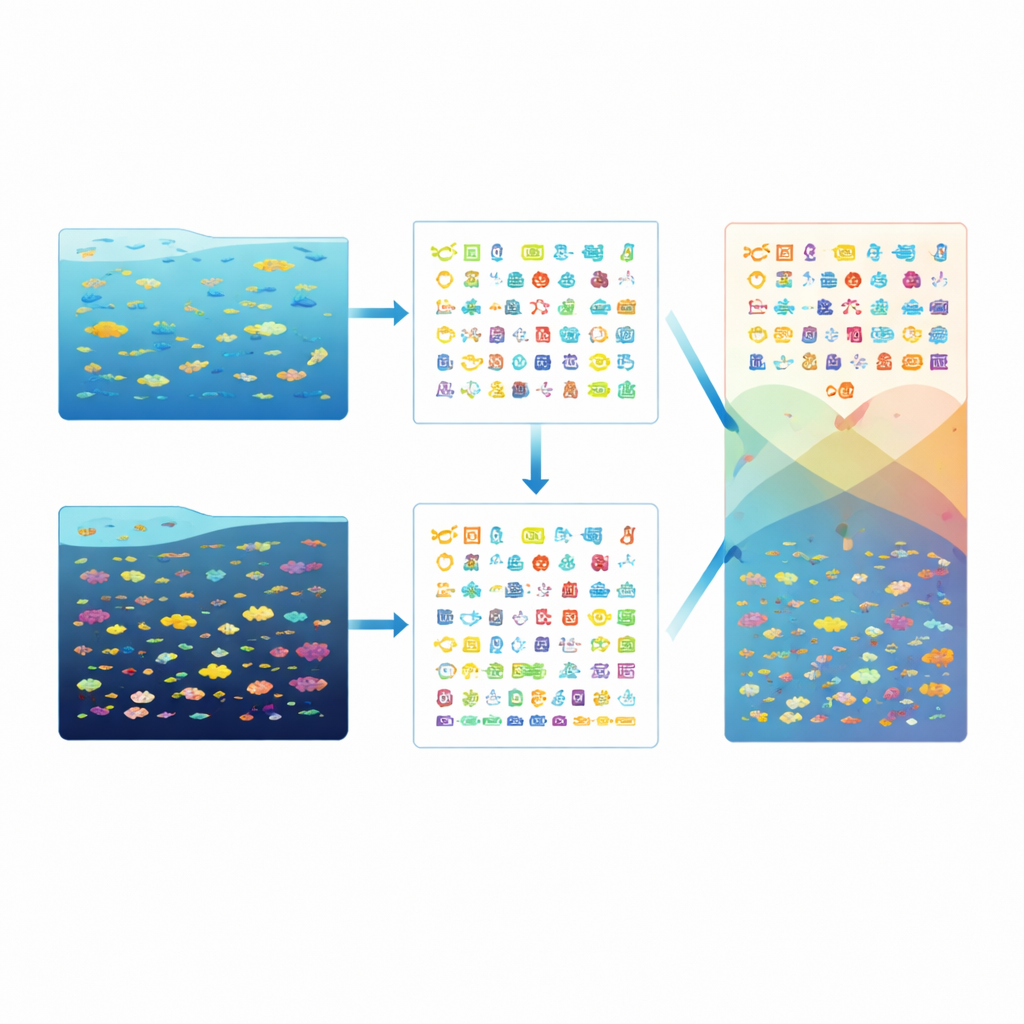
Lorsque l’équipe a trié l’ADN pour identifier les types d’organismes présents, elle a constaté que chaque échantillon contenait un mélange remarquablement riche de formes de vie : entre 58 et 67 lignées majeures (phyla), plus de 100 classes et plus de 6 000 espèces par station. Pourtant, l’équilibre changeait avec la profondeur. Les eucaryotes — organismes aux cellules plus complexes, incluant de nombreux types d’algues microscopiques — étaient plus fréquents dans la couche profonde riche en chlorophylle, tandis que certaines bactéries qui prospèrent en surface, dans des eaux bien éclairées et pauvres en nutriments, devenaient moins abondantes avec la profondeur. D’autres groupes bactériens étaient enrichis dans la couche profonde, révélant un schéma vertical clair quant aux dominances dans chaque zone de la colonne d’eau.
Ce que les gènes microbiens révèlent sur le travail océanique
Au-delà du simple dénombrement des espèces, les chercheurs ont examiné ce que les gènes eux-mêmes suggèrent sur le fonctionnement de ces communautés. En comparant leur catalogue de gènes à plusieurs bases de données de référence, ils ont pu attribuer des fonctions probables à de nombreux gènes, y compris ceux impliqués dans l’utilisation de différentes formes de carbone, d’azote et de soufre. Des analyses statistiques ont recherché les gènes plus fréquents à une profondeur ou une station qu’à une autre, mettant en évidence comment la température, l’oxygène et les niveaux de nutriments peuvent façonner les « boîtes à outils » que portent ces microbes. Les contrôles de qualité sur le séquençage, l’assemblage et l’annotation montrent que le jeu de données est suffisamment complet et fiable pour servir de référence.
Une ressource partagée pour les questions océanographiques futures
Plutôt que de tirer une conclusion étroite et unique, ce travail livre un catalogue d’ADN et de gènes bien documenté et accessible au public que d’autres pourront exploiter pour répondre à de nombreuses questions. Il offre un instantané détaillé de la façon dont la vie microscopique est organisée de la surface au maximum de chlorophylle profond dans une région clé de l’ouest du Pacifique, ainsi que les plans génétiques qui permettent à ces organismes de conduire des cycles chimiques vitaux. Pour les non-spécialistes, la leçon est simple : l’océan bleu apparemment vide cache des communautés microbiennes stratifiées et dynamiques, et ce jeu de données ouvert donne aux scientifiques un nouvel outil puissant pour observer comment ces couches vivantes pourraient changer à mesure que la planète se réchauffe.
Citation: Thangaraj, S., Sun, J. Depth Resolved Metagenomic Dataset from Surface and Deep Chlorophyll Maximum Layers in the Western Pacific Ocean. Sci Data 13, 324 (2026). https://doi.org/10.1038/s41597-026-06706-5
Mots-clés: microbiome marin, métagénomique, océan Pacifique occidental, maximum de chlorophylle profond, biogéochimie océanique