Clear Sky Science · fr
Une ressource organisée de génomes chimiolithoautotrophes et de gènes marqueurs pour la prédiction des voies de fixation du CO₂
Des micro‑organismes qui contribuent à l’équilibre du bilan carbone de la Terre
Cachés dans les sols, les océans et des milieux extrêmes, certains micro‑organismes peuvent synthétiser leur propre biomasse en utilisant le dioxyde de carbone (CO₂) comme source principale de carbone. Ces « chimistes » microscopiques sont essentiels pour maintenir l’équilibre du cycle du carbone terrestre et pourraient inspirer de nouvelles méthodes de capture du CO₂ industriel. Jusqu’à présent, les scientifiques manquaient toutefois d’un moyen simple et fiable pour lire l’ADN d’un microbe et déterminer quelle stratégie de fixation du CO₂ il utilise. Cette étude présente un catalogue de gènes triés sur le volet et un nouvel outil informatique, AutoFixMark, conçus pour combler cette lacune.
Plusieurs voies pour convertir l’air en biomasse
Tous les organismes fixant le CO₂ ne procèdent pas de la même manière. Les microbes ont développé au moins sept voies naturelles qui transforment le CO₂ en matière organique. Certaines, comme le cycle de Calvin–Benson–Bassham courant chez les plantes et de nombreuses bactéries, sont bien connues ; d’autres, comme la voie réductive de la glycine découverte seulement en 2020, restent peu documentées. Ces voies se retrouvent chez de nombreux embranchements de l’arbre de la vie et réutilisent souvent des enzymes similaires, ce qui complique la distinction par simple séquence génomique. Les logiciels existants peuvent prédire des capacités métaboliques globales, mais ils n’ont pas été optimisés ni testés de manière approfondie pour identifier précisément les voies de fixation du CO₂.
Construire une carte de référence propre des microbes fixateurs de CO₂
Les chercheurs ont commencé par assembler deux collections de génomes soigneusement vérifiées. D’abord, ils ont sélectionné 15 micro‑organismes bien étudiés dont les voies de fixation du CO₂ ont été décrites en détail. Ces organismes de référence, couvrant plusieurs groupes bactériens et archéens, ont servi de modèles pour définir les enzymes clés véritablement distinctives de chaque voie. Ensuite, ils ont constitué un ensemble de référence de 347 génomes chimiolithoautotrophes — des microbes qui tirent leur énergie de produits chimiques inorganiques et construisent leur biomasse à partir du CO₂. Chaque génome de ce grand ensemble a été associé manuellement, à partir de la littérature, à des voies de fixation du CO₂ spécifiques, fournissant un jeu de vérité solide pour tester les prédictions.
Gènes marqueurs et règles simples au lieu de boîtes noires
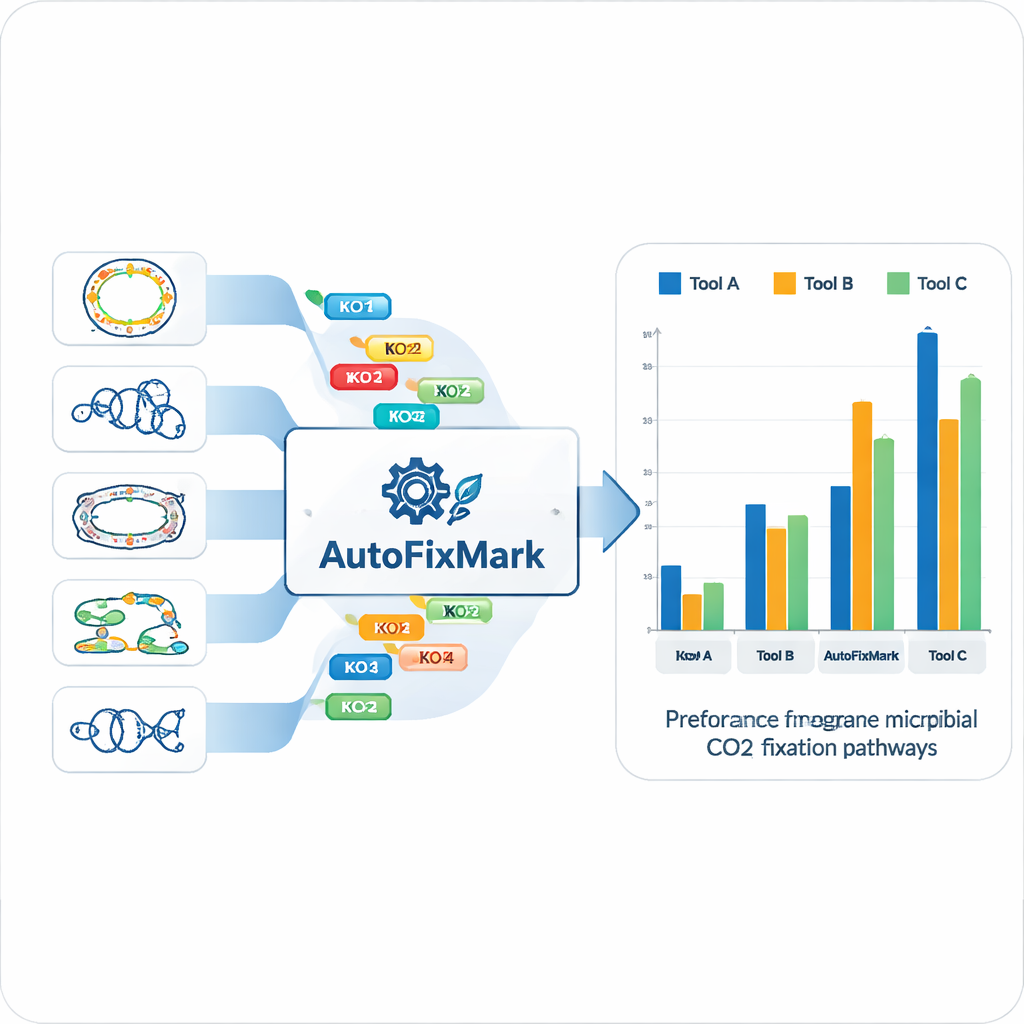
À partir des 15 génomes de référence, l’équipe a identifié des « gènes marqueurs » pour chacune des sept voies de fixation du CO₂ et les a mappés à des identifiants KEGG Orthology (KO) standardisés. Plutôt que de s’appuyer sur des méthodes d’apprentissage automatique opaques, elle a codé des règles transparentes expliquant comment ces marqueurs se combinent. Certaines réactions peuvent être catalysées par l’une ou l’autre de plusieurs enzymes de substitution, traitées par une règle « one_of ». D’autres font intervenir des complexes multi‑sous‑unités et exigent « all_of » un ensemble défini de KO. Pour la voie réductive de la glycine, dont tous les composants ne sont pas encore complètement compris, l’outil utilise des règles « at_least » qui requièrent la présence d’un nombre minimum de sous‑unités. Ces règles logiques sont stockées dans un fichier JSON lisible par machine qui constitue la base de connaissances d’AutoFixMark.
Un outil léger qui dépasse les logiciels établis
AutoFixMark est un petit programme basé sur des règles, écrit en Python. Il prend en entrée une liste d’identifiants KO pour les gènes d’un génome microbien, généralement produite par un autre outil appelé KofamScan, puis vérifie quelles règles de marqueurs sont satisfaites pour chacune des sept voies. Les auteurs ont comparé AutoFixMark à deux outils d’annotation métabolique largement utilisés, METABOLIC et gapseq, en s’appuyant sur leur ensemble de référence de 347 génomes. Les trois outils ont donné de bons résultats pour des voies classiques comme le cycle de Calvin, le cycle tricarboxylique réductif et la voie de Wood–Ljungdahl. Cependant, AutoFixMark s’est nettement démarqué pour des voies plus récentes ou moins courantes telles que le cycle 3‑hydroxypropionate/4‑hydroxybutyrate, le cycle dicarboxylate/4‑hydroxybutyrate et la voie réductive de la glycine, dont certaines ne sont même pas prises en charge par les logiciels concurrents.
Ce que ces résultats signifient pour les études climatiques et écologiques
Les jeux de gènes triés, le programme AutoFixMark et l’ensemble complet de génomes de référence sont disponibles publiquement. Les chercheurs peuvent désormais analyser aussi bien des microbes isolés que des génomes assemblés à partir de métagénomes pour déterminer quelles stratégies de fixation du CO₂ ils sont génétiquement aptes à utiliser. Il est important de noter que les auteurs insistent sur le fait qu’AutoFixMark prédit un potentiel génétique, et non l’activité effective d’une voie en conditions réelles. Nombre de ces voies biochimiques peuvent fonctionner en sens inverse, selon l’équilibre énergétique de la cellule. Néanmoins, disposer d’un moyen robuste et transparent pour identifier les microbes fixateurs de CO₂ aidera les scientifiques à cartographier où et comment la vie retire le carbone de l’atmosphère, à orienter les expérimentations sur des voies émergentes et à soutenir la conception de futures biotechnologies basées sur le CO₂.
Citation: Kawashima, S., Okabeppu, Y., Miyazawa, S. et al. A curated resource of chemolithoautotrophic genomes and marker genes for CO₂ fixation pathway prediction. Sci Data 13, 121 (2026). https://doi.org/10.1038/s41597-026-06655-z
Mots-clés: fixation microbienne du carbone, métabolisme autotrophe, annotation de génome, captage du CO2