Clear Sky Science · fr
Un jeu de données annoté de colorations de Gram provenant d’hémocultures positives
Pourquoi des réponses rapides aux infections sont cruciales
Lorsque des bactéries ou des champignons pénètrent dans le sang, chaque heure sans traitement adapté peut faire la différence entre la vie et la mort. Les médecins s’appuient sur un examen de laboratoire rapide appelé coloration de Gram pour identifier le type d’agent et choisir des antibiotiques précoces. Mais l’interprétation de ces lames colorées au microscope est un travail manuel et spécialisé, qui prend du temps et peut varier d’un technologue à l’autre. Cette étude décrit une nouvelle collection d’images issues de lames d’hémocultures réelles, soigneusement annotée, conçue pour aider les ordinateurs à apprendre à lire automatiquement les colorations de Gram et à soutenir une prise en charge plus rapide et plus fiable.
Transformer des lames hospitalières réelles en données
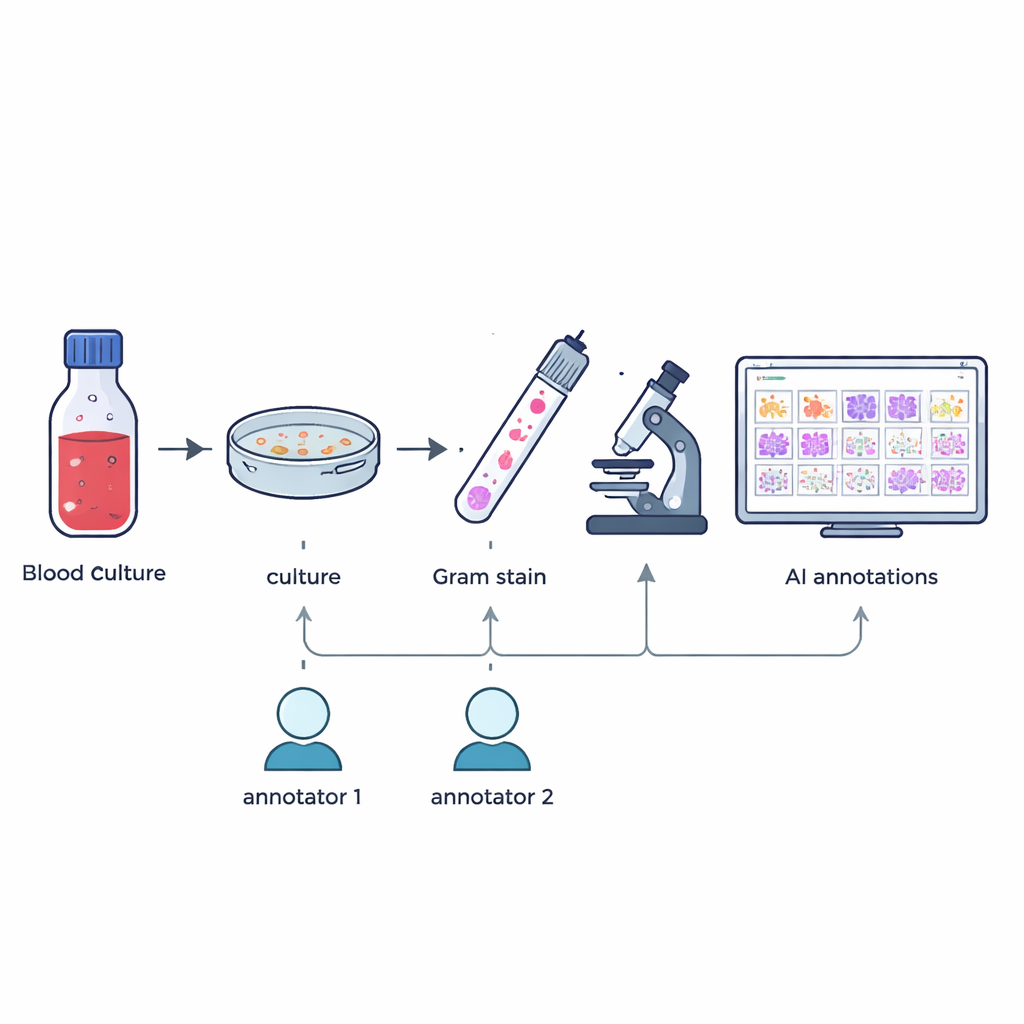
Les chercheurs ont rassemblé 57 espèces différentes de bactéries et de champignons cultivées à partir de flacons d’hémoculture positifs prélevés dans le cadre du travail hospitalier courant. De janvier à mai 2024, dès qu’un flacon signalait une positivité, le personnel préparait des frottis colorés selon la méthode de Gram sur lames de verre et confirmait l’espèce exacte par une méthode d’identification haute précision appelée spectrométrie de masse MALDI-TOF. Sans modifier les routines normales ni prélever d’échantillons supplémentaires, l’équipe a ensuite capturé des images numériques en haute résolution de champs typiques au microscope à immersion à 100×, aboutissant à 505 grandes images en couleur qui reflètent ce que voient les technologues en pratique réelle.
Annotation précise de formes minuscules
Construire un jeu d’entraînement utile pour l’intelligence artificielle suppose de connaître exactement où se trouve chaque microbe dans chaque image. Deux technologistes en microbiologie expérimentés ont tracé indépendamment des encadrés autour des cellules microbiennes individuelles ou des amas dans chaque image, guidés uniquement par ce qu’ils voyaient au microscope. Un outil logiciel sur mesure a comparé les deux jeux de marquages : les encadrés suffisamment chevauchants ont été fusionnés et les divergences ont été signalées. Un expert senior, riche de plus de 20 ans d’expérience, a ensuite examiné ces cas à la main. Ce processus en plusieurs étapes a produit 7 528 annotations vérifiées mettant en évidence des cocci (cellules rondes), des bacilles (cellules en bâtonnets) et des champignons, tout en écartant les objets partiels ou douteux.
Ce que contient le jeu de données
La ressource finale combine plusieurs couches d’information. Les 505 images sont fournies en fichiers JPEG haute résolution, et les encadrés finaux validés par des experts sont stockés au format JSON COCO standard, largement utilisé en vision par ordinateur. Des fichiers supplémentaires relient chaque image à l’espèce microbienne, à son statut Gram positif ou Gram négatif, à son groupe de morphologie général, au type de flacon d’hémoculture dont elle provient et au temps nécessaire pour que la culture devienne positive. Comme chaque image contient une seule espèce, tous les encadrés d’une image donnée partagent les mêmes caractéristiques biologiques. Les utilisateurs peuvent choisir entre un unique fichier d’annotations volumineux ou des fichiers séparés par image, et un script Python simple est inclus pour visualiser n’importe quelle image avec ses encadrés superposés.
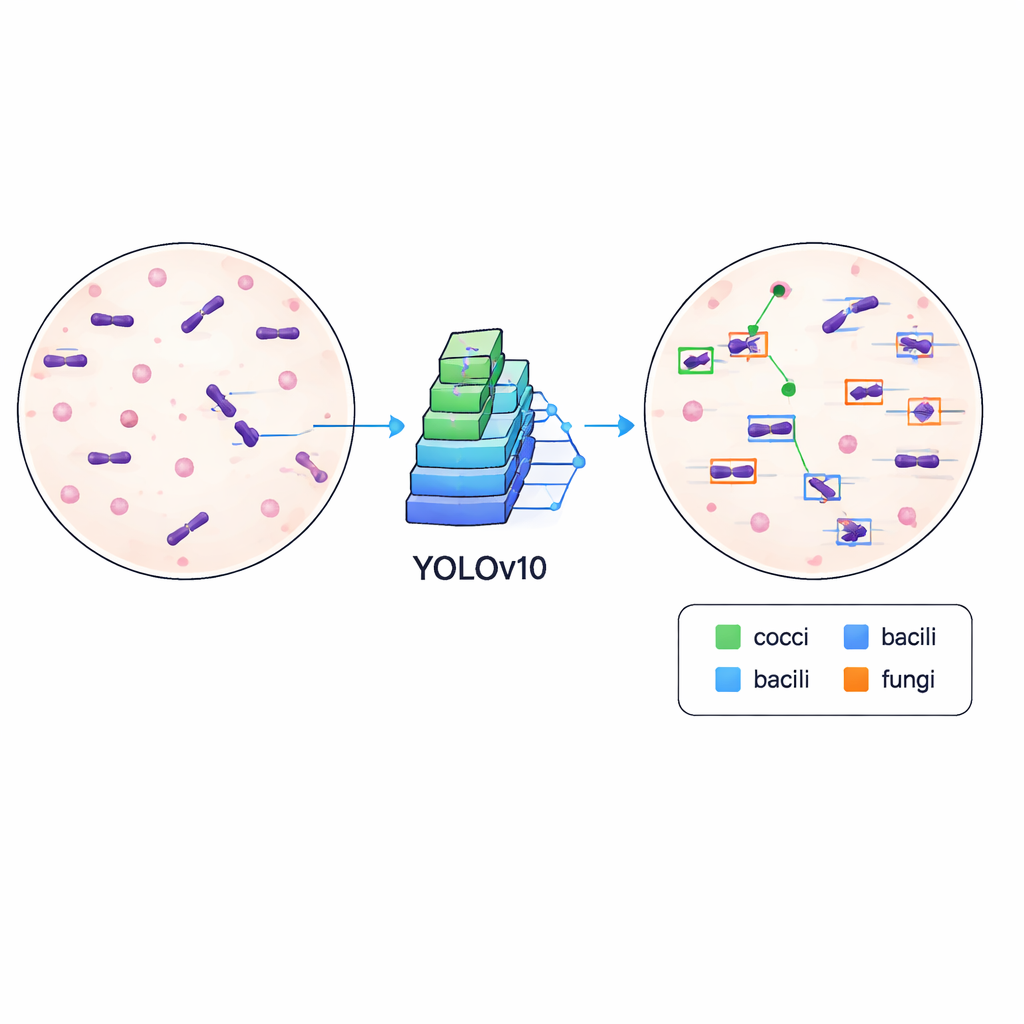
Apprendre aux ordinateurs à repérer les microbes
Pour montrer que le jeu de données est à la fois propre et utile, les auteurs ont entraîné un algorithme moderne de détection d’objets connu sous le nom de YOLOv10 pour repérer et classer les microbes dans les images. Ils ont partagé les données en jeux d’entraînement et de validation et ont exécuté le modèle pendant 500 itérations d’entraînement sur une carte graphique haut de gamme, en suivant la qualité des encadrés dessinés et la capacité à distinguer les différents types cellulaires. Le système entraîné a atteint une précision moyenne (mAP) d’environ 84,6 % à un seuil de correspondance standard, ce qui indique qu’il peut localiser et étiqueter de manière fiable des microbes malgré la variabilité des lames, notamment l’intensité de la coloration, les débris de fond et la mise au point.
Usages possibles de cette ressource
Parce que les données respectent des formats courants, elles peuvent s’intégrer à de nombreuses chaînes existantes de vision par ordinateur. Les chercheurs peuvent d’abord entraîner un système à distinguer les vrais microbes des débris, aidant les laboratoires à filtrer les faux signaux d’hémoculture positifs. Ils peuvent aussi regrouper les microbes par grandes formes, correspondant à ce dont les cliniciens ont besoin pour un rapport précoce dit « de niveau 1 » qui guide le choix initial des antibiotiques. Un objectif plus ambitieux est de distinguer les espèces individuelles par des indices visuels subtils. Les auteurs notent des limites : certaines cellules sont groupées, certaines lames proviennent d’une seule source par espèce et la mise au point peut varier — comme dans la pratique réelle. Néanmoins, chaque encadré inclus a été soigneusement vérifié, faisant de ce jeu de données un point de départ fiable.
Ce que cela signifie pour les patients
En termes simples, ce travail transforme des lames d’hémoculture de routine en un terrain d’entraînement partagé pour des logiciels intelligents. En rendant publiques à la fois les images et les marquages d’experts, l’étude abaisse la barrière pour des équipes du monde entier qui souhaitent concevoir et tester des outils d’IA capables de lire rapidement et de façon cohérente les colorations de Gram. Bien que ces systèmes ne remplacent pas les microbiologistes humains, ils pourraient aider à détecter plus tôt des infections dangereuses, réduire les erreurs d’interprétation et favoriser une utilisation plus appropriée des antibiotiques. Pour les patients, cela peut se traduire par des traitements plus rapides et plus précis quand cela compte le plus.
Citation: Yi, Q., Gou, X., Zhu, R. et al. An annotated dataset of Gram stains from positive blood cultures. Sci Data 13, 294 (2026). https://doi.org/10.1038/s41597-026-06651-3
Mots-clés: infections du sang, coloration de Gram, jeu de données d’imagerie médicale, intelligence artificielle, diagnostic en microbiologie