Clear Sky Science · fr
Première assemblée et annotation du génome au niveau chromosomique d’un raie d’eau douce en danger (Fontitrygon garouaensis) d’Afrique
Un habitant rarissime des rivières mis sous le projecteur génomique
Dans les rivières boueuses d’Afrique de l’Ouest vit une raie peu commune qui a fait ce que presque aucun de ses parents requins et raies n’a fait : elle s’est installée de façon permanente en eau douce. Cette raie d’eau douce au corps lisse, Fontitrygon garouaensis, est aussi en danger et peu étudiée. L’article décrit ici fournit la première carte complète de son ADN au niveau chromosomique, offrant un outil puissant pour comprendre comment une lignée marine aussi ancienne s’est adaptée à la vie en rivière et comment mieux la protéger.
Pourquoi cette raie est importante
Les requins et les raies appartiennent à l’une des plus anciennes branches de l’arbre des vertébrés, s’étant séparés des ancêtres des poissons osseux il y a des centaines de millions d’années. Pourtant, malgré leur importance évolutive, leurs génomes restent peu documentés, surtout pour les espèces d’eaux africaines. Fontitrygon garouaensis est particulièrement remarquable : c’est la seule raie connue entièrement adaptée aux systèmes d’eau douce africains, et elle présente des traits corporels distinctifs tels qu’une rangée d’épines dorsales réduite ou absente. Étant donné que la transition des mers salées vers les rivières douces est rare et physiologiquement contraignante pour les requins et les raies, cette espèce constitue une expérience naturelle sur la façon dont les animaux réajustent leur biologie pour affronter de nouveaux milieux.
Construire une carte génétique de référence
Pour décrypter le plan génétique de la raie, les chercheurs ont prélevé une femelle adulte dans le fleuve Niger au Nigeria et extrait de l’ADN et de l’ARN de haute qualité à partir de plusieurs tissus. Ils ont ensuite utilisé une stratégie « hybride » combinant trois approches de séquençage de pointe. Le séquençage Illumina à lectures courtes fournit d’énormes nombres de petits fragments d’ADN, le séquençage PacBio HiFi à lectures longues génère des tranches beaucoup plus longues et continues, et le séquençage Hi-C capture la manière dont l’ADN se plie et interagit à l’intérieur du noyau cellulaire. En tissant ces jeux de données avec des logiciels spécialisés, l’équipe a assemblé un génome d’environ 4,19 milliards de lettres d’ADN, organisé en 41 molécules de type chromosomique — comparable en taille à certains des plus grands génomes de requins connus.
Ce que révèle le génome
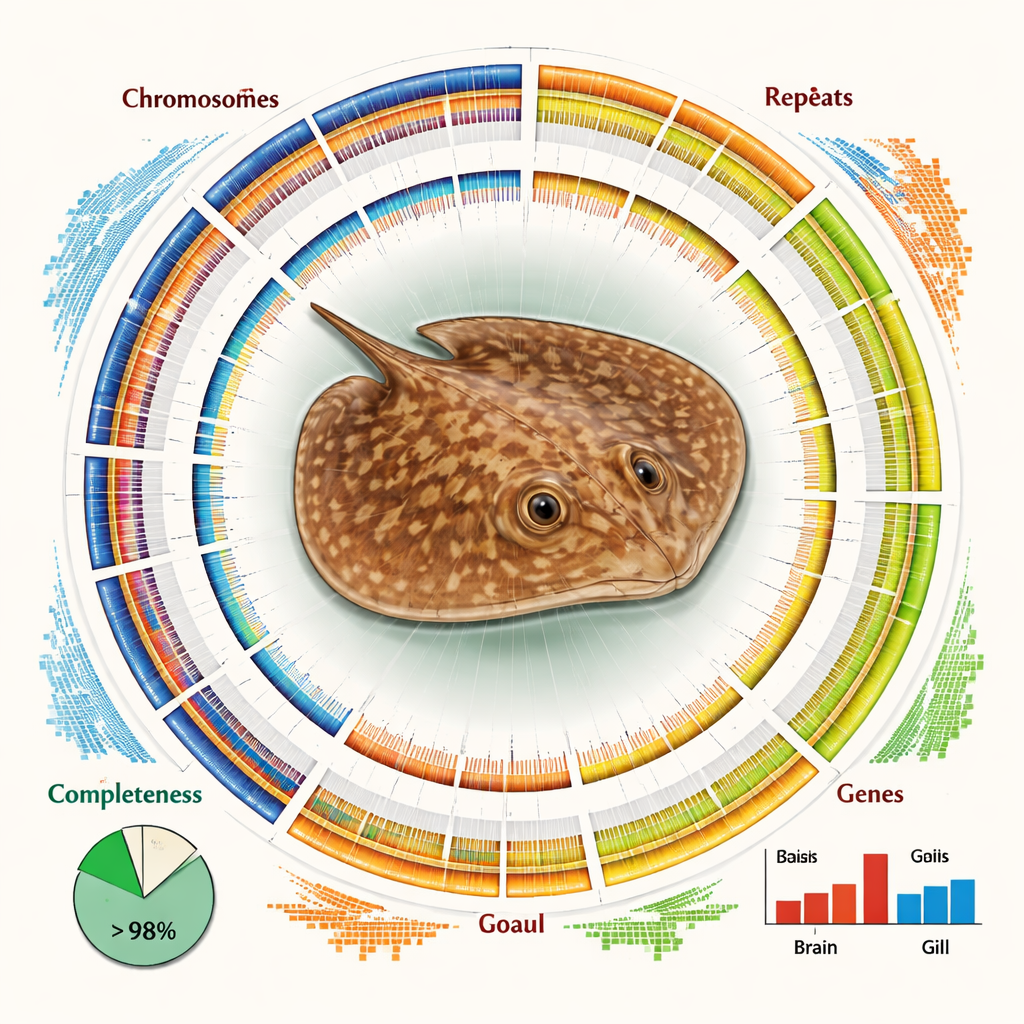
L’assemblage final est à la fois volumineux et remarquablement complet. Des contrôles qualité indépendants montrent que plus de 93 % des gènes vertébrés essentiels attendus sont présents et intacts, et que plus de 84 % de la séquence totale est attribuée de façon fiable à des chromosomes spécifiques. Le génome est dominé par de l’ADN répétitif — des séquences qui apparaissent de nombreuses fois — représentant à peu près les deux tiers de sa longueur. Nombre de ces répétitions appartiennent à des éléments génétiques mobiles tels que les LINEs et les LTRs, qui se sont copiés et insérés dans le génome au fil du temps évolutif. Malgré cette complexité, les chercheurs ont identifié près de 30 000 gènes codant des protéines et ont pu attribuer des fonctions probables à plus de 98 % d’entre eux en s’appuyant sur des bases de données internationales de protéines et de voies biologiques.
Indices sur la vie en eau douce et l’évolution
Disposer d’une carte au niveau chromosomique a permis à l’équipe d’aller au-delà d’un simple inventaire de gènes. En comparant les chromosomes de la raie avec ceux de requins et de raies apparentés, ils ont mis au jour une histoire de réarrangements structurels — cassures, fusions et réorganisations de segments chromosomiques entiers — qui distingue cette lignée. Ces modifications ont peut‑être contribué à façonner les traits uniques et la niche écologique de l’espèce. Les auteurs ont aussi examiné l’activité génique dans deux tissus clés : les branchies, qui assurent la respiration et l’équilibre en sels avec l’eau environnante, et le cerveau. Ils ont observé des différences nettes dans les gènes exprimés, les gènes des branchies étant enrichis en voies liées à l’utilisation d’énergie et au métabolisme des lipides, ce qui suggère des ajustements biochimiques nécessaires pour survivre en eau douce.
Une nouvelle base pour la conservation
Au fond, ce travail transforme une raie de rivière obscure et menacée en l’un des poissons cartilagineux les mieux caractérisés au niveau de l’ADN. Pour les non‑spécialistes, cela signifie que les scientifiques disposent désormais d’un manuel de référence détaillé pour l’espèce, depuis ses chromosomes jusqu’aux gènes individuels. Cette référence pourra guider des études futures sur sa capacité à faire face à la dégradation de la qualité de l’eau, sur la structuration de ses populations dans les bassins fluviaux, et sur ses liens de parenté avec d’autres raies. Tout aussi important, elle fournit une base génomique pour la planification de la conservation, offrant de nouvelles façons de suivre la diversité génétique, d’identifier des populations distinctes à protéger et de comprendre comment cette spécialiste rare de l’eau douce pourrait réagir aux pressions environnementales en cours.
Citation: Nneji, L.M., Oladipo, S.O., Oyebanji, O.O. et al. First Chromosome-level Genome Assembly and Annotation of an Endangered Freshwater Stingray (Fontitrygon garouaensis) from Africa. Sci Data 13, 302 (2026). https://doi.org/10.1038/s41597-026-06646-0
Mots-clés: raie d’eau douce, assemblage de génome, évolution des élasmobranches, génomique de la conservation, biodiversité des rivières africaines