Clear Sky Science · fr
Assemblage génomique au niveau des chromosomes de Sparganium angustifolium Michx. (Typhaceae)
Une plante discrète des lacs avec une grande histoire génomique
Sparganium à feuilles étroites est une plante aquatique d’apparence modeste que l’on peut ramer sans lui prêter attention, et pourtant elle façonne discrètement la vie de nombreux lacs et étangs nordiques. Elle abrite de petits poissons, nourrit les oiseaux aquatiques et tapisse la surface de l’eau de feuilles flottantes. Dans cette étude, des scientifiques dévoilent le plan génétique détaillé de cette plante, ouvrant une nouvelle fenêtre sur la façon dont les plantes s’adaptent à la vie aquatique et fournissant une référence précieuse pour la conservation comme pour la biologie fondamentale. 
Pourquoi cet habitant sous‑l’eau compte
Sparganium angustifolium est répandu dans les régions tempérées de l’hémisphère Nord. Contrairement aux plantes qui ressemblent à des roseaux et qui restent majoritairement au‑dessus de la surface, cette espèce pousse en eaux plus profondes, avec de longues feuilles fines partiellement submergées ou flottantes. Ses touffes épaisses créent de véritables forêts sous‑marines qui offrent des abris aux animaux aquatiques, tandis que ses fruits et ses feuilles nourrissent canards et autres oiseaux sauvages. Étant proche de la base d’un rameau important de l’arbre phylogénétique des graminées et leurs alliées (l’ordre des Poales, qui comprend aussi des cultures comme le riz et le maïs), elle constitue un point de comparaison clé pour comprendre comment les plantes ont fait le saut de la terre ferme vers les milieux aquatiques.
Construire un plan génétique à haute résolution
Pour élucider le génome de la plante, les chercheurs ont collecté un spécimen dans une rivière de Mongolie intérieure, en Chine, et ont utilisé plusieurs techniques de séquençage de l’ADN de pointe. Ils ont combiné des lectures longues et très précises, du séquençage à lectures courtes et une méthode appelée Hi‑C, qui capture la façon dont différentes régions d’ADN se positionnent les unes par rapport aux autres dans l’espace 3D de la cellule. En tissant ces données, ils ont assemblé l’ADN de la plante en 15 chromosomes, couvrant presque l’intégralité du génome — environ 487 millions de « lettres » du code génétique. Les mesures de qualité de l’assemblage montrent que de longues portions d’ADN ont été reliées sans cassures et que plus de 96 % des gènes de base attendus chez les plantes sont présents, indiquant un génome de référence très complet et fiable.
ADN répétitif et milliers de gènes
Une fois le génome assemblé, l’équipe a entrepris d’en identifier les caractéristiques principales. Ils ont trouvé 23 767 gènes codant des protéines — des segments d’ADN susceptibles d’être traduits en protéines qui construisent et font fonctionner les cellules de la plante. Pour estimer les fonctions probables de ces gènes, ils les ont mis en regard de plusieurs bases de données scientifiques majeures et ont pu attribuer une fonction probable à plus de 96 % d’entre eux. Les chercheurs ont également découvert que la majorité du génome — un peu plus de 70 % — est constituée d’ADN répétitif, dont une grande partie sous forme d’éléments génétiques sauteurs appelés rétrotransposons. Ces séquences ne codent pas directement pour des protéines, mais elles influencent fortement la taille et la structure du génome et peuvent modifier l’activité des gènes voisins. 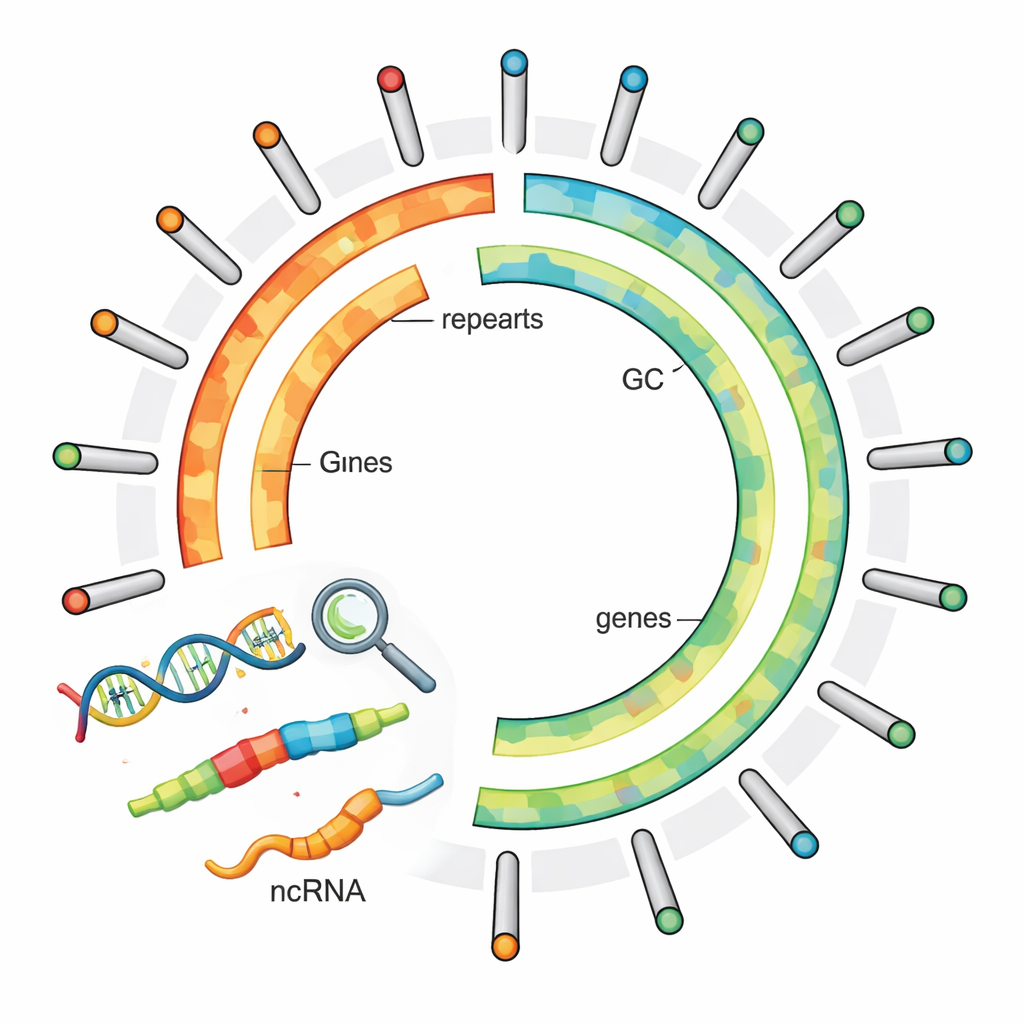
La boîte à outils d’ARN jusque‑là cachée de la plante
Au‑delà des gènes codant pour des protéines, le génome contient de nombreux ARN non codants, des molécules qui contribuent à contrôler et affiner l’activité des gènes. Les chercheurs ont identifié plus de 3 300 de ces éléments, y compris des milliers d’ARN ribosomiques qui forment le cœur des usines à protéines de la cellule, des centaines d’ARN de transfert qui livrent les briques pour fabriquer de nouvelles protéines, et des petits ARN capables d’orienter l’activation ou la répression de gènes. Cette riche boîte à outils d’ARN suggère que Sparganium à feuilles étroites possède de multiples couches de régulation pour répondre aux variations de lumière, d’oxygène, de température et de mouvement de l’eau dans son milieu aquatique.
D’une plante à un tableau évolutif plus large
En rendant ce génome au niveau chromosomique disponible publiquement dans les bases de données internationales, les auteurs offrent une ressource puissante aux scientifiques étudiant l’adaptation des plantes à la vie aquatique. La comparaison de ce génome avec ceux d’espèces apparentées vivant au bord de l’eau ou sur la terre ferme peut révéler quels gènes et traits d’ADN sont partagés et lesquels sont propres aux modes de vie pleinement aquatiques. Pour les non‑spécialistes, la conclusion est simple : en décodant le script génétique d’une plante de lac apparemment ordinaire, les chercheurs ont posé les bases pour comprendre comment les plantes se modifient pour prospérer sous l’eau, un savoir qui pourrait à terme éclairer la conservation des zones humides et même l’amélioration de cultures plus résistantes.
Citation: Shi, X., Xue, J. & Xu, X. Chromosome-level genome assembly of narrow-leaf bur-reed (Sparganium angustifolium Michx., Typhaceae). Sci Data 13, 284 (2026). https://doi.org/10.1038/s41597-026-06640-6
Mots-clés: plantes aquatiques, assemblage du génome, écologie des zones humides, évolution des plantes, Sparganium