Clear Sky Science · fr
Reséquençage du génome complet et diversité génétique de cinq races bovines indigènes de Chine
Pourquoi les vaches locales nous concernent tous
Dans la province du Sichuan, en Chine, de petits exploitants dépendent de bovins locaux jaunes et robustes capables d’affronter des collines escarpées, des étés chauds et humides et une alimentation parcimonieuse. Ces animaux soutiennent discrètement la sécurité alimentaire et les moyens de subsistance ruraux, mais leurs traits uniques risquent de se perdre à mesure que les races modernes et les croisements se répandent. Cette étude lit presque chaque lettre de l’ADN de plusieurs races bovines du Sichuan, créant une carte génétique détaillée qui peut contribuer à protéger ces animaux, améliorer la production de viande et préparer le bétail à un climat en mutation.
Des bovins adaptés à des paysages difficiles
Le Sichuan est l’un des points chauds de la diversité bovine en Chine, avec des millions d’animaux répartis entre bassins, collines et hautes terres. Les bovins jaunes locaux ont été façonnés par des siècles de survie en environnements rugueux et par la sélection attentive d’éleveurs qui privilégiaient la force, la résistance aux maladies et la capacité à vivre sur des fourrages pauvres. Pourtant, ces mêmes races voient aujourd’hui leurs effectifs diminuer et leur diversité génétique s’éroder. Le croisement non contrôlé, les déplacements saisonniers des troupeaux, les épidémies, les inondations et le mélange rapide des animaux dû au commerce estompent les limites entre races traditionnelles. Sans conservation délibérée, les forces biologiques distinctes de ces bovins pourraient disparaître.
Lire l’histoire génétique complète
Pour comprendre et protéger cette diversité, les chercheurs ont prélevé du sang de 56 bovins jaunes provenant de cinq comtés du Sichuan, chacun représentant une race locale. Ils ont également inclus l’ADN de 10 yaks d’altitude comme groupe comparatif, ou groupe externe, afin de situer la génétique des bovins dans un contexte évolutif plus large. En utilisant des techniques modernes de séquençage à haut débit, ils ont généré environ 2,3 téraoctets de données d’ADN, lisant chaque génome animal environ 13 fois pour garantir la précision. Les lectures ont ensuite été alignées sur un génome de référence bovin standard, plus de 99 % d’entre elles se plaçant au bon endroit — un signe de très haute qualité des données.
Des millions de différences dans le code de l’ADN
Une fois les génomes alignés, l’équipe les a balayés à la recherche de différents types de variations génétiques. Ils ont identifié environ 31 millions de changements d’une seule lettre dans la séquence d’ADN, ainsi que plus de deux millions de petites insertions et délétions, des dizaines de milliers de changements structurels de plus grande taille et plus de 240 000 régions où des fragments d’ADN sont manquants ou dupliqués. La plupart de ces différences se situent en dehors des parties codantes des gènes, mais un nombre substantiel tombe à l’intérieur ou à proximité de gènes susceptibles d’influer sur des caractères importants. Le schéma des variations le long des chromosomes, en particulier le comportement distinct du chromosome X, reflète à la fois la biologie des bovins et les pressions évolutives auxquelles ils ont été soumis au fil du temps.
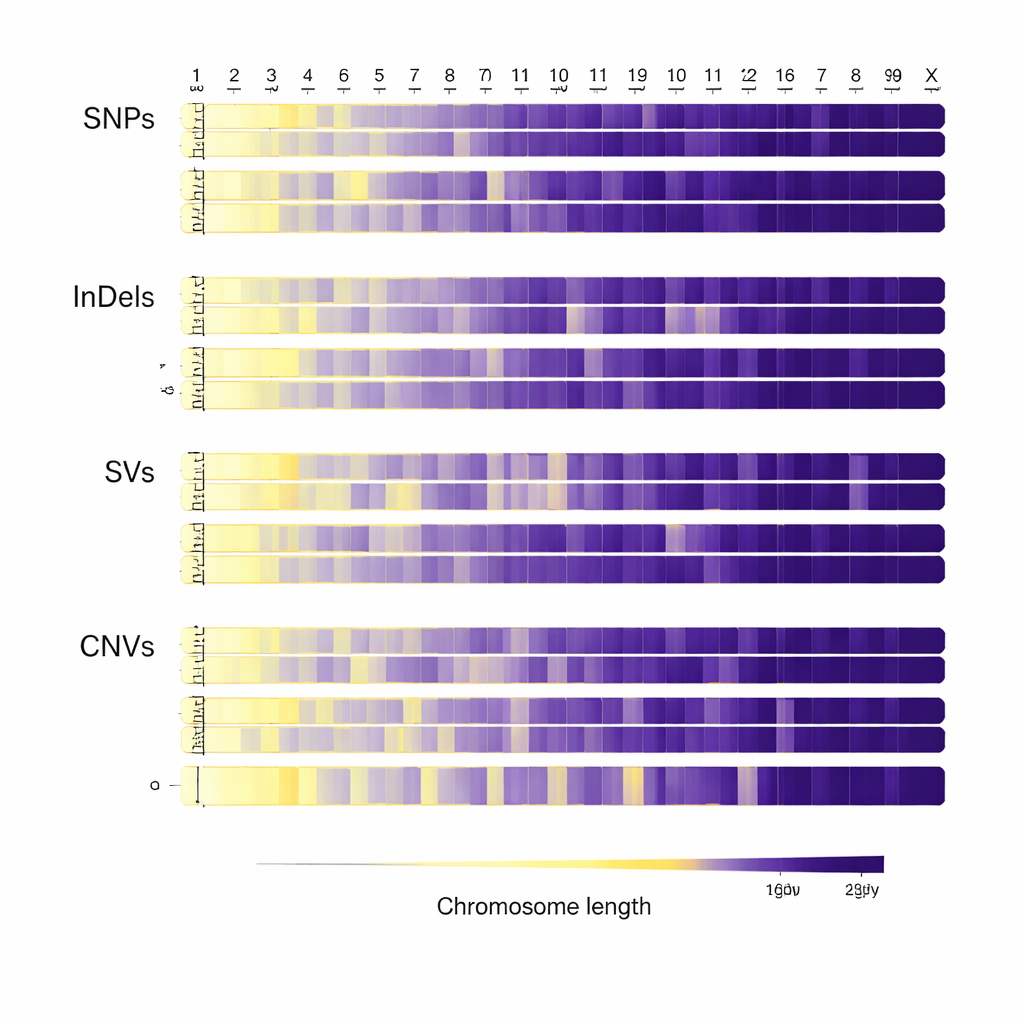
Transformer des données brutes en connaissances biologiques
De manière cruciale, les chercheurs n’ont pas seulement compté les modifications d’ADN — ils les ont annotées pour en prédire les effets possibles sur la fonction des gènes. En utilisant des outils bioinformatiques largement adoptés, ils ont rattaché chaque variant à sa position dans ou près des gènes et mis en évidence les changements susceptibles de perturber des protéines ou d’altérer la régulation génique. Ils ont ensuite rendu toutes les données de séquences brutes et les listes de variants traitées librement accessibles dans des bases de données internationales. Cette ouverture permet aux scientifiques du monde entier d’exploiter les données pour rechercher des gènes liés à la tolérance à la chaleur et à l’humidité, à la résistance aux maladies, à l’utilisation efficace d’aliments de faible qualité et à la qualité de la viande, ou pour comparer les bovins du Sichuan à d’autres races.
Du code caché au bénéfice pratique
Pour les non-spécialistes, ce travail peut être vu comme la prise d’un instantané génétique à haute résolution de certains des bovins les plus résistants de Chine. En cataloguant en détail leurs différences d’ADN et en partageant ouvertement les résultats, l’étude pose les bases essentielles de programmes d’élevage qui préservent la résilience des animaux traditionnels tout en améliorant la productivité. Dans un avenir marqué par le stress climatique et l’évolution des maladies, ces informations aideront les agriculteurs et les sélectionneurs à maintenir des bovins robustes, localement adaptés, qui soutiennent une production de viande durable et protègent un patrimoine agricole irremplaçable.
Citation: Wang, W., Li, L., Chen, Y. et al. Whole-genome resequencing and genetic diversity of five indigenous cattle breeds from China. Sci Data 13, 282 (2026). https://doi.org/10.1038/s41597-026-06610-y
Mots-clés: génétique bovine, races indigènes, diversité génétique, séquençage du génome complet, conservation du bétail