Clear Sky Science · fr
Assemblages du génome au niveau des chromosomes de deux lignées inbred de maïs aux architectures végétales contrastées
Pourquoi la forme du maïs compte pour nourrir le monde
Des bords de route aux rayons des supermarchés, le maïs est omniprésent. Mais toutes les plantes de maïs ne se ressemblent pas — ni n’agissent de la même façon. Certaines poussent hautes avec des feuilles larges et étalées, d’autres sont plus courtes et dressées. Ces différences d’« architecture végétale » déterminent combien de plants on peut loger dans un champ et, en fin de compte, combien de nourriture on peut récolter par hectare. Cette étude déchiffre, avec un niveau de détail remarquable, l’ADN de deux lignées inbred de maïs aux architectures opposées, créant une carte de référence que sélectionneurs et chercheurs peuvent utiliser pour concevoir des cultures à haut rendement et adaptées au climat.

Deux plants de maïs, deux silhouettes très différentes
Les chercheurs se sont concentrés sur deux lignées de maïs inbred, D132 et Yu82, qui diffèrent nettement dans leur mode de croissance. D132 présente une structure ouverte et étalée : elle est plus grande, son épi (la partie portant les grains) est plus haut, et ses feuilles s’étendent plus largement. Yu82, en revanche, est compacte : elle est plus courte, l’épi est plus proche du sol, et les feuilles sont plus dressées et étroites. Ces traits ne sont pas cosmétiques. Une structure compacte permet aux agriculteurs d’implanter plus de tiges par mètre carré sans ombrage excessif ni forte concurrence, condition essentielle pour augmenter le rendement en densités élevées. En comparant les « manuels d’instructions » complets en ADN de ces deux lignées, l’équipe vise à découvrir les bases génétiques de l’architecture des plantes chez le maïs.
Construire des cartes d’ADN quasi complètes chromosome par chromosome
Pour capturer ces manuels, l’équipe a combiné plusieurs technologies de séquençage d’ADN de pointe. Des plates‑formes à lectures longues, capables de lire de très grands fragment d’ADN d’un seul tenant, ont servi à assembler les pièces de base de chaque génome. Des plates‑formes à lectures courtes, qui produisent de nombreux petits fragments très précis, ont ensuite été utilisées pour polir et corriger les erreurs. La technologie Hi‑C, qui mesure comment différentes régions de l’ADN se touchent physiquement dans la cellule, a permis aux chercheurs d’assembler les fragments en chromosomes complets. Pour Yu82, ils ont aussi utilisé la cartographie optique, qui image des molécules d’ADN extrêmement longues pour aider à ordonner et joindre les fragments. Le résultat est deux assemblages du génome au niveau des chromosomes : D132 d’environ 2,17 milliards de lettres d’ADN et Yu82 d’environ 2,19 milliards, avec plus de 90–99 % de leurs séquences correctement placées sur les dix chromosomes du maïs.
Ce qu’ils contiennent : gènes, répétitions et structures partagées
Une fois les génomes assemblés, les scientifiques en ont catalogué le contenu. Chaque lignée porte environ 41 000 gènes codant pour des protéines — segments d’ADN qui donnent des instructions pour construire des protéines. Ils ont aussi trouvé que plus de quatre cinquièmes de chaque génome sont constitués d’« ADN sauteur », connu sous le nom d’éléments transposables. Ces séquences répétitives, souvent qualifiées de « déchets » génomiques, influencent fortement la taille du génome et peuvent affecter l’activation ou la répression des gènes. Pour vérifier la qualité, l’équipe a comparé ses assemblages à plusieurs génomes de référence du maïs existants et à des milliers de gènes végétaux bien caractérisés. Les nouvelles cartes montrent une grande complétude et correspondent étroitement à la structure et à l’ordre des gènes observés chez d’autres lignées de maïs bien étudiées, confirmant qu’elles constituent une base fiable pour de futures recherches.
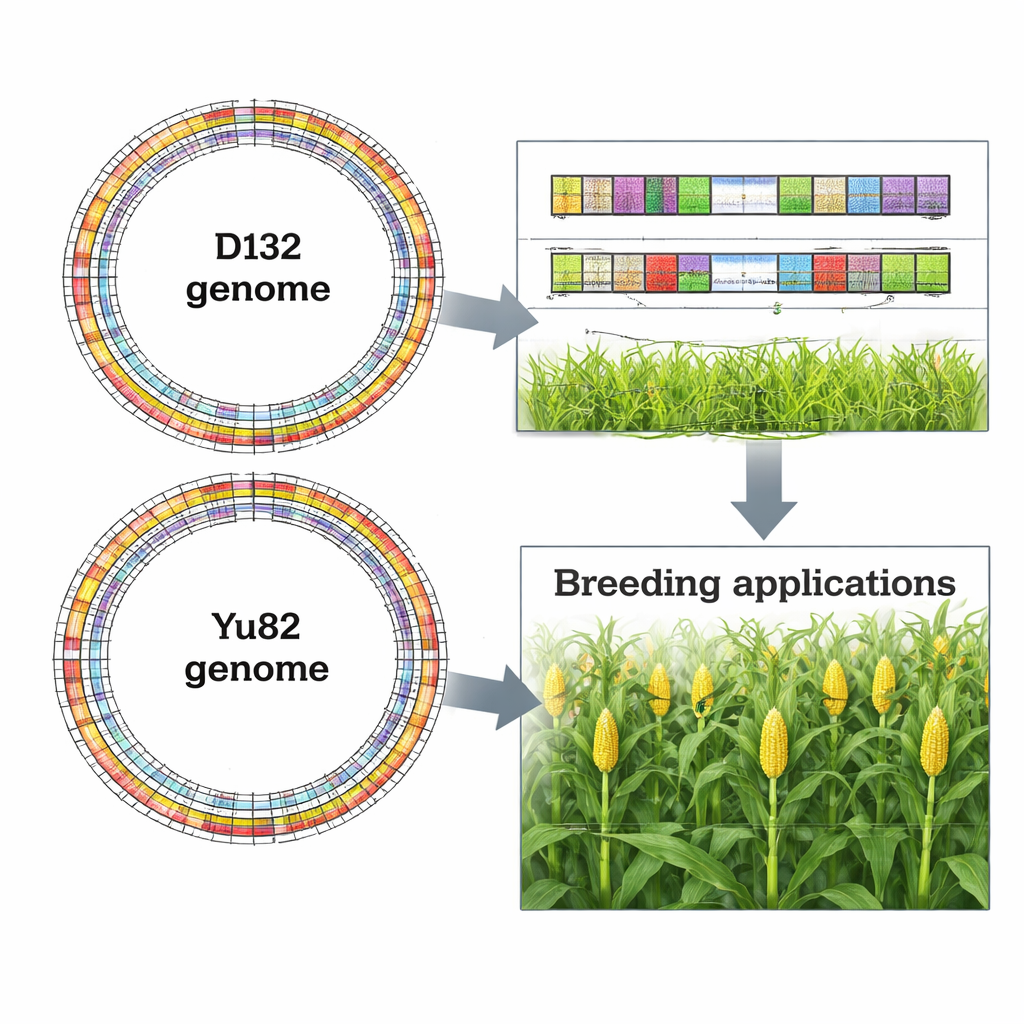
De l’ADN brut à des indices utiles pour le croisement
Au‑delà du simple inventaire des gènes, les auteurs ont utilisé de vastes collections de données d’ARN — des instantanés des gènes actifs dans différents tissus — pour affiner les modèles de gènes et attribuer des indices fonctionnels à la plupart des gènes dans les deux génomes. Ils ont ensuite examiné comment les génomes de D132 et Yu82 s’alignent entre eux et par rapport à d’autres variétés de maïs, identifiant de longs segments où l’ordre des gènes est conservé. Ces comparaisons mettent en évidence des régions stables ainsi que des points chauds où la structure ou le contenu génique diffère. Ces régions variables sont de premiers candidats susceptibles d’abriter des gènes et des éléments régulateurs qui déterminent la hauteur de la plante, l’angle des feuilles, la position des épis et les systèmes racinaires — précisément les traits qui distinguent les plantes ouvertes et étalées des plantes compactes adaptées à une forte densité de plantation.
Comment ce travail aide à produire plus de maïs sur moins de terres
Pour les non‑spécialistes, l’essentiel est que cette étude fournit deux cartes d’ADN détaillées et de haute qualité de plants de maïs qui poussent de manières très différentes. Ces cartes servent de plans de référence : sélectionneurs et généticiens peuvent désormais repérer plus facilement des gènes précis et des variations d’ADN qui contrôlent l’architecture végétale, tester leur impact sur la performance en champs denses et combiner les versions favorables dans des hybrides de nouvelle génération. Dans un monde où la demande en grains augmente alors que les terres cultivables sont limitées, la capacité à concevoir des plants de maïs qui prospèrent à forte densité — et à le faire grâce à une information génétique précise — pourrait jouer un rôle important pour produire plus de nourriture tout en utilisant la terre et les ressources de façon plus efficiente.
Citation: Yao, W., Li, S., Ren, J. et al. Chromosome-level genome assemblies of two maize inbred lines with contrasting plant architectures. Sci Data 13, 276 (2026). https://doi.org/10.1038/s41597-026-06603-x
Mots-clés: génome du maïs, architecture des plantes, amélioration des cultures, culture à haute densité, assemblage du génome