Clear Sky Science · fr
Assemblage du génome sans lacunes de bout en bout de Opsariichthys evolans (Cypriniformes : Cyprinidae)
Un poisson de ruisseau avec une histoire génomique
Les cours d’eau torrentueux du sud-est de la Chine et de Taïwan abritent un petit poisson coloré nommé Opsariichthys evolans. Peu connu en dehors de la région, cette espèce joue un rôle écologique central et constitue une œuvre naturelle, avec des bandes vives et des colorations nuptiales frappantes. Depuis plus d’un siècle, les scientifiques débattent de sa classification et de sa place dans l’arbre phylogénétique des poissons d’eau douce. Cette étude apporte une pièce clé du puzzle : le premier génome complet et sans lacunes de O. evolans, séquencé d’un bout à l’autre d’un chromosome.
Pourquoi ce poisson compte
O. evolans vit dans des ruisseaux clairs et courants, où il contribue à l’équilibre des réseaux trophiques et sert d’indicateur sensible de la qualité de l’eau. Les mâles développent des bandes latérales vives et des tubercules granulaires sur la tête et autour des yeux pendant la période de reproduction, ainsi qu’un museau sombre noir violacé. Ces traits remarquables, associés à la préférence de l’espèce pour les eaux rapides, en font un modèle idéal pour étudier l’adaptation des animaux à leur milieu. Parallèlement, les changements d’origine humaine — pollution, fragmentation des habitats et espèces invasives — réduisent ses populations, rendant cruciale la compréhension de sa biologie pour la conservation.
Une confusion de noms qui dure
Pendant des décennies, les biologistes ont eu du mal à décider si O. evolans appartenait au genre Opsariichthys ou à Zacco. Les premiers taxonomistes avaient décrit l’espèce comme Zacco evolans, en s’appuyant surtout sur des caractères externes tels que la forme des nageoires et les bandes corporelles. Des études ultérieures, plus détaillées, ont montré que le motif des bandes et les tubercules nuptiaux diffèrent de ceux du similaire Zacco platypus. Des analyses de l’ADN mitochondrial suggéraient que O. evolans s’intègre mieux dans Opsariichthys, mais certaines données de gènes nucléaires la rapprochaient de Zacco. Sans génome complet, le tableau évolutif restait flou et le débat sur sa position exacte dans l’arbre des poissons perdurait.

Lire chaque lettre du génome
Pour trancher ces questions, les chercheurs ont prélevé un mâle sauvage dans une rivière de la province d’Anhui, en Chine, et ont soigneusement conservé neuf tissus différents. Ils ont ensuite combiné plusieurs technologies de séquençage de l’ADN de pointe, chacune apportant ses atouts, pour lire le code génétique de l’animal. Des fragments courts et très précis ont servi à polir la séquence, tandis que des lectures longues et ultra-longues issues des plateformes PacBio et Oxford Nanopore ont couvert les régions difficiles et assemblé les chromosomes d’un bout à l’autre. La technologie Hi-C, qui capture la façon dont l’ADN se replie à l’intérieur de la cellule, a permis d’ordonner les segments en chromosomes complets. Le résultat final est un génome télomère-à-télomère, sans lacunes, d’environ 0,89 milliard de paires de bases, organisé en 39 chromosomes avec un fragment continu d’ADN par chromosome.
Ce que révèle le génome
Le génome final a passé des contrôles de qualité stricts, capturant plus de 99 % des gènes conservés attendus et s’alignant étroitement avec des séquences connues de poissons apparentés. Près de la moitié du génome est constituée de séquences répétées, dont beaucoup sont des « gènes sauteurs » capables de se déplacer et de remodeler le génome au fil de l’évolution. L’équipe a identifié près de 30 000 gènes codant des protéines et des milliers d’ARN non codants, dont la majorité a pu être annotée à l’aide des principales bases de données biologiques. En comparant ce nouveau génome avec ceux de deux proches parents — Opsariichthys bidens et Zacco platypus — les scientifiques ont constaté que la structure chromosomique globale est très similaire, confirmant des liens évolutifs étroits. Dans ce cadre, ils ont repéré des gènes candidats et des voies susceptibles d’être impliqués dans la coloration des bandes et les adaptations à la vie en courant rapide, fournissant des indices sur l’évolution de son apparence et de son mode de vie distinctifs.
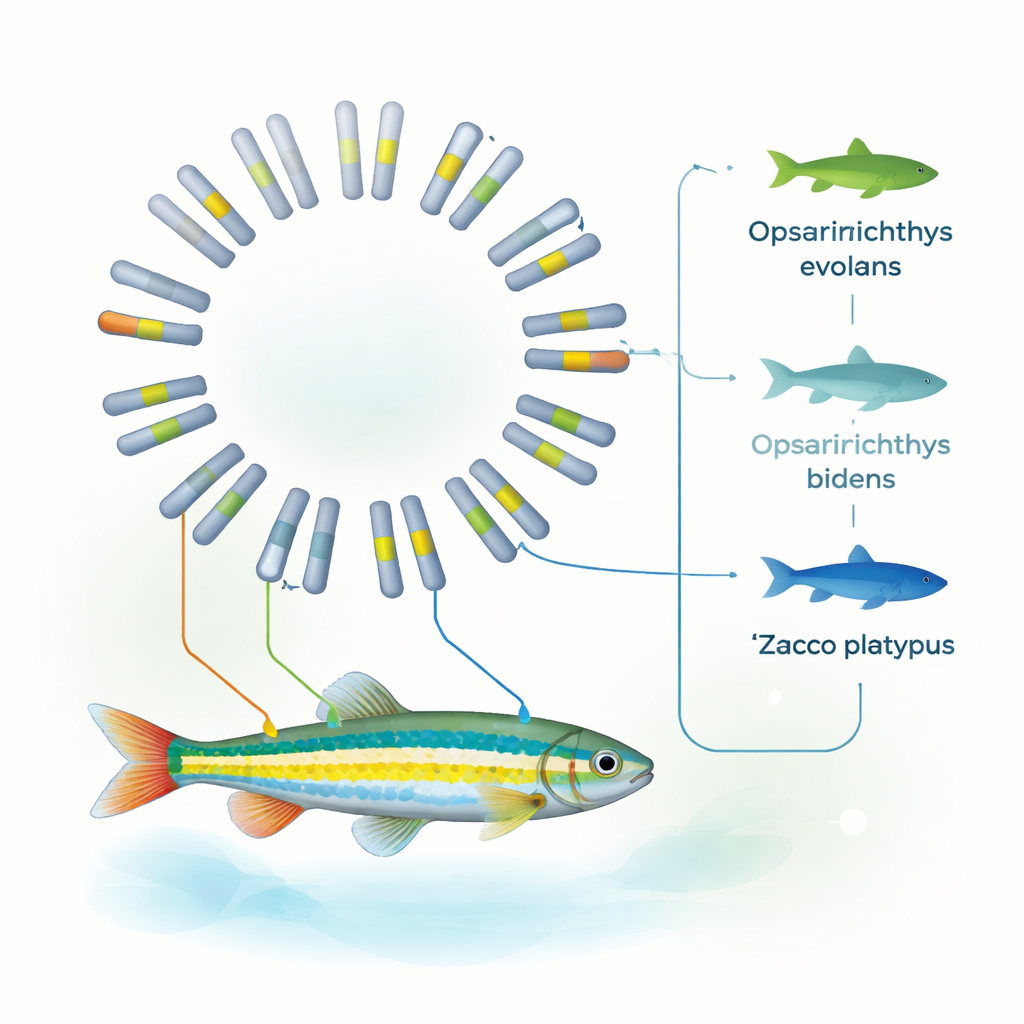
Clarifier sa place dans l’arbre des poissons
En utilisant des familles de gènes partagées entre dix espèces de poissons différentes, l’équipe a reconstruit un arbre évolutif détaillé. Leur analyse indique que O. evolans a divergé de Z. platypus il y a environ 8 à 19 millions d’années et que sa structure génomique est particulièrement proche de celle de O. bidens. Ces résultats, conjugués aux preuves mitochondriales antérieures, soutiennent le placement de O. evolans dans le genre Opsariichthys, et non dans Zacco. Autrement dit, le génome complet confirme ce que l’observation attentive des bandes, de la couleur du museau et des structures nuptiales laissait présager : l’apparence peut tromper, mais quand la morphologie et un génome complet concordent, les lignes taxonomiques s’éclaircissent nettement.
Pourquoi un génome complet change la donne
Pour les non-spécialistes, cet accomplissement revient à passer d’une carte floue et déchirée à un atlas net et haute résolution d’une espèce. Avec un génome complet et sans lacunes, les chercheurs peuvent désormais retracer l’origine des couleurs remarquables de O. evolans, son profil hydrodynamique adapté à la vie en eaux rapides, et ses relations avec d’autres cyprinidés d’Asie de l’Est avec une précision inédite. Cette ressource aidera à affiner la classification des poissons, guidera les efforts de conservation des écosystèmes de ruisseaux vulnérables et approfondira notre compréhension de la façon dont de petites différences d’ADN produisent la riche diversité observée chez les poissons d’eau douce.
Citation: Wang, P., Wang, X., Yin, D. et al. Telomere-to-telomere gap-free genome assembly of the Opsariichthys evolans (Cypriniformes: Cyprinidae). Sci Data 13, 263 (2026). https://doi.org/10.1038/s41597-026-06588-7
Mots-clés: assemblage du génome, poisson d’eau douce, télomère à télomère, évolution des poissons, génomique comparative