Clear Sky Science · fr
Alignement sémantique du modèle de métadonnées de l’Archive génome-phénotype humaine allemande dans le domaine génomique européen
Pourquoi le partage des données génomiques demande plus que de simples fichiers
La médecine moderne repose de plus en plus sur la lecture de notre ADN pour diagnostiquer des maladies et adapter les traitements. Mais la véritable puissance de la génomique apparaît lorsque les données de nombreux hôpitaux et pays peuvent être combinées. Cela ne fonctionne que si chaque jeu de données est décrit de façon claire et compatible et si des lois sur la vie privée comme le RGPD européen sont strictement respectées. Cet article explique comment l’Archive génome-phénotype humaine allemande (GHGA) construit un « système de description » détaillé pour les études génomiques afin que les données précieuses puissent être trouvées, comprises et partagées en toute sécurité à l’échelle de l’Europe.
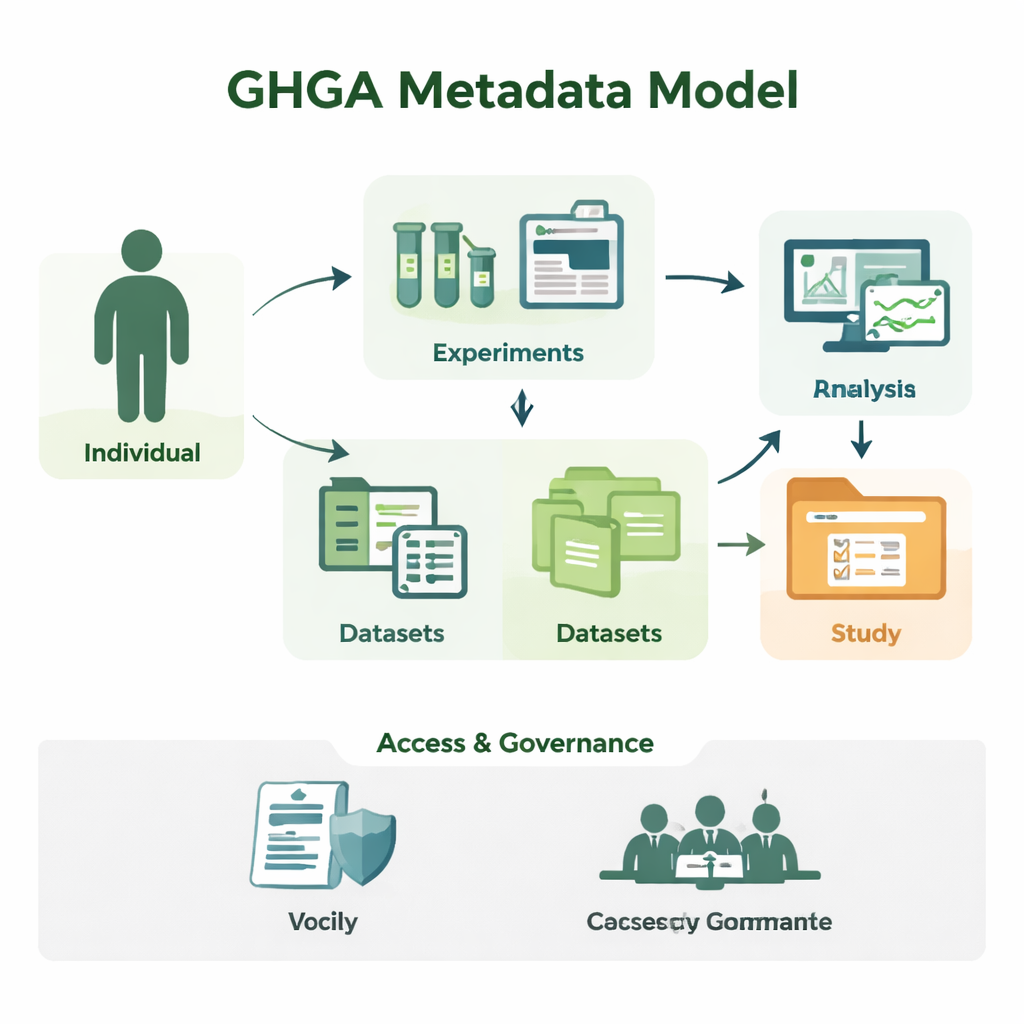
Des séquences brutes aux études compréhensibles
La recherche génomique produit d’énormes volumes de données de séquences, mais à elle seule, une séquence d’ADN n’a pas de sens. Les chercheurs doivent savoir qui est l’origine de l’échantillon, quel tissu a été utilisé, comment l’expérience a été menée et dans quelles conditions les données peuvent être réutilisées. GHGA capture ces informations contextuelles sous forme de métadonnées. Son modèle organise les métadonnées en 16 blocs fonctionnels, tels que la personne participant à l’étude (l’« Individu »), l’échantillon prélevé, l’expérience et l’analyse réalisées, les fichiers de données générés, ainsi que les jeux de données et études qui les regroupent. En séparant les détails scientifiques des éléments administratifs comme les conditions d’accès, le modèle reflète le fonctionnement d’un laboratoire et d’un portail de données réels, mais d’une façon que les ordinateurs peuvent traiter de manière fiable.
Conserver l’utilité des données tout en rendant les personnes non identifiables
Parce que GHGA gère des données sensibles de santé humaine, l’équipe a dû concevoir le modèle de façon à être riche scientifiquement sans faciliter l’identification des personnes derrière les données. Le RGPD européen définit comme données personnelles toute information qui pourrait raisonnablement être liée à un individu, même si les noms sont supprimés. L’article décrit une analyse de confidentialité attentive qui a montré comment la combinaison de détails tels que l’âge, le code postal et des diagnostics rares peut révéler des identités. En réponse, le portail public de GHGA évite les données de localisation très fines, regroupe les âges en larges tranches plutôt qu’en années précises, et fusionne les codes de diagnostic détaillés en catégories plus grossières. De cette façon, les chercheurs peuvent toujours savoir si un jeu de données est pertinent pour leur travail, tandis que l’effort nécessaire pour isoler une personne devient irréaliste.
Vérifier la compatibilité avec l’écosystème génomique européen
Pour être réellement utile, les métadonnées de GHGA doivent s’intégrer dans un réseau européen plus large d’archives et d’outils génomiques. Les auteurs ont donc comparé leur modèle, élément par élément, avec quatre autres cadres largement utilisés : deux versions de l’European Genome-phenome Archive (EGA), la norme ISA-tab et le modèle FAIR Genomes issu des soins de santé néerlandais. Ils ont réalisé un « passage en correspondance » détaillé qui a examiné, pour chaque champ GHGA, s’il existait un équivalent dans les autres modèles et réciproquement. Ils ont constaté que la plupart des propriétés clés de GHGA ont des contreparties claires ailleurs, en particulier pour la description des études, des échantillons, des expériences, des analyses et des formats de fichiers. Cela signifie que les jeux de données GHGA peuvent être compris et intégrés aux côtés des données stockées dans d’autres systèmes européens.
Trouver un terrain d’entente — et ce qui manque encore
De cette comparaison, l’équipe a extrait 25 champs de métadonnées « consensuels » qui apparaissent dans au moins trois des cinq modèles. Ceux-ci couvrent l’essentiel, comme le sexe et l’état de santé des participants, le tissu utilisé, le type de séquençage et l’instrument, la méthode d’analyse, les formats de fichiers, ainsi que les descriptions basiques de l’étude et les coordonnées de contact. Ces champs partagés s’alignent sur les lignes directrices minimales déjà existantes et peuvent servir de liste de contrôle centrale pour toute personne concevant de nouveaux portails de données génomiques. Dans le même temps, l’analyse a révélé des informations que certains modèles collectent mais que GHGA omet actuellement ou n’accepte que sous forme libre et textuelle, comme les dates exactes de prélèvement et de séquençage, les diagnostics exclus et les noms de contact détaillés. Beaucoup de ces omissions sont des compromis délibérés en faveur de la confidentialité et de l’anonymat.
Ce que cela signifie pour la recherche en santé à venir
Globalement, l’étude montre que le modèle de métadonnées de GHGA est détaillé, flexible et étroitement aligné sur les pratiques internationales, tout en respectant les règles strictes de confidentialité européennes. Il couvre déjà tous les champs que d’autres archives considèrent comme obligatoires, et il peut être étendu aux nouvelles technologies telles que les omiques unicellulaires et spatiales. En offrant une manière claire de décrire qui et quoi implique une étude génomique, comment les données ont été produites et dans quelles conditions elles peuvent être réutilisées, GHGA contribue à transformer des silos de données isolés en une ressource de recherche connectée. Pour les patients, cela augmente la probabilité que leurs données, une fois données, puissent contribuer en toute sécurité à des découvertes et à de meilleurs traitements au-delà des frontières pendant des années.
Citation: Mauer, K., Iyappan, A., Parker, S. et al. Semantic alignment of the German Human Genome-Phenome Archive metadata model in Europe’s genomics field. Sci Data 13, 242 (2026). https://doi.org/10.1038/s41597-026-06575-y
Mots-clés: partage de données génomiques, normes de métadonnées, confidentialité et RGPD, GHGA, médecine personnalisée