Clear Sky Science · fr
Métabarcoding et données métagénomiques le long de gradients environnementaux aquatiques sur les côtes de France et du Chili
Vie cachée dans des mers changeantes
Le long des côtes du monde, des lagunes paisibles aux fjords spectaculaires, la vie microscopique s’adapte en permanence à des conditions changeantes. Ces organismes minuscules animent les cycles du carbone et des nutriments qui soutiennent la pêche, la qualité de l’eau et même le climat. Pourtant, de nombreux milieux côtiers, en particulier des systèmes complexes comme les lagunes et les fjords, restent peu explorés au niveau génétique. Cette étude vise à changer la donne en créant un jeu de données ouvert et riche sur les microbes côtiers de France et du Chili, offrant une nouvelle fenêtre sur la manière dont la vie marine réagit à un environnement en constante évolution.
Les littoraux comme laboratoires naturels
Les eaux côtières sont rarement stables. Les orages, les apports fluviaux, l’évaporation et les marées peuvent faire varier la température et la salinité sur de courtes distances et des périodes brèves. Les nutriments qui nourrissent les microalgues peuvent monter en flèche ou chuter, et les activités humaines ajoutent des perturbations supplémentaires. Une telle variation crée une mosaïque d’habitats qui sélectionne différentes communautés microbiennes et favorise de nouvelles adaptations. Pour saisir cette complexité, les chercheurs ont échantillonné 26 sites le long des côtes françaises et chiliennes, incluant lagunes, estuaires, fjords, ports, plages, eaux côtières proches et un site en haute mer. Certains sites français ont été visités chaque mois pendant un an pour suivre les saisons, tandis que les sites chiliens ont été prélevés en automne austral, fournissant un instantané large de mondes côtiers contrastés. 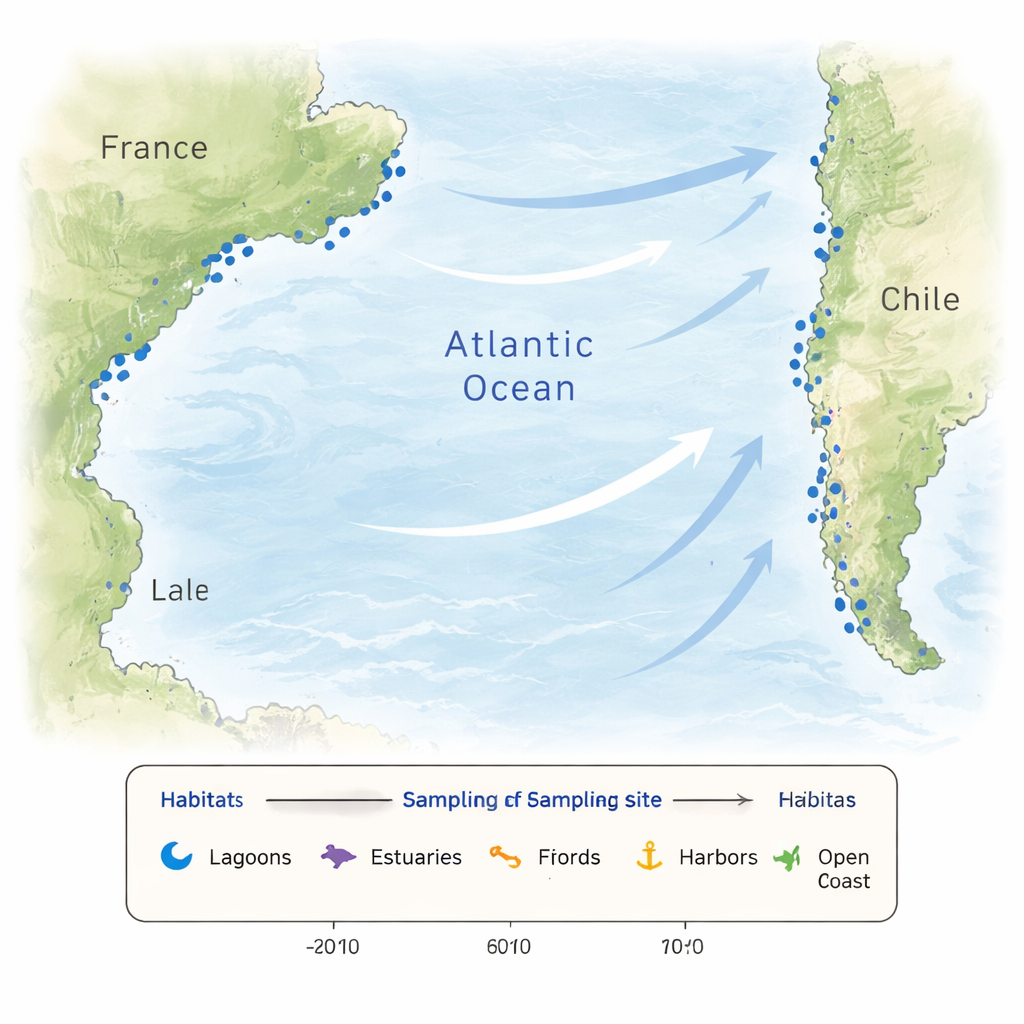
Des seaux d’eau aux empreintes génétiques
À chaque site, l’équipe a prélevé de grands volumes d’eau de mer, principalement de la surface éclairée par le soleil mais aussi de couches plus profondes dans certains fjords et en haute mer. Ils ont mesuré des conditions environnementales de base telles que la température, la salinité et les nutriments, ainsi que des indicateurs d’activité biologique comme la chlorophylle (proxy pour les algues), la matière organique dissoute, la production bactérienne et la respiration. De retour au laboratoire, les microbes ont été concentrés sur des filtres fins et leur ADN a été extrait. Une série de tests s’est concentrée sur un gène marqueur standard (16S rRNA), qui fonctionne comme un code-barres pour identifier bactéries et archées. Cette approche de métabarcoding a révélé plus de 53 000 variantes d’ADN distinctes et a montré que certains échantillons ne partageaient parfois que trois variantes, soulignant à quel point des communautés voisines peuvent être différentes.
Reconstruire des génomes à partir d’une soupe génétique
La seconde voie d’analyse était plus ambitieuse : la métagénomique shotgun, où tout l’ADN d’un échantillon est séquencé simultanément. À l’aide de méthodes avancées d’assemblage et de tri, l’équipe a reconstruit 1 372 génomes provisoires, appelés génomes reconstitués à partir de métagénomes (MAGs). Beaucoup de ces génomes n’ont pas pu être rattachés à des espèces connues, et seulement environ 4 % correspondaient à des espèces microbiennes décrites formellement. Dans certains groupes, comme certaines bactéries et archées adaptées à des conditions particulières, plus de la moitié des protéines prédites n’avaient aucune fonction connue. Les chercheurs ont également constitué un catalogue géant de plus de 23 millions de gènes non redondants, constatant qu’environ 31 % n’avaient pas d’équivalents dans les grandes bases de référence. Cela indique la présence d’un réservoir profond de biologie non caractérisée dans les eaux côtières.
Habitat extrême, outils nouveaux
Certains sites, en particulier des lagunes hypersalines en France, se sont démarqués comme des foyers de nouveauté génétique. Là, la salinité variait de presque normale à plus de deux fois la salinité océanique en quelques mois seulement. Ces conditions stressantes peuvent favoriser des microbes extrêmotolérants dotés d’enzymes fonctionnant encore en milieu très salé ou à haute température. De telles enzymes sont de plus en plus recherchées pour des usages industriels dans les détergents, les biocarburants, le dépollution et la transformation alimentaire. En reliant des mesures environnementales détaillées aux données de gènes et de génomes, ce jeu de données aide à repérer où ces organismes et outils biochimiques inhabituels sont les plus susceptibles d’être trouvés. 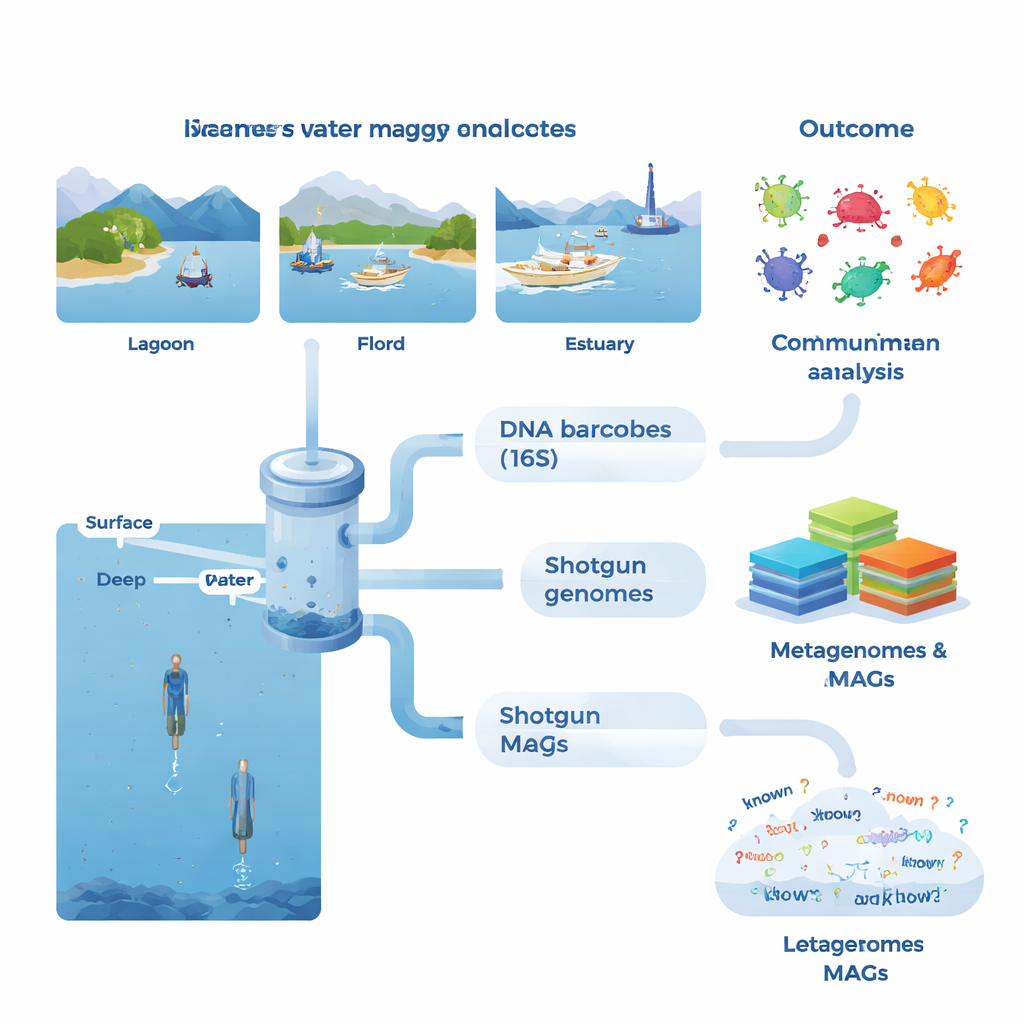
Une ressource publique pour l’avenir des océans
Plutôt que de présenter une seule découverte, ce travail livre une ressource ouverte et soigneusement validée que d’autres scientifiques peuvent exploiter. Toutes les séquences d’ADN, reconstructions de génomes, catalogues de gènes et mesures environnementales sont archivés publiquement, ainsi que le code informatique utilisé pour les traiter. Pour les non-spécialistes, le message clé est que les microbes côtiers sont à la fois divers et pleins de surprises, notamment dans des milieux négligés comme les lagunes et les fjords. En exploitant ces données, les chercheurs seront mieux armés pour comprendre comment la vie microscopique le long de nos côtes réagit au réchauffement, à la pollution et aux perturbations — et pour tirer parti de gènes nouveaux pouvant bénéficier à la biotechnologie et à la gestion de l’environnement.
Citation: Maeke, M.D., Hassenrück, C., Aguilar-Muñoz, P. et al. Metabarcoding and metagenomic data across aquatic environmental gradients along the coasts of France and Chile. Sci Data 13, 29 (2026). https://doi.org/10.1038/s41597-026-06572-1
Mots-clés: microbiomes côtiers, métagénomique, lagunes et fjords, biodiversité marine, ADN environnemental