Clear Sky Science · fr
Séquences d’images de feuilles à haute résolution avec alignement géométrique pour le phénotypage dynamique des maladies foliaires
Observer la progression des maladies des plantes en temps réel
Les agriculteurs et les jardiniers remarquent généralement les maladies des plantes seulement après l’apparition de taches brunes et de stries jaunes. Mais que se passerait-il si nous pouvions voir ces symptômes apparaître heure après heure et comprendre précisément comment le climat, la variété de la plante et différents agents pathogènes façonnent une épidémie ? Cet article présente un jeu de données public qui fait exactement cela pour le blé, l’une des cultures alimentaires les plus importantes au monde. En suivant des feuilles individuelles avec une caméra sur plusieurs jours et semaines, les auteurs ouvrent une nouvelle fenêtre sur la façon dont les maladies foliaires démarrent, se propagent et interagissent.
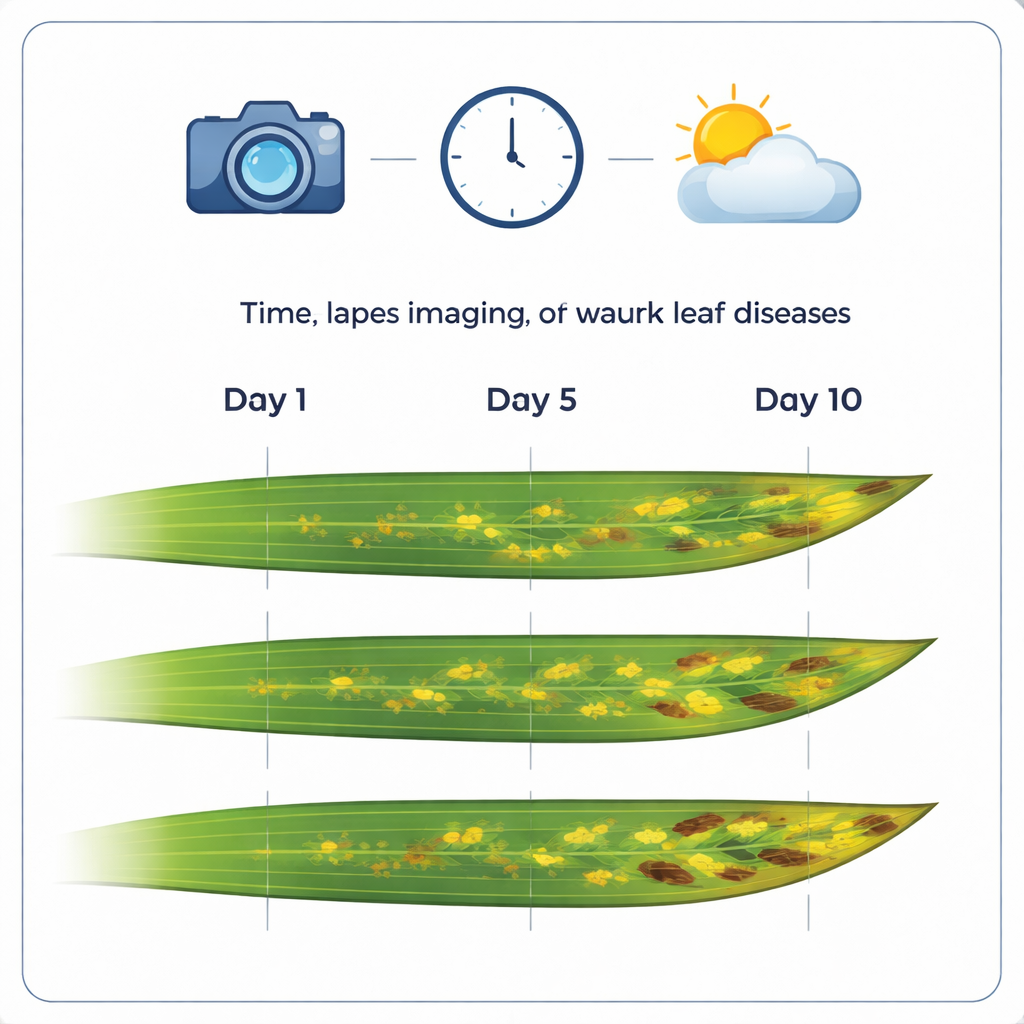
Une nouvelle photothèque de feuilles malades
Le cœur du travail est une collection soigneusement constituée de 12 520 images couleur à haute résolution de feuilles de blé. Ces images sont regroupées en 1 032 séquences en time-lapse, chacune suivant la même feuille pendant environ deux semaines avec des photos quasi quotidiennes. Bon nombre des feuilles présentent des maladies majeures du blé telles que la rouille brune, la rouille jaune et la tache septorienne (Septoria tritici). En conservant une résolution d’image très fine (environ trois centièmes de millimètre par pixel), le jeu de données capture de petits détails comme les lésions individuelles, les pustules de rouille et de minuscules organes fructifères où les champignons produisent des spores.
Maintenir chaque feuille au même emplacement
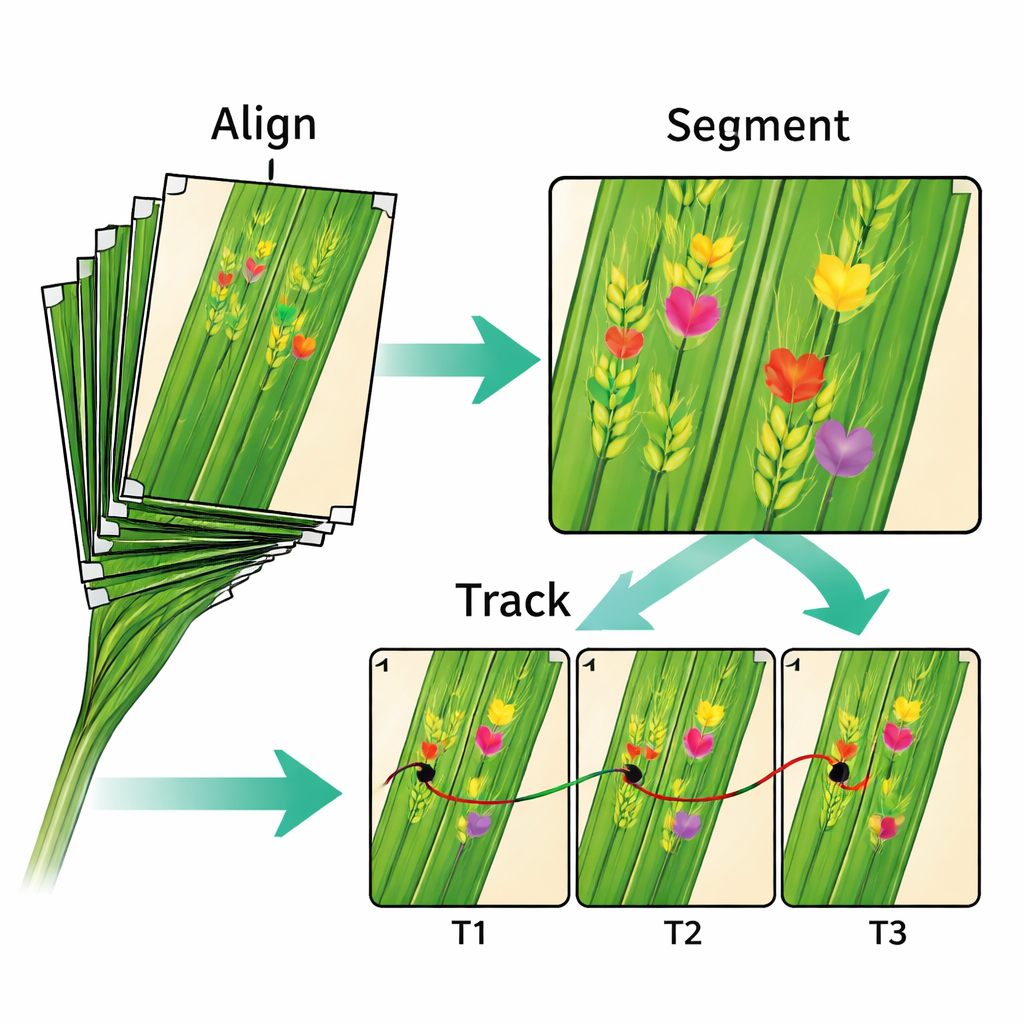
Un des principaux défis techniques dans l’étude de telles séries temporelles est que les feuilles bougent et changent de forme. Pour y remédier, les chercheurs ont aplati délicatement chaque feuille contre une plaque transparente et ajouté de petites marques blanches à l’encre comme points de référence. Des logiciels de vision par ordinateur ont ensuite utilisé ces marques pour aligner toutes les images d’une séquence afin que la même zone de tissu apparaisse au même endroit d’un jour à l’autre. L’erreur d’alignement médiane est de seulement 0,16 millimètre — suffisante pour suivre la plupart des lésions à mesure qu’elles s’étendent. Outre les images, l’équipe fournit les transformations mathématiques utilisées pour l’alignement, afin que d’autres puissent tester des méthodes alternatives ou améliorer les approches existantes.
Des images à la maladie mesurable
Après l’alignement, les auteurs ont appliqué des modèles d’apprentissage profond pour localiser et délimiter les symptômes sur chaque feuille. La chaîne de traitement détecte des points-clés, segmente les zones malades et relie une même lésion sur plusieurs jours en se basant sur le recouvrement des régions délimitées. Cela permet de mesurer la vitesse de croissance des taches individuelles, le moment d’apparition de nouvelles pustules et le nombre d’organes fructifères développés. Le jeu de données inclut aussi des relevés météorologiques, des informations sur les traitements fongicides et les inoculations, ainsi que des détails sur 15 cultivars de blé aux formes foliaires et niveaux de résistance contrastés. Ces compléments permettent aux scientifiques d’explorer comment le développement de la maladie dépend de la génétique de la plante, des choix de gestion et des conditions changeantes du champ.
Tester des outils d’imagerie plus intelligents
Au-delà de la santé des plantes elle-même, le jeu de données constitue un terrain de jeu pour les informaticiens et les ingénieurs. Les auteurs montrent que leur approche actuelle, étape par étape — aligner d’abord, puis segmenter, puis suivre — fonctionne raisonnablement bien mais reste dépourvue de contexte et nécessite des contrôles de qualité manuels. Ils soutiennent que la véritable opportunité réside dans des systèmes plus intégrés, « bout en bout », qui apprennent simultanément l’alignement, la détection des symptômes et le suivi, à l’image d’avancées similaires en imagerie médicale. Parce que les données comprennent à la fois les images brutes et des sorties traitées telles que des masques et des coordonnées de repères, les chercheurs peuvent évaluer de nouveaux algorithmes et les comparer directement à la chaîne existante.
Ce que cela signifie pour les récoltes futures
Pour les non-spécialistes, le message pratique est que nous apprenons à surveiller les maladies des plantes avec la même précision et la même continuité que celles utilisées en médecine moderne. En transformant les feuilles en récits en time-lapse plutôt qu’en instantanés, ce jeu de données aide les scientifiques à déterminer quels types de résistance comptent vraiment sur le terrain et sous quels schémas météorologiques les épidémies s’accélèrent ou ralentissent. Bien que les données actuelles proviennent d’un seul site et se concentrent sur le blé, les méthodes et outils peuvent être adaptés à d’autres cultures et stress. À long terme, un tel suivi détaillé pourrait guider les sélectionneurs vers une résistance aux maladies plus durable et soutenir des systèmes d’alerte précoce qui protègent les rendements avant que les dégâts ne deviennent visibles à l’œil nu.
Citation: Anderegg, J., McDonald, B.A. High-Resolution Leaf Image Sequences with Geometric Alignment for Dynamic Phenotyping of Foliar Diseases. Sci Data 13, 247 (2026). https://doi.org/10.1038/s41597-026-06567-y
Mots-clés: maladies foliaires du blé, imagerie en time-lapse, phénotypage des plantes, pathologie végétale numérique, résistance aux maladies des cultures