Clear Sky Science · fr
Données IRM cérébrales de l’évolution d’un traceur injecté intrathécal sur 72 heures pour des simulations intégrées aux données
Pourquoi cette étude sur les fluides cérébraux est importante
Nos cerveaux baignent en permanence dans un liquide clair appelé liquide cérébrospinal, qui aide à amortir, nourrir et peut‑être nettoyer le cerveau. Les scientifiques supposent que ce liquide pourrait aussi constituer une voie efficace pour l’administration de médicaments et l’élimination des déchets liés à des maladies comme Alzheimer et Parkinson. Pourtant, observer comment des substances se déplacent réellement dans ce liquide chez un être humain vivant a été extrêmement difficile. Cet article présente un jeu de données rare et ouvert qui capture la diffusion d’un traceur inoffensif dans le cerveau d’une personne sur trois jours, offrant aux chercheurs du monde entier un terrain détaillé pour tester des hypothèses et construire des modèles informatiques du flux des fluides cérébraux.
Un seul volontaire, de nombreuses acquisitions détaillées
Le jeu de données, surnommé « Gonzo », provient d’un homme âgé en bonne santé qui a accepté non seulement de subir une procédure d’imagerie invasive mais aussi de partager ouvertement l’ensemble de ses scans. Une petite dose d’un produit de contraste pour IRM a été injectée dans l’espace rempli de liquide autour de sa moelle épinière au bas du dos. De là, le traceur s’est mélangé au liquide entourant le cerveau et est entré progressivement dans le tissu cérébral. L’équipe de recherche a ensuite scanné sa tête avant l’injection et à quatre moments ultérieurs sur 72 heures, en utilisant plusieurs types de séquences IRM. Ils ont également prélevé des échantillons de sang entre les scans pour mesurer la quantité de traceur passée dans la circulation sanguine. Cette combinaison d’images et de mesures permet aux scientifiques de suivre quand et où le traceur apparaît, ainsi que la vitesse à laquelle il se déplace et est éliminé.
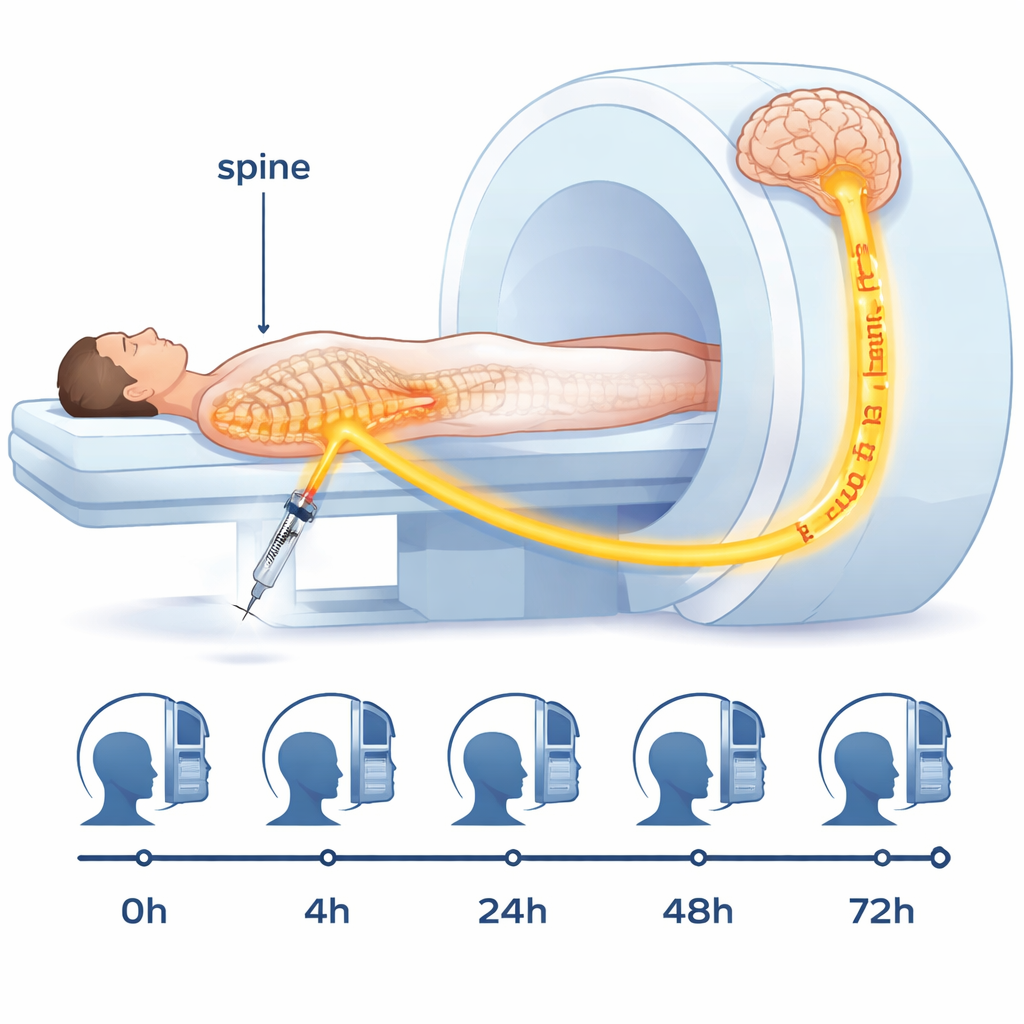
Transformer des images brutes en cartes cérébrales exploitables
Les appareils IRM modernes génèrent d’énormes volumes de données, mais pour être utiles à des simulations et à des mesures précises, ces images brutes doivent être traitées avec soin. Dans ce projet, l’équipe a converti tous les scans dans un format de fichier commun et bien documenté et les a alignés dans le même référentiel tridimensionnel afin que chaque scan corresponde au même cerveau. Ils ont ensuite utilisé des logiciels établis pour segmenter le cerveau en régions, telles que la matière grise, la matière blanche et les espaces remplis de liquide. À partir de séquences IRM particulières, ils ont calculé des cartes de propriétés physiques comme le temps de relaxation T1 et la diffusion, qui sont sensibles à la présence du traceur et au mouvement de l’eau dans les tissus. Ces étapes transforment des images floues en noir et blanc en cartes quantitatives précises pouvant alimenter directement des modèles mathématiques et informatiques.
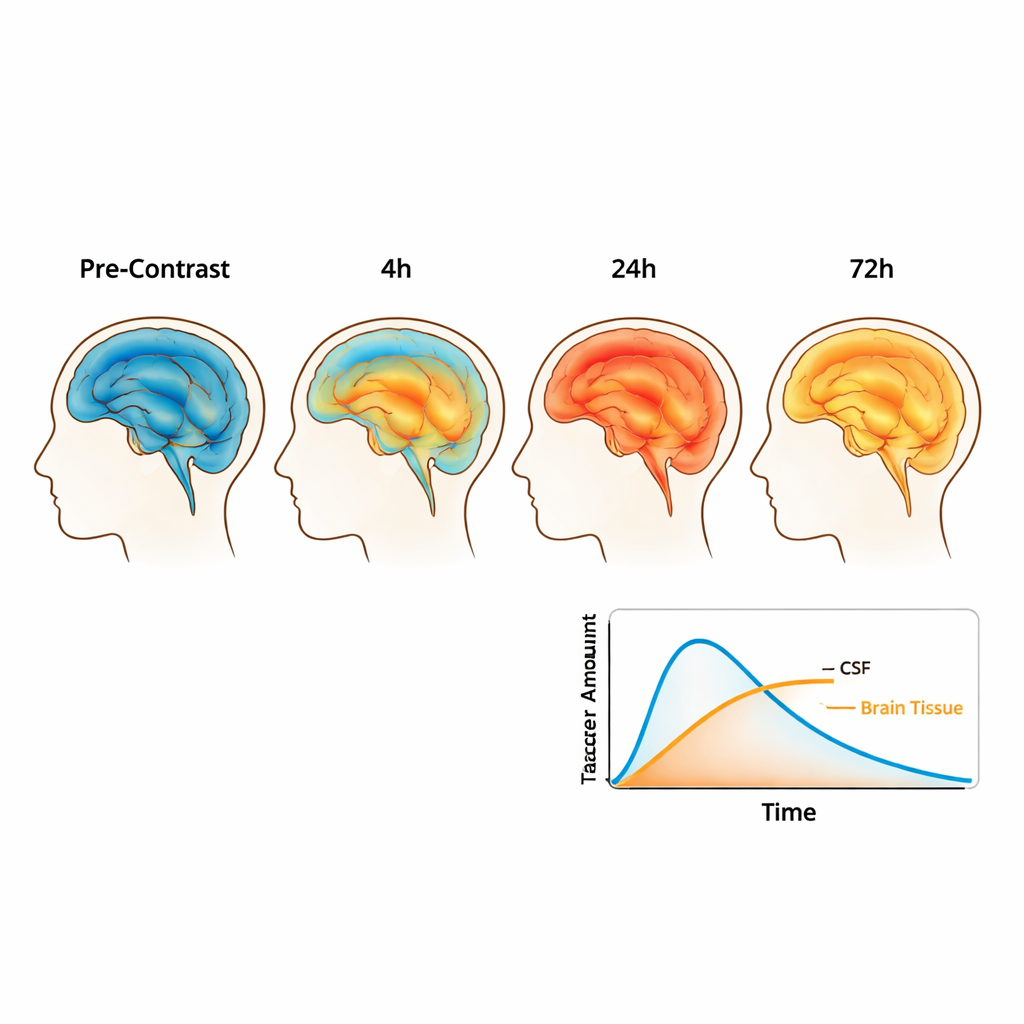
Suivre le traceur dans les fluides et les tissus cérébraux
À partir de ces cartes traitées, les auteurs ont estimé la concentration du traceur dans chaque petit volume du cerveau et des liquides environnants à chaque point temporel. Au début, la majorité du traceur reste dans les espaces liquidiens qui enveloppent le cerveau, mais au cours de la première journée il se propage plus largement et pénètre dans le tissu lui‑même. Après 24 heures, près de la moitié du traceur injecté est retrouvée dans la tête, répartie à peu près également entre le tissu cérébral et les espaces liquidiens. À 48 et 70 heures, la quantité totale commence à diminuer et devient plus uniformément distribuée, traduisant à la fois une clairance hors du cerveau et un mélange continu. L’équipe a aussi extrait des mesures de la facilité avec laquelle l’eau diffuse à travers différents tissus, ce qui aide à caractériser la structure microscopique de la matière blanche et grise et peut influencer la façon dont les substances se propagent.
Construire un modèle cérébral 3D pour les simulations
Au‑delà des images, l’étude fournit des modèles informatiques tridimensionnels prêts à l’emploi du cerveau du volontaire. Les chercheurs ont construit des maillages détaillés — des réseaux d’éléments tétraédriques — qui approchent la forme du cerveau, de ses espaces liquidiens et des principales structures internes. Ils ont ensuite mappé les concentrations de traceur et les propriétés de diffusion issues de l’IRM sur ce maillage. Cela permet aux ingénieurs et aux mathématiciens d’exécuter des simulations réalistes du déplacement des molécules dans le tissu cérébral et le long des voies fluides, de tester des théories concurrentes sur les mécanismes de « nettoyage » du cerveau et de concevoir de nouvelles méthodes d’analyse, sans avoir à recommencer le lourd travail de traitement d’images. Le jeu de données est organisé en plusieurs archives téléchargeables, depuis les scans bruts jusqu’aux maillages entièrement préparés, afin que les utilisateurs choisissent le niveau adapté à leur expertise.
Ce que cela signifie pour la recherche cérébrale future
Les auteurs soulignent clairement que les données d’une seule personne ne peuvent répondre à des questions médicales ni étayer des affirmations statistiques générales sur les maladies. Les profils de flux de liquide cérébral varient largement d’un individu à l’autre, aussi ce jeu de données doit‑il être considéré comme un banc d’essai de haute qualité plutôt que comme un échantillon de population. Sa valeur réelle réside dans le fait de fournir aux chercheurs un cas de référence commun et ouvert : un cerveau humain profondément caractérisé avec l’évolution d’un traceur cartographiée dans le temps. En rendant chaque étape de traitement transparente et en partageant le code avec les données, l’étude abaisse la barrière d’entrée pour que d’autres développent et valident des modèles de transport des fluides cérébraux. À long terme, de tels modèles pourraient aider à clarifier comment le cerveau élimine ses déchets, comment ce processus se dégrade dans la maladie et comment nous pourrions mieux administrer des médicaments directement via les voies fluides du cerveau.
Citation: Riseth, J.N., Koch, T., Lian, S.L. et al. Human brain MRI data of intrathecally injected tracer evolution over 72 hours for data-integrated simulations. Sci Data 13, 245 (2026). https://doi.org/10.1038/s41597-026-06564-1
Mots-clés: liquide cérébrospinal, système glymphatique, IRM cérébrale, transport de traceur, simulation cérébrale