Clear Sky Science · fr
L’étude HUNT identifie des facteurs génétiques hôtes associés de façon reproductible à la composition du microbiote intestinal humain
Pourquoi vos gènes et vos bactéries intestinales comptent
Chacun de nous porte des trillions de microbes dans ses intestins qui aident à digérer les aliments, à entraîner notre système immunitaire et peuvent même influencer notre risque de maladie. Cette étude pose une question apparemment simple : dans quelle mesure cet écosystème intérieur est-il inscrit dans notre ADN ? En scrutant les génomes de dizaines de milliers de personnes et en les comparant à la composition détaillée de leur microbiote intestinal, les chercheurs montrent que certains gènes humains orientent de façon répétée le microbiome dans des directions particulières — et que ces variations se relient à des affections telles que la maladie cœliaque, les hémorroïdes et des problèmes cardiaques, ainsi qu’au poids corporel.
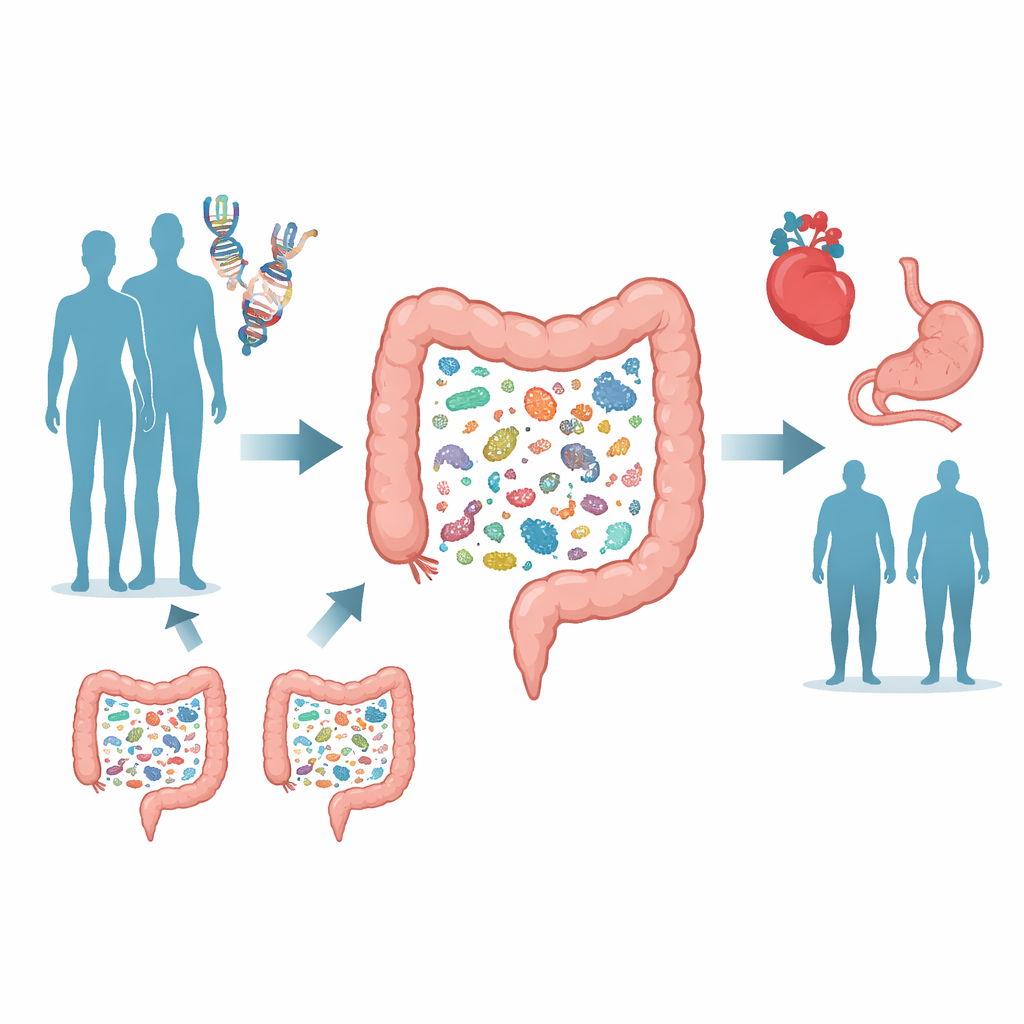
Rechercher des motifs dans une foule
Pour repérer des liens gène–microbe, l’équipe s’est appuyée sur l’étude de santé de Trøndelag en Norvège, où plus de 12 000 adultes ont fourni à la fois du sang pour l’analyse de l’ADN et des échantillons de selles pour le profilage microbien. Contrairement à de nombreux projets antérieurs qui utilisaient des empreintes bactériennes relativement grossières, ce travail reposait sur un séquençage métagénomique approfondi, qui lit une grande partie de l’ADN de chaque échantillon et peut distinguer des centaines d’espèces bactériennes distinctes et leurs capacités métaboliques. Les scientifiques ont ensuite réalisé une étude d’association à l’échelle du génome, sondant près de huit millions de variants génétiques humains pour voir lesquels s’alignaient avec des différences dans l’abondance relative de 546 espèces intestinales communes et avec des mesures de la diversité microbienne globale.
Six points chauds génétiques qui façonnent l’intestin
L’analyse a révélé une empreinte génétique étonnamment marquée. Douze associations robustes ont émergé entre des variants d’ADN humains et des espèces bactériennes spécifiques, regroupées en six régions du génome. Deux de ces régions, près du gène LCT impliqué dans la digestion du lactose et du gène du groupe sanguin ABO, avaient été impliquées auparavant, mais quatre — près de HLA-DQB1, MUC12, SLC37A2 et FUT2 — étaient nouvelles ou nouvellement confirmées. Par exemple, les personnes porteuses de la version persistante de la lactase (LCT) avaient tendance à héberger moins de Bifidobacterium adolescentis, une espèce qui prospère sur le sucre du lait restant dans l’intestin lorsque le lactose n’est pas complètement dégradé. La région FUT2, qui influence l’affichage des sucres du groupe sanguin à la surface de la muqueuse intestinale, était liée à plusieurs espèces bactériennes qui semblent se nourrir de ces surfaces recouvertes de sucres.
Des microbes au risque de maladie
Le tableau est devenu plus intrigant lorsque les chercheurs ont superposé ces résultats génétiques à de vastes bases de données sur les maladies humaines. Des variants dans la région HLA-DQB1 liés à des niveaux plus élevés d’une espèce d’Agathobacter étaient également associés à un risque réduit de maladies auto-immunes, y compris la maladie cœliaque. Les personnes atteintes de la maladie cœliaque dans la cohorte norvégienne présentaient des niveaux particulièrement bas de ce microbe, ce qui suggère que la maladie peut, en partie, remodeler la communauté intestinale. Une autre région, près du gène MUC12, était connectée à la fois à l’abondance d’une bactérie appelée Coprobacillus cateniformis et à un risque réduit de maladie hémorroïdaire. Des travaux en laboratoire ont montré que MUC12 est fortement exprimé dans les cellules qui tapissent le côlon, laissant entendre que des modifications subtiles de cette barrière mucineuse pourraient influencer quelles bactéries prospèrent et comment elles affectent, en retour, les petits vaisseaux et tissus délicats du rectum.
Fonctions microbiennes, santé cardiaque et poids corporel
Au-delà des espèces individuelles, l’équipe a examiné ce que les microbes sont capables de faire en regroupant leurs gènes en modules fonctionnels, tels que les systèmes de transport et les circuits de régulation. Les mêmes régions génétiques humaines — LCT, ABO et FUT2 — influaient également sur ces fonctions microbiennes, suggérant que notre ADN façonne non seulement qui est présent dans l’intestin, mais aussi ce qu’ils font. Au site FUT2, par exemple, des variants associés au statut de « non-secrétant » coïncidaient avec des bactéries liées à des métabolites potentiellement nocifs et avec un risque accru d’hypercholestérolémie et d’hypertension. Enfin, à l’aide d’une technique appelée randomisation mendélienne, qui utilise des variants génétiques comme expériences naturelles, les chercheurs ont trouvé des preuves qu’un indice de masse corporelle plus élevé modifie causalement le microbiome : les personnes génétiquement prédisposées à un poids plus élevé avaient tendance à présenter une diversité microbienne globale plus faible et des changements cohérents dans de nombreuses espèces.
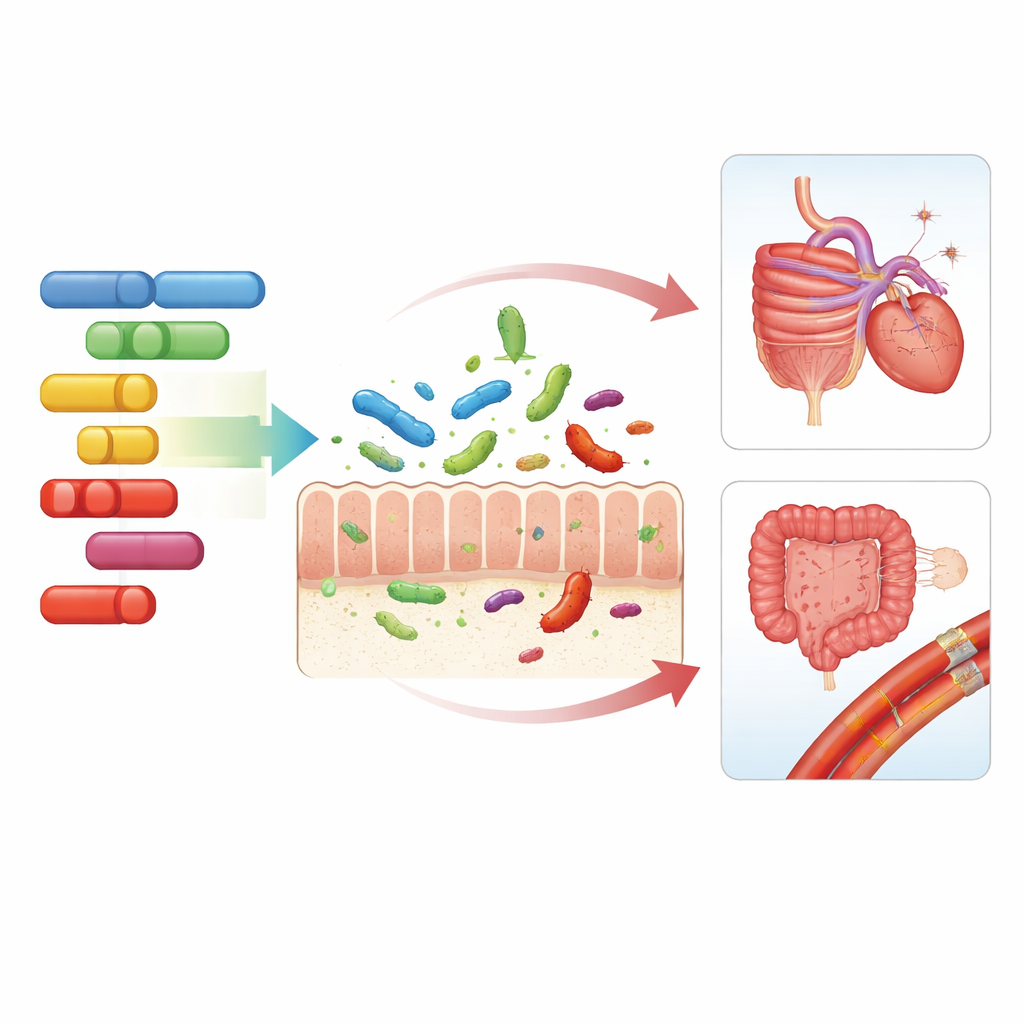
Qu’est-ce que cela signifie pour la santé quotidienne
Dans l’ensemble, ces résultats dessinent le portrait d’une conversation à trois entre nos gènes, nos microbes intestinaux et notre santé. Certains segments d’ADN humain favorisent ou défavorisent subtilement des résidents bactériens et des activités microbiennes spécifiques, qui interfèrent ensuite avec les risques de maladies digestives, de problèmes cardiaques et vasculaires et avec les effets d’un excès de poids. Si ces influences génétiques n’expliquent qu’une partie de l’énorme variation des communautés intestinales — et ne se traduisent pas encore par des tests cliniques — elles aident à clarifier pourquoi les individus réagissent différemment au même régime ou au même environnement et orientent vers des approches plus personnalisées de la nutrition et de la prévention des maladies prenant en compte à la fois le génome et le microbiome.
Citation: Moksnes, M.R., Coward, E., Nethander, M. et al. The HUNT study identifies host genetic factors reproducibly associated with human gut microbiota composition. Nat Genet 58, 530–539 (2026). https://doi.org/10.1038/s41588-026-02502-4
Mots-clés: microbiote intestinal, génétique humaine, microbiote et maladie, poids corporel et microbes, étude d’association à l’échelle du génome