Clear Sky Science · fr
Construction de séquences d’ADN complexes et diversifiées en utilisant des jonctions à trois brins
Construire de nouvelles histoires génétiques
La biologie moderne peut lire et modifier l’ADN à une vitesse étonnante, mais la rédaction de longues séquences génétiques sur mesure reste en retard. Cet écart freine tout, de la conception de nouveaux médicaments à la création de matériaux plus écologiques. Cette étude présente « Sidewinder », une nouvelle méthode d’assemblage d’ADN destinée à rendre l’écriture de gènes complexes et personnalisés aussi fiable et évolutive que leur lecture.
Pourquoi l’assemblage d’ADN mérite d’être repensé
Chaque cellule fonctionne grâce à l’ADN, une longue chaîne de lettres chimiques qui codent les instructions de la vie. Les scientifiques ne peuvent synthétiser chimiquement que de courtes portions d’ADN ; les gènes plus longs doivent donc être assemblés à partir de nombreux petits fragments, comme des phrases reconstituées à partir de mots découpés. Les méthodes actuelles utilisent toutes des bords complémentaires sur ces fragments pour guider leur accolement. Mais ces bords deviennent partie intégrante de l’ADN final, ce qui empêche de les optimiser librement pour un assemblage parfait sans modifier aussi le gène. À mesure que les designs s’allongent et se complexifient, ce compromis intégré entraîne davantage d’erreurs, des rendements plus faibles et des limites pratiques sur ce qu’on peut construire.
Un chemin secondaire qui guide sans laisser de trace
Sidewinder résout ce problème en ajoutant un troisième brin d’ADN d’aide qui n’apparaît jamais dans le produit fini. Les fragments d’ADN sont préparés avec deux caractéristiques à leurs extrémités : de courtes « amorces » (toeholds) qui finiront par former la connexion finale et sans couture, et de plus longues « codes-barres » conçues uniquement pour dialoguer avec leurs partenaires prévus. Lorsqu’on mélange ces fragments à une température contrôlée, les codes-barres des pièces voisines se reconnaissent et s’enroulent en une hélice latérale temporaire, formant une jonction à trois brins qui rapproche les amorces correspondantes. Une enzyme scelle alors les fragments principaux d’ADN. Enfin, les codes-barres auxiliaires sont retirés, laissant une séquence propre et continue sans cicatrices ni étiquettes supplémentaires. 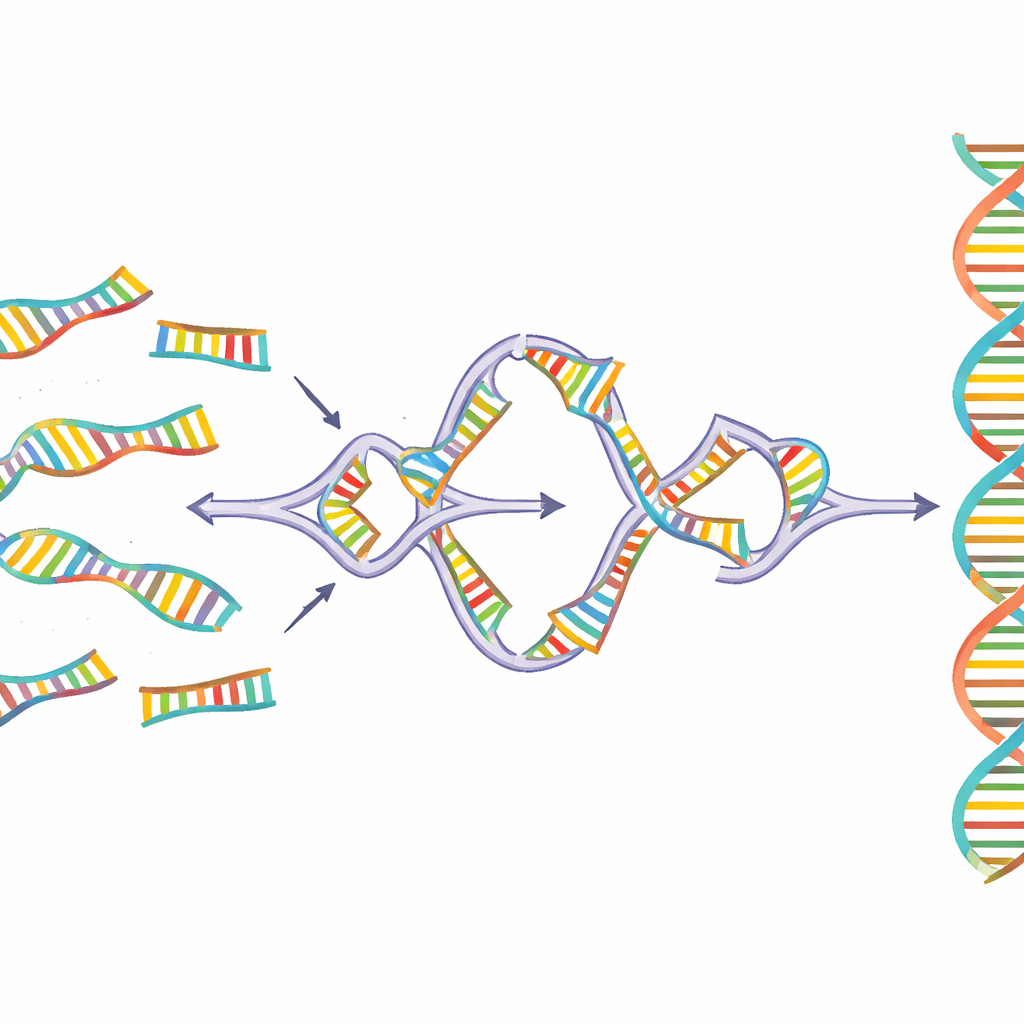
De dizaines de fragments à des gènes difficiles
Pour démontrer les capacités de Sidewinder, les auteurs ont assemblé des constructions d’ADN à partir de 5, 10, 20 et même 40 fragments distincts en une seule réaction. Les méthodes contemporaines de pointe échouent au-delà de quelques fragments, produisant des mélanges désordonnés ou des échecs complets, tandis que Sidewinder a systématiquement fourni un produit unique de la bonne taille. Le séquençage longue lecture a confirmé que, dans un test à 40 fragments, plus de 96 % des lectures étaient de véritables produits Sidewinder et que chacun d’eux était assemblé dans l’ordre parfait. L’équipe a ensuite éprouvé la méthode sur des séquences en « mode difficile » : un gène humain à très haute teneur en G et C, et un segment de protéine semblable à de la soie riche en répétitions. Ce type de séquence défie souvent les assemblages standards car elles s’auto‑accrochent de manière perturbante. Sidewinder a néanmoins produit des assemblages quasi parfaits, même lorsque toutes les jonctions partageaient délibérément la même séquence d’amorce, ce qui serait presque impossible à contrôler avec les techniques plus anciennes.
Beaucoup de gènes en même temps et des océans de variantes
Parce que les codes‑barres de Sidewinder définissent de façon unique qui peut s’apparier, plusieurs gènes peuvent être construits dans le même tube sans contamination croisée. Les chercheurs ont mélangé des fragments pour trois protéines marqueuses de couleurs différentes et les ont assemblés en une seule potée. Avec les amorces appropriées, ils pouvaient amplifier sélectivement n’importe quel gène ou le mélange, et le séquençage a montré que les croisements incorrects entre designs étaient extrêmement rares. 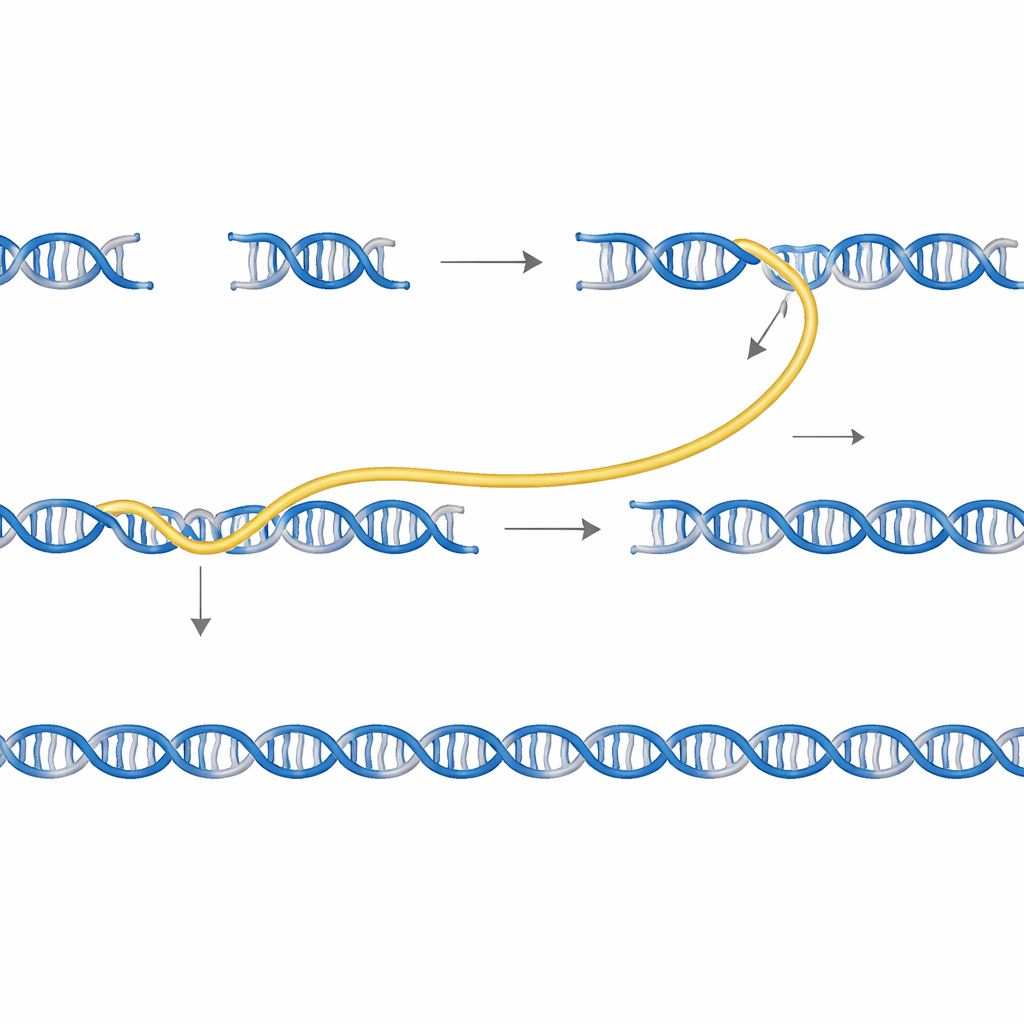
Ce que cela signifie pour l’ingénierie biologique future
La réussite clé de Sidewinder est de séparer les « instructions d’assemblage » de l’histoire finale de l’ADN. En déplaçant l’information guide sur un brin latéral amovible, les chercheurs peuvent concevoir des jonctions extraordinairement spécifiques et fiables sans être contraints de compromettre le gène lui‑même. Le résultat est une méthode polyvalente pour construire des séquences d’ADN longues, difficiles et très variées avec une précision comparable, et à certains égards supérieure, à la qualité des fragments de départ. À mesure que des outils comme l’IA proposent des designs génétiques audacieux, des techniques comme Sidewinder pourraient devenir essentielles pour transformer ces idées en molécules réelles destinées à la médecine, aux matériaux, à l’agriculture et au‑delà.
Citation: Robinson, N.E., Zhang, W., Ghosh, R. et al. Construction of complex and diverse DNA sequences using DNA three-way junctions. Nature 651, 491–500 (2026). https://doi.org/10.1038/s41586-025-10006-0
Mots-clés: assemblage d’ADN, biologie synthétique, bibliothèques de gènes, nanotechnologie de l’ADN, ingénierie des protéines