Clear Sky Science · fr
SMART : agrégation spatiale multi-omique utilisant des réseaux de neurones graphes et l’apprentissage métrique
Voir les tissus comme des cartes de voisinage
Nos corps sont constitués de quartiers cellulaires animés, où gènes, protéines et organisation de l’ADN coopèrent à des emplacements précis. De nouveaux microscopes et outils de séquençage peuvent désormais lire plusieurs de ces couches moléculaires directement dans des coupes de tissu, mais transformer ce flot de données spatiales et multi‑couches en images claires de l’organisation des organes reste un défi informatique majeur. Cette étude présente SMART, une méthode informatique qui aide les scientifiques à fusionner ces signaux complexes en cartes détaillées montrant où résident les différentes communautés cellulaires et comment elles sont disposées.
Pourquoi cartographier les voisinages cellulaires est difficile
Les technologies modernes de « multi‑omiques spatiales » peuvent mesurer plusieurs types d’informations moléculaires à la fois — comme l’ARN, les protéines de surface et l’accessibilité de la chromatine — tout en conservant la position exacte de chaque mesure dans une coupe tissulaire. Chaque type, ou « omique », offre un point de vue différent sur le comportement cellulaire, mais ils sont bruités, de très haute dimension et ne s’alignent pas naturellement les uns avec les autres. De plus, des cellules d’un même type ne sont pas toujours regroupées ; elles peuvent apparaître comme des îlots dispersés à travers un organe. Les outils logiciels existants ignorent souvent la disposition spatiale, simplifient à l’excès les relations entre omiques ou peinent à monter en charge sur les très grands jeux de données produits par les nouveaux instruments.
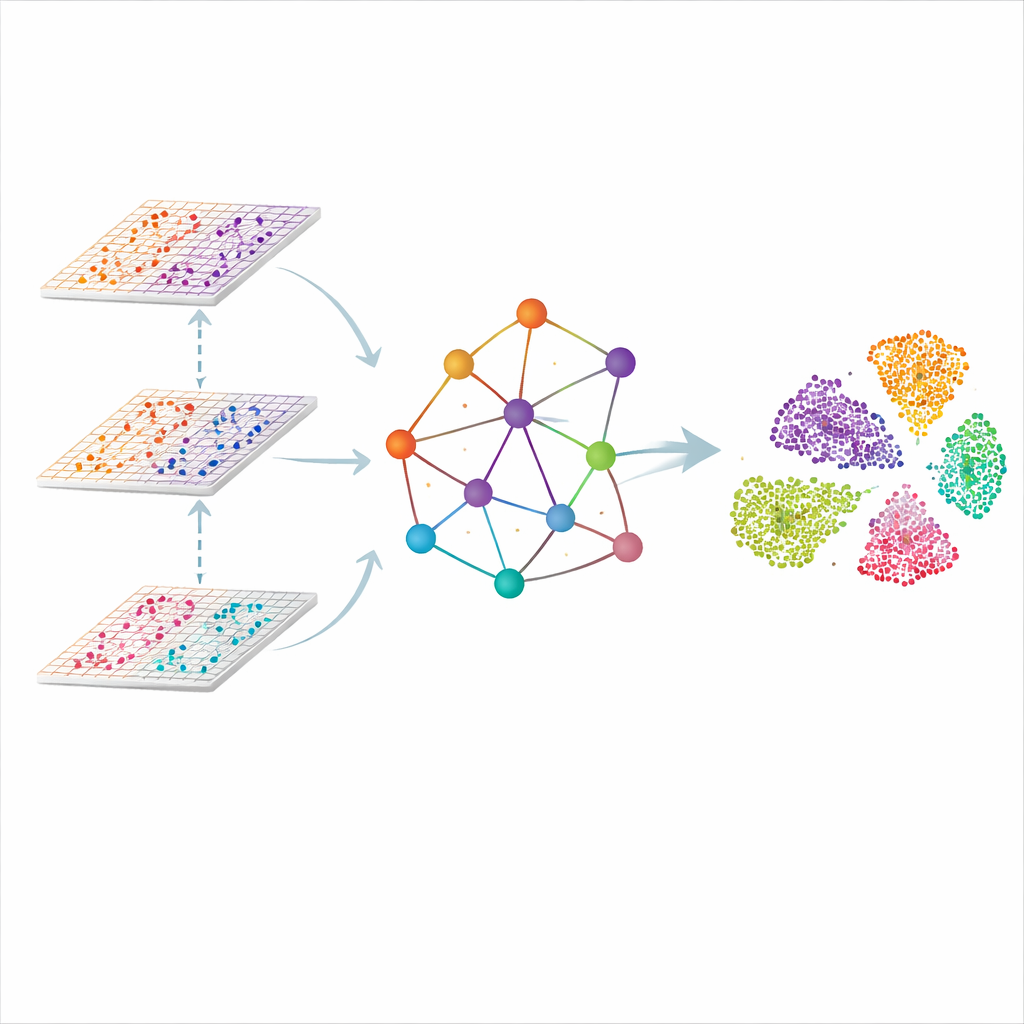
Un graphe du tissu, pas seulement une liste de cellules
SMART aborde le problème en traitant chaque point de mesure dans le tissu comme un nœud d’un réseau. Les points voisins sont reliés pour former un graphe spatial, et les lectures moléculaires de chaque omique sont d’abord compressées en un ensemble réduit de caractéristiques coordonnées qui captent des motifs globaux plutôt que des gènes individuels. Un type de réseau neuronal conçu pour les graphes transmet ensuite l’information le long des liaisons, permettant à chaque point « d’écouter » ses voisins tout en gardant une trace de la contribution de chaque omique. Le résultat est une représentation partagée et de faible dimension dans laquelle des régions similaires du tissu — comme des couches distinctes du cerveau ou des zones d’un nœud lymphatique — se regroupent naturellement.
Apprendre au modèle ce qui doit être similaire
Se contenter de suivre les voisins physiques ne suffit pas, car des cellules du même type peuvent être éloignées. SMART ajoute un second ingrédient emprunté aux systèmes de reconnaissance faciale : l’apprentissage métrique avec triplets. Pour chaque point, la méthode trouve automatiquement un autre point aux motifs moléculaires très proches (un « positif ») et un point clairement différent (un « négatif »). Elle ajuste ensuite la représentation interne pour que les positifs soient rapprochés et les négatifs éloignés, même s’ils sont distants sur la coupe tissulaire. Cette lutte d’attraction/répulsion s’exécute en parallèle d’une étape de reconstruction qui force SMART à préserver les détails clés de chaque couche omique, équilibrant continuité spatiale et spécificité moléculaire.
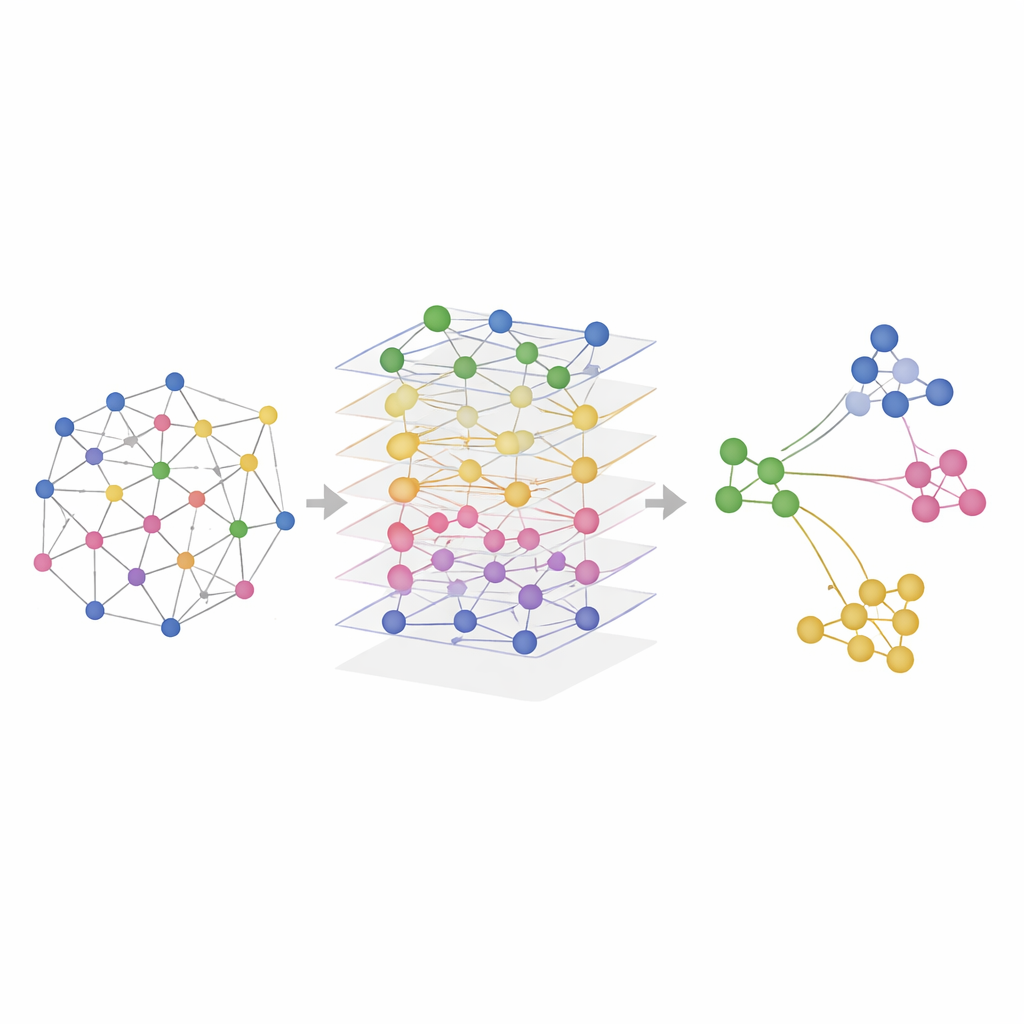
Tester SMART sur de vrais tissus
Les chercheurs ont testé SMART sur des données simulées et sur des expériences réelles mesurant des combinaisons d’ARN, de protéines et d’accessibilité de la chromatine dans des cerveaux de souris, des rateaux (spleens) de souris, des ganglions lymphatiques humains et des amygdales. Dans des simulations contrôlées où les régions spatiales vraies étaient connues, SMART a le mieux retrouvé les motifs de référence et a préservé les relations présentes dans chaque couche omique. Sur des jeux de données réels, SMART a identifié de manière constante des structures anatomiques fines — comme des régions cérébrales spécifiques ou des zones de cellules immunitaires dans les organes lymphoïdes — plus nettement que les méthodes concurrentes, tout en gardant des besoins computationnels modestes. Une version apparentée, appelée SMART‑MS, étend ces mêmes idées à plusieurs coupes tissulaires, alignant les tranches d’un même organe et corrigeant les différences techniques entre expériences.
Cartes rapides pour la prochaine vague de biologie spatiale
En termes simples, SMART est un moteur de cartographie pour la prochaine génération d’atlas moléculaires. En combinant une modélisation en réseau de la disposition tissulaire avec un sens intégré de ce qui doit être « similaire », il peut transformer d’immenses et désordonnées collections de mesures multi‑omiques spatiales en cartes de voisinage cohérentes des organes. Cela permet aux chercheurs de repérer plus facilement où résident certains types cellulaires et microenvironnements, comment ils évoluent au cours du développement ou de la maladie, et comment s’articulent les nouvelles technologies expérimentales. À mesure que les données spatiales augmentent en taille et en complexité, des outils comme SMART et SMART‑MS seront essentiels pour convertir des mesures brutes en connaissances biologiques.
Citation: Du, Z., Chen, Q., Huang, W. et al. SMART: spatial multi-omic aggregation using graph neural networks and metric learning. Nat Commun 17, 2876 (2026). https://doi.org/10.1038/s41467-026-70821-5
Mots-clés: multi-omiques spatiales, réseaux de neurones graphes, microenvironnement tissulaire, intégration de données, biologie unicellulaire