Clear Sky Science · fr
Profilage mécanistique basé sur la solubilité des thérapies médicamenteuses combinatoires
Pourquoi associer des médicaments peut compter
Les soins anticancéreux modernes reposent souvent sur des combinaisons de médicaments, mais déterminer quelles molécules fonctionnent le mieux ensemble reste largement empirique. Cette étude se concentre sur la leucémie myéloïde aiguë, un cancer du sang agressif qui récidive fréquemment après traitement. Les chercheurs présentent une nouvelle manière d’observer, à grande échelle, comment les protéines cellulaires réagissent lorsque deux médicaments sont administrés simultanément. Leur approche aide à expliquer pourquoi certaines combinaisons sont à la fois plus efficaces et moins toxiques, et propose une feuille de route pour concevoir des thérapies combinatoires plus intelligentes et plus précises pour les cancers difficiles.
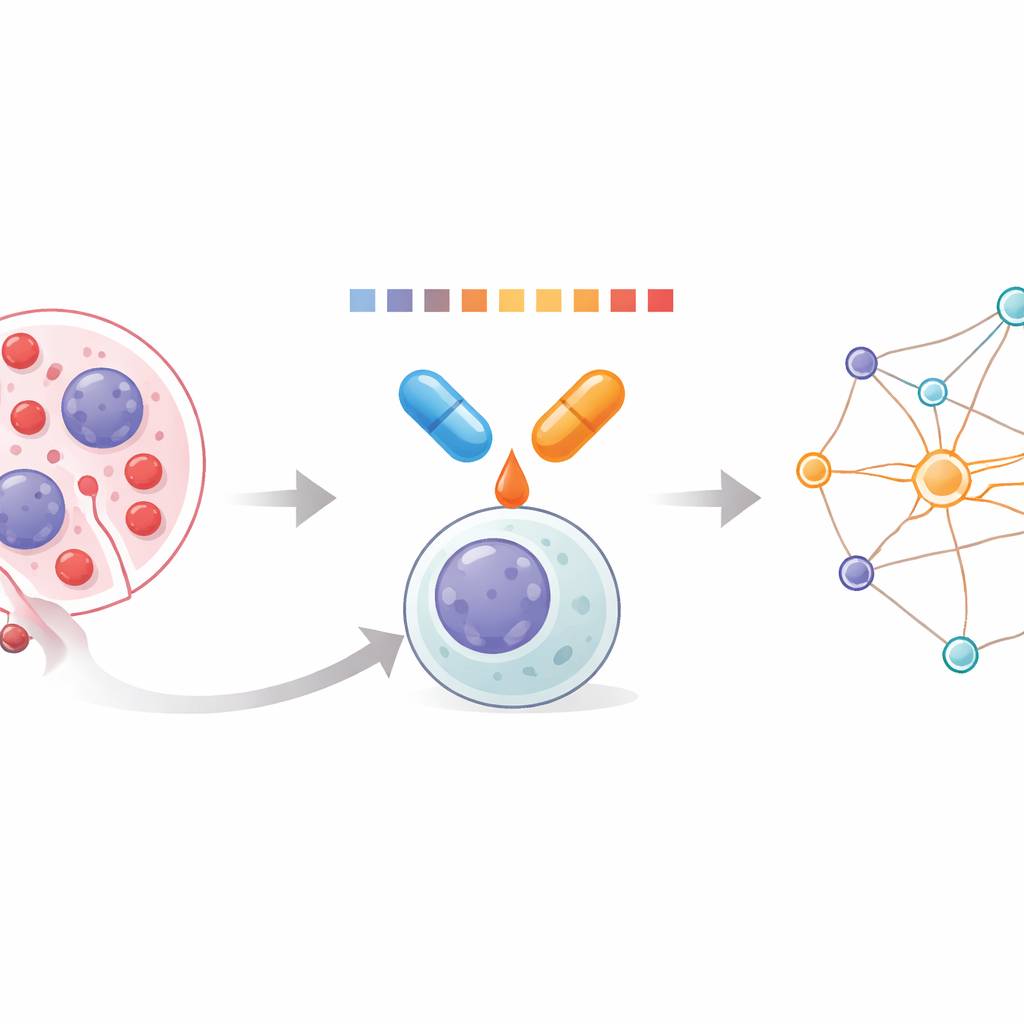
Plongée à l’intérieur des cellules leucémiques
La leucémie myéloïde aiguë (LMA) survient lorsque des globules blancs immatures dans la moelle osseuse prolifèrent de façon incontrôlée et déplacent la formation normale du sang. Parce que la LMA est pilotée par de nombreuses altérations génétiques différentes, les médicaments uniques fonctionnent rarement longtemps. Les combinaisons peuvent être plus efficaces, mais les cliniciens disposent de peu d’outils pour voir comment des paires de médicaments agissent ensemble au niveau des milliers de protéines à l’intérieur de la cellule. L’équipe à l’origine de ce travail a cherché à mesurer directement ces effets combinés, en utilisant une méthode qui lit la facilité avec laquelle les protéines se dissolvent ou s’agrègent lorsqu’on les chauffe. Les changements de solubilité révèlent quelles protéines sont stabilisées ou déstabilisées par le traitement, offrant une fenêtre sur l’impact réel des médicaments.
Une nouvelle façon de profiler les paires de médicaments
Les chercheurs ont développé un protocole qu’ils appellent Combinatorial Proteome Integral Solubility/Stability Alteration analysis, ou CoPISA. Des cellules, ou leurs extraits protéiques, sont exposés au médicament A, au médicament B, à la combinaison A+B, ou sans médicament. Chaque échantillon est ensuite brièvement chauffé selon une série de températures, et les protéines encore dissoutes sont capturées et quantifiées par spectrométrie de masse. Plutôt que d’ajuster des courbes complexes protéine par protéine, la méthode utilise l’aire totale sous le profil de dénaturation de chaque protéine comme mesure compacte de son comportement. Comparer ces aires entre traitements montre quelles protéines deviennent plus ou moins solubles selon les conditions, révélant des schémas propres aux médicaments seuls versus aux combinaisons.
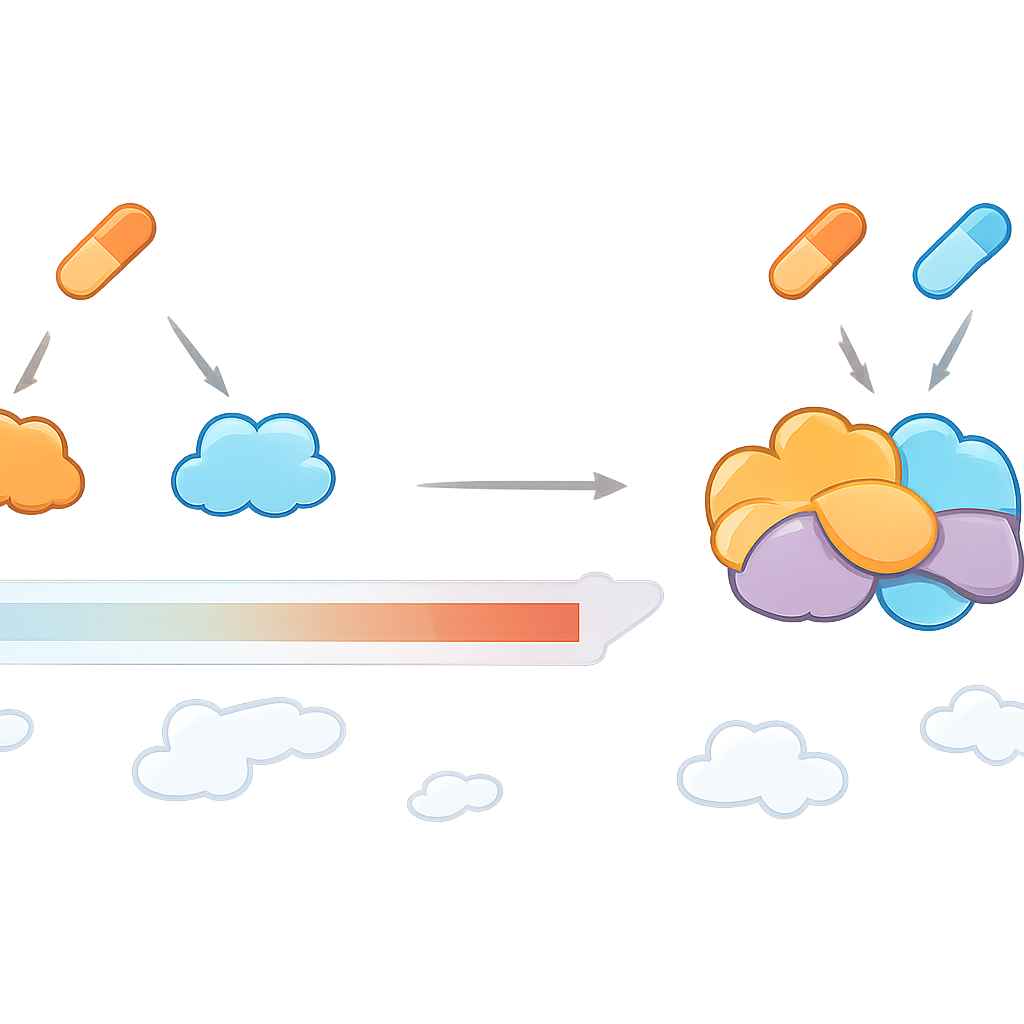
Trouver des cibles qui n’apparaissent qu’avec les deux médicaments
CoPISA a été appliqué à deux paires de médicaments choisies avec soin pour la LMA : LY3009120 avec sapanisertib (appelée LS), et ruxolitinib avec ulixertinib (RU). Ces paires avaient déjà montré une forte activité et une toxicité relativement faible dans des échantillons de patients, des lignées cellulaires et des modèles de poisson-zèbre. CoPISA a mis au jour non seulement des protéines affectées par chaque médicament seul, mais aussi un ensemble distinct de protéines dont la solubilité ne changeait que lorsque les deux médicaments étaient présents. Les auteurs décrivent cela comme un « ciblage conjonctionnel », similaire à une porte logique ET : la protéine répond uniquement si les deux entrées (médicaments) sont actives. Pour LS, ces effets spécifiques à la combinaison convergent vers des processus tels que le conditionnement de l’ADN, de petites étiquettes protéiques appelées SUMO qui contrôlent la stabilité du génome, et l’adhérence des cellules leucémiques à leur environnement tissulaire. Pour RU, les cibles uniques indiquent un affaiblissement des points de contrôle de la réparation de l’ADN, une production d’énergie mitochondriale altérée et un traitement de l’ARN perturbé.
Cartographier les points faibles du cancer
En superposant leurs données de solubilité sur de larges cartes de gènes et voies liés à la LMA, les chercheurs ont pu voir comment chaque traitement remodelait le câblage interne du cancer. De nombreux gènes bien connus de la LMA — tels que DNMT3A, NPM1 et TP53 — étaient affectés d’une manière qui n’apparaissait que sous thérapie combinatoire, renforçant l’idée que les paires de médicaments peuvent révéler des vulnérabilités invisibles aux agents seuls. L’équipe a également examiné les modifications chimiques des protéines, comme l’acétylation, la méthylation et la phosphorylation, qui agissent comme des interrupteurs moléculaires. Ils ont constaté que certaines formes modifiées de protéines clés, notamment NPM1 et le facteur de réparation de l’ADN BLM, étaient ciblées spécifiquement par les combinaisons, suggérant que des changements de localisation et de signalisation protéique contribuent à l’effet renforcé.
Ce que cela signifie pour les traitements futurs
Au total, l’étude montre que les combinaisons médicamenteuses peuvent créer leur propre paysage unique de cibles protéiques, plutôt que de simplement additionner les effets de chaque médicament. CoPISA fournit un moyen pratique de cartographier ce paysage, mettant en lumière des protéines et des voies qui ne deviennent vulnérables que lorsque deux médicaments agissent de concert. Pour les patients, cela pourrait se traduire par des thérapies combinatoires choisies non seulement parce qu’elles réduisent les tumeurs en laboratoire, mais parce qu’elles mobilisent les points faibles profonds du cancer tout en limitant la toxicité inutile. Bien que démontrée ici pour la LMA, l’approche est largement applicable et pourrait aider à orienter la conception rationnelle de traitements combinés dans de nombreuses maladies complexes.
Citation: Gholizadeh, E., Zangene, E., Vadadokhau, U. et al. Solubility based mechanistic profiling of combinatorial drug therapy. Nat Commun 17, 2744 (2026). https://doi.org/10.1038/s41467-026-70394-3
Mots-clés: leucémie myéloïde aiguë, combinaisons médicamenteuses, protéomique, solubilité des protéines, thérapie ciblée