Clear Sky Science · fr
Refonte inter-espèces de gènes tirant parti des informations d’orthologues et de la modélisation générative
Pourquoi la refonte de gènes entre espèces compte
La biotechnologie moderne doit souvent déplacer des gènes d’un microbe à un autre pour produire des médicaments, des enzymes ou des outils de dépollution. Pourtant, un gène performant dans son microbe d’origine peut échouer dans un nouvel hôte et produire peu de protéine. Cet article présente un nouveau système d’intelligence artificielle, OrthologTransformer, qui apprend de l’évolution elle-même pour réécrire des gènes afin qu’ils paraissent « natifs » dans une autre espèce, améliorant leurs performances et ouvrant de nouvelles possibilités pour la technologie verte et l’industrie.
Les limites des astuces actuelles d’ajustement des gènes
Depuis des décennies, les scientifiques utilisent une stratégie appelée optimisation des codons pour aider des gènes étrangers à fonctionner dans de nouveaux hôtes. L’idée est simple : le code génétique comporte plusieurs « codons » de trois lettres pouvant coder le même acide aminé, et différentes espèces préfèrent différents codons. Les outils traditionnels remplacent les codons rares par des codons préférés sans changer la séquence d’acides aminés de la protéine. Cela aide souvent, mais ignore de nombreuses autres caractéristiques importantes pour la performance d’un gène, comme le repliement de l’ARN, les signaux régulateurs et le rythme de production de la protéine. Dans certains cas, une sur-optimisation des codons peut même nuire au rendement protéique. Pendant ce temps, la nature résout l’adaptation inter-espèces de manière plus riche : les gènes apparentés dans différentes espèces, appelés orthologues, présentent couramment des changements d’acides aminés et de petites insertions ou délétions ainsi que des échanges de codons, tout en préservant la fonction globale.
Apprendre le mode d’emploi de la nature pour réécrire les gènes
OrthologTransformer considère la refonte des gènes comme une forme de traduction linguistique : donnée une séquence d’ADN d’une bactérie, il la « traduit » en la manière dont ce gène pourrait vraisemblablement apparaître dans une autre espèce. Le modèle repose sur l’architecture Transformer utilisée dans les outils linguistiques modernes, mais ici il opère sur des codons plutôt que sur des mots. Il est entraîné sur des millions de gènes orthologues appariés naturellement provenant de plus de deux mille espèces bactériennes, avec des jetons spéciaux indiquant de quelle espèce on convertit et vers quelle espèce. En observant comment l’évolution a déjà équilibré fonction et adaptation à l’hôte, le système apprend quand de simples échanges de codons suffisent et quand des changements discrets d’acides aminés ou des ajustements de longueur sont tolérés. Dans des tests couvrant 45 espèces bactériennes et des centaines de combinaisons source–cible, les gènes réécrits par l’IA ressemblaient davantage aux orthologues natifs de l’espèce cible que ceux issus de l’optimisation classique des codons et d’un optimiseur neuronal de codons de pointe, tout en conservant une grande similarité au niveau protéique. 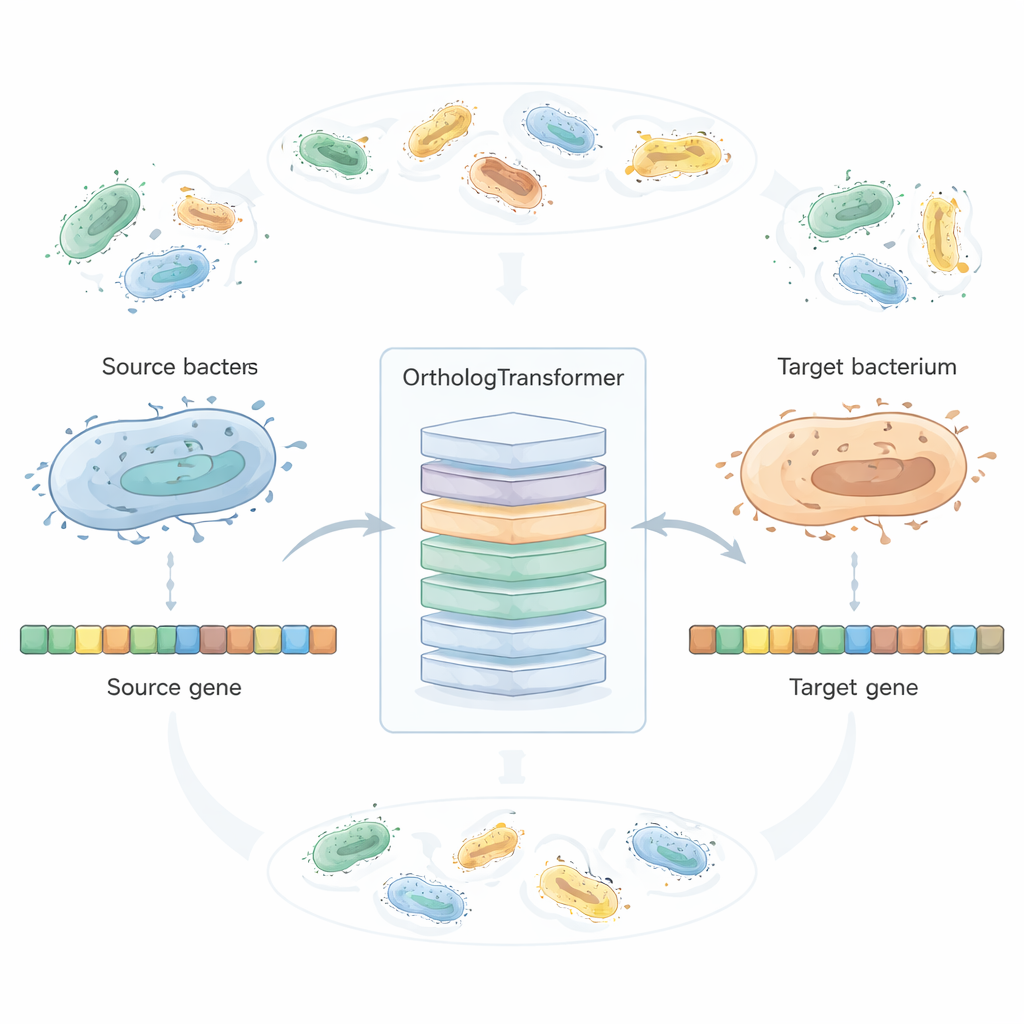
Mettre au travail des enzymes mangeuses de plastique conçues par l’IA
Pour montrer que ce n’est pas qu’un tour computationnel, l’équipe s’est concentrée sur PETase, une enzyme de la bactérie Ideonella sakaiensis capable de dégrader le PET plastique, le matériau utilisé pour la plupart des bouteilles de boisson. Ideonella croît lentement et n’est pas idéale pour un usage industriel, aussi les chercheurs ont-ils demandé à OrthologTransformer de réécrire le gène PETase pour un hôte à croissance plus rapide, Bacillus subtilis. Ils ont généré un panel de douze variantes de gènes réécrits, explorant différents réglages d’entraînement et une procédure de recherche supplémentaire qui orientait les séquences vers une composition ADN de type Bacillus et des structures d’ARN favorables. Malgré certaines variantes comportant de nombreux changements d’ADN et quelques substitutions d’acides aminés, les modèles informatiques prédisaient que la forme tridimensionnelle centrale de l’enzyme était préservée. Quand ces conceptions ont été construites et testées dans des cellules vivantes de Bacillus, plusieurs ont produit de grandes quantités de PETase sécrétée, et toutes ont montré une activité mesurable de dégradation du plastique.
Un design par IA qui surpasse l’optimisation standard
Une séquence conçue par l’IA, appelée AI-L2, s’est particulièrement distinguée. Les cellules de Bacillus portant ce gène sécrétaient des quantités particulièrement élevées de PETase et ont généré environ trois fois plus de produit de dégradation du plastique que toute autre souche lors d’un test de sept jours, et environ dix fois plus que des témoins typiquement optimisés en codons lorsqu’on mesure les produits de réaction. Des images au microscope de films de PET exposés aux cellules AI-L2 montraient des crevasses profondes et des trous où le plastique avait été rongé, bien plus spectaculaires que dans d’autres conditions. Des tests enzymatiques détaillés ont montré que la version AI-L2 de la PETase n’était pas seulement produite plus efficacement, mais traitait aussi son substrat plus rapidement, lui conférant une efficacité catalytique supérieure à celle des enzymes d’origine et optimisées en codons. Une expérience parallèle chez Escherichia coli a montré qu’une version de PETase conçue par OrthologTransformer, même lorsqu’elle ne changeait que l’usage des codons sans altérer la séquence d’acides aminés, surpassait néanmoins un gène optimisé en codons sur la base de fréquences, soulignant que le modèle capture des préférences subtiles et spécifiques à l’hôte que les méthodes traditionnelles manquent. 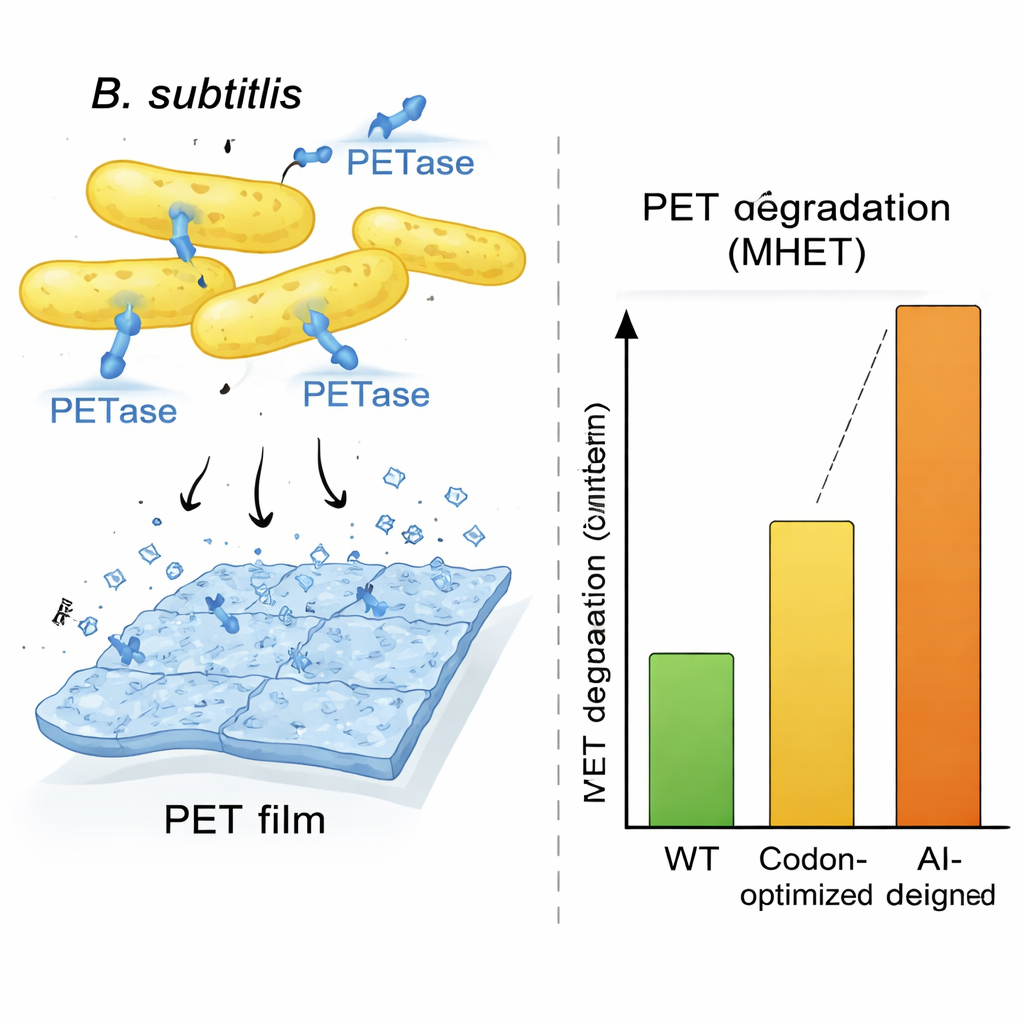
Ce que cela signifie pour la biologie et la technologie de demain
Concrètement, OrthologTransformer ressemble à un traducteur expert qui non seulement réécrit l’« orthographe » d’un gène pour un nouveau microbe, mais apporte aussi de petites modifications informées par l’évolution à la « phrase » elle-même quand il sait qu’elles seront sûres ou bénéfiques. En apprenant directement comment les gènes se sont naturellement adaptés à travers des milliers d’espèces bactériennes, il peut proposer de l’ADN réécrit qui fonctionne mieux dans de nouveaux hôtes que des conceptions limitées aux seuls échanges de codons. La création réussie d’une enzyme mangeuse de plastique plus puissante dans Bacillus subtilis suggère que cette refonte de gènes guidée par l’IA pourrait accélérer le développement de biocatalyseurs industriels, de microbes de dépollution et, à terme, même de thérapies géniques médicales, aidant les organismes à lire et utiliser des gènes étrangers comme s’ils étaient les leurs.
Citation: Akiyama, M., Tashiro, M., Huang, Y. et al. Cross-species gene redesign leveraging ortholog information and generative modeling. Nat Commun 17, 2120 (2026). https://doi.org/10.1038/s41467-026-69966-0
Mots-clés: refonte de gènes, biologie synthétique, gènes orthologues, IA en biotechnologie, enzymes dégradant le plastique