Clear Sky Science · fr
Un indice de sélection génomique non linéaire accélère l’amélioration multi-caractères des cultures
Un meilleur croisement pour un monde plus affamé
Alors que la population mondiale augmente et que le climat devient moins prévisible, les sélectionneurs de plantes doivent améliorer plusieurs caractères des cultures en même temps — comme le rendement, la hauteur et la date de floraison — plus rapidement que jamais. Cet article présente un nouvel outil mathématique qui aide les sélectionneurs à faire exactement cela en utilisant l’information ADN de manière plus réaliste, en capturant non seulement les effets individuels des gènes mais aussi leurs interactions. L’approche promet d’accélérer la création de nouvelles variétés de maïs et de blé sans qu’il soit nécessaire de mesurer chaque plante sur le terrain.
Pourquoi combiner de nombreux caractères est si difficile
Les sélectionneurs ne se préoccupent rarement d’un seul caractère. Par exemple, ils veulent un rendement en grain plus élevé, mais aussi des plantes plus courtes et plus robustes qui fleurissent au bon moment. Les « indices de sélection » classiques transforment plusieurs caractères en un seul score pour classer les plantes. Traditionnellement, ces indices supposent que chaque caractère contribue d’une manière simple, linéaire, et que les effets des différents caractères s’additionnent. La biologie réelle est plus complexe : les caractères s’influencent mutuellement, et il peut exister des points optimaux où « plus » n’est plus meilleur. Ignorer ces interactions non linéaires peut ralentir le progrès génétique et même orienter la sélection dans la mauvaise direction.
De lignes simples à des courbes flexibles
Les outils génomiques antérieurs permettaient aux sélectionneurs d’utiliser des marqueurs ADN répartis dans le génome pour prédire la qualité des descendants d’une plante, donnant lieu aux indices de sélection génomique dits linéaires. Ceux-ci fonctionnent bien quand les effets des gènes sont principalement additifs. Les auteurs étendent une idée plus ancienne et plus flexible — l’indice de sélection phénotypique quadratique, qui intégrait déjà des termes au carré et des interactions entre caractères — à l’ère de l’ADN. Leur nouvel outil, appelé Indice de Sélection Génomique Quadratique (QGSI), utilise des prédictions de valeurs de sélection génomique et les combine via des termes linéaires et courbes (quadratiques). Cela permet à l’indice de capturer des schémas complexes tels que les interactions gène–gène et les combinaisons optimales de caractères, même lorsque les mesures de terrain ne sont pas disponibles à chaque cycle.
Tester le nouvel indice
Pour savoir si cette complexité supplémentaire est payante, les chercheurs ont comparé le QGSI avec des indices linéaires et quadratiques n’utilisant que des données de terrain, ainsi qu’avec des indices génomiques linéaires qui utilisent l’ADN mais restent simples. Ils ont réalisé des simulations informatiques de sélection du maïs sur 10 cycles de sélection et ont aussi analysé deux jeux de données réels de maïs et cinq de blé provenant de programmes de sélection internationaux. Deux méthodes de prédiction de la valeur génétique à partir de l’ADN ont été testées : un modèle additif standard et un modèle à noyau gaussien plus flexible capable de capter des interactions géniques subtiles. Dans ces différents contextes, le QGSI a systématiquement produit des réponses de sélection plus importantes — c’est‑à‑dire une amélioration globale plus grande des caractères — que les indices linéaires, et a généralement surpassé l’indice phénotypique quadratique également.
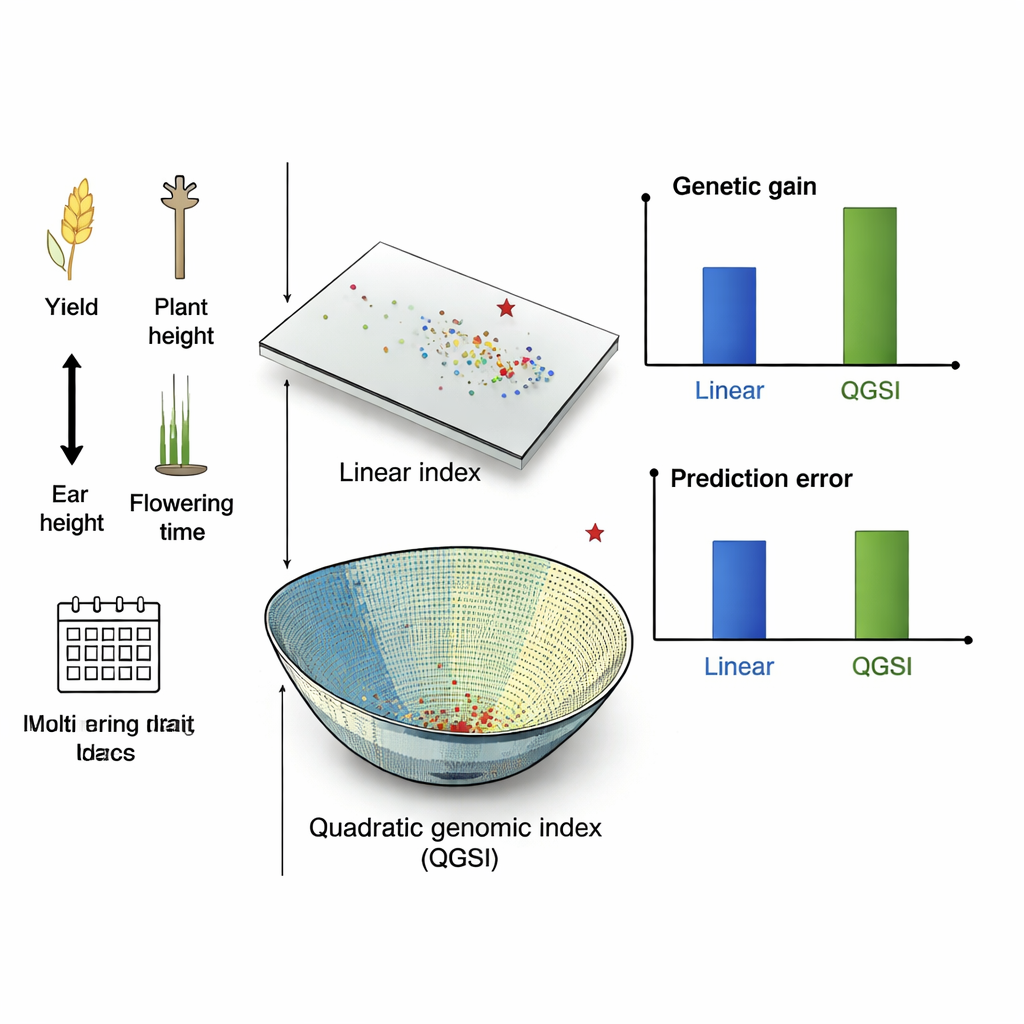
Meilleurs gains, moins d’erreurs, plus d’équilibre
Dans les cycles simulés de maïs, le QGSI a apporté les gains les plus élevés, devançant à la fois les indices génomiques linéaires et les indices quadratiques basés uniquement sur les mesures de terrain. Il avait aussi tendance à présenter une erreur de prédiction plus faible, ce qui signifie que ses scores étaient des guides plus fiables pour le choix des parents. Dans des populations réelles de maïs du Mexique et du Zimbabwe, le QGSI a obtenu des gains supérieurs de 80–90 % par rapport aux indices génomiques linéaires lorsque plusieurs caractères étaient améliorés simultanément. Dans des essais de blé menés sous différentes conditions d’irrigation et de pluviométrie, la tendance était similaire : les indices quadratiques surpassaient les indices linéaires, et l’association du QGSI avec le modèle à noyau gaussien a fourni les améliorations les plus fortes et les plus stables selon les environnements, en particulier pour le rendement en grain tout en maintenant la hauteur des plantes et le temps de floraison dans des plages acceptables.
Ce que cela signifie pour les cultures futures
Pour les non-spécialistes, le message clé est que les sélectionneurs disposent désormais d’un système de notation plus réaliste qui reflète la façon dont les gènes et les caractères interagissent réellement, plutôt que de les forcer dans un modèle linéaire. Les auteurs recommandent d’utiliser l’indice phénotypique quadratique lorsque seules des données de terrain sont disponibles aux premiers stades, et de passer au QGSI une fois que des données génomiques et des cycles de sélection rapides sont en place. En capturant mieux les relations génétiques non linéaires, le QGSI peut accélérer l’amélioration multi‑caractères des cultures et contribuer à fournir de nouvelles variétés de maïs et de blé à plus haut rendement, plus résilientes et mieux adaptées à des environnements difficiles.
Citation: Jesús Cerón-Rojas, J., Montesinos-López, O.A., Montesinos-López, A. et al. Nonlinear genomic selection index accelerates multi-trait crop improvement. Nat Commun 17, 1991 (2026). https://doi.org/10.1038/s41467-026-69890-3
Mots-clés: séléction génomique, amélioration des cultures, maïs, blé, amélioration multi-caractères