Clear Sky Science · fr
Étendre la portée des réseaux de neurones graphiques grâce à des encodages globaux
Pourquoi les liaisons à longue distance dans les molécules comptent
Des nouveaux médicaments aux batteries améliorées, bon nombre des avancées actuelles reposent sur des modèles informatiques capables de prédire comment des milliers d'atomes se repoussent et s'attirent. Une classe populaire de modèles d'IA, dite réseaux de neurones graphiques, est devenue un outil de référence pour cette tâche. Pourtant, ces modèles ont un angle mort : ils se concentrent principalement sur les voisins proches, alors que des atomes éloignés peuvent s'influencer fortement via des forces électriques et quantiques. Cet article présente RANGE, une méthode permettant d'offrir à ces réseaux neuronaux une sorte de vue globale afin qu'ils puissent « ressentir » et prédire les effets à longue distance sans devenir excessivement lents ni gourmands en mémoire.
Comment l'IA actuelle ne voit que le voisinage
Les réseaux de neurones graphiques considèrent une molécule ou un matériau comme un réseau de nœuds (atomes) reliés par des arêtes (leurs relations). À chaque étape, chaque nœud met à jour son état en ne communiquant qu'avec ses voisins proches situés dans une distance fixe. Répéter cela de nombreuses fois propage lentement l'information, mais cette stratégie présente deux inconvénients majeurs. D'une part, les messages peuvent se brouiller en passant par de nombreux intermédiaires, un problème connu sous le nom de sur-lissage. D'autre part, des voies étroites dans le graphe peuvent limiter la quantité d'information transmise, provoquant un écrasement de l'information (oversquashing). Les deux problèmes deviennent sérieux lorsqu'il s'agit de capturer des forces agissant sur plusieurs angströms, comme l'électrostatique et la dispersion dans de grandes molécules ou cristaux. Simplement étendre la distance d'interaction ou empiler plus de couches rend les modèles coûteux et ne résout pas entièrement ces goulots d'étranglement.
Ajouter des hubs virtuels pour une communication globale
RANGE (Relaying Attention Nodes for Global Encoding) reconfigure ce schéma en ajoutant un petit ensemble de « nœuds maîtres » virtuels qui ne correspondent à aucun atome réel. Ils servent plutôt de hubs globaux. Après une étape ordinaire de passage de messages entre atomes voisins, l'information provenant de tous les atomes est rassemblée dans ces hubs au moyen d'un mécanisme d'attention : chaque nœud maître apprend quelles parties du système il doit privilégier. Cette agrégation crée des résumés grossiers de l'état de la molécule. Dans une seconde étape de diffusion, ces résumés sont renvoyés à chaque atome, à nouveau via l'attention afin que chaque atome décide combien il doit écouter chaque nœud maître tout en conservant sa mémoire locale via des auto-boucles. Parce que chaque atome se connecte directement à chaque nœud maître, la communication à longue portée peut se produire en une seule étape, transformant le graphe en un réseau à « petit monde » où des régions éloignées peuvent s'influencer rapidement et efficacement. 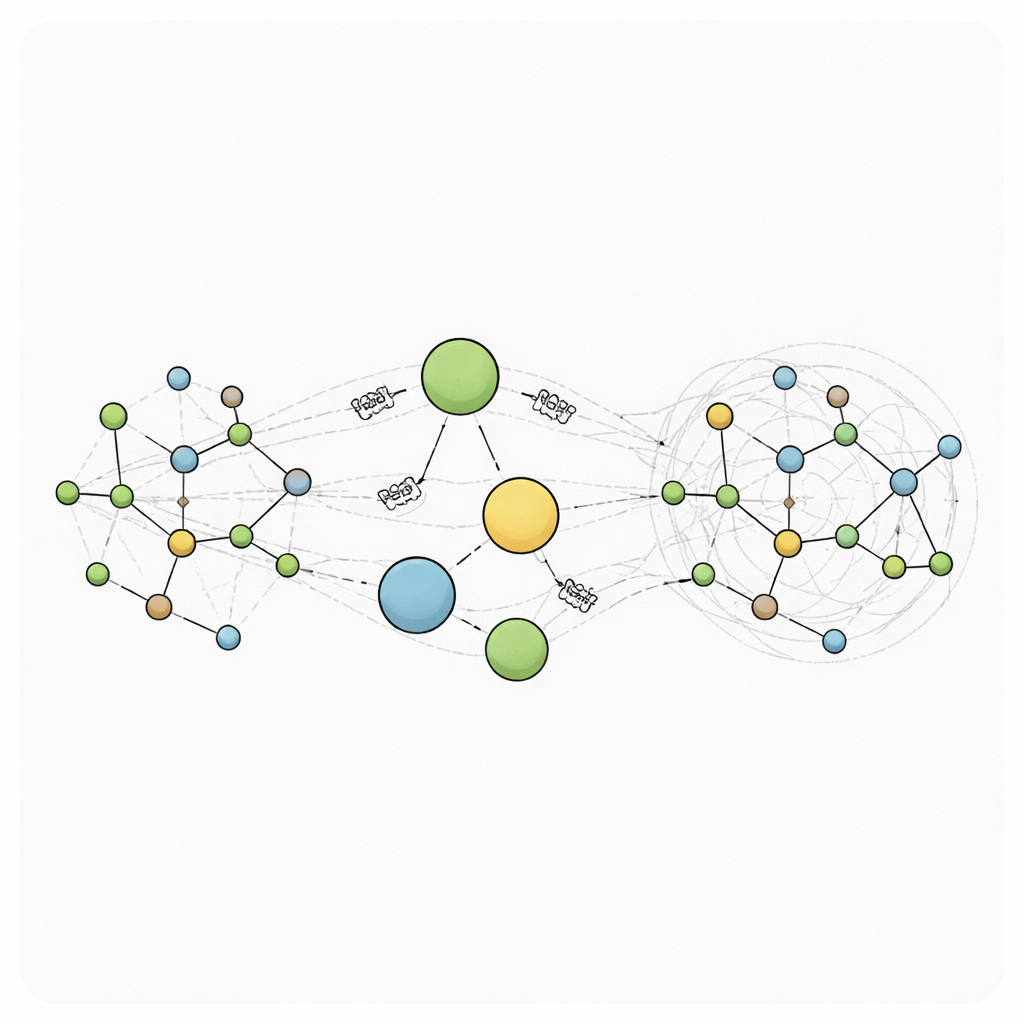
Voir les forces à longue portée que d'autres manquent
Les chercheurs ont testé RANGE en l'attachant à plusieurs modèles de champs de force moléculaires à la pointe et en les comparant avec leurs versions originales purement locales. Ils ont utilisé des systèmes difficiles où les effets à longue portée sont connus pour être cruciaux : un cristal salin avec un ion sodium supplémentaire agissant comme dopant, un dimère d'or approchant une surface oxydée dopée, et des paires de molécules organiques interagissant à des distances variables. Les modèles standards ont largement échoué à percevoir comment des réarrangements de charges lointains ou des dopants cachés modifiaient le paysage énergétique ; leurs prédictions changeaient à peine lorsque l'environnement à longue portée variait. En revanche, les modèles augmentés par RANGE ont correctement capturé les différentes courbes d'énergie et ont pu extrapoler à des séparations supérieures à celles vues pendant l'entraînement, avec des erreurs jusqu'à quatre fois plus faibles pour des dimères chargés difficiles.
Précision sans casser l'ordinateur
De manière cruciale, RANGE apporte cette vision améliorée sans le coût informatique élevé des autres approches globales. Des techniques empruntées à la physique, comme la sommation d'Ewald ou les corrections basées sur la transformée de Fourier, nécessitent des opérations qui croissent grossièrement comme le carré du nombre d'atomes ou dépendent de grands maillages, les rendant lourdes pour les grands systèmes et les simulations répétées. RANGE, par conception, évolue linéairement avec la taille du système : chaque nœud maître se connecte à tous les atomes, mais le nombre de nœuds maîtres croît modestement et est contrôlé par un schéma de régularisation qui empêche leur redondance. Les benchmarks sur des jeux de données plus vastes montrent que RANGE réduit systématiquement les erreurs sur les forces prédites, même lorsque les modèles sous-jacents utilisent des coupures d'interaction courtes, et ce avec seulement une augmentation modérée du temps d'exécution et de la mémoire. L'équipe a également effectué des simulations de dynamique moléculaire sur des dizaines de nanosecondes pour des molécules complexes, constatant que les champs de force basés sur RANGE restaient stables et exploraient des conformations et états réalistes. 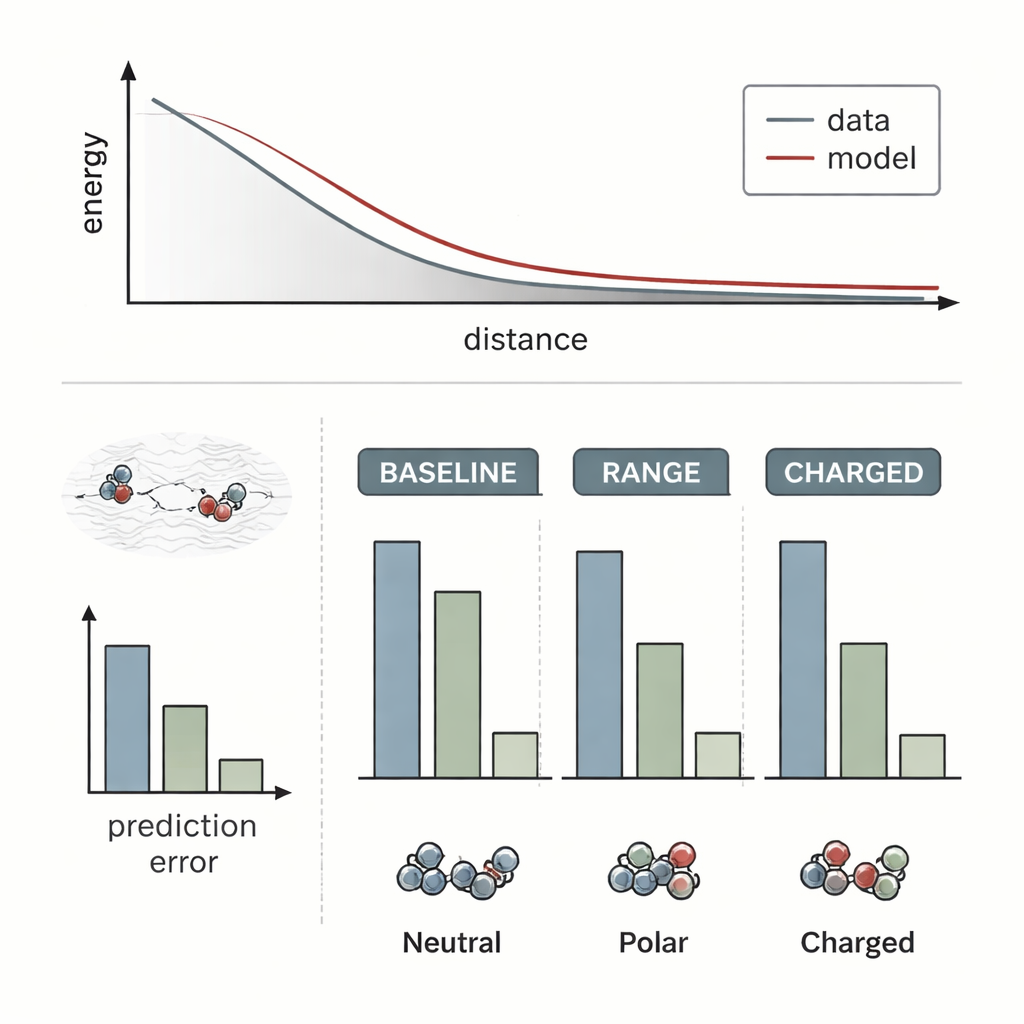
Une vision d'ensemble plus claire des mondes moléculaires
Pour les non-spécialistes, le message clé est que RANGE offre aux modèles d'IA basés sur les graphes un nouveau moyen de penser globalement tout en opérant localement. En introduisant des hubs virtuels intelligents et un flux d'information piloté par l'attention, il surmonte les goulots d'étranglement habituels qui empêchent les réseaux neuronaux de saisir les effets à longue distance et à plusieurs corps dans les molécules et matériaux. Cela signifie des prédictions plus fiables pour les systèmes où des régions éloignées s'influencent subtilement — des molécules médicamenteuses flexibles aux nanostructures étendues — sans facture computationnelle prohibitive. À mesure que ces méthodes sont appliquées à des environnements toujours plus grands et plus complexes, elles promettent des outils d'IA capables de mieux refléter la trame réelle et à longue portée des interactions physiques.
Citation: Caruso, A., Venturin, J., Giambagli, L. et al. Extending the range of graph neural networks with global encodings. Nat Commun 17, 1855 (2026). https://doi.org/10.1038/s41467-026-69715-3
Mots-clés: réseaux de neurones graphiques, interactions à longue portée, simulations moléculaires, champs de forces appris par machine, mécanismes d'attention