Clear Sky Science · fr
Découverte de peptides antimicrobiens ciblant Acinetobacter baumannii via une chaîne de traitement basée sur l’apprentissage par quelques exemples pré‑entraînée et ajustée
Pourquoi c’est important pour la santé de tous les jours
Les infections résistantes aux médicaments augmentent si rapidement qu’à la moitié du siècle elles pourraient tuer chaque année plus de personnes que le cancer. L’un des agents les plus préoccupants est Acinetobacter baumannii, un germe hospitalier tenace qui résiste à de nombreux antibiotiques et infecte souvent les patients sous ventilation. Cette étude montre comment des scientifiques ont combiné intelligence artificielle et expériences de laboratoire pour découvrir rapidement de nouveaux petits candidats médicaments capables de tuer cette bactérie tout en causant beaucoup moins de dommages à l’organisme que notre médicament de dernier recours actuel.
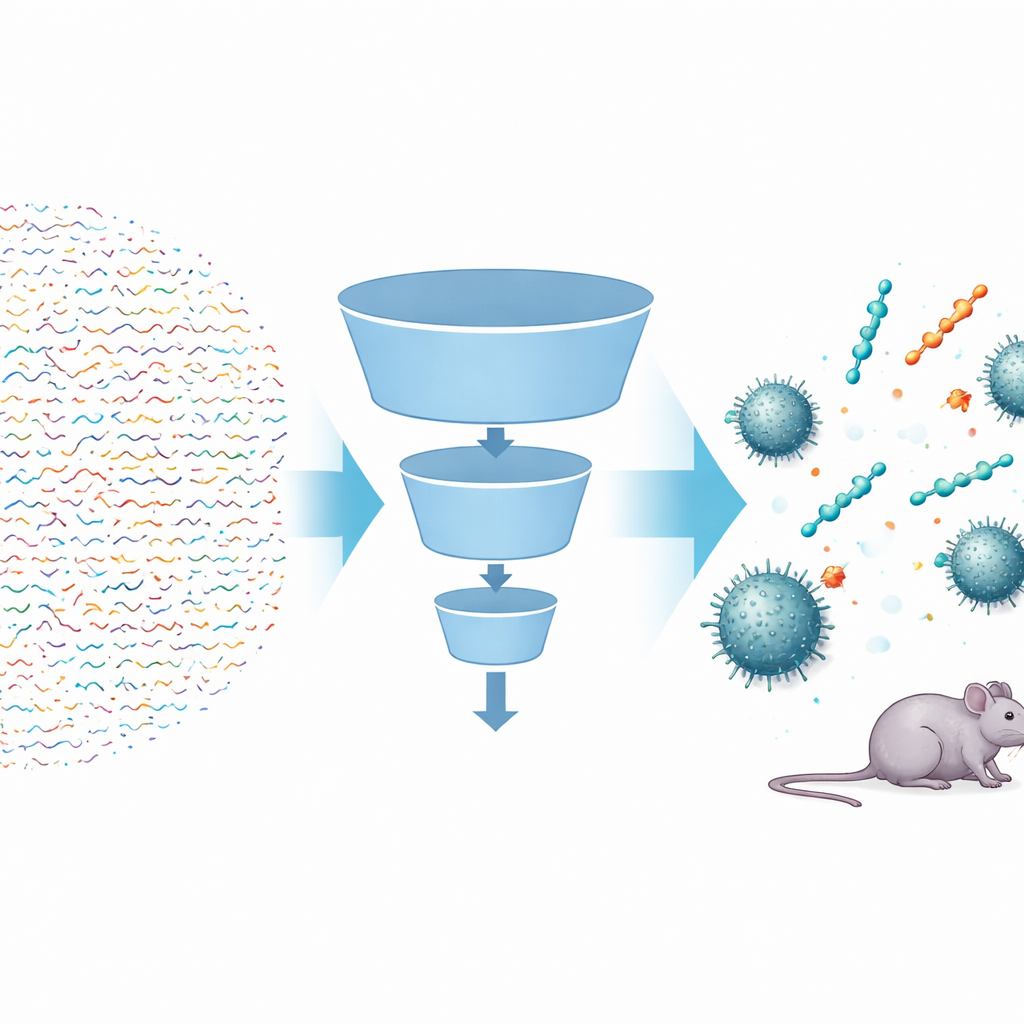
Un super‑microbe hospitalier difficile à éradiquer
Acinetobacter baumannii est une bactérie à Gram négatif qui prospère en unité de soins intensifs, notamment chez les patients dépendants de ventilateurs. Sa coque extérieure robuste et son génome qui évolue rapidement la rendent résistante à de nombreux antibiotiques courants. Aujourd’hui, l’une des rares options restantes est un médicament appelé polymyxine B, mais il peut gravement endommager les reins et la bactérie peut malgré tout développer une résistance. Parallèlement, une classe prometteuse de petits fragments protéiques appelés peptides antimicrobiens a été explorée contre d’autres microbes, mais très peu se sont avérés spécifiquement efficaces contre A. baumannii. Le criblage traditionnel par essai‑erreur est tout simplement trop lent et coûteux pour parcourir l’immensité des séquences peptidiques courtes possibles.
Utiliser des algorithmes intelligents pour explorer un espace immense
Les chercheurs ont construit une chaîne de traitement en plusieurs étapes basée sur l’intelligence artificielle, appelée FSLSMEP, pour balayer des bibliothèques entières de peptides courts — composés de six, sept ou huit unités — soit des dizaines de milliards de candidats. Le défi était qu’ils ne disposaient que de 148 peptides connus actifs contre A. baumannii, beaucoup trop peu pour les méthodes d’apprentissage automatique standard. Pour contourner cela, ils ont commencé par un puissant modèle pré‑entraîné qui avait déjà « lu » des centaines de millions de séquences protéiques naturelles et appris des règles générales sur le comportement de ces molécules. Ils ont ensuite affiné ce modèle en deux étapes : d’abord sur un jeu de peptides plus large actifs contre une bactérie apparentée, Pseudomonas aeruginosa, puis enfin sur les rares données d’A. baumannii. En parallèle, trois modules reliés — un pour trier les peptides probables des improbables, un pour les classer, et un pour estimer la puissance potentielle de chacun — ont fonctionné comme des filtres successifs dans un entonnoir.
Des prédictions informatiques aux succès en éprouvette
Après avoir d’abord écarté les peptides les moins prometteurs à l’aide de règles chimiques simples, l’équipe a soumis près de quatre millions de candidats à leur pipeline. Le classificateur a éliminé la plupart des séquences qui ne semblaient pas antimicrobiennes ; le modèle de classement a favorisé celles dont les caractéristiques suggéraient une forte activité ; et le modèle de régression a prédit la concentration minimale nécessaire pour arrêter la croissance bactérienne. À partir de soixante‑quatre millions de peptides à six unités, le système n’a proposé que dix candidats principaux. Lorsqu’ils ont été synthétisés et testés en laboratoire, neuf d’entre eux ont montré une activité antibactérienne réelle, un taux de réussite remarquable en découverte de médicaments. Les mêmes modèles entraînés ont ensuite été appliqués, sans nouvel entraînement, à des espaces de peptides beaucoup plus vastes de sept et huit unités, dont les chercheurs ont choisi d’autres séquences les mieux classées pour les tests. Là encore, la plupart se sont révélées actives, y compris des heptapeptides aussi puissants que la polymyxine B contre certaines souches.
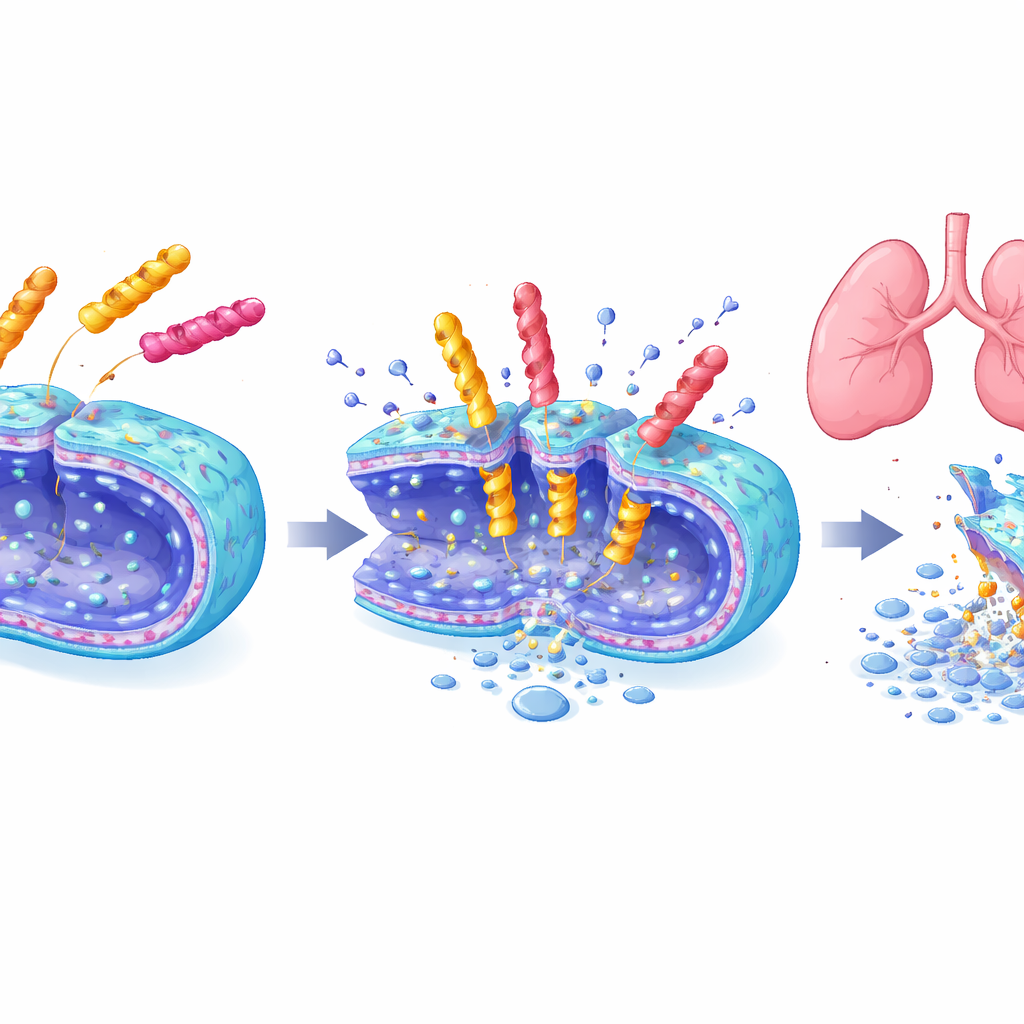
Tueurs puissants avec une approche plus douce
Trois peptides principaux — un issu des bibliothèques à six, sept et huit unités — ont été examinés en détail. Ils ont rapidement éliminé les populations d’A. baumannii en quelques minutes à quelques heures, endommagé les membranes bactériennes comme on l’a observé en microscopie électronique, et ont également été actifs contre plusieurs autres microbes dangereux. Dans le même temps, ils ont peu nui aux cellules de mammifères en culture ou aux globules rouges, contrairement à certains peptides antimicrobiens existants. Lors d’expositions prolongées, les bactéries n’ont pas facilement développé de résistance à ces nouvelles molécules, alors que la résistance à la polymyxine B est montée rapidement. Plus frappant encore, dans un modèle murin de pneumonie, une dose inhalée de l’heptapeptide EME7(7) a éliminé les infections pulmonaires aussi efficacement que la polymyxine B sans endommager les reins, alors que la polymyxine B provoquait des lésions rénales évidentes et des augmentations des marqueurs sanguins du stress rénal.
Ce que cela signifie pour les médicaments futurs
Ce travail montre qu’une chaîne de traitement IA soigneusement conçue peut transformer un jeu de données minuscule et incomplet en un moteur puissant de découverte de nouveaux peptides antimicrobiens. En combinant un pré‑entraînement large, un affinage par étapes et plusieurs couches de filtrage, les chercheurs ont exploré efficacement des bibliothèques entières de peptides courts et trouvé des candidats qui combattent à la fois un dangereux super‑microbe hospitalier et semblent plus sûrs pour les organes vitaux. La même stratégie a également permis de trouver des peptides actifs contre le pathogène fongique Candida albicans, suggérant qu’elle pourrait être réutilisée pour rechercher de nombreux autres types de peptides thérapeutiques. Pour les patients, cette approche pourrait éventuellement se traduire par de nouveaux médicaments traitant des infections tenaces sans les effets secondaires sévères et la résistance rapide qui minent les antibiotiques de dernier recours d’aujourd’hui.
Citation: Huang, J., Zhang, W., Wang, A. et al. Discovery of antimicrobial peptides targeting Acinetobacter baumannii via a pre-trained and fine-tuned few-shot learning-based pipeline. Nat Commun 17, 2475 (2026). https://doi.org/10.1038/s41467-026-69306-2
Mots-clés: peptides antimicrobiens, résistance aux antibiotiques, Acinetobacter baumannii, découverte de médicaments par apprentissage automatique, few‑shot learning