Clear Sky Science · fr
Multiplicité hétérogène de variants blaCTX-M sur le même plasmide favorise l’adaptabilité évolutive chez Klebsiella pneumoniae clinique
Pourquoi cela compte pour la médecine moderne
Les infections résistantes aux antibiotiques représentent une menace croissante dans les hôpitaux du monde entier, et les médecins s’appuient de plus en plus sur des médicaments de dernier recours pour sauver des vies. Cette étude explique comment une bactérie courante en milieu hospitalier, Klebsiella pneumoniae, peut utiliser une astuce génétique subtile pour résister à des combinaisons d’antibiotiques puissantes conçues pour dépasser la résistance. En dévoilant cette stratégie, la recherche aide à comprendre pourquoi certaines infections récidivent malgré des traitements agressifs — et fournit des pistes pour permettre aux médecins de garder une longueur d’avance.
Un germe hospitalier sous pression
L’histoire commence en unité de soins intensifs, où deux patients ont été infectés par des souches de K. pneumoniae presque identiques. Une souche était facilement traitée par la combinaison moderne ceftazidime/avibactam, tandis que l’autre montrait une forte résistance. Les comparaisons génétiques ont montré que les deux souches portaient la même grande famille d’enzymes de résistance, appelées bêta‑lactamases, sur un plasmide partagé — un petit cercle d’ADN mobile à l’intérieur des bactéries. Mais dans la souche résistante, l’une de ces enzymes avait changé subtilement, et cette variante, nommée CTX‑M‑249, permettait à la bactérie d’ignorer la combinaison médicamenteuse qui aurait dû la tuer.
Un petit changement aux grandes conséquences
Des tests biochimiques plus approfondis ont révélé que CTX‑M‑249 échangeait un type de protection contre un autre. La version habituelle, CTX‑M‑65, est excellente pour dégrader certains antibiotiques comme le céfotaxime, mais reste vulnérable à l’inhibiteur avibactam. CTX‑M‑249, modifiée seulement en deux positions de la protéine, devient performante face au couple ceftazidime plus avibactam mais perd une grande partie de son efficacité contre le céfotaxime. Sur le papier, cela ressemble à un compromis évolutif classique : gagner une défense tout en en affaiblissant une autre. Pourtant la souche clinique a évité cet inconvénient en portant plusieurs copies étroitement apparentées du gène simultanément, de sorte que différentes versions de l’enzyme pouvaient coexister dans la même lignée bactérienne.
Plusieurs copies, plusieurs options
Grâce au séquençage à lectures longues et à des méthodes de comptage précises, les chercheurs ont découvert que le plasmide de la souche résistante portait deux sites séparés blaCTX‑M, et que l’un d’eux pouvait exister en plusieurs versions légèrement différentes. En l’absence de pression médicamenteuse, environ la moitié de la population portait la version CTX‑M‑65 ancienne et presque autant portait CTX‑M‑249, avec une petite fraction présentant des formes intermédiaires. Lorsque les bactéries ont été exposées à des doses croissantes de ceftazidime/avibactam, à la fois le nombre de copies du gène et la part de CTX‑M‑249 ont fortement augmenté. Parfois, cela s’est produit par une augmentation du nombre de plasmides par cellule ; à des niveaux plus élevés d’antibiotique, le plasmide lui‑même a produit de courts répétitions en tandem du gène de résistance. En pratique, les bactéries utilisaient la duplication d’ADN comme un bouton de réglage qu’elles pouvaient monter ou descendre pour s’adapter aux antibiotiques environnants.
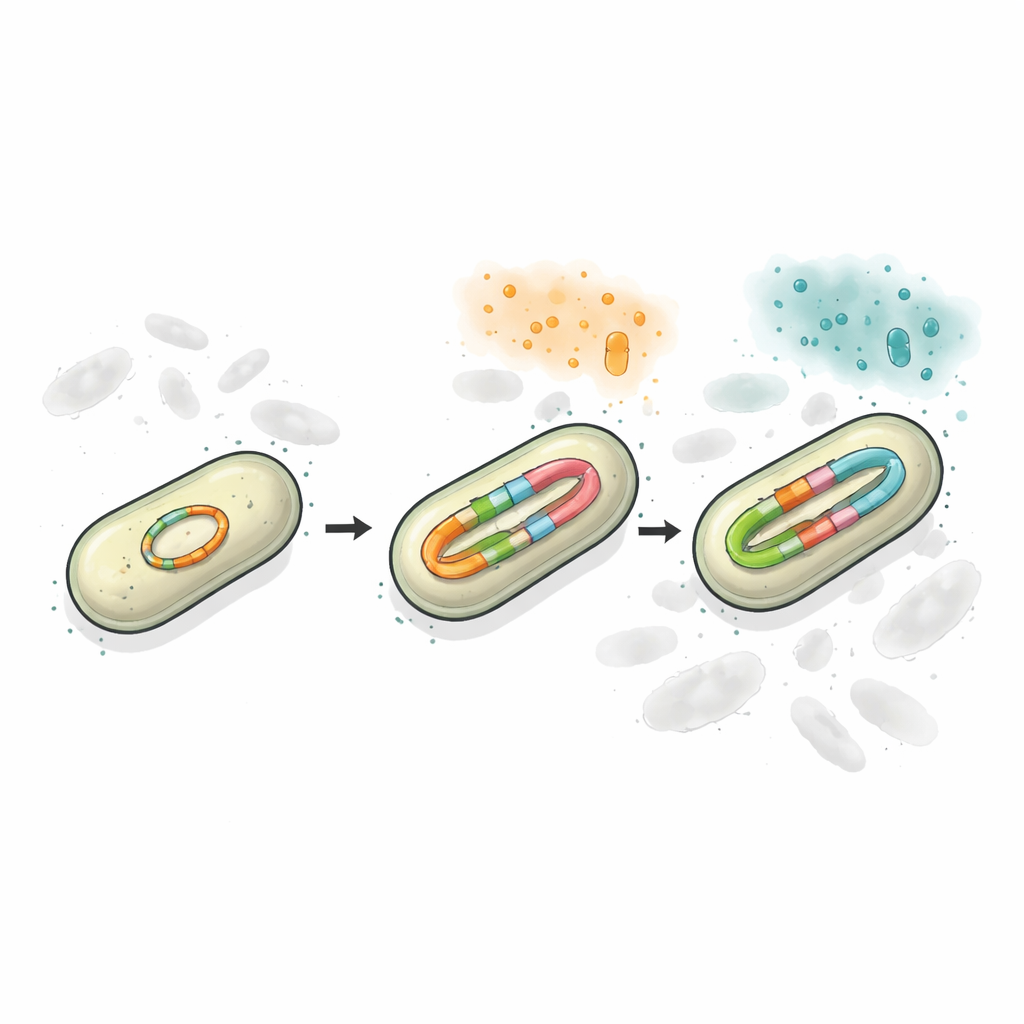
Conserver la diversité sur un seul cercle d’ADN
Pour tester comment cet agencement influence la survie, l’équipe a construit des modèles simplifiés en laboratoire dans lesquels les bactéries portaient soit une seule version de résistance, soit deux versions sur des plasmides séparés, soit les deux versions codées ensemble sur un même plasmide. Lors d’un défi avec deux céphalosporines différentes, les systèmes mixtes ont surpassé les souches à gène unique, car au moins une version de l’enzyme pouvait faire face à chaque médicament. Cependant, la configuration où les deux variantes du gène étaient présentes sur le même plasmide s’est révélée la plus stable. Lorsque des antibiotiques étaient appliqués pendant plusieurs jours ou alternés d’un médicament à l’autre, les cellules portant deux plasmides séparés perdaient souvent l’un d’eux, sacrifiant une partie de leur protection. En revanche, le plasmide « deux en un » était hérité comme un ensemble, préservant les deux options de résistance même lorsqu’il imposait un coût de croissance à court terme.
Un schéma plus large chez des bactéries dangereuses
Des modèles mathématiques ont reproduit ces expériences, montrant que, au‑dessus de certains niveaux d’antibiotiques, les bactéries portant un seul plasmide contenant plusieurs variantes de résistance dominent finalement les populations mixtes. Les chercheurs ont ensuite examiné des milliers de génomes de K. pneumoniae provenant d’hôpitaux, d’exploitations agricoles, d’aliments et de l’environnement. Ils ont fréquemment trouvé plusieurs copies légèrement différentes de gènes de résistance clés — en particulier chez des isolats cliniques humains soumis à une forte exposition aux médicaments. Cela suggère que la construction d’une « hétérogénéité multicopie » au sein des plasmides n’est pas une rare curiosité, mais une tactique répandue que les bactéries utilisent pour se prémunir contre des traitements changeants.
Ce que cela signifie pour les patients et le traitement
Pour un non‑spécialiste, le message central est que certaines bactéries ne portent pas simplement un seul gène de résistance ; elles portent des familles de versions apparentées regroupées sur le même élément d’ADN mobile, leur fournissant une boîte à outils flexible contre différents médicaments. Cet agencement leur permet de maintenir la résistance sur de longues périodes, même lorsque les médecins changent de thérapie, et aide à expliquer pourquoi certaines infections sont si difficiles à éradiquer. En même temps, l’étude montre que des combinaisons de médicaments soigneusement choisies — comme associer ceftazidime/avibactam avec du céfotaxime — peuvent exploiter des faiblesses de ce système et supprimer même ces souches bien armées. Comprendre comment les bactéries construisent et utilisent ces plasmides multicopies est donc crucial pour concevoir des stratégies antibiotiques plus intelligentes et ralentir la progression de la résistance.
Citation: Weng, R., Zhu, J., Wu, X. et al. Heterogeneous multicopy of blaCTX-M variants on the same plasmid enhances evolutionary adaptability in clinical Klebsiella pneumoniae. Nat Commun 17, 2460 (2026). https://doi.org/10.1038/s41467-026-69266-7
Mots-clés: résistance aux antibiotiques, Klebsiella pneumoniae, plasmides, bêta-lactamases, thérapie multi‑médicamenteuse