Clear Sky Science · fr
TANGO : Analyse et curation des particules en cryo‑tomographie électronique
Voir les cellules en 3D, puis comprendre la foule
La cryo‑tomographie électronique permet aux scientifiques de figer des cellules en action et de les capturer en trois dimensions, un peu comme mettre en pause un film avec un niveau de détail proche de l’échelle atomique. Mais une fois que des milliers de « points » moléculaires ont été localisés à l’intérieur d’une cellule, un nouveau problème surgit : comment savoir qui est à côté de qui, qui forme des équipes et où se cachent les motifs importants dans cette ville moléculaire surpeuplée ? Cette étude présente TANGO, un cadre logiciel qui transforme des cartes 3D brutes de particules en récits exploitables sur la manière dont les molécules sont arrangées et coopèrent.
Des points dans la glace à une carte des voisins moléculaires
La cryo‑tomographie électronique commence par incliner un échantillon congelé dans le microscope pour enregistrer de nombreuses images 2D. Celles‑ci sont recombinées en un volume 3D, appelé tomogramme, où les complexes moléculaires individuels apparaissent comme des taches floues. Les méthodes existantes utilisent déjà ces données pour affiner la forme des molécules par moyennage de nombreuses copies, mais elles négligent en grande partie un trésor tout aussi riche : les positions et orientations exactes de chaque particule. TANGO a été conçu pour exploiter cette information sous‑estimée. Il considère toutes ces particules comme des points dans l’espace, chacun avec une direction, et analyse comment elles sont positionnées et orientées les unes par rapport aux autres. Ce faisant, il va au‑delà de la simple question « à quoi ressemble cette molécule ? » pour s’interroger « comment ces molécules sont‑elles organisées ensemble dans la cellule ? » 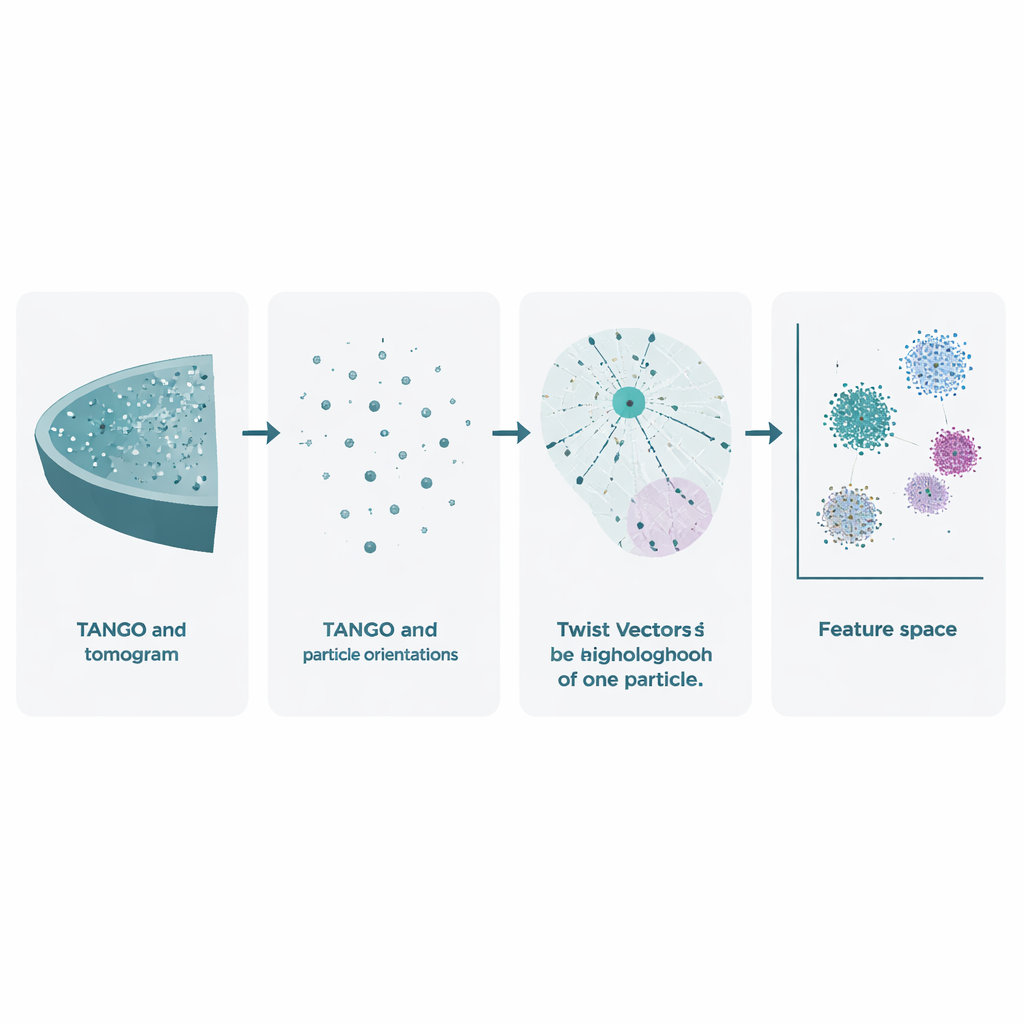
Capturer les torsions et les rotations avec un nouveau descripteur
Au cœur de TANGO se trouve l’idée des « vecteurs de torsion ». Pour une particule donnée, le logiciel examine tous ses voisins dans un rayon choisi et enregistre deux éléments : où chaque voisin se situe dans l’espace 3D et comment il est orienté par rapport à la particule centrale. Ces relations position‑angle combinées sont encodées sous forme de descriptions numériques concises appelées descripteurs de torsion. Comme TANGO réoriente systématiquement les voisinages dans un référentiel commun, ces descripteurs sont insensibles à la rotation globale de l’échantillon dans le microscope. Cela permet de comparer de manière cohérente des voisinages locaux entre différents tomogrammes et expériences.
Nettoyer des données bruitées et reconstruire des assemblages moléculaires
Les données expérimentales réelles sont bruyantes : les méthodes de repérage automatiques peuvent inclure de nombreuses particules parasites et perdre la trace de l’appartenance des petits éléments à des structures plus grandes. TANGO s’attaque à ce problème en transformant le réseau de relations de torsion en un graphe, où les particules sont des nœuds et les liens de voisinage des arêtes. En analysant la façon dont les nœuds se connectent, TANGO peut regrouper les particules au sein de leurs assemblages parent appropriés et éliminer les valeurs aberrantes qui ne correspondent pas à la géométrie attendue. Les auteurs montrent que cette approche récupère avec précision l’architecture en anneau des pores nucléaires dans l’enveloppe nucléaire, l’agencement tubulaire des microtubules et les coques approximativement sphériques des particules virales de type HIV immatures. Dans chaque cas, TANGO à la fois nettoie les listes de particules et restaure l’appartenance des pièces, souvent en égalant ou en améliorant une curation manuelle soignée.
Dénicher des défauts subtils et des motifs dans les réseaux
De nombreux virus et structures cellulaires forment des réseaux répétitifs, comme des carrelages moléculaires sur des surfaces courbes. TANGO utilise ses descripteurs de torsion pour mesurer la régularité de ces motifs et détecter les endroits où ils se courbent ou se rompent. Un ingrédient clé est un « score angulaire » qui compare les orientations tout en respectant les symétries intrinsèques, comme la symétrie six‑fold des hexamères. Appliqué aux capsides matures du VIH, TANGO détecte des pentamères — unités à cinq éléments nécessaires pour fermer la coque conique — dissimulés au milieu de vastes champs d’hexamères. Dans les réseaux du VIH immature, il sépare les régions bien ordonnées des régions déformées et relie les faibles scores angulaires aux zones irrégulières et fracturées de la coque. Des analyses similaires sur des données de chromatine synthétique et de ribosomes révèlent des nucléosomes empilés, des arrangements hélicoïdaux ADN‑protéine et des paires récurrentes de ribosomes rappelant des états de traduction décrits auparavant. 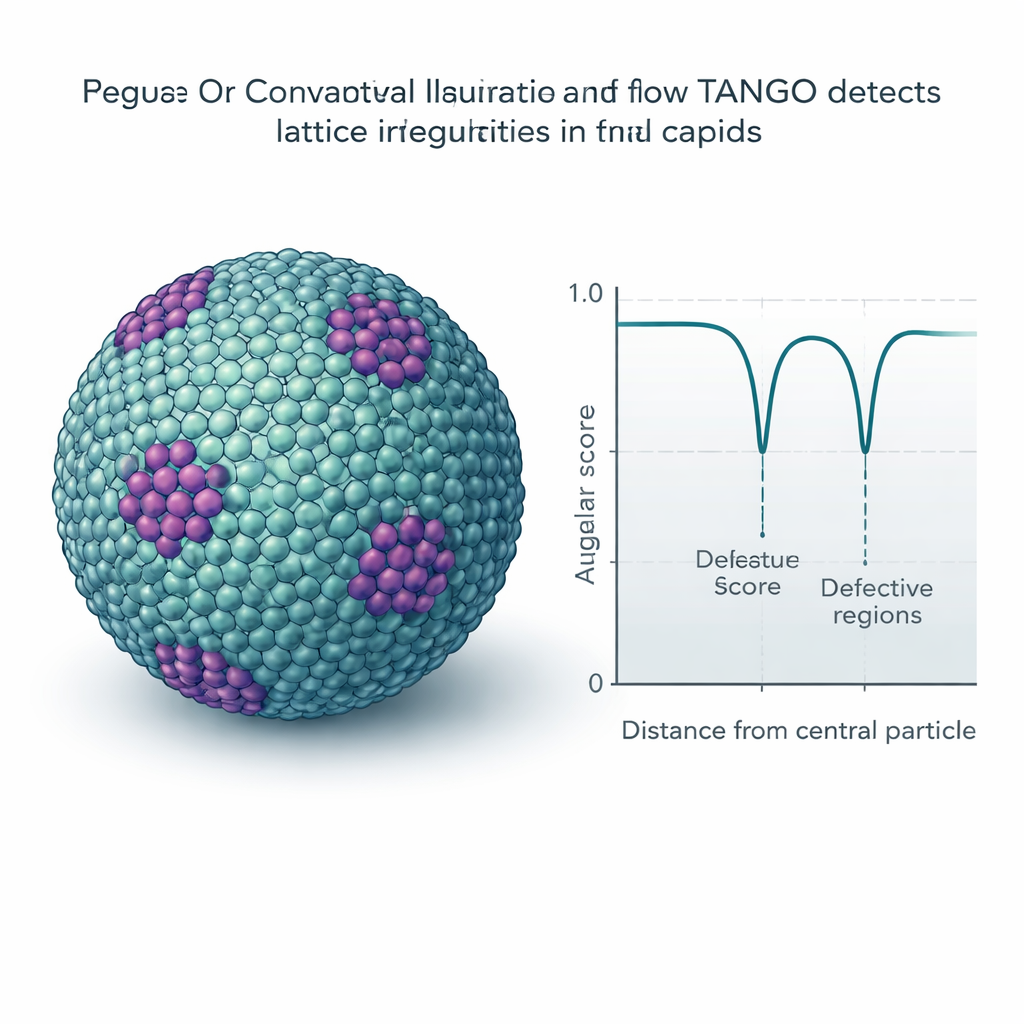
Une boîte à outils flexible pour explorer l’architecture cellulaire
TANGO est implémenté comme un logiciel Python open source et est fourni avec une interface graphique afin que les utilisateurs puissent tester différentes formes de voisinage, filtres et caractéristiques sans programmation lourde. Parce qu’il est modulaire, les chercheurs peuvent intégrer leurs propres mesures géométriques ou descripteurs de motifs et les utiliser immédiatement dans le même flux de travail. Pour les novices, cela abaisse la barrière à l’exploration de l’organisation spatiale ; pour les experts, cela fournit un cadre pouvant évoluer avec de nouvelles idées et jeux de données.
Pourquoi cela compte pour la compréhension des cellules vivantes
Concrètement, ce travail offre aux biologistes un moyen de passer d’images statiques de molécules individuelles à des cartes dynamiques montrant comment ces molécules sont disposées et coopèrent à l’intérieur des cellules. En encodant les relations « qui est près de qui » et « comment ils sont orientés » en caractéristiques numériques robustes, TANGO transforme des données microscopiques 3D bruitées en motifs pouvant être regroupés, comparés et testés statistiquement. Cela peut révéler des assemblages cachés, localiser des défauts dans les coques virales et mettre au jour des arrangements moléculaires rares liés à des maladies ou à l’action de médicaments. À mesure que la cryo‑tomographie électronique se généralise, des outils comme TANGO aideront à transformer des nuages denses de particules en éclairages précis sur la chorégraphie interne de la vie.
Citation: Schreiber, M., Turoňová, B. TANGO: Analysis and curation of particles in cryo-electron tomography. Nat Commun 17, 1557 (2026). https://doi.org/10.1038/s41467-026-69195-5
Mots-clés: cryo‑tomographie électronique, organisation spatiale, réseaux moléculaires, capsides virales, ribosomes