Clear Sky Science · fr
PRICE : détection directe et robuste des microARNs à résolution d’un seul nucléotide
Pourquoi de minuscules messages génétiques comptent
À l’intérieur de chaque cellule se trouve une multitude de très petites molécules d’ARN appelées microARNs, qui ajustent finement l’activation ou l’inactivation des gènes. Un changement d’une seule « lettre » dans ces courtes molécules peut faire basculer l’équilibre vers la santé ou la maladie, y compris des cancers. Les cliniciens et chercheurs aimeraient pouvoir lire directement ces minuscules différences dans le sang ou les tissus, mais les méthodes actuelles sont souvent lentes, coûteuses et pas assez précises pour repérer de façon fiable un changement d’une seule lettre. Cet article présente une nouvelle technique de laboratoire, appelée PRICE, qui promet de lire ces coquilles microscopiques dans les microARNs de façon plus simple et plus précise, ouvrant la voie à une détection plus précoce des cancers et à un meilleur suivi du comportement des tumeurs.
Une nouvelle manière de trier des molécules qui se ressemblent
Les microARNs sont extrêmement courts, ce qui rend difficile de les distinguer lorsque leurs séquences diffèrent d’un seul élément. De nombreux outils actuels, comme la PCR et le séquençage de l’ARN, comptent bien les microARNs de façon générale, mais peinent lorsque deux versions sont presque identiques, ou exigent une préparation d’échantillon complexe et des instruments coûteux. Les auteurs combinent deux idées puissantes pour surmonter ces limites : un « ciseau » moléculaire programmable issu de la famille CRISPR, et des fragments synthétiques proches de l’ADN appelés acides nucléiques peptidiques (PNA). L’enzyme CRISPR Cas13a peut être programmée pour reconnaître un ARN spécifique, et une fois sa cible trouvée elle commence à couper des molécules rapporteurs à proximité, produisant un signal fluorescent intense. Les PNA, quant à eux, sont de courts brins qui se lient particulièrement fortement aux séquences d’ARN correspondantes mais perdent leur affinité de façon abrupte si une seule lettre est erronée.
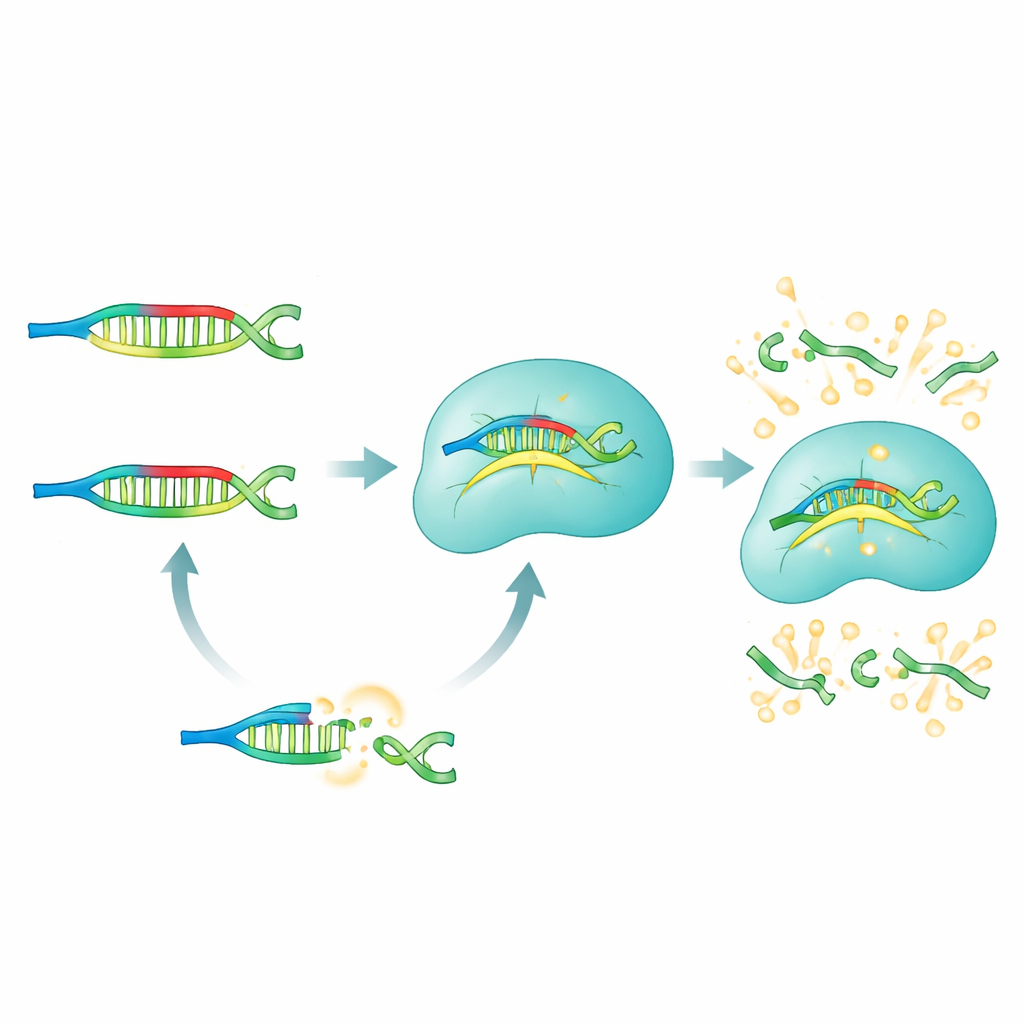
Comment fonctionne la méthode PRICE
Dans le système PRICE, les PNA jouent le rôle de bloqueurs sélectifs qui taisent tout ce que les chercheurs ne veulent pas voir. Pour un microARN d’intérêt donné, l’équipe conçoit un panneau de bloqueurs PNA qui correspondent parfaitement à toutes les versions « incorrectes » — celles contenant des changements d’une seule lettre indésirables — tout en étant délibérément non appariés avec la cible choisie. Lorsqu’un échantillon biologique (sérum, cellules ou tissu) est mélangé avec ces PNA, les microARNs non ciblés sont fortement liés et efficacement masqués. La vraie cible reste non liée et libre d’interagir avec le complexe Cas13a, qui a été préprogrammée avec un ARN guide reconnaissant ce microARN. Seule cette cible non bloquée peut activer Cas13a, qui passe alors en mode coupe et découpe des molécules rapporteurs fluorescentes, générant une émission lumineuse forte et facile à mesurer.
Ajuster la précision au niveau d’une seule lettre
Les auteurs ont exploré systématiquement comment concevoir des bloqueurs PNA assez forts pour saisir le microARN mutant indésirable, mais assez faibles pour ignorer la séquence cible qui diffère d’une seule lettre. Ils ont constaté que deux règles de conception comparables à des règles de température sont cruciales : le PNA doit former un appariement stable avec le mutant indésirable à la température corporelle ou au‑dessus, mais former un appariement beaucoup plus faible avec la cible qui se défait bien en dessous de cette température. En s’appuyant sur ces règles et un modèle prédictif simple, ils ont conçu des PNA qui réduisent les faux signaux issus de microARNs mutants de plus de 70 % tout en laissant le vrai signal pratiquement intact. Fait important, l’ajout des PNA n’a pas réduit la sensibilité globale : PRICE pouvait toujours détecter des microARNs à des concentrations de seulement quelques dizaines de femtomoles par litre, comparable aux meilleurs tests basés sur l’amplification mais sans les étapes supplémentaires de copie.
Tester la méthode sur des échantillons cancéreux
Pour montrer que PRICE n’est pas qu’un gadget théorique, l’équipe s’est concentrée sur la famille let‑7 de microARNs, fortement impliquée en biologie du cancer. Ils ont démontré que PRICE peut distinguer des microARNs cibles dans des mélanges contenant de nombreux membres familiaux presque identiques et peut même détecter des variants rares représentant seulement 5 % d’un échantillon. Les chercheurs se sont ensuite tournés vers du matériel clinique réel : lignées cellulaires de cancer du foie, biopsies tissulaires et sérum de patients. Tant dans le tissu tumoral que dans le sang, PRICE a détecté de façon cohérente des niveaux réduits de certains microARNs let‑7 chez les patients comparativement aux témoins non cancéreux, en accord avec des études antérieures. Lors d’une comparaison directe avec la RT‑qPCR standard, PRICE a montré au minimum une capacité comparable et souvent meilleure pour distinguer les cas cancéreux des cas non cancéreux, en particulier dans les échantillons sériques de faible abondance où les résultats PCR deviennent bruités.
Pourquoi cela compte pour les diagnostics futurs
Au fond, ce travail montre qu’il est possible de lire directement des différences d’une seule lettre dans de minuscules ARN régulateurs de façon pratique et évolutive. En laissant les PNA verrouiller les séquences similaires indésirables et en confiant la lecture finale à une enzyme CRISPR, PRICE offre une boîte à outils flexible pour concevoir des tests retargetables simplement en échangeant le panneau de bloqueurs et l’ARN guide. Au‑delà du cancer du foie et de la famille let‑7, la même stratégie pourrait être étendue à de nombreuses autres maladies où de petites modifications d’ARN importent, et même à des variants d’ADN lorsque combinée à des enzymes CRISPR apparentées. Les auteurs montrent également un lecteur compact multi‑canal capable d’exécuter des essais PRICE en dehors de grands laboratoires centraux, suggérant des tests de proximité possibles. Si elle est développée davantage, PRICE pourrait devenir une manière pratique de surveiller des variations génétiques subtiles qui signalent un cancer et d’autres maladies bien avant l’apparition des symptômes.
Citation: Wang, B., Zhou, S., Zhang, X. et al. PRICE: direct and robust detection of microRNAs at single-nucleotide resolution. Nat Commun 17, 2647 (2026). https://doi.org/10.1038/s41467-026-69181-x
Mots-clés: diagnostic des microARN, CRISPR Cas13a, acide nucléique peptidique, variation d’un seul nucléotide, biomarqueurs du cancer du foie