Clear Sky Science · fr
Les interactions protéine-protéine sont une source majeure d’épistasie dans les réseaux d’interactions génétiques
Pourquoi c’est important pour comprendre les gènes
Quand des médecins ou des tests génétiques indiquent qu’un gène « cause » une maladie, cela paraît simple. En réalité, l’effet d’un gène donné dépend souvent fortement de ce que font les autres gènes simultanément. Cet article explore pourquoi les combinaisons de variations génétiques peuvent se comporter de façon imprévisible et montre que beaucoup de ces surprises s’expliquent par la manière dont les protéines codées par ces gènes s’assemblent physiquement dans la cellule. Comprendre ce lien pourrait améliorer notre capacité à prévoir le risque de maladie et à repérer des cibles médicamenteuses exploitant des points faibles dans le cancer et d’autres affections.
Deux cartes cachées à l’intérieur de chaque cellule
Les biologistes utilisent deux types de cartes puissantes pour comprendre le fonctionnement cellulaire. La première est la carte des interactions génétiques, qui montre ce qui arrive à une cellule lorsque deux gènes sont perturbés ensemble : parfois l’effet double est bien pire que prévu, parfois plus doux. Ces effets non additifs sont appelés épistasie et compliquent la prédiction des phénotypes à partir de l’ADN seul. La seconde carte est celle des interactions protéine–protéine, qui recense quelles protéines se touchent physiquement pour former des complexes et des voies. Jusqu’ici, ces deux cartes étaient généralement étudiées séparément, et il n’était pas clair à quel point elles étaient liées.
La force d’association des protéines conditionne les effets gène–gène
Les auteurs ont combiné de larges jeux de données issus de levure et de cellules humaines mesurant à la fois la fréquence de rencontre des protéines et la force avec laquelle elles se lient. Ils ont ensuite superposé les données d’interactions génétiques sur ce paysage physique. Un motif clair est apparu : les paires de gènes dont les protéines forment des complexes solides et équilibrés — où les deux partenaires sont présents en quantités similaires et se lient approximativement en proportions 1:1 — tendent à montrer de fortes interactions négatives quand les deux gènes sont perdus. Concrètement, l’inactivation d’un gène seul affaiblit la cellule modérément, mais la perte des deux à la fois est particulièrement dommageable, reflétant le rôle central du complexe partagé. En revanche, les partenariats protéiques plus faibles ou déséquilibrés produisent des effets génétiques plus doux et plus variés.
Convertir les forces d’association en prédictions au niveau du réseau
Savoir simplement quelles protéines se touchent ne suffit pas ; l’important est la solidité de ces contacts. Pour en tenir compte, les chercheurs ont utilisé la spectrométrie de masse quantitative pour estimer les affinités de liaison — la facilité avec laquelle les paires protéiques se dissocient — sur des milliers d’interactions. Ils ont constaté que, à mesure que la liaison devient plus forte, l’interaction génétique négative moyenne entre les gènes correspondants suit une courbe sigmoïde lisse, très similaire à la façon dont un site de liaison se remplit quand la concentration augmente. Ceci valait aussi bien pour la levure que pour les cellules humaines. En utilisant cette relation quantitative, ils ont montré que la structure d’un réseau d’interactions génétiques peut être partiellement reconstruite à partir des seules données de liaison protéique, des groupes de gènes apparentés réapparaissant à partir des mesures protéiques.
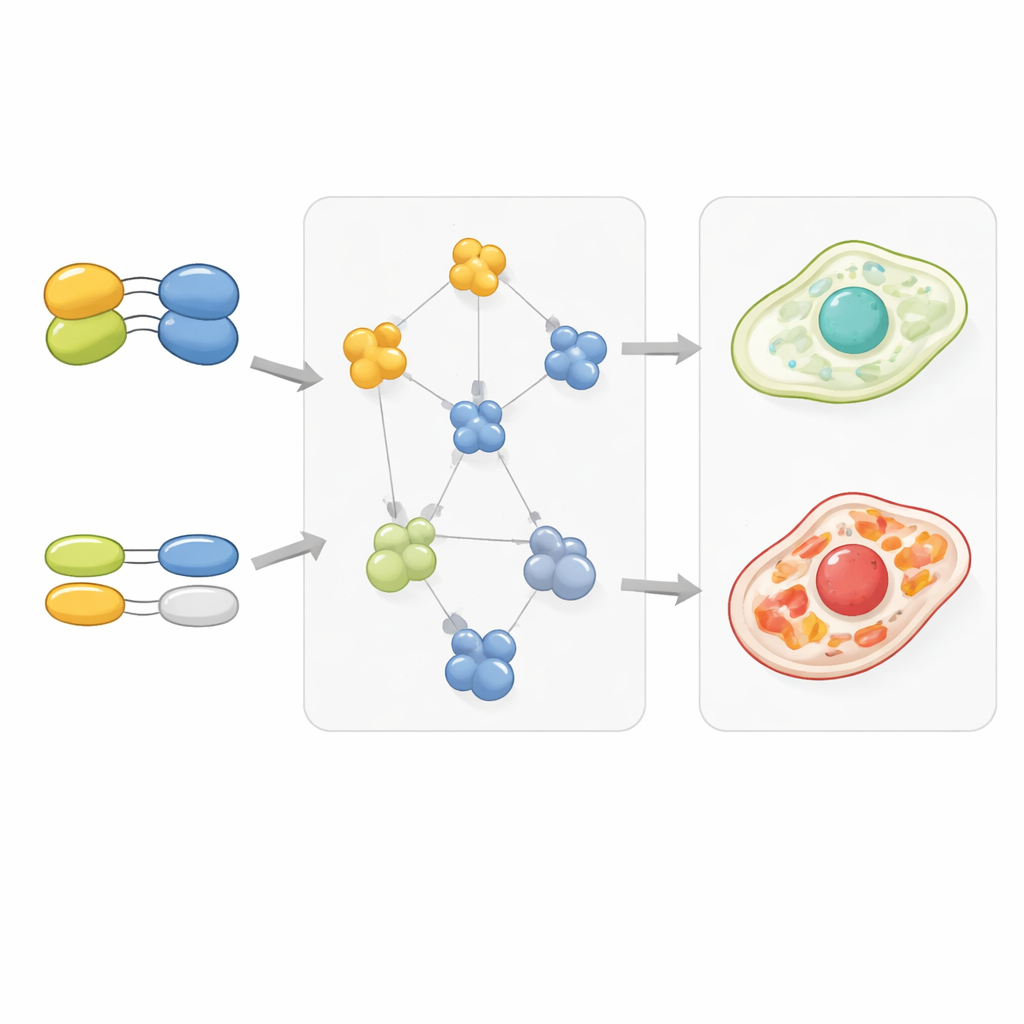
Gènes dupliqués et schémas de câblage cellulaires
L’étude a également examiné les gènes qui ont des duplications, appelés paralogues, qui servent souvent de secours les uns pour les autres. Les paires de gènes dont un ou les deux partenaires avaient des duplicatas montraient généralement des interactions génétiques plus faibles avec d’autres gènes, ce qui suggère que la redondance atténue l’impact de la perte d’une copie unique. Fait marquant, les protéines codées par des gènes dupliqués avaient aussi tendance à lier leurs partenaires plus faiblement, comme si l’évolution avait réduit l’adhérence pour maintenir l’équilibre des complexes malgré des copies supplémentaires. Lorsque les duplicatas divergeaient davantage en séquence et en fonction, une copie conservait souvent des interactions fortes et ciblées tandis que l’autre perdait ou affaiblissait beaucoup de ses contacts, un schéma qui reflétait les changements dans les interactions génétiques de ces gènes avec le reste de la cellule.
Hubs partagés qui relient les systèmes cellulaires
Au-delà des paires individuelles, les auteurs se sont demandé si les formes à grande échelle des cartes génétiques et protéiques correspondent. Ils ont trouvé que des groupes de gènes qui forment des amas dans les données d’interactions génétiques correspondent souvent étroitement à des complexes protéiques connus. Tout aussi important, les mêmes types de protéines « connectrices » relient fréquemment ces complexes dans les deux cartes, formant des motifs récurrents module–connecteur–module. Par exemple, des facteurs de transport qui déplacent des cargos à travers le pore nucléaire et des protéines de signalisation comme Ras apparaissent comme des connecteurs partagés, reliant des processus cellulaires distants aussi bien dans les réseaux physiques que génétiques.
Ce que cela signifie pour les gènes, la maladie et la thérapie
Le message central pour un public non spécialiste est que beaucoup d’effets gène–gène déroutants ne sont pas si mystérieux : ils proviennent du fait que les protéines codées par ces gènes dépendent physiquement les unes des autres, et l’intensité de cette dépendance peut être mesurée. En reliant l’épistasie génétique à la chimie de la liaison protéique, ce travail nous rapproche de la capacité à prédire comment des combinaisons de mutations affecteront les cellules, y compris dans les maladies humaines. À long terme, de telles cartes intégrées pourraient aider à identifier des combinaisons de gènes qui, lorsqu’elles sont ciblées ensemble, affaiblissent sélectivement les cellules cancéreuses ou révèlent de nouvelles façons de rétablir l’équilibre dans des réseaux protéiques perturbés.
Citation: Castellanos-Girouard, X., Serohijos, A.W.R. & Michnick, S.W. Protein-protein interactions are a major source of epistasis in genetic interaction networks. Nat Commun 17, 2398 (2026). https://doi.org/10.1038/s41467-026-69152-2
Mots-clés: interactions génétiques, réseaux protéiques, épistasie, complexes protéiques, biologie des systèmes