Clear Sky Science · fr
Amplifier la détection des boucles enhanceur‑promoteur via des méthodes de normalisation pour les données d’interaction chromatinienne
Voir les boucles cachées dans notre ADN
À l’intérieur de chaque cellule, de longues molécules d’ADN se replient et forment des boucles en trois dimensions, rapprochant des régions éloignées du génome. Certaines de ces boucles relient physiquement des interrupteurs on/off appelés enhancers aux gènes qu’ils contrôlent, influençant le développement cellulaire et l’apparition de maladies comme le cancer. Cet article présente une nouvelle méthode computationnelle, Raichu, qui facilite grandement la détection de ces boucles régulatrices subtiles dans des expériences à l’échelle du génome, ouvrant une fenêtre plus nette sur le lien entre le repliement de l’ADN et l’activité génique.
Pourquoi les petites boucles d’ADN comptent
Nos génomes ne sont pas disposés comme des fils droits de lettres. Ils se replient en une structure 3D complexe à l’intérieur du noyau. Dans cet état replié, des régions éloignées peuvent se toucher, formant des boucles de chromatine. Certaines boucles servent de charpente pour organiser des quartiers entiers du génome. D’autres sont des boucles régulatrices qui rapprochent des promoteurs de gènes d’enhancers distants qui augmentent leur activité. La perturbation de ces boucles régulatrices a été liée à des troubles du développement et à des cancers, d’où l’intérêt des scientifiques pour les cartographier en détail.
Le défi de lire les cartes 3D du génome
Des techniques comme Hi‑C et méthodes apparentées capturent des millions à des milliards de contacts ADN–ADN et les résument sous forme de cartes thermiques, où chaque pixel reflète la fréquence de rencontre entre deux régions du génome. Cependant, ces cartes sont entachées d’artéfacts techniques : certaines régions sont plus faciles à mesurer que d’autres en raison de la composition de la séquence, de la qualité de l’alignement ou de la façon dont elles sont découpées dans l’expérience. Pour clarifier les données, les chercheurs utilisent des méthodes de normalisation comme ICE et KR qui équilibrent les cartes pour que chaque région paraisse avoir une visibilité égale. Si ces outils mettent en évidence des structures larges — domaines étendus et boucles structurelles fortes —, les auteurs montrent qu’ils estompent involontairement les boucles enhanceur–promoteur plus faibles mais biologiquement cruciales.
Une nouvelle manière de nettoyer le signal
Raichu adopte une approche différente pour traiter les données de contacts chromatinien. Plutôt que de forcer chaque région du génome à paraître également visible, il modélise chaque interaction comme la somme de trois composantes : une décroissance générale de la fréquence de contact avec l’augmentation de la distance le long du chromosome, un biais spécifique à chaque position, et un signal résiduel propre à ce contact particulier. À l’aide d’un algorithme d’optimisation, Raichu estime le profil de biais qui explique le mieux les données observées tout en maintenant la tendance globale dépendante de la distance fixe. Les contacts sont ensuite ajustés en divisant par ces valeurs de biais. Cela préserve la décroissance globale naturelle des interactions tout en corrigeant sélectivement les distorsions techniques, laissant apparaître des signaux plus nets de contacts ADN spécifiques et réels.
Découvrir des milliers de boucles régulatrices manquées
Lorsque les auteurs ont appliqué Raichu à des jeux de données humains et murins profondément séquencés, la méthode a révélé presque deux fois plus de boucles de chromatine que les méthodes standard, tout en retrouvant presque toutes les boucles connues auparavant. Les boucles supplémentaires détectées par Raichu étaient fortement enrichies en marques biochimiques d’enhancers et de promoteurs actifs et en liaisons de facteurs de transcription qui contrôlent l’activité génique. Nombre de ces boucles étaient soutenues indépendamment par d’autres technologies 3D du génome et même par imagerie haute résolution, confirmant qu’elles reflètent une proximité physique réelle dans le noyau. Fait important, l’avantage de Raichu persistait même lorsque les données étaient raréfiées pour simuler des profondeurs de séquençage plus faibles, lors de l’étude de méthodes spécialisées comme Micro‑C et Micro‑C par capture de régions, et même en poolant un petit nombre de cellules uniques.
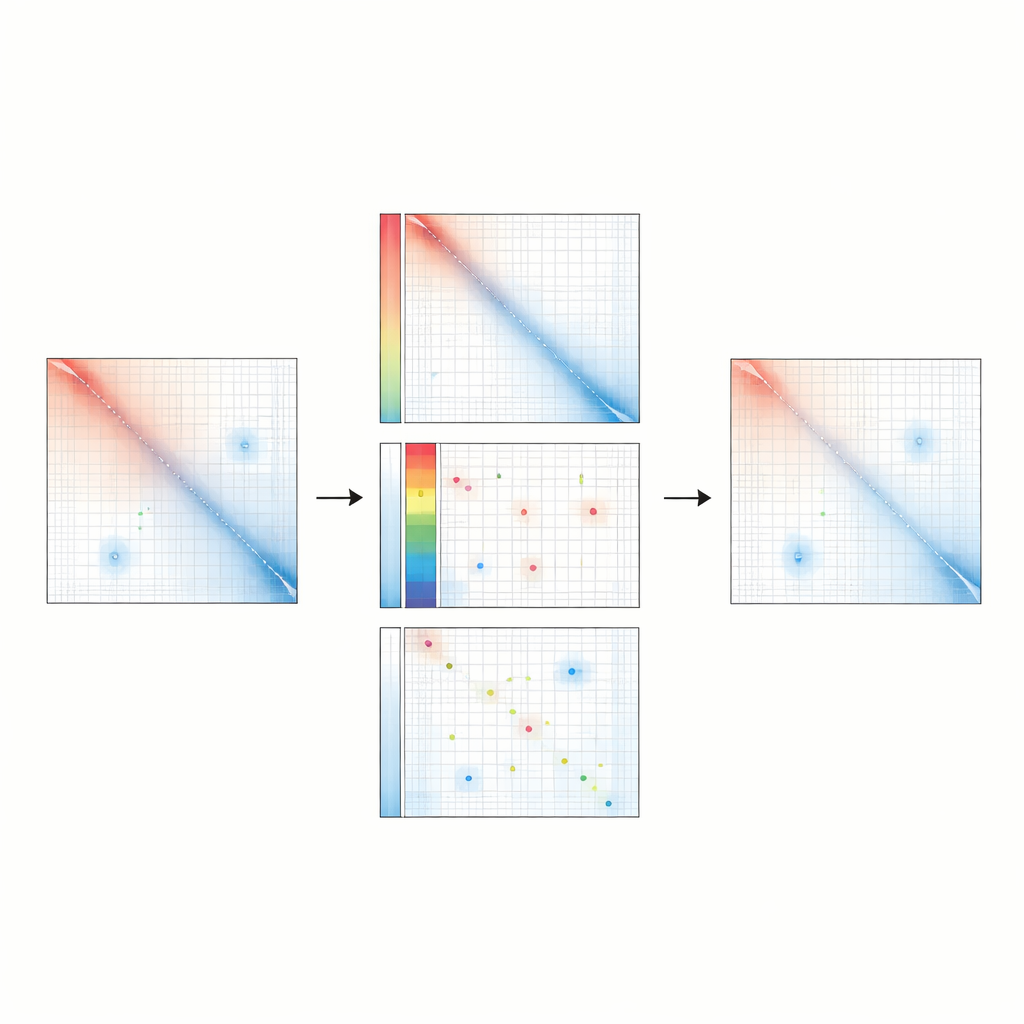
Révéler des changements subtils et des motifs évolutifs
Parce que Raichu est particulièrement sensible aux boucles régulatrices, il repère mieux les différences significatives entre des conditions qui pourraient autrement paraître similaires. Dans un modèle cellulaire humain modifié portant une variante de risque pour la leucémie, Raichu a mis au jour de nouvelles boucles n’apparaissant que dans l’état à risque, reliant des gènes clés à leurs enhancers et s’alignant sur des changements d’activité génique. Chez des cellules progénitrices neuronales de souris et d’humain, Raichu a détecté des milliers de boucles enhanceur–promoteur conservées entre espèces et reliant souvent des enhancers distants à des gènes impliqués dans le développement cérébral. Ces résultats suggèrent que de nombreux contacts régulateurs importants étaient cachés au grand jour, masqués par les approches de normalisation antérieures.
Ce que cela signifie pour la recherche génomique future
Pour un lecteur non spécialiste, le message principal est que la façon dont nous traitons les grands jeux de données génomiques peut influencer radicalement la biologie que nous percevons. En repensant l’étape de nettoyage des cartes 3D du génome, Raichu restaure des signaux faibles mais importants qui relient des interrupteurs géniques à leurs cibles. Cela facilite le suivi de la manière dont le repliement de l’ADN contrôle l’activité génique en santé et en maladie, de la cellule unique aux tissus entiers et entre espèces. À mesure que davantage d’études adopteront Raichu, les chercheurs pourront s’attendre à des cartes plus riches de la communication enhanceur–promoteur et à une image plus claire de la manière dont les changements d’architecture génomique contribuent au développement, au cancer et à d’autres pathologies complexes.
Citation: Wang, X., Shi, D., Xue, F. et al. Boosting the detection of enhancer-promoter loops via normalization methods for chromatin interaction data. Nat Commun 17, 2299 (2026). https://doi.org/10.1038/s41467-026-69082-z
Mots-clés: organisation 3D du génome, boucles enhanceur‑promoteur, analyse des données Hi‑C, normalisation de la chromatine, régulation génique