Clear Sky Science · fr
Des motifs étendus de Shine‑Dalgarno gouvernent l'initiation de la traduction chez Staphylococcus aureus
Comment un germe hospitalier ajuste ses usines à protéines
Staphylococcus aureus est un germe courant pouvant provoquer des infections cutanées bénignes comme des maladies potentiellement mortelles. Pour survivre dans l’organisme et résister aux traitements, il doit sans cesse réorganiser les protéines qu’il produit. Cet article révèle comment S. aureus contrôle la toute première étape de la production protéique d’une manière différente des bactéries modèles comme Escherichia coli, et montre comment ce contrôle est lié à la formation de biofilms, un facteur majeur des infections chroniques et tolérantes aux antibiotiques.
Une « poignée de main » cachée entre le gène et le ribosome
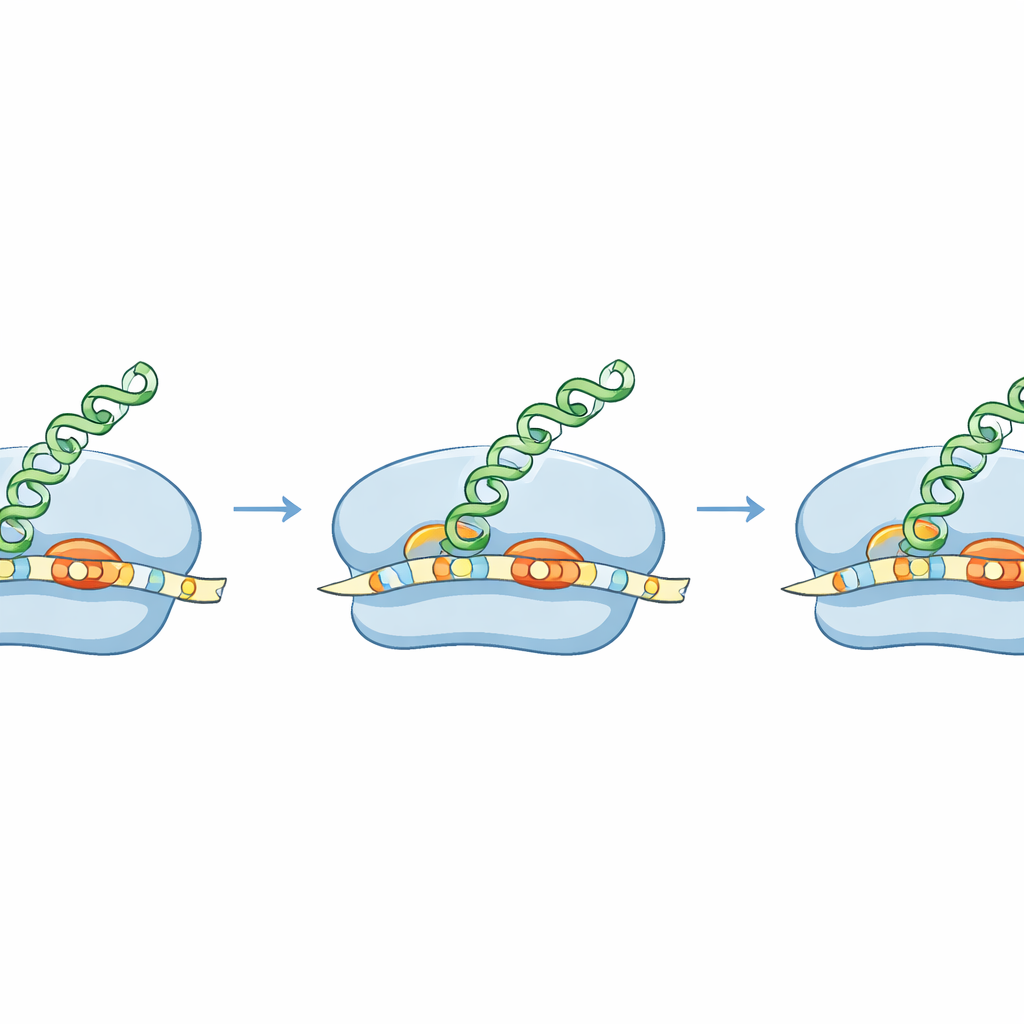
Pour transformer un gène en protéine, les bactéries utilisent des ribosomes, des machines moléculaires qui parcourent l’ARN messager (ARNm) pour trouver où commencer la lecture. De nombreux ARNm bactériens contiennent une courte séquence, connue depuis longtemps sous le nom de région Shine–Dalgarno, qui aide le ribosome à se fixer au bon endroit. En « congelant » les ribosomes au moment où ils commencent la traduction et en séquençant les fragments d’ARN protégés, les auteurs ont établi une carte à haute résolution des sites d’initiation à travers le génome de S. aureus. Ils ont découvert que S. aureus utilise souvent une version inhabituellement longue de cette séquence d’ancrage, positionnée très près du signal de départ, formant une « fermeture éclair » étendue entre l’ARNm et l’ARN ribosomique. Cet appariement étendu est beaucoup plus marqué que chez E. coli et semble caractériser la façon dont S. aureus choisit où commencer.
Règles spécifiques à l’espèce pour démarrer la synthèse protéique
L’équipe a montré que cette hélice d’ancrage étendue a des conséquences réelles. Dans plusieurs gènes naturels de S. aureus, les premières bases peuvent être lues de plusieurs manières, offrant des sites concurrents pour l’initiation de la traduction. À l’aide de ribosomes purifiés, de systèmes sans cellules et de cellules vivantes, les chercheurs ont comparé la manière dont S. aureus et E. coli traitent ces débuts ambigus. Les ribosomes de S. aureus choisissaient de manière fiable le même site « correct » utilisé dans la bactérie elle‑même, guidés par l’hélice d’ancrage longue et l’espacement préféré entre cette hélice et le site de départ. Les ribosomes d’E. coli, en revanche, favorisaient un autre départ proche qui donnerait une protéine alternative. Cela signifie qu’un même ARNm peut produire des protéines différentes selon l’espèce, ouvrant la voie à la conception de messages lisibles uniquement par des bactéries ciblées.
Nouvelles petites protéines et signaux de départ faibles
Parce que leur méthode localise précisément l’arrivée des ribosomes aux sites d’initiation, les auteurs ont également pu découvrir de nombreux gènes courts auparavant manqués. Ils ont identifié des dizaines de petits cadres de lecture ouverts, y compris de courtes séquences « en amont » situées juste avant des gènes plus grands et connus. Certaines de ces courtes régions codent probablement de minuscules protéines ayant leur propre fonction ; d’autres semblent surtout agir comme régulateurs. L’étude a en outre révélé que S. aureus commence parfois la traduction sur des triplets d’initiation « non canoniques » généralement considérés comme de faibles signaux. Dans ces cas, des motifs d’ancrage forts et étendus semblent compenser le départ faible, modulant la production protéique de sorte que certains facteurs, y compris des régulateurs métaboliques, ne soient synthétisés qu’en faible quantité ou en réponse aux conditions de croissance.
Un capteur moléculaire reliant les nutriments à la croissance du biofilm
Un élément amont court, nommé rbfL, est apparu comme un exemple frappant de contrôle traductionnel lié à la virulence. Il se situe juste avant rbf, un gène qui code pour un facteur de transcription favorisant la formation de biofilm. La séquence rbfL code un minipeptide « leader » riche en arginine, incluant des codons d’arginine très rares décodés par des ARN de transfert peu abondants. Lorsque l’arginine est limitée, ces codons sont traduits lentement et les ribosomes butent sur la région qui chevauche le site d’ancrage de rbf lui‑même, bloquant physiquement l’arrivée de nouveaux ribosomes sur rbf. Lorsque l’arginine ou son ARN de transfert correspondant est abondant, l’obstacle est levé et rbf est produit plus efficacement. Dans des expériences de croissance, l’ajout d’arginine supplémentaire a stimulé la formation de biofilm, reliant directement ce capteur moléculaire à un mode de vie communautaire qui résiste aux antibiotiques.
Pourquoi ces découvertes sont importantes
Ce travail montre que S. aureus a évolué des motifs d’ancrage étendus et de petits éléments en amont pour affiner où et quand commence la synthèse protéique. Ces caractéristiques le distinguent non seulement de bactéries modèles comme E. coli, mais elles relient aussi la détection des nutriments au contrôle des régulateurs de biofilm. Pour un lecteur non spécialiste, l’essentiel est que les « boutons de démarrage » de la production protéique de la bactérie sont plus élaborés qu’on ne le pensait — et que ces commutateurs spécialisés contribuent à déterminer quand S. aureus devient plus dangereux. Comprendre ces règles d’initiation uniques pourrait orienter la conception d’antibiotiques spécifiques à l’espèce ou d’outils génétiques destinés à perturber sélectivement les bactéries nuisibles tout en épargnant les souches bénéfiques.
Citation: Kohl, M.P., Bahena-Ceron, R., Chane-Woon-Ming, B. et al. Extended Shine-Dalgarno motifs govern translation initiation in Staphylococcus aureus. Nat Commun 17, 2678 (2026). https://doi.org/10.1038/s41467-026-69079-8
Mots-clés: Staphylococcus aureus, initiation de la traduction, Shine‑Dalgarno, petits ORF, régulation du biofilm