Clear Sky Science · fr
FidlTrack : le suivi de particules uniques conscient de la structure et haute fidélité résout le mouvement moléculaire intracellulaire dans les organelles détectant le traitement de l’APP
Observer des molécules uniques à l’intérieur de cellules vivantes
À l’intérieur de chaque cellule, d’innombrables molécules sont en mouvement permanent, se heurtant, se liant et se séparant. Les microscopes modernes peuvent suivre ces molécules une par une, offrant la promesse d’un aperçu détaillé du fonctionnement de la vie à ses plus petites échelles. Mais lorsque de nombreuses molécules se déplacent rapidement dans des espaces étroits et sinueux tels que le réticulum endoplasmique ou les mitochondries, leurs trajectoires s’emmêlent et deviennent faciles à mal interpréter. Cet article présente FidlTrack, une nouvelle méthode pour démêler cet enchevêtrement afin que les chercheurs puissent avoir confiance dans ce qu’ils observent lorsqu’ils suivent des molécules uniques en temps réel.
Pourquoi il est si difficile de suivre de minuscules déplacements
Le suivi de particule unique consiste à suivre le même point lumineux à travers de nombreuses images d’un film. Sur une surface cellulaire relativement plane, où les molécules se déplacent lentement et sont espacées, cela reste faisable. En profondeur dans la cellule, cependant, les molécules diffusent beaucoup plus vite et se concentrent dans des tubes et des feuillets étroits et enroulés. Entre deux images, le même point peut avoir parcouru une grande distance, et plusieurs points identiques peuvent se trouver à portée. Les logiciels traditionnels doivent « deviner » quel point dans l’image suivante correspond à la même molécule, et ces suppositions peuvent facilement être erronées. Pire, des trajectoires correctes et incorrectes peuvent sembler très similaires, rendant difficile de savoir quelles parties des données sont fiables.
Concevoir des expériences pour des données honnêtes
Les chercheurs ont d’abord construit un simulateur réaliste générant des films de « vérité terrain » de molécules en diffusion, où les trajectoires réelles sont connues. Ils ont utilisé ces jeux de données synthétiques pour tester systématiquement comment des facteurs clés affectent la fiabilité du suivi : la vitesse de déplacement des molécules, le nombre d’objets apparaissant dans chaque image, la fréquence d’acquisition et la distance maximale autorisée pour un saut entre images. À partir de cela, ils ont créé des cartes montrant, pour chaque situation donnée, quels réglages maximisent la fraction de mouvements correctement reconstruits. Ces cartes montrent que pour des molécules se déplaçant lentement à des densités modérées, le suivi peut être très fiable, mais que pour des molécules rapides à haute densité, les erreurs augmentent rapidement et l’ajout de plus de molécules n’apporte plus d’information utile.
Repérer et éliminer les étapes douteuses
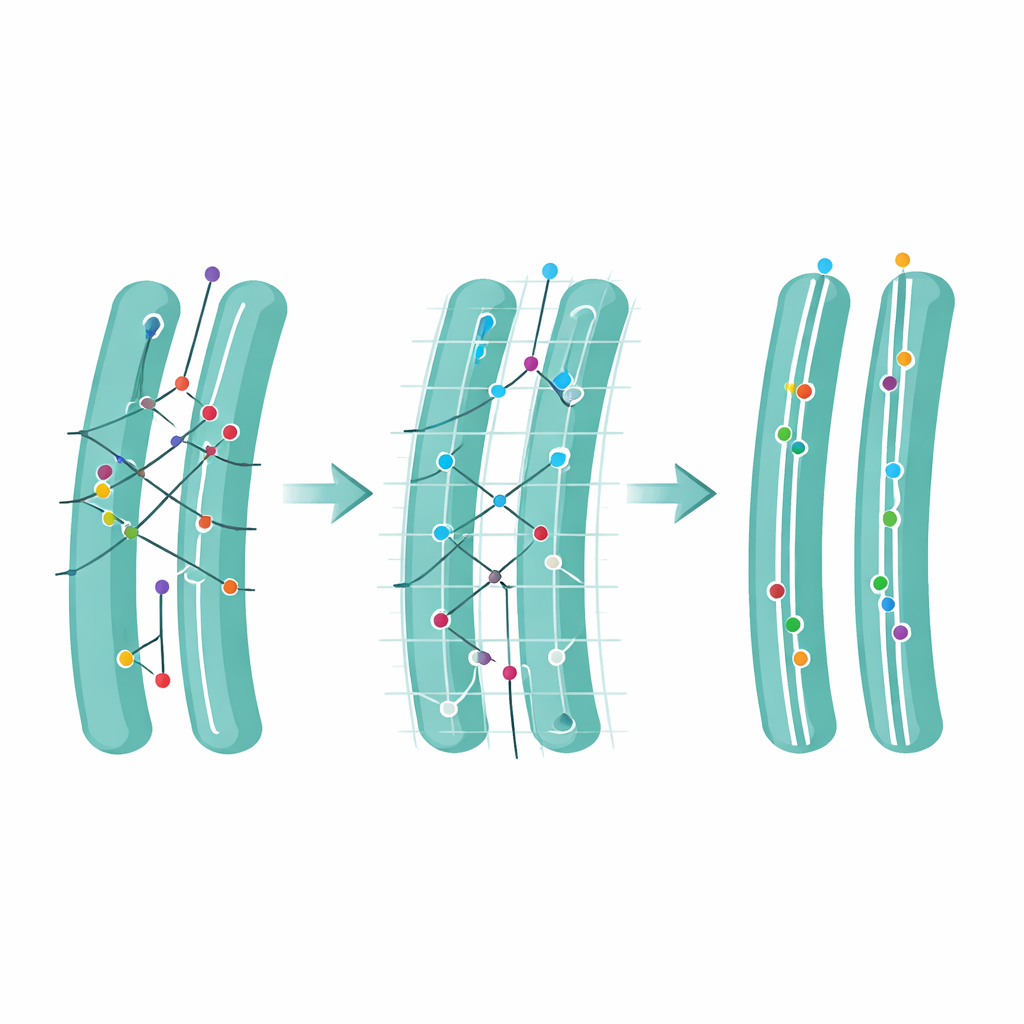
Ensuite, l’équipe a abordé une idée subtile mais puissante : l’ambiguïté. Un déplacement est qualifié d’ambigu lorsqu’il existe plus d’un point possible accessible pour la prochaine image, forçant l’algorithme à choisir entre plusieurs liaisons plausibles. À l’aide de leurs simulations, les auteurs ont montré qu’une grande partie des erreurs de suivi provient de ces étapes ambiguës. Ils ont défini un score d’ambiguïté qui compte la fréquence de telles situations, puis exploré ce qui se passe si toutes les étapes ambiguës sont supprimées après le suivi. Cet élagage sacrifie une partie des données et raccourcit les trajectoires, mais il augmente fortement la fiabilité globale de ce qui reste et améliore les estimations de la vitesse de diffusion des molécules. Appliqué à des films réels d’un marqueur dans le réticulum endoplasmique, l’ambiguïté était plus élevée dans les régions encombrées près du noyau cellulaire, et la suppression des liaisons ambiguës a clarifié ces zones sans dégrader les régions plus simples.
Laisser l’architecture cellulaire guider le suivi
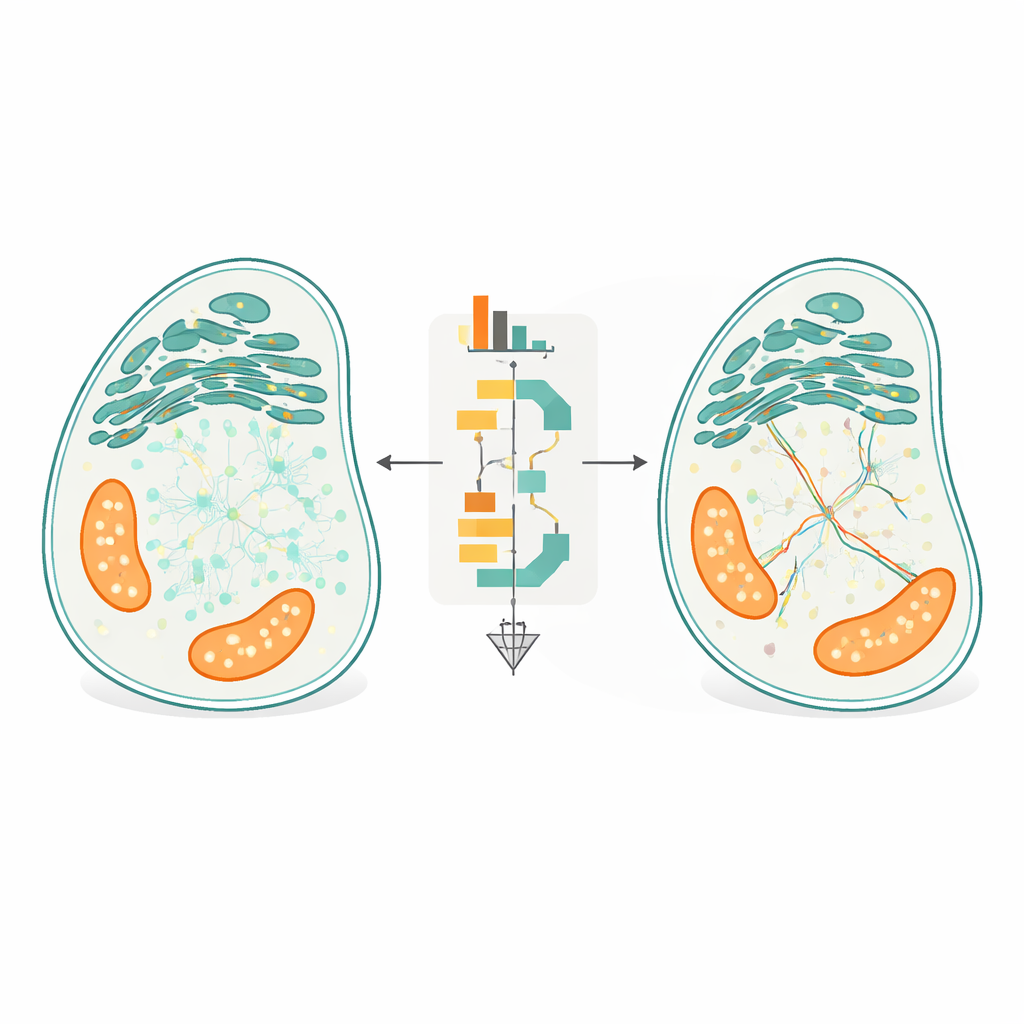
L’innovation centrale de FidlTrack est le suivi « conscient de la structure ». Plutôt que de traiter chaque point comme se déplaçant dans l’espace vide, la méthode utilise des images de l’architecture interne de la cellule — comme les contours du réticulum endoplasmique, des mitochondries ou des prolongements neuronaux fins — pour contraindre les trajets possibles des molécules. L’image de l’organite est convertie en un graphe de pixels connectés, et les distances sont mesurées le long de ce graphe plutôt qu’en lignes droites à travers l’espace. Les liaisons qui exigeraient qu’une molécule saute d’un tubule à un autre séparé peuvent ainsi être signalées comme impossibles et rejetées. Dans des simulations de tubes très rapprochés et dans des films réels de processus neuronaux et d’organelles, cette conscience de la structure a réduit les liaisons ambiguës jusqu’à moitié et multiplié la quantité de données de mouvement non ambiguës et fiables.
Révéler des comportements cellulaires cachés et des événements pertinents pour la maladie
Équipés de ces outils — réglages optimisés, filtrage de l’ambiguïté et conscience de la structure — les auteurs ont réexaminé plusieurs questions biologiques auparavant hors de portée. Dans le réticulum endoplasmique, ils ont pu suivre nettement comment les protéines se déplacent lorsqu’elles rencontrent des sites d’exportation qui canalisent la cargaison vers l’appareil de Golgi, distinguant des « survols » brefs de séjours plus longs. Ils ont capturé des moments rares où la protéine liée à Alzheimer, APP, est clivée par l’enzyme BACE1, visible comme un passage soudain d’un mouvement lent ancré à la membrane à une diffusion libre plus rapide. Ils ont également suivi des molécules de type anticorps conçues dans le RE et, à partir des variations de leur mouvement, déduit quand elles étaient liées à leur cible ou en dérive libre. Dans ces cas divers, FidlTrack a récupéré des trajectoires plus fiables et accentué des différences que les méthodes classiques avaient soit estompées soit sous-estimées.
Ce que cela signifie pour la biologie cellulaire future
Pour les non-spécialistes, le message clé est que toutes les trajectoires de molécules uniques ne se valent pas : certaines sont dignes de confiance, d’autres trompeuses, et jusqu’à présent il était difficile de les distinguer. FidlTrack offre une manière pratique et open-source de mesurer la fiabilité d’un jeu de données donné et d’améliorer cette fiabilité en ajustant les paramètres expérimentaux, en supprimant les étapes ambiguës et en utilisant la géométrie propre à la cellule comme guide. Cela rend possible d’observer les molécules naviguer dans l’intérieur complexe de la cellule avec une plus grande confiance et de détecter des événements rares ou subtils, depuis le tri des protéines jusqu’à des processus pertinents pour la maladie, qui étaient auparavant noyés dans le bruit.
Citation: Parutto, P., Yuan, Y., Davì, V. et al. FidlTrack: high-fidelity structure-aware single particle tracking resolves intracellular molecular motion in organelles sensing APP processing. Nat Commun 17, 2639 (2026). https://doi.org/10.1038/s41467-026-69067-y
Mots-clés: suivi de particule unique, dynamique intracellulaire, structure des organelles, mouvement des protéines, maladie d’Alzheimer