Clear Sky Science · fr
AACRNL passé d’un facteur de virulence à un parasite épigénétique stimulant l’expansion du génome chez des eucaryotes libres
Quand de vieilles toxines apprennent de nouveaux tours
Nos génomes ne sont pas des manuels silencieux. Ce sont des arènes encombrées où gènes, virus et ADN mobile se disputent sans cesse l’espace et le contrôle. Cette étude révèle un acteur inattendu de ce conflit : une protéine qui a commencé sa vie comme toxine utilisée par des microbes pour attaquer des hôtes, mais qui a depuis été reprogrammée au sein d’animaux libres comme une sorte de « parasite épigénétique » contribuant à étendre sa propre empreinte dans le génome.
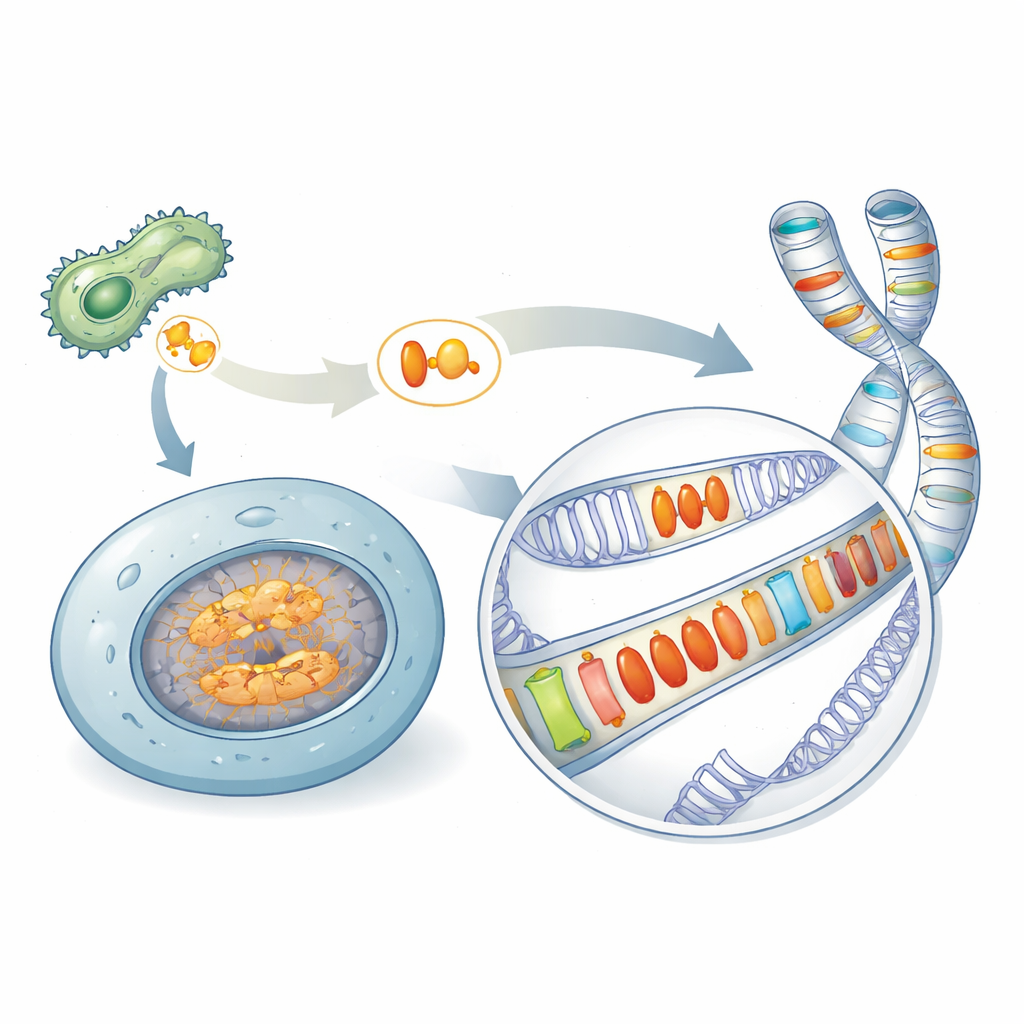
Un héritage caché d’armes microbiennes
De nombreux microbes pathogènes s’appuient sur des protéines spécialisées, appelées effecteurs, pour saboter les défenses des organismes qu’ils infectent. Une famille célèbre, connue sous le nom de Crinklers, était considérée comme propre aux pathogènes. En parcourant une grande variété d’espèces, les auteurs ont découvert des protéines apparentées — regroupées ici sous le nom AACRNL — dans des lieux inattendus, notamment chez des éponges, des coraux, des oursins et des poissons osseux qui ne sont pas des pathogènes classiques. Ces protéines AACRNL conservent le noyau toxine‑like capable de modifier chimiquement d’autres protéines, mais leur portion antérieure de « livraison », que les pathogènes utilisent pour pénétrer les cellules hôtes, s’est largement effritée. Ce changement structural suggère une transition d’une action contre d’autres organismes vers une action à l’intérieur des propres cellules de l’hôte.
Un basculement égoïste dans le génome
Chez les poissons osseux, les gènes AACRNL se trouvent en copies multiples disséminées sur différents chromosomes. En comparant les segments d’ADN voisins, les chercheurs ont montré que certaines lignées AACRNL ont arrêté de se copier, tandis que d’autres se sont multipliées avec l’aide de segments d’ADN sautants voisins appelés transposons. Ces transposons agissent comme des navettes génomiques : lorsqu’ils se déplacent ou se dupliquent, ils peuvent emporter AACRNL avec eux. Le résultat est une mosaïque de copies répétées d’AACRNL intégrées parmi des séquences de transposons, caractéristique d’un gène qui se propage pour son propre bénéfice plutôt que pour celui de l’hôte.
Désactiver le bouton muet du génome
En temps normal, les cellules tiennent cet ADN mobile sous contrôle strict. Un garde‑fou clé est une marque chimique sur les protéines d’emballage de l’ADN, connue sous le nom H3K27me3, qui aide à maintenir éteintes les régions dangereuses ou bruyantes. Les auteurs ont découvert qu’une version active d’AACRNL chez les poissons, appelée AACRNLβ, peut modifier chimiquement EZH2, l’enzyme qui pose cette marque répressive. Lorsque AACRNLβ altère EZH2, la quantité de H3K27me3 à son propre locus et aux transposons voisins diminue, l’ADN local s’ouvre, et AACRNLβ ainsi que ses voisins transposons sont exprimés plus fortement. En pratique, la protéine appuie sur son propre bouton « marche » et lève les freins sur les éléments mobiles mêmes qui peuvent la transporter vers de nouveaux emplacements dans le génome.
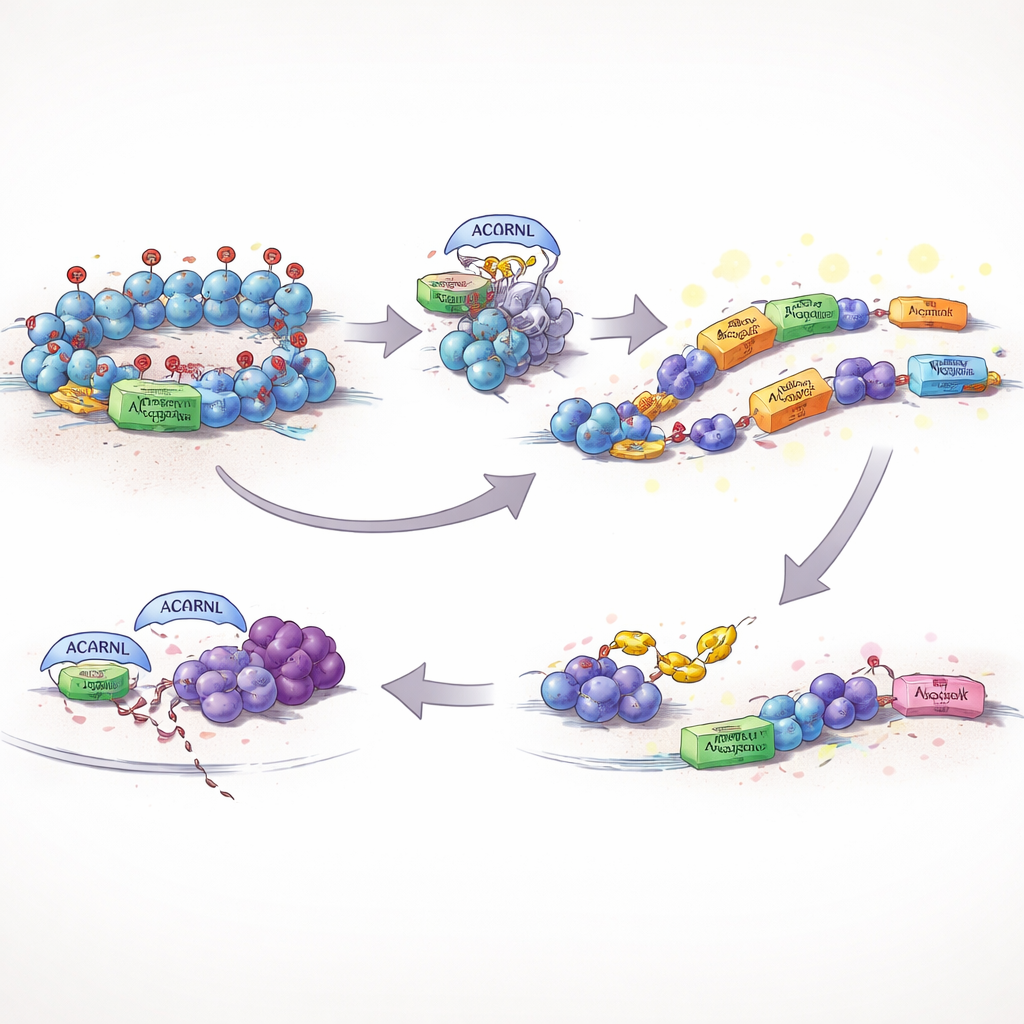
Échapper aux chiens de garde immunitaires
Déchaîner des transposons et une activité génétique inhabituelle risque d’attirer l’attention du système immunitaire. L’étude montre qu’AACRNLβ gère aussi ce problème. Elle ajoute une petite marque chimique à TRAF6, une protéine centrale qui aide à activer les signaux antiviraux et inflammatoires. Marquée ainsi, TRAF6 devient moins stable et est de plus en plus ciblée pour l’élimination par la machinerie de recyclage cellulaire. Avec ce hub de signal affaibli, les voies de défense clés s’activent moins fortement, créant un environnement plus tolérant dans lequel AACRNLβ et ses transposons associés peuvent persister et se copier avec moins de conséquences en cas de détection.
Une course aux armements délicate à l’intérieur de la cellule
L’histoire ne se termine pas avec AACRNLβ qui agirait sans contrôle. La même protéine TRAF6 ciblée par AACRNLβ peut, à son tour, apposer ses propres marques sur AACRNLβ, signalant la protéine de type parasite pour destruction. Cet aller‑retour ressemble à une course aux armements moléculaire : AACRNLβ utilise une chimie dérivée des toxines pour courber la chromatine et l’immunité à son avantage, tandis que les protéines hôtes ripostent en la dégradant et en rendant son activité sporadique et risquée. Les auteurs soutiennent que ce bras de fer a permis à une ancienne arme microbienne de survivre comme un résident égoïste des génomes d’organismes libres, augmentant le contenu d’ADN et remodelant de l’intérieur les règles du conflit génétique.
Pourquoi cela change notre regard sur les génomes
Pour un non‑spécialiste, le message clé est que les génomes ne sont pas que des plans optimisés pour la survie de l’hôte. Ils abritent aussi des opportunistes. Ce travail montre que même des toxines classiques peuvent être domestiquées en tels éléments, utilisant leur chimie destructive d’origine pour contourner les verrous épigénétiques et les alarmes immunitaires, et se propager dans le génome au fil du temps évolutif. Comprendre ce type de conflit caché aide à expliquer pourquoi les génomes sont si volumineux, complexes et dynamiques — et suggère que d’autres toxines « retraitées » pourraient silencieusement réécrire l’ADN dans de nombreuses espèces, y compris peut‑être la nôtre.
Citation: Xu, T., Geng, S., Lv, X. et al. AACRNL evolved from virulence factor to epigenetic parasite driving genome expansion in free-living eukaryotes. Nat Commun 17, 2130 (2026). https://doi.org/10.1038/s41467-026-69012-z
Mots-clés: éléments génétiques égoïstes, évolution du génome, régulation épigénétique, transposons, immunité innée