Clear Sky Science · fr
Perspectives mécanistiques sur le déroulement dirigé par PCBP1 de certains ADN en i-motif au point de contrôle G1/S
Des plis d’ADN qui jouent le rôle de feux tricolores
À l’intérieur de nos cellules, le code génétique n’est pas qu’une simple échelle droite d’ADN. Certaines portions peuvent se plier en formes inhabituelles qui fonctionnent comme de minuscules interrupteurs et contribuent à réguler le moment où les cellules répliquent leur ADN et se divisent. Cette étude s’intéresse à l’une de ces formes, appelée i-motif, et à une protéine nommée PCBP1 qui peut reconnaître et dérouler ces structures juste au moment où la cellule se prépare à répliquer son ADN. Comprendre cette interaction éclaire la manière dont les cellules préservent la stabilité de leur génome et ce qui peut dérailler dans le cancer.
Des nœuds d’ADN étranges dans des régions liées au cancer
On apprend généralement que l’ADN forme la célèbre double hélice, mais certains segments riches en cytosine (C) peuvent se replier en un nœud à quatre brins connu sous le nom d’i-motif. Ces structures apparaissent préférentiellement dans des régions de contrôle de gènes qui stimulent la croissance cellulaire, comme cMYC et BCL2. Pendant des années, les chercheurs ont débattu de l’existence d’i-motifs en cellules vivantes, car ils sont plus faciles à détecter in vitro dans des conditions acides que dans l’environnement proche du neutre des cellules. Grâce à des anticorps spécialisés qui reconnaissent les i-motifs, des travaux récents, dont la présente étude, ont confirmé qu’ils se forment bien dans les noyaux cellulaires—et qu’ils se regroupent souvent près de gènes clés de croissance et liés au cancer.
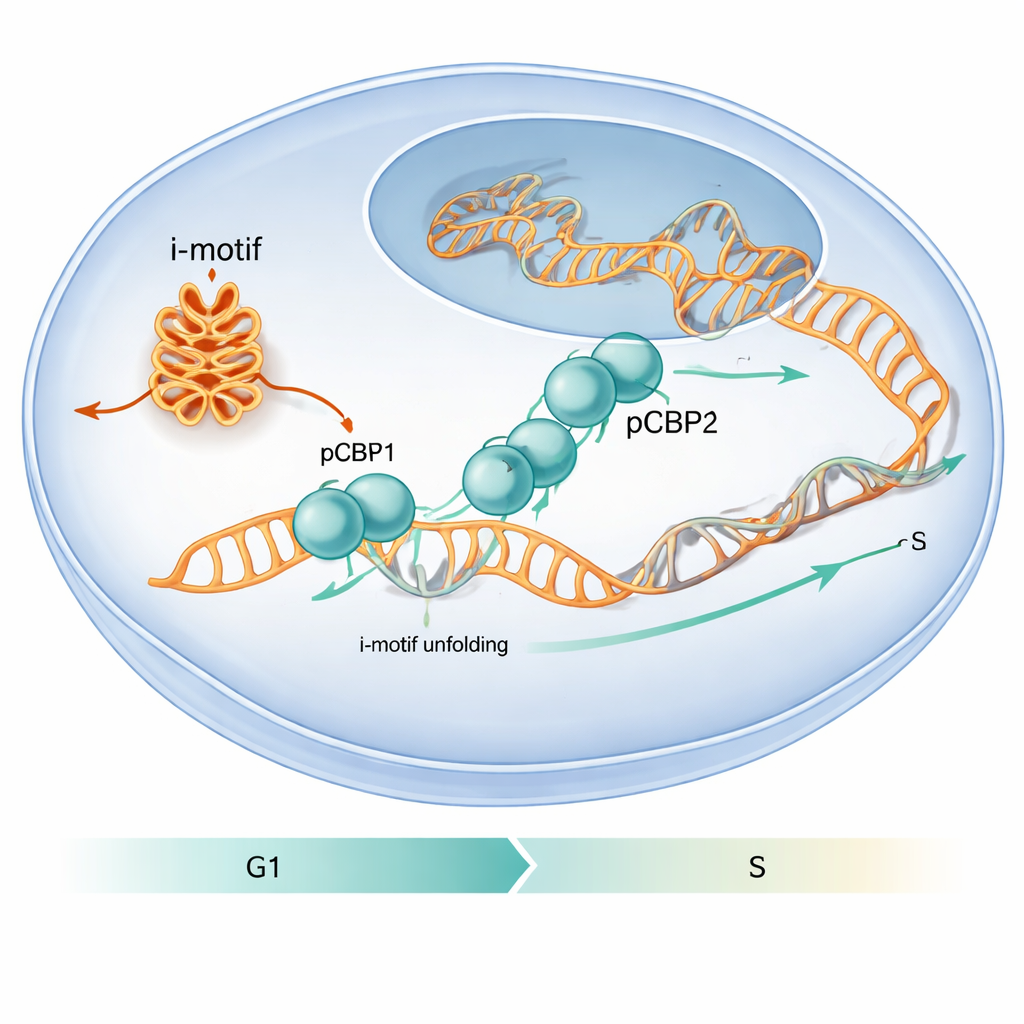
Une protéine qui repère des plis d’ADN particuliers
Les auteurs ont cherché à savoir comment les protéines cellulaires traitent ces replis d’ADN inhabituels. Ils se sont focalisés sur PCBP1, une protéine déjà connue pour se lier aux régions riches en C de l’ADN et de l’ARN et pour influencer le cycle cellulaire. En analysant des cartes de liaison à l’échelle du génome et en réalisant des expériences ciblées, ils ont observé que PCBP1 se localise fréquemment sur des régions riches en C susceptibles de former des i-motifs, en particulier autour des sites d’initiation des gènes. Dans des expériences cellulaires menées sur des lignées tumorales humaines, des régions promotrices de cMYC, BCL2 et la séquence ILPR liée à l’insuline ont montré à la fois des signaux i-motif forts et une forte occupation par PCBP1, ce qui suggère que PCBP1 est un gardien dédié de ces structures.
Comment PCBP1 saisit et déroule le nœud
Dans des essais in vitro, les chercheurs ont comparé l’affinité de PCBP1 pour des i-motifs repliés et pour la même séquence d’ADN dépliée. Ils ont ajusté l’acidité pour que l’ADN reste soit replié soit relâché, tout en conservant la stabilité de la protéine. PCBP1 a toujours préféré l’i-motif replié, s’y liant environ deux fois plus fortement qu’à la même séquence dépliée, et ne se liant que faiblement à des formes d’ADN non apparentées. Une fois lié, PCBP1 pouvait activement favoriser le déroulement, permettant au brin en i-motif de s’apparier avec son brin complémentaire. Cependant, tous les i-motifs ne se comportaient pas de la même manière : certains, comme la structure du promoteur de cMYC, se déroulaient rapidement, tandis que d’autres, comme ceux de BCL2, résistaient et se déroulaient lentement. Des caractéristiques supplémentaires, telles que des épingles (hairpins) dans l’ADN et le degré de protonation des cytosines (charge positive supplémentaire), pouvaient soit faciliter soit gêner l’activité de déroulement de PCBP1.
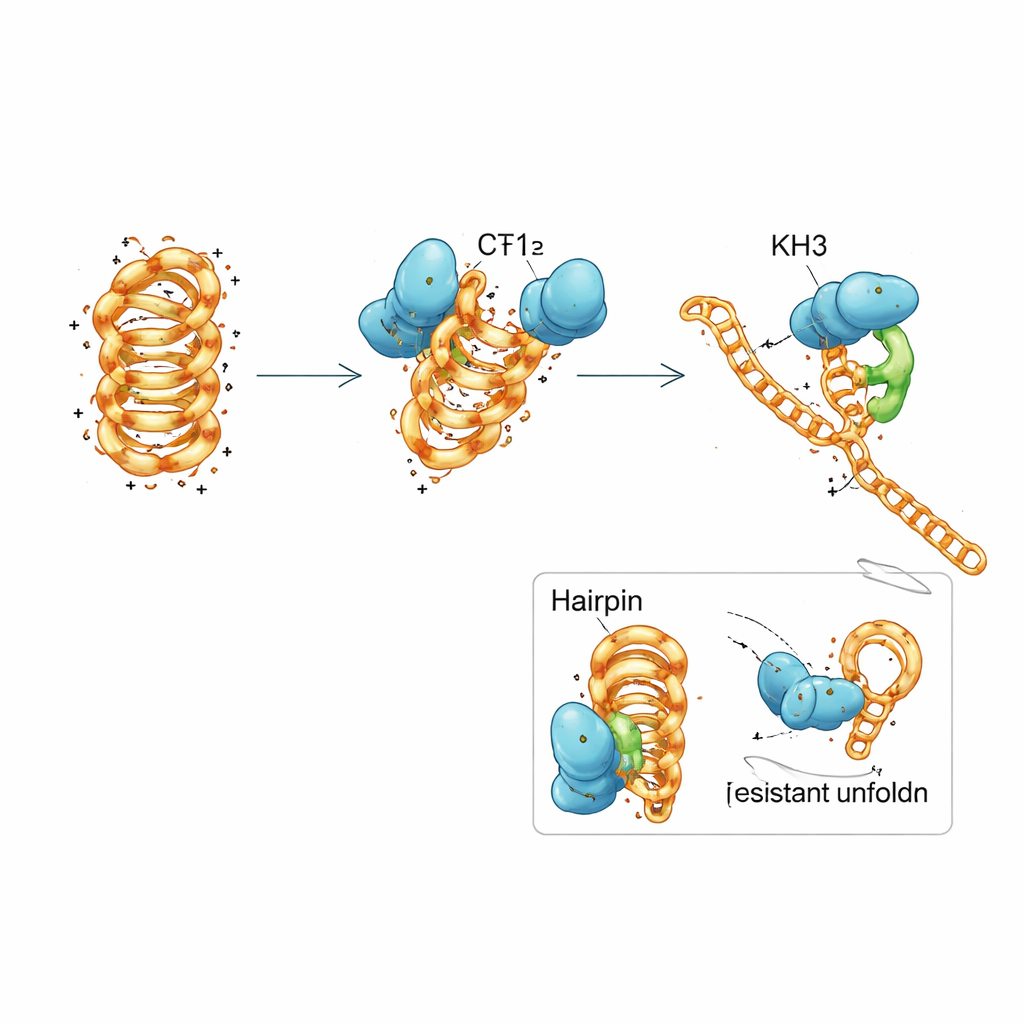
Un effort d’équipe au sein d’une seule protéine
PCBP1 est composé de trois modules répétés appelés domaines KH, des motifs courants qui saisissent de courts segments d’acides nucléiques. L’équipe a disséqué PCBP1 en fragments et découvert qu’aucun domaine KH isolé ne pouvait reproduire entièrement le comportement de la protéine entière. Les deux premiers domaines ensemble pouvaient se fixer à la fois à l’ADN replié et déplié et pousser l’i-motif vers une forme moins stable, mais n’entraînaient qu’un déroulement complet lent. Le troisième domaine, isolé, se liait à peine. Lorsque les trois domaines étaient présents et pouvaient coopérer, la protéine retrouvait sa forte préférence pour les i-motifs repliés et sa capacité efficace à les dérouler. Des mesures biophysiques détaillées et des simulations informatiques ont suggéré un mécanisme par étapes : KH1 et KH2 s’ancrent d’abord sur des régions de boucle flexibles de l’i-motif et perturbent partiellement certaines paires de bases, ce qui permet ensuite à KH3 de s’engager et de pousser la structure vers un état ouvert, prêt pour la réplication.
Maintenir le cycle cellulaire à l’heure
Les travaux montrent aussi que cette chorégraphie moléculaire influence le comportement cellulaire. Lorsque les chercheurs ont réduit les niveaux de PCBP1 dans des cellules humaines, davantage d’i-motifs sont apparus à des promoteurs géniques spécifiques, les marqueurs de dommage à l’ADN ont augmenté et les cellules se sont bloquées au point de contrôle critique G1/S—le moment juste avant le début de la réplication de l’ADN. Dans des conditions normales, la présence de PCBP1 sur les régions formant des i-motifs atteint un pic autour de ce point de contrôle, puis décline au début de la phase S à mesure que les i-motifs sont résolus. Ce calendrier suggère que PCBP1 agit comme un gardien : il se lie et déroule des i-motifs particuliers au moment opportun afin de permettre la progression harmonieuse de la réplication de l’ADN et de préserver l’intégrité du génome. Pour un lecteur non spécialiste, le message est que des plis d’ADN inhabituels peuvent fonctionner comme des bouchons temporaires, et que PCBP1 est l’un des outils spécialisés que la cellule utilise pour les enlever, contribuant à prévenir des erreurs qui pourraient sinon favoriser le cancer.
Citation: Sengupta, P., Gillet, N., Obi, I. et al. Mechanistic insights into PCBP1-driven unfolding of selected i-motif DNA at G1/S checkpoint. Nat Commun 17, 1149 (2026). https://doi.org/10.1038/s41467-026-68822-5
Mots-clés: ADN en i-motif, protéine PCBP1, point de contrôle du cycle cellulaire, stabilité du génome, structure secondaire de l’ADN