Clear Sky Science · fr
HIV-seq révèle des différences d'expression génique entre les cellules transcrivant le VIH chez des personnes virémiques et des personnes sous traitement suppressif
Pourquoi cette recherche importe pour les personnes vivant avec le VIH
Les traitements modernes du VIH peuvent réduire la charge virale dans le sang à des niveaux indétectables, transformant une infection autrefois mortelle en une maladie chronique et gérable. Pourtant, si le traitement est interrompu, le virus rebondit presque toujours. Cet article explore un groupe caché de cellules immunitaires infectées qui maintiennent le VIH en vie à couvert, et présente une nouvelle technologie, « HIV‑seq », qui permet aux scientifiques de voir enfin ce que ces cellules font, une à une. Comprendre ces cellules furtives pourrait orienter des stratégies futures visant non seulement à contrôler le VIH, mais peut‑être à le guérir.
Trouver le virus qui se cache en pleine vue
Le VIH persiste dans l'organisme en intégrant son matériel génétique dans des cellules immunitaires longue durée, en particulier les cellules T CD4. Certaines de ces cellules infectées restent silencieuses, tandis que d'autres produisent activement des fragments d'ARN viral ou des protéines même lorsque les tests sanguins indiquent une charge indétectable. Ces cellules du « réservoir actif » peuvent alimenter une inflammation chronique et provoquer un rebond viral rapide si le traitement est interrompu. Cependant, le séquençage ARN unicellulaire standard les manque souvent, car les transcrits du VIH peuvent être rares et fréquemment dépourvus de queue poly‑A sur laquelle la technologie s'appuie habituellement. Les auteurs ont cherché à résoudre ce problème de détection afin de pouvoir comparer les cellules productrices de VIH chez des personnes avec une infection non contrôlée (virémie) à celles sous thérapie antirétrovirale (TAR) efficace.
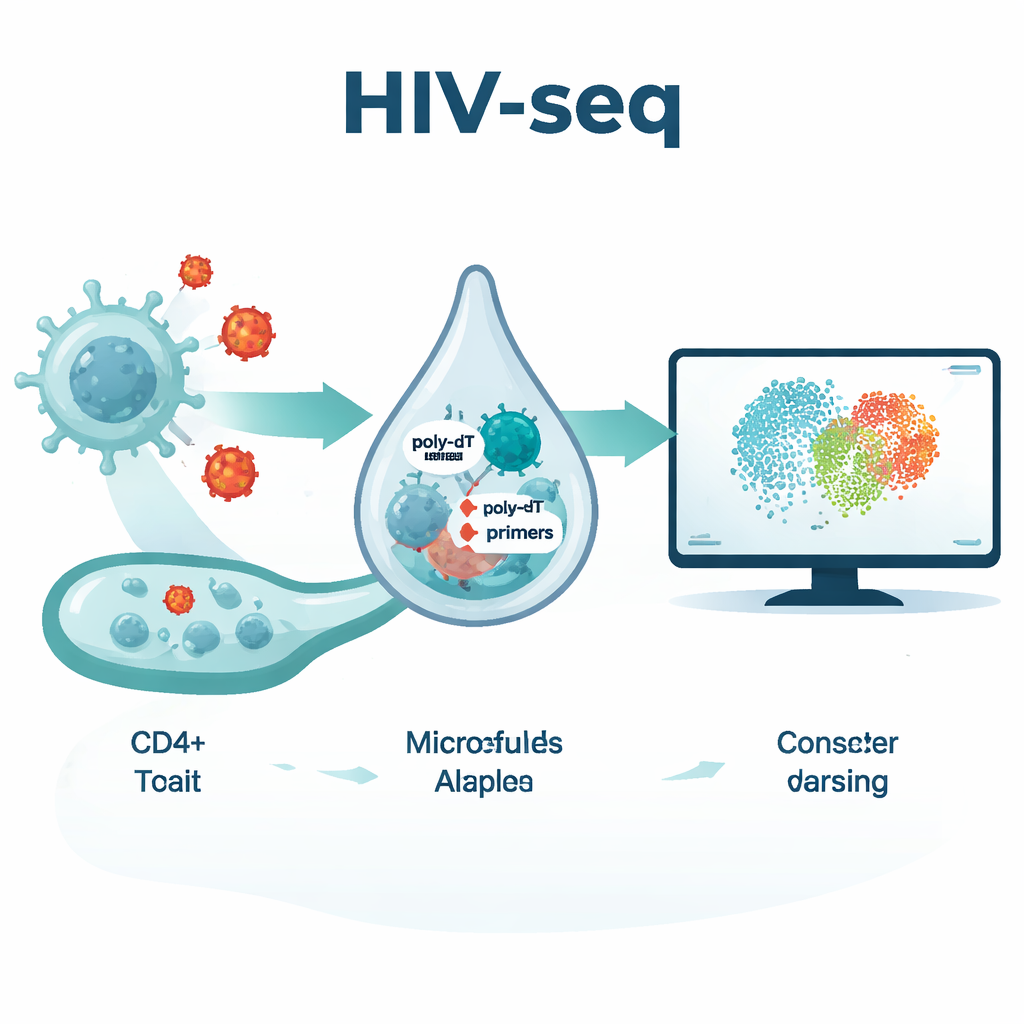
Un nouveau regard : la méthode HIV‑seq
L'équipe a développé HIV‑seq en ajoutant plusieurs amorces de capture spécifiques du VIH, soigneusement conçues, à la chimie de séquençage unicellulaire habituelle. Ces amorces supplémentaires se lient à des régions conservées du génome du VIH, améliorant la récupération de l'ARN viral qu'il porte ou non une queue poly‑A. Ils ont combiné cela avec des anticorps marqués par code-barres ADN mesurant simultanément des dizaines de protéines de surface, fournissant à chaque cellule séquencée un profil moléculaire riche. Lors d'essais comparatifs sur des cellules sanguines de personnes non traitées, HIV‑seq a à peu près doublé le nombre de lectures virales par cellule infectée sans déformer les profils d'expression génique de la cellule hôte ni produire de faux signaux chez des donneurs séronégatifs. Cela a permis aux chercheurs de définir les cellules positives pour l'ARN du VIH comme celles présentant au moins un transcrit viral détecté avec confiance et de cartographier la position de ces cellules dans le paysage plus large des cellules T.
À quoi ressemblent les cellules productrices de VIH lors d'une infection active
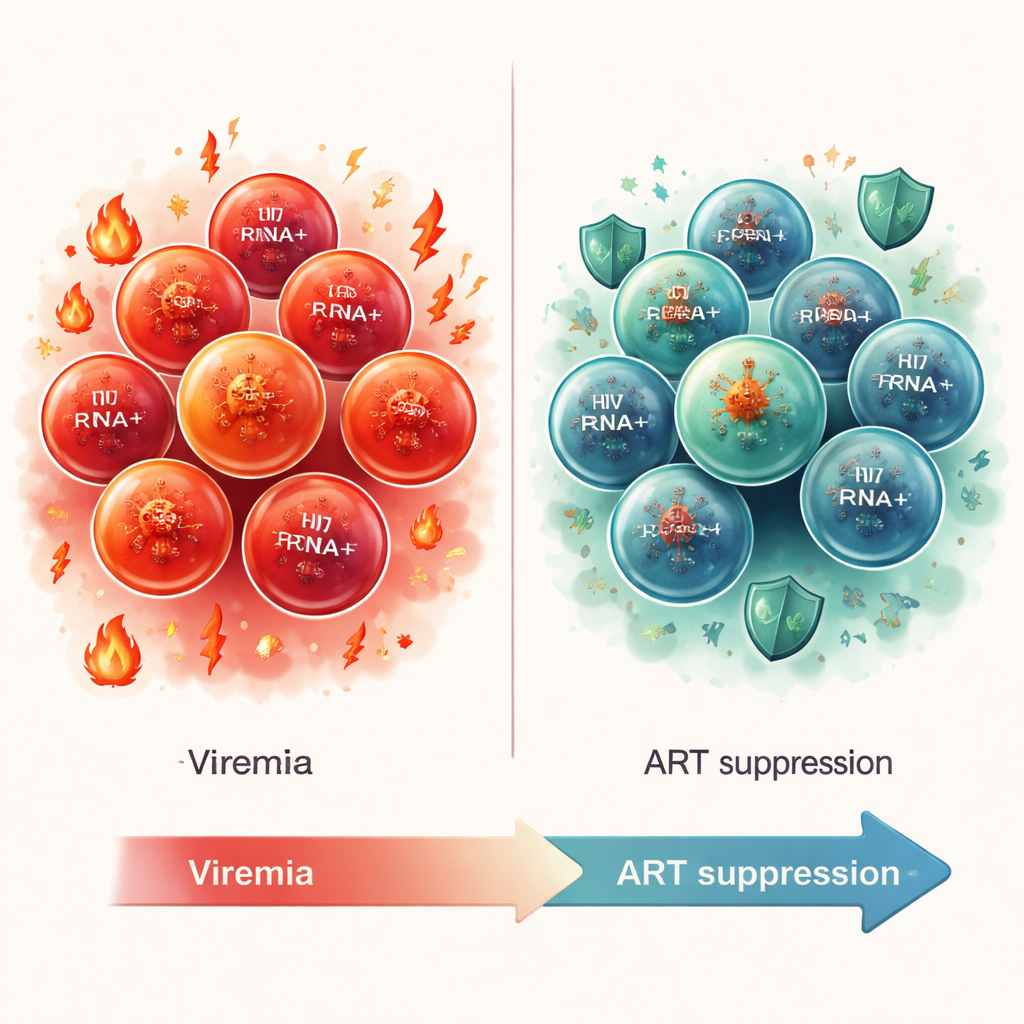
En appliquant HIV‑seq à quatre personnes non traitées, les auteurs ont analysé plus de 85 000 cellules T CD4 et identifié 1 072 cellules transcrivant activement le VIH. Ces cellules infectées étaient rarement des cellules naïves ; elles se regroupaient principalement parmi les cellules T mémoire effectrices déjà activées par des rencontres immunitaires antérieures. Un sous‑ensemble frappant présentait un profil cytotoxique ou « tueur », exprimant des gènes pour les granzymes, la perforine et d'autres molécules typiquement associées aux cellules qui détruisent des cibles infectées. Parallèlement, les cellules positives pour le VIH présentaient des niveaux réduits de plusieurs défenses antivirales naturelles et de facteurs de restriction, suggérant un environnement interne plus favorable à la réplication virale. Des analyses de voies ont montré une activité accrue de circuits de signalisation connus pour stimuler l'expression des gènes du VIH, notamment NFAT et la protéine kinase C, ainsi que des voies de chimiochine pouvant influencer la localisation de ces cellules dans l'organisme.
Comment les cellules productrices de VIH évoluent sous traitement efficace
Les chercheurs ont ensuite examiné trois des mêmes individus après au moins six mois de TAR efficace, lorsque le virus dans le sang était supprimé. Comme prévu, les cellules productrices de VIH étaient beaucoup plus rares, mais HIV‑seq a pu détecter 25 de ces cellules parmi plus de 75 000 cellules T CD4. Ces cellules étaient de nouveau enrichies parmi les cellules T mémoire effectrices, mais leur caractère avait changé : elles ne se regroupaient plus dans le groupe fortement cytotoxique. Elles se concentraient plutôt dans des sous‑ensembles de cellules T mémoire marqués par le récepteur à l'IL‑7 et d'autres caractéristiques des cellules de longue durée capables d'auto‑renouvellement. Nombre d'entre elles exprimaient la protéine de survie BCL‑2, et leurs signatures géniques indiquaient l'activation de voies liées au TGF‑β connues pour atténuer l'inflammation et pouvant aider à maintenir le VIH dans un état de faible activité, plus difficile à détecter. Comparées aux réponses antivirales et inflammatoires vigoureuses observées pendant la virémie, les cellules positives pour le VIH sous TAR présentaient un profil anti‑inflammatoire, plus « tolérant ».
Implications pour les stratégies futures de guérison du VIH
Pour un observateur non spécialiste, ces résultats dessinent l'image d'un VIH caméléon : lors d'une infection non traitée, les cellules infectées ressemblent à des combattants à vie courte qui propagent à la fois le virus et l'inflammation ; une fois la réplication active calmée par la TAR, les cellules productrices restantes ressemblent à des survivantes de longue durée qui se cachent derrière des signaux apaisants anti‑inflammatoires et des programmes de survie robustes. HIV‑seq offre un nouvel outil puissant pour suivre ces cellules insaisissables au niveau unicellulaire, aidant les chercheurs à identifier les voies cellulaires qui les soutiennent et comment elles pourraient être exposées ou éliminées. En clarifiant comment les cellules transcrivant le VIH diffèrent entre l'infection active et les états supprimés par traitement, ce travail fournit des indices concrets pour concevoir des approches de « réveil‑et‑tuer » (shock‑and‑kill) ou de « bloquer‑et‑verrouiller » (block‑and‑lock) susceptibles, un jour, de réduire ou même d'éliminer le réservoir viral.
Citation: Frouard, J., Telwatte, S., Luo, X. et al. HIV-seq reveals gene expression differences between HIV-transcribing cells from viremic and suppressed people with HIV. Nat Commun 17, 1540 (2026). https://doi.org/10.1038/s41467-026-68797-3
Mots-clés: réservoir du VIH, séquençage unicellulaire, thérapie antirétrovirale, latence virale, cellules T mémoire immunitaires