Clear Sky Science · fr
La trans-clivage par CRISPR-Cas9 est entravée par un R-loop bordé, un espaceur allongé et un domaine HNH inactif
Pourquoi de petites coupures d’ADN comptent
CRISPR-Cas9 est célèbre comme un scalpel moléculaire capable de couper l’ADN à des sites choisis, mais cet outil présente un second comportement, moins reconnu : une fois activé, il peut aussi grignoter d’autres fragments de matériel génétique à proximité. Comprendre quand cette coupure « collatérale » s’allume ou s’éteint est crucial pour concevoir des thérapies d’édition génique plus sûres et des tests diagnostiques plus sensibles. Cette étude dissèque les caractéristiques physiques du complexe Cas9–ADN–ARN qui déterminent si Cas9 effectue discrètement sa coupure prévue ou commence aussi à dégrader des brins simples d’ADN errants.
Comment les ciseaux CRISPR se déclenchent
Pour agir, Cas9 se lie à un court segment d’ARN guide qui le dirige vers une séquence d’ADN correspondante dans un génome. Quand Cas9 trouve sa cible, l’ARN guide s’apparie avec un brin d’ADN, forçant les deux brins à s’écarter et créant une région hybride ADN–ARN appelée R-loop. Dans son rôle classique, Cas9 coupe ensuite les deux brins d’ADN à cet endroit. Mais des travaux récents ont montré qu’une fois Cas9 activé de cette façon, son domaine de clivage RuvC peut aussi trancher de l’ADN simple brin non lié, comme des stretches de poly(T), ailleurs dans la solution. Les auteurs ont voulu savoir : quelles caractéristiques géométriques et structurelles exactes de l’ADN cible et de l’ARN guide rendent cette activité collatérale forte, faible ou absente ?
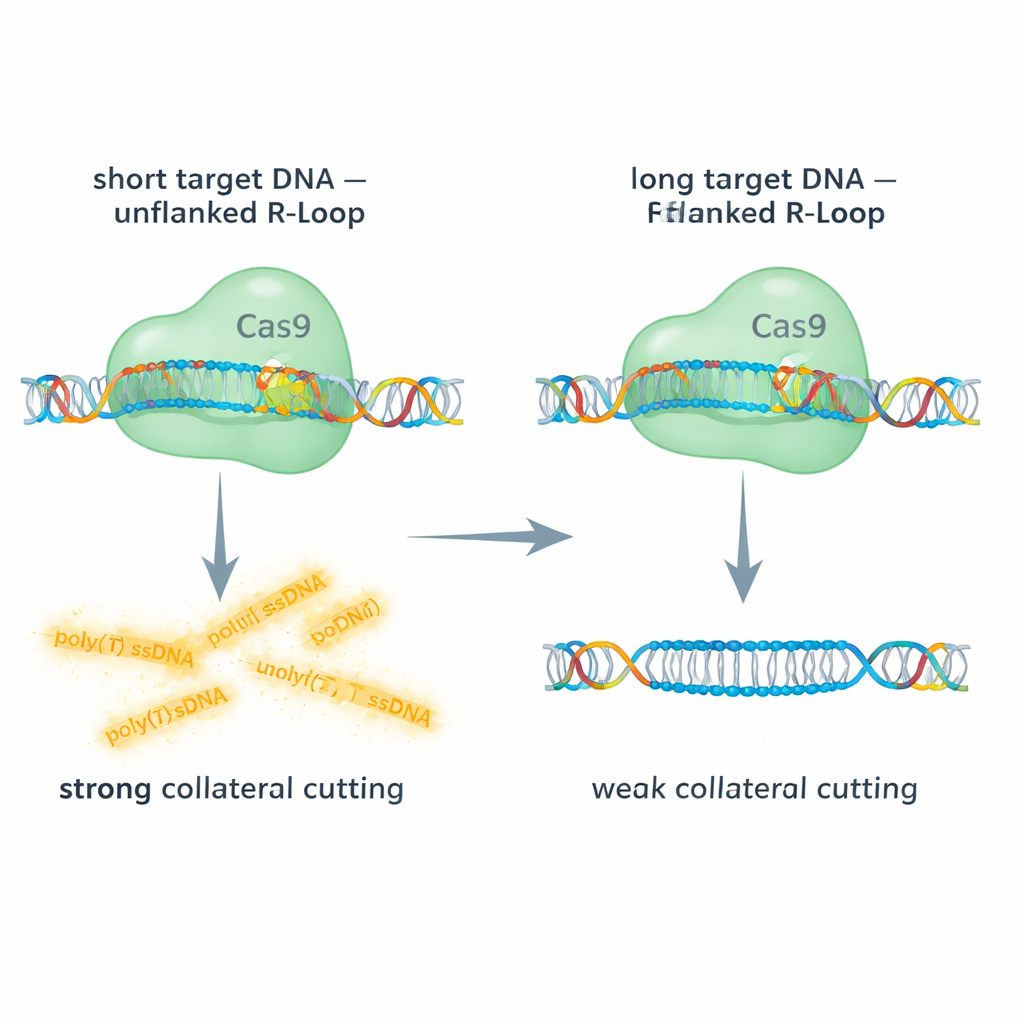
Cibles courtes versus longues : donner de l’espace au Cas9
L’équipe a comparé l’action de Cas9 sur des cibles d’ADN double brin courtes et longues, en utilisant des lectures fluorescentes pour suivre à la fois la coupure sur cible et le clivage collatéral d’une sonde d’ADN simple brin. Avec des cibles courtes, le R-loop à l’extrémité 5′ de l’ARN guide est « non bordé » : il n’y a pas d’ADN double brin supplémentaire se poursuivant au‑delà de la région hybride. Dans ces conditions, Cas9 a montré une activité collatérale robuste sur l’ADN simple brin. En revanche, lorsqu’ils ont utilisé des segments d’ADN plus longs laissant un ADN double brin supplémentaire bordant le R-loop, le clivage collatéral a chuté de façon spectaculaire, parfois d’environ 90 %, bien que la coupure principale sur la cible ait toujours eu lieu. Le ciblage d’ADN simple brin long, qui supprime complètement le R-loop, a en grande partie restauré l’activité collatérale. Ces comparaisons montrent qu’un « capuchon » d’ADN double brin adjacent au R-loop rigidifie le complexe et gêne physiquement l’accès ou la flexibilité nécessaires au domaine RuvC de Cas9 pour trancher d’autres brins.
Ajuster finement avec la longueur de l’ARN guide et les mésappariements
Les chercheurs ont ensuite exploré comment l’ARN guide lui‑même module ce comportement. Ils ont introduit de petits mésappariements entre le guide et l’ADN cible et ont suivi la capacité de Cas9 à couper. La coupure principale sur la cible a toléré de nombreux mésappariements d’une seule base, mais le clivage collatéral était plus fragile et dépendait fortement de la position précise du mésappariement, soulignant sa sensibilité. Ensuite, ils ont allongé systématiquement l’espaceur de l’ARN guide au‑delà des 20 nucléotides habituels. Même si Cas9 pouvait toujours se fixer et couper l’ADN cible, l’activité collatérale a diminué presque linéairement avec l’augmentation de la longueur de l’espaceur : l’ajout de seulement deux bases supplémentaires a réduit l’activité collatérale d’environ la moitié, et quatre bases supplémentaires l’ont encore diminuée. Dans des tests pratiques utilisant du matériel génétique du SARS‑CoV‑2, seuls des amplicons d’ADN conçus pour produire un R-loop non bordé avec un guide de longueur standard ont donné un signal collatéral fort, mettant en évidence comment la conception des amorces et des guides peut faire ou défaire les essais de détection basés sur CRISPR.
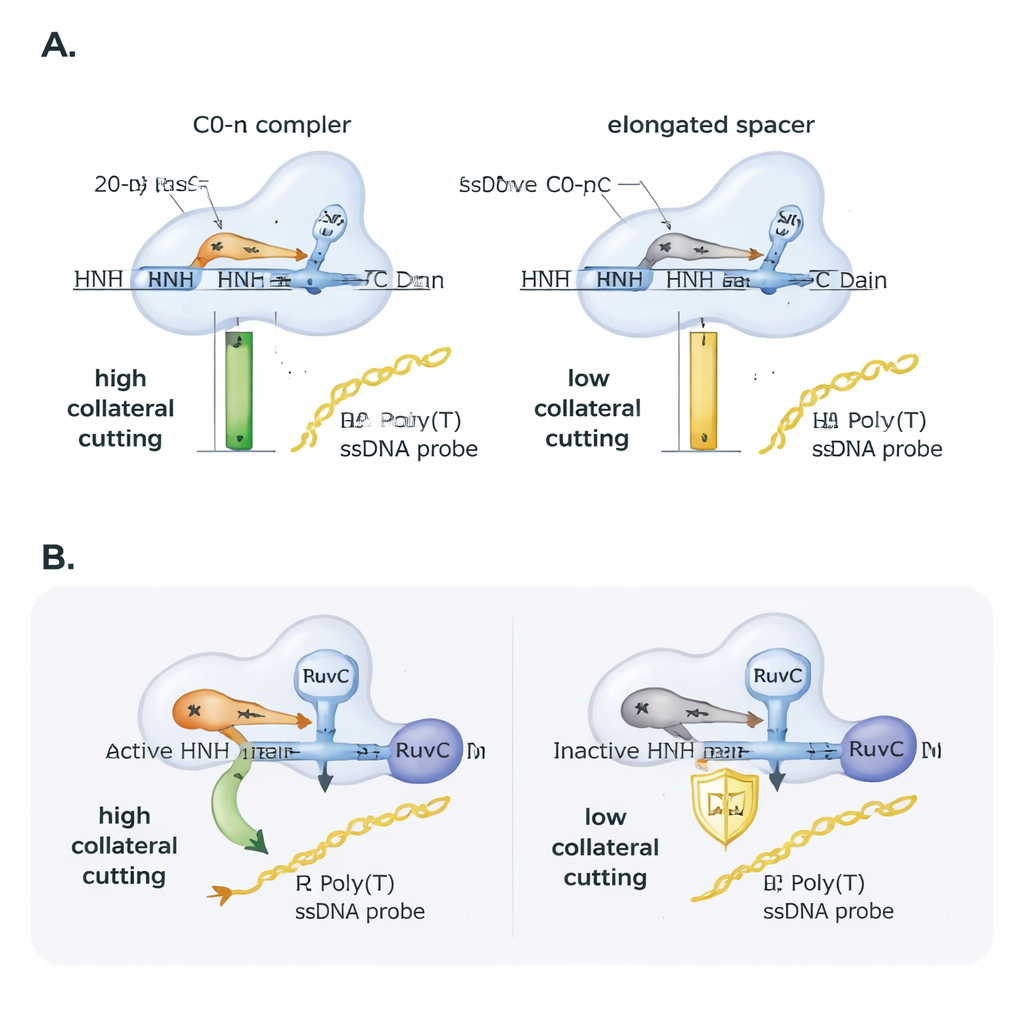
Un domaine auxiliaire essentiel en coulisse
Cas9 possède deux domaines de clivage, RuvC et HNH. Des travaux antérieurs liaient le clivage collatéral directement à RuvC, mais cette étude montre que HNH a aussi son importance. Lorsque les auteurs ont utilisé une variante de Cas9 avec un domaine HNH inactif, l’activité collatérale a plongé, bien que la fixation à la cible et le comportement de nicking soient restés. Fait intéressant, si on fournissait à Cas9 une cible d’ADN déjà nickée sur un brin, la version à HNH inactif retrouvait une activité collatérale similaire à l’enzyme normale. Cela suggère que le rôle de HNH est en partie mécanique : en coupant ou en assouplissant le brin ciblé, il aide la protéine à adopter une conformation qui expose RuvC aux ADN simple brin voisins. Des analyses structurelles de modèles 3D existants soutiennent cette vue, montrant que des R-loops non bordés et des guides de longueur standard laissent l’extrémité 5′ de l’ARN « s’appuyer » contre Cas9 et positionnent favorablement les régions catalytiques, tandis que des R-loops bordés et des guides allongés compactent davantage la protéine et protègent probablement le site RuvC des brins libres.
Ce que cela implique pour les outils futurs
Pour les non‑spécialistes, le message principal est que le comportement de Cas9 n’est pas tout ou rien : de petits détails géométriques — jusqu’où l’ADN s’étend, la longueur du guide et si un domaine auxiliaire peut achever sa coupure — déterminent si l’enzyme se cantonne à sa tâche principale ou broie aussi des brins simples voisins. Des cibles courtes laissant le R-loop non bordé, des guides standards de 20 bases et un domaine HNH actif favorisent conjointement un clivage collatéral fort ; un ADN flanquant long, des guides allongés ou un HNH inactif le suppriment. Ces connaissances offrent aux chercheurs un réglage plus précis de Cas9, les aidant à concevoir des systèmes d’édition génique plus sûrs qui évitent les dommages collatéraux indésirables, ou des essais diagnostiques plus puissants qui exploitent délibérément cette activité collatérale pour détecter de très faibles quantités de matériel viral ou génétique.
Citation: Montagud-Martínez, R., Ruiz, R., Baldanta, S. et al. CRISPR-Cas9 trans-cleavage is hindered by a flanked R-loop, an elongated spacer, and an inactive HNH domain. Nat Commun 17, 1998 (2026). https://doi.org/10.1038/s41467-026-68789-3
Mots-clés: CRISPR-Cas9, clivage collatéral, R-loop, espaceur de l ARN guide, diagnostics d acides nucléiques