Clear Sky Science · fr
Aeromonas en Asie du Sud : aperçus génomiques d’un pathogène environnemental et réservoir de résistance aux antimicrobiens
Pourquoi une bactérie de l’eau importe pour les humains et les poissons
Aeromonas est une bactérie aquatique courante, présente dans les rivières, les étangs, les lacs et même l’eau potable. Pendant des années, elle est restée dans l’ombre, éclipsée par des germes mieux connus comme la bactérie du choléra. Cette étude montre qu’Aeromonas n’est pas seulement une cause sous‑estimée de maladies chez l’homme et les animaux, mais aussi un important réservoir caché de gènes conférant une résistance aux antibiotiques essentiels. Mieux connaître ce microbe aide à comprendre comment une eau insalubre peut, silencieusement, alimenter des infections difficiles à traiter chez les personnes comme chez la vie aquatique.
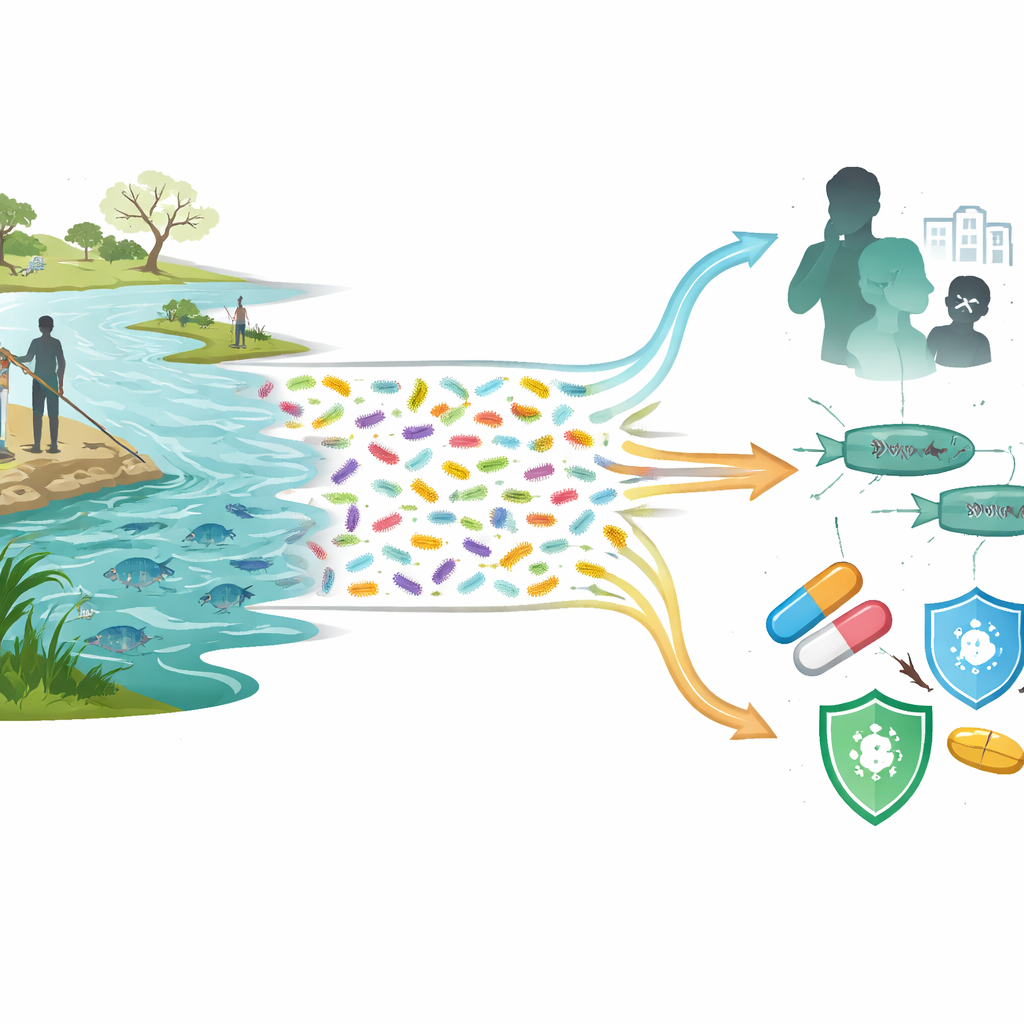
De nombreuses espèces cachées en pleine vue
Les chercheurs ont assemblé et analysé les génomes de 1 853 bactéries Aeromonas provenant du monde entier, en se concentrant sur près d’un millier d’échantillons nouvellement séquencés du Bangladesh et de l’Inde. Ces prélèvements provenaient à la fois de patients et de sources environnementales comme des rivières, étangs, caniveaux et eau potable. En comparant des milliers de gènes partagés, ils ont constaté que le genre Aeromonas est très diversifié, comptant au moins 28 espèces distinctes et plus de 900 lignées génétiques inédites. Fait important, les échantillons issus de personnes malades ne formaient pas une branche génétique séparée de ceux trouvés dans l’eau ou chez les animaux. Cela suggère que les mêmes souches circulant dans l’environnement peuvent infecter les humains de manière opportuniste, plutôt que d’appartenir à un sous‑ensemble « propre à l’homme ».
Des souches partagées entre pays et milieux
En Asie du Sud, plusieurs espèces d’Aeromonas sont réapparues à de nombreuses reprises dans des prélèvements cliniques et environnementaux. A. caviae et A. veronii étaient particulièrement fréquentes, accompagnées de A. dhakensis, A. enteropelogenes et A. hydrophila. Bien que certains schémas locaux aient émergé — par exemple A. veronii dominant les échantillons d’eau dans le nord de l’Inde et A. caviae étant plus courant dans des cas diarrhéiques au Pakistan — les mêmes espèces apparaissaient souvent dans les rivières, étangs, poissons et selles humaines. En examinant de plus près certaines espèces, l’équipe a observé que les sous‑groupes génétiques contenaient généralement un mélange d’isolats environnementaux et cliniques. Ce mélange soutient l’idée que les infections humaines sont étroitement liées à l’exposition à de l’eau contaminée plutôt qu’à une lignée spécialisée exclusivement pathogène pour l’homme.
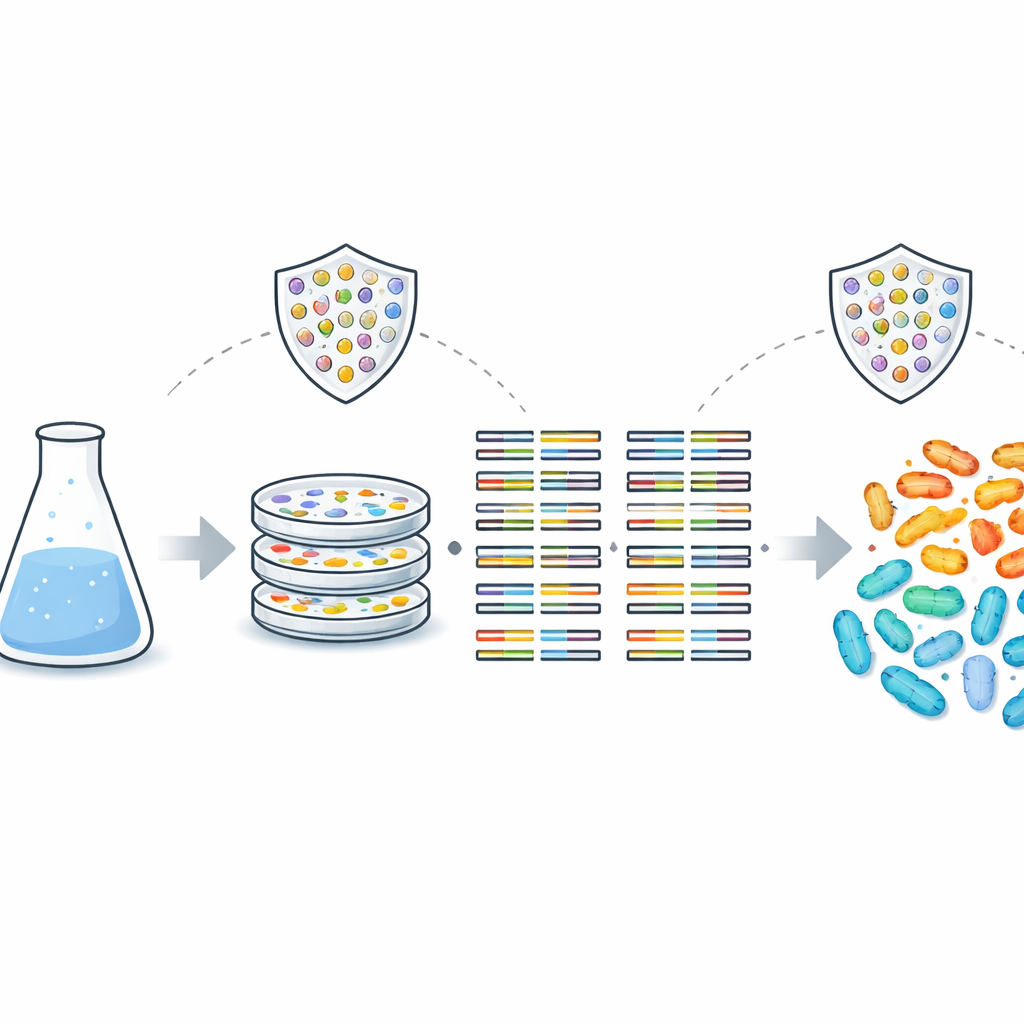
Virulence et résistance disséminées au sein du genre
Les scientifiques ont ensuite cherché à savoir si des outils génétiques spécifiques de virulence ou de résistance aux médicaments étaient associés à des contextes particuliers. Ils ont criblé chaque génome à la recherche de gènes de « virulence » connus permettant aux bactéries d’adhérer aux cellules, de former des biofilms, de se mouvoir par flagelles ou de sécréter des toxines. Ces gènes suivaient des schémas correspondant surtout à l’identité des espèces, et non à l’origine clinique ou environnementale des échantillons. Autrement dit, les souches d’origine hydrique portent déjà bon nombre des mêmes gènes liés à la maladie que les isolats cliniques. L’équipe a également répertorié 162 gènes de résistance aux antibiotiques différents, couvrant 16 classes de médicaments. Presque tous les génomes contenaient des gènes capables d’inactiver les bêta‑lactamines, un vaste groupe qui inclut de nombreux traitements de première ligne. Fait préoccupant, des gènes mobiles de résistance à la colistine — associée aux thérapies de dernier recours — ont été trouvés dans plusieurs espèces d’Aeromonas sur plusieurs continents.
L’eau comme réservoir d’infections difficiles
La comparaison des souches du Bangladesh, de l’Inde et du Pakistan a révélé des différences régionales marquées dans le mélange de gènes de résistance, mais un thème commun : les échantillons d’eau environnementale contenaient fréquemment une grande variété de facteurs de résistance, parfois plus diversifiés que ceux observés chez des souches cliniques de la même espèce. Beaucoup des mêmes gènes de résistance apparaissaient dans les deux contextes, soulignant que rivières, étangs et eaux usées peuvent servir de terrains d’entraînement où les bactéries acquièrent et échangent des défenses génétiques. Dans le même temps, les souches cliniques présentaient souvent des niveaux globaux de résistance plus élevés, reflet d’un usage intensif d’antibiotiques à l’hôpital. L’étude a aussi montré qu’Aeromonas est souvent confondu avec la bactérie du choléra lorsqu’il est cultivé sur des milieux de laboratoire standard, en particulier dans la surveillance environnementale, ce qui peut fausser les estimations de la présence de Vibrio cholerae dans les régions à risque de choléra.
Ce que cela signifie pour la santé et l’environnement
Pour un non‑spécialiste, la conclusion est que Aeromonas est une bactérie aquatique commune pouvant provoquer diarrhée et infections graves, mais son importance réelle tient peut‑être aux gènes qu’elle transporte : des éléments puissants qui réduisent l’efficacité d’antibiotiques clés. Ces gènes sont largement partagés entre les souches présentes dans les eaux de surface, les poissons et les patients humains, ce qui signifie que des voies navigables polluées peuvent discrètement accumuler et redistribuer des traits de résistance qui réapparaîtront ensuite à l’hôpital. Les auteurs soutiennent qu’Aeromonas devrait être traité comme un « sentinelle » environnemental dans la surveillance One Health — liant la santé humaine, animale et des écosystèmes — et que des outils génomiques modernes sont nécessaires pour l’identifier correctement et surveiller la propagation de la résistance aux antibiotiques dans nos systèmes hydriques.
Citation: Singh, N., Golicha, R.O., Thakur, C. et al. Aeromonas in South Asia: genomic insights into an environmental pathogen and reservoir of antimicrobial resistance. Nat Commun 17, 2214 (2026). https://doi.org/10.1038/s41467-026-68712-w
Mots-clés: Aeromonas, résistance aux antimicrobiens, bactéries d’origine hydrique, diarrhée de type choléra, One Health