Clear Sky Science · fr
Méthodes à haut débit utilisant la robotique et la vision par ordinateur pour le développement de cocktails phagiques thérapeutiques
Pourquoi cela compte pour les infections courantes
La résistance aux antibiotiques transforme des infections autrefois routinières, comme les infections des voies urinaires (IVU), en problèmes tenaces et parfois mortels. Cette étude décrit comment des scientifiques exploitent des robots, des caméras et l’analyse de données pour concevoir des médicaments à base de virus, appelés cocktails de phages, capables d’attaquer spécifiquement les bactéries résistantes responsables des IVU. Le travail montre comment un laboratoire automatisé de type industriel peut trier un très grand nombre d’associations virus–bactérie pour concevoir un traitement prêt à l’emploi qui fonctionne pour la plupart des patients.
Transformer une infection courante en cas d’étude
Les IVU font partie des raisons les plus fréquentes pour lesquelles les gens reçoivent des antibiotiques, en particulier les femmes, dont beaucoup souffrent d’infections répétées. Le principal responsable est une forme d’E. coli qui est devenue de plus en plus résistante aux médicaments standards. Les antibiotiques traditionnels agissent de manière large et peuvent perturber les microbes utiles de l’organisme, tout en poussant les bactéries à développer des résistances. Les phages — des virus qui infectent les bactéries — offrent une option plus ciblée, mais chaque phage tend à attaquer seulement certaines souches bactériennes. Le défi consiste à trouver le bon mélange de phages qui, ensemble, peuvent gérer la diversité réelle des E. coli responsables d’IVU.
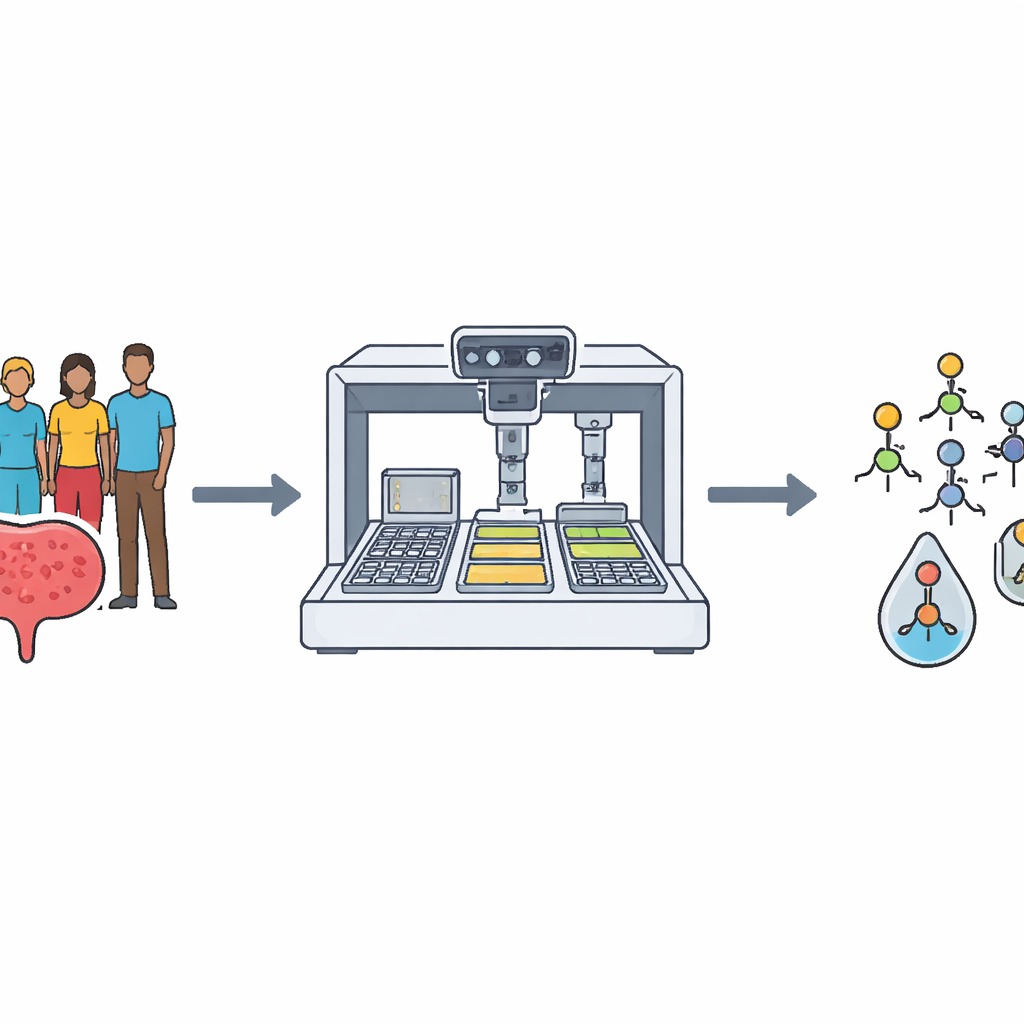
Constituer une bibliothèque réaliste de bactéries problématiques
L’équipe a d’abord constitué un large et divers panel de souches d’E. coli responsables d’IVU afin de refléter ce qui est observé en clinique. À partir d’environ 1 700 isolats collectés auprès de patients et de sources commerciales, et guidée par des données génétiques provenant d’environ 10 000 génomes d’E. coli disponibles publiquement, elle a sélectionné 356 souches pour un « Clinical Panel ». Ces souches couvraient les principales lignées génétiques, provenaient de patients de 39 États américains et incluaient de nombreuses souches résistantes à plusieurs classes d’antibiotiques. Chaque souche a été soigneusement cultivée, portionnée, barcodée et stockée dans des congélateurs automatisés pour que des robots puissent les prélever de manière répétée et fiable pour les essais.
Des robots et des caméras à la recherche du meilleur mélange de virus
Puis les chercheurs se sont tournés vers l’autre côté de l’équation : les phages. Ils ont collecté plus d’un millier d’échantillons environnementaux, principalement des eaux usées, et ont utilisé leur Clinical Panel pour identifier 1 143 phages ciblant E. coli, dont 421 sont devenus les principaux outils de travail. Une plateforme robotique sur mesure a utilisé des pipettes multi-canaux, des incubateurs et des lecteurs de plaques pour mélanger bactéries, phages et milieux de culture dans de minuscules puits et suivre la croissance bactérienne sur 20 heures. En comparant la croissance des puits traités par des phages à des témoins non traités, le système mesurait l’efficacité de chaque phage — ou combinaison de phages — à supprimer la croissance bactérienne. Progressivement, cela a produit environ 1,5 million de courbes de croissance et plus de 3,8 millions d’enregistrements réactionnels phage–bactérie, qui ont alimenté un modèle de prédiction de cocktails suggérant de nouvelles combinaisons prometteuses à tester.
Laisser la vision par ordinateur compter les survivants
Les lectures optiques rendent compte de la turbidité globale mais détectent difficilement quand seul un petit nombre de bactéries subsiste. Pour quantifier une élimination en profondeur, l’équipe a ajouté un second test automatisé. Des robots ont dilué les échantillons, les ont déposés sur des milieux gélosés et les ont incubés afin que les rares bactéries survivantes forment des colonies visibles. Des caméras haute résolution ont ensuite photographié les boîtes. Une chaîne d’analyse d’images personnalisée a utilisé trois algorithmes différents pour compter les colonies et les zones claires induites par les phages, recoupant les résultats et signalant les désaccords pour révision humaine. Sur plus de deux millions de dépôts, le système automatisé a égalé ou dépassé la précision d’analystes entraînés tout en opérant à une bien plus grande échelle, fournissant des comptes fiables de bactéries vivantes et de particules phagiques.
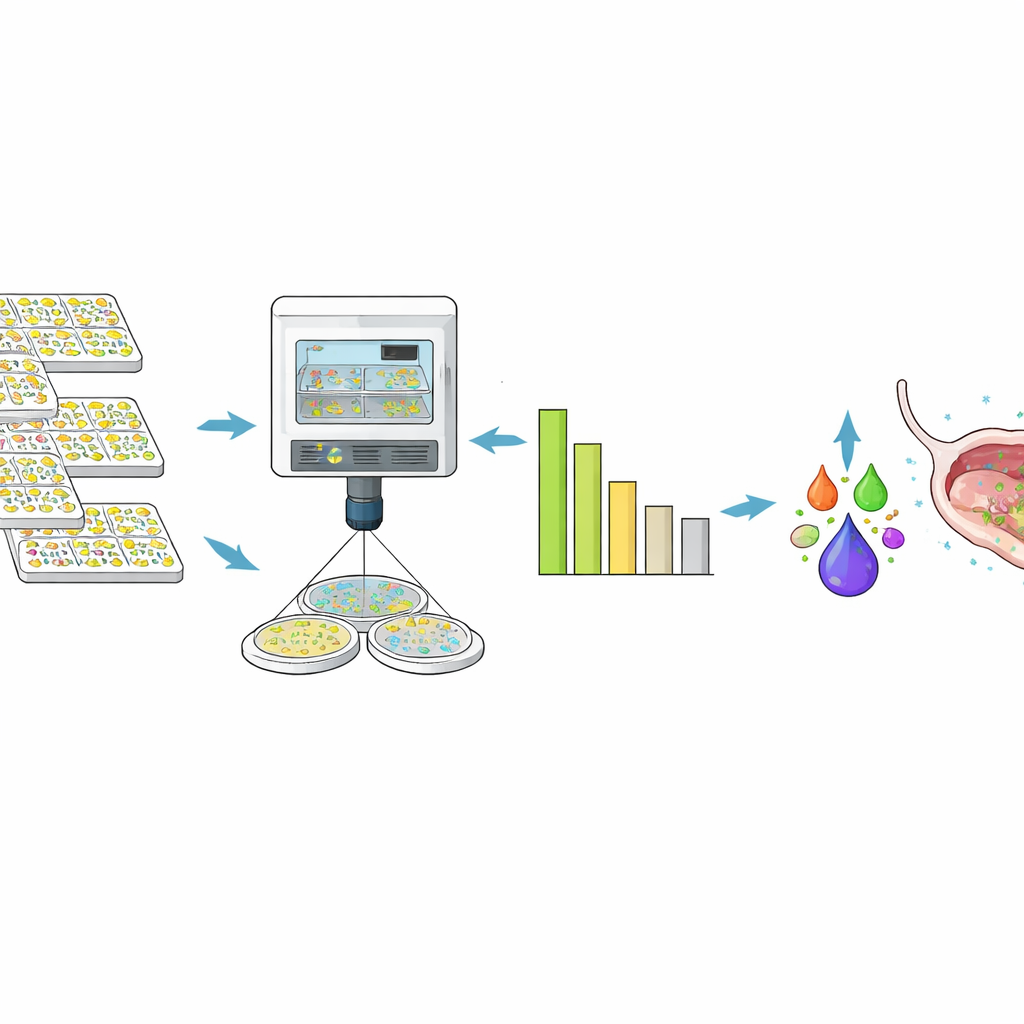
De millions de tests à un cocktail puissant
En utilisant ces tests à haut débit et ces outils de prédiction, les chercheurs ont réduit des milliers de possibilités à un cocktail de six phages, LBP-EC01. Fabriqué selon des conditions pharmaceutiques, ce cocktail a montré une activité en laboratoire contre 96,4 % des 356 souches du Clinical Panel et a réduit le nombre de bactéries d’au moins 100 000 fois dans la majorité des cas. Lorsque l’équipe a testé des isolats d’E. coli issus de la première partie d’un essai clinique de phase 2 en cours chez des femmes atteintes d’IVU aiguës, 97 % des souches uniques étaient sensibles au cocktail, et le profil d’activité correspondait étroitement à celui observé dans le panel préconstruit. Fait important, ils n’ont trouvé aucune preuve que les bactéries des patientes aient développé une résistance génétique aux phages pendant la période suivie.
Ce que cela signifie pour les traitements futurs
En résumé, ce travail montre que l’automatisation et l’imagerie soigneusement conçues peuvent réduire l’incertitude de la thérapie par phages. En associant des collections réalistes de bactéries de patients à des tests robotisés et à la vision par ordinateur, les chercheurs ont créé un cocktail de phages à large spectre qui reste efficace contre des isolats cliniques du monde réel. Bien que des essais plus larges soient nécessaires pour confirmer des bénéfices cliniques, l’approche propose une feuille de route pour développer des médicaments phagiques fixes et évolutifs destinés à lutter contre les infections multirésistantes et à réduire la dépendance aux antibiotiques traditionnels.
Citation: Penke, T.J.R., Hammack, A.T., McMillan, L.J. et al. High-throughput methods leveraging robotics and computer vision for the development of therapeutic phage cocktails. Nat Commun 17, 2192 (2026). https://doi.org/10.1038/s41467-026-68684-x
Mots-clés: thérapie par phages, infection des voies urinaires, résistance aux antibiotiques, automatisation de laboratoire, vision par ordinateur