Clear Sky Science · fr
Une analyse génomique multicentrique souligne la propagation régionale du choléra en Afrique
Pourquoi il est important de suivre les micro-organismes au-delà des frontières
Le choléra continue de rendre malade et de tuer des dizaines de milliers de personnes chaque année en Afrique, et pourtant des questions fondamentales subsistent sur la façon dont les épidémies démarrent, se propagent entre pays et réapparaissent. Cette étude rassemble des scientifiques et des équipes de santé publique de sept pays africains pour suivre la bactérie responsable du choléra en lisant son code génétique. En comparant des centaines de génomes bactériens, les chercheurs montrent comment les vagues récentes de choléra ont franchi les frontières, quels types de souches circulent où, et comment ces connaissances peuvent affiner les efforts pour prévenir de futures épidémies.
Regarder le choléra à l’échelle du continent
Pour dépasser les rapports de cas épars, les Centres africains de contrôle et de prévention des maladies ont lancé une collaboration appelée le Consortium de génomique du choléra en Afrique (CholGEN). Des laboratoires au Cameroun, en République démocratique du Congo, au Malawi, au Mozambique, au Nigeria, en Ouganda et en Zambie ont séquencé 763 génomes de haute qualité du Vibrio cholerae O1, principalement entre 2019 et 2024. Il s’agit du plus grand ensemble de génomes de choléra jamais généré au sein même de l’Afrique. En plaçant ces nouveaux génomes aux côtés d’environ 1 800 échantillons séquencés auparavant provenant d’Afrique et d’Asie, l’équipe a pu reconstruire comment les récentes épidémies africaines s’inscrivent dans la pandémie mondiale de choléra qui dure depuis longtemps.
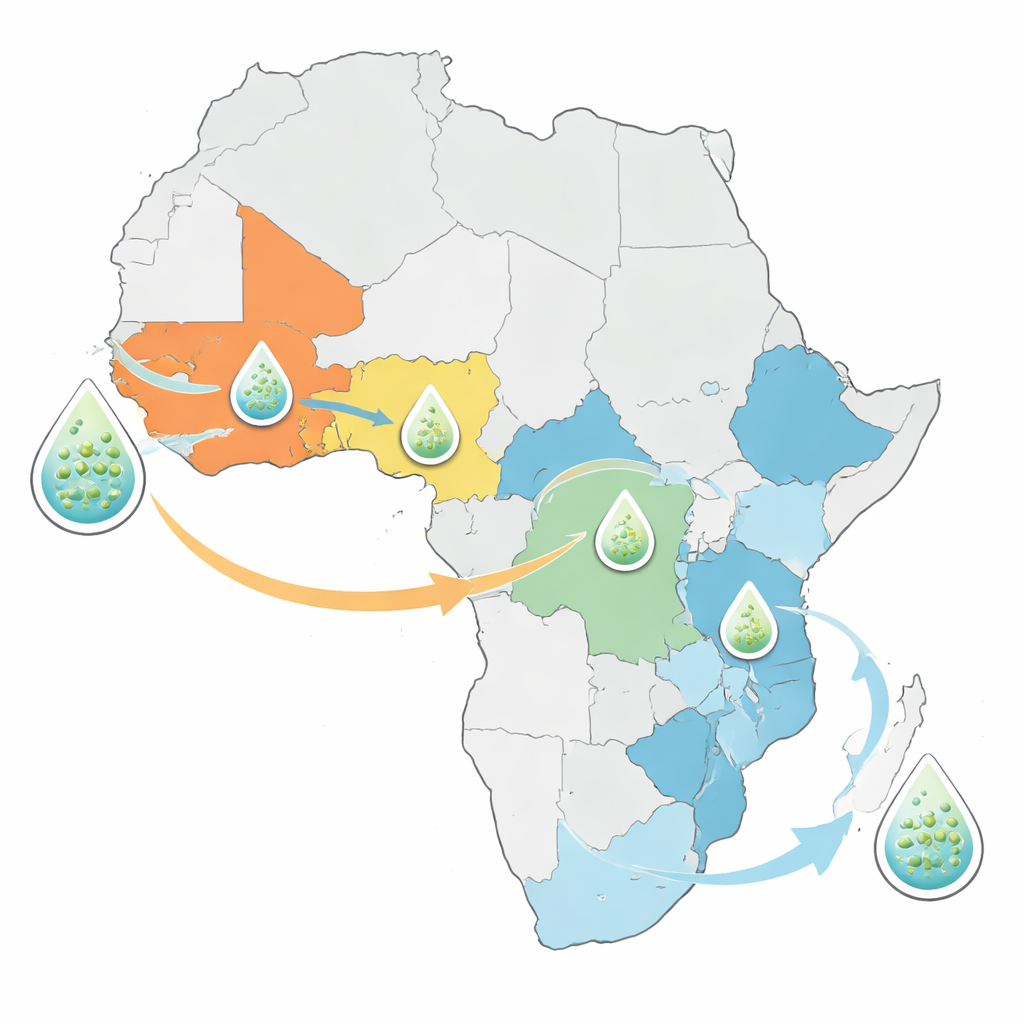
Anciennes souches, nouvelles routes
L’analyse montre que les souches de choléra responsables des épidémies actuelles en Afrique ne constituent pas une menace entièrement nouvelle. Au contraire, toutes les bactéries récemment séquencées descendent d’introductions connues de la lignée de la septième pandémie qui a atteint l’Afrique depuis l’Asie en 1970. Les pays d’Afrique de l’Ouest et d’Afrique centrale, comme le Nigeria, le Cameroun et la République démocratique du Congo, sont souvent dominés par une ou deux lignées persistantes depuis des décennies. Les pays d’Afrique de l’Est et d’Afrique australe présentent, en revanche, un mélange de plusieurs lignées simultanément. Une lignée en particulier, désignée AFR15, s’est propagée rapidement ces dernières années et est liée à des flambées exceptionnellement importantes au Malawi, en Zambie et dans les pays voisins, ainsi qu’à des épidémies dans certaines régions du Moyen-Orient et de l’Asie du Sud.
La taille des épidémies n’est pas dictée par les gènes
On pourrait supposer que la propagation explosive d’AFR15 tient à des changements génétiques majeurs qui la rendent plus virulente ou plus apte à échapper aux traitements. Toutefois, lorsque les chercheurs ont comparé le rythme et le type de mutations entre plusieurs lignées actives, ils n’ont pas trouvé de différences marquantes. Les bactéries évoluaient à des vitesses similaires, et les types de mutations ainsi que les gènes affectés se ressemblaient d’une lignée à l’autre. Les profils globaux de gènes de résistance aux antibiotiques sont également restés majoritairement stables dans le temps et entre pays. L’exception principale concerne l’Ouganda, où les bactéries ont acquis un grand élément d’ADN mobile appelé plasmide, portant plusieurs gènes de résistance, probablement importé avec des souches liées à des épidémies au Yémen et au Liban. Même dans ce cas, l’étude n’a pas identifié de nouveaux gènes pouvant, à eux seuls, expliquer la gravité des récentes épidémies africaines.
Parcours cachés révélés par un meilleur échantillonnage
Parce que les génomes bactériens portent la trace des lieux où des souches apparentées ont été trouvées, l’équipe a pu déduire la fréquence des traversées de frontières par le choléra. Ils ont détecté de nombreux exemples de propagation internationale entre pays voisins, notamment des échanges répétés entre la Zambie et la République démocratique du Congo. Mais en regardant de plus près, ils ont constaté que les signaux statistiques de sauts transfrontaliers étaient les plus forts dans les années et les lieux où l’échantillonnage était intensif. Cela suggère que les déplacements réels du choléra sont plus fréquents que ce que révèlent les données actuelles ; de nombreux événements de transmission passent probablement inaperçus simplement parce que personne ne séquence les bactéries dans ces lieux ou à ces moments. Pour y remédier, les auteurs ont développé un cadre permettant d’estimer la quantité d’information nouvelle qu’un pays gagne en séquençant des échantillons supplémentaires, en équilibrant diversité génétique, nombre d’introductions et données existantes.
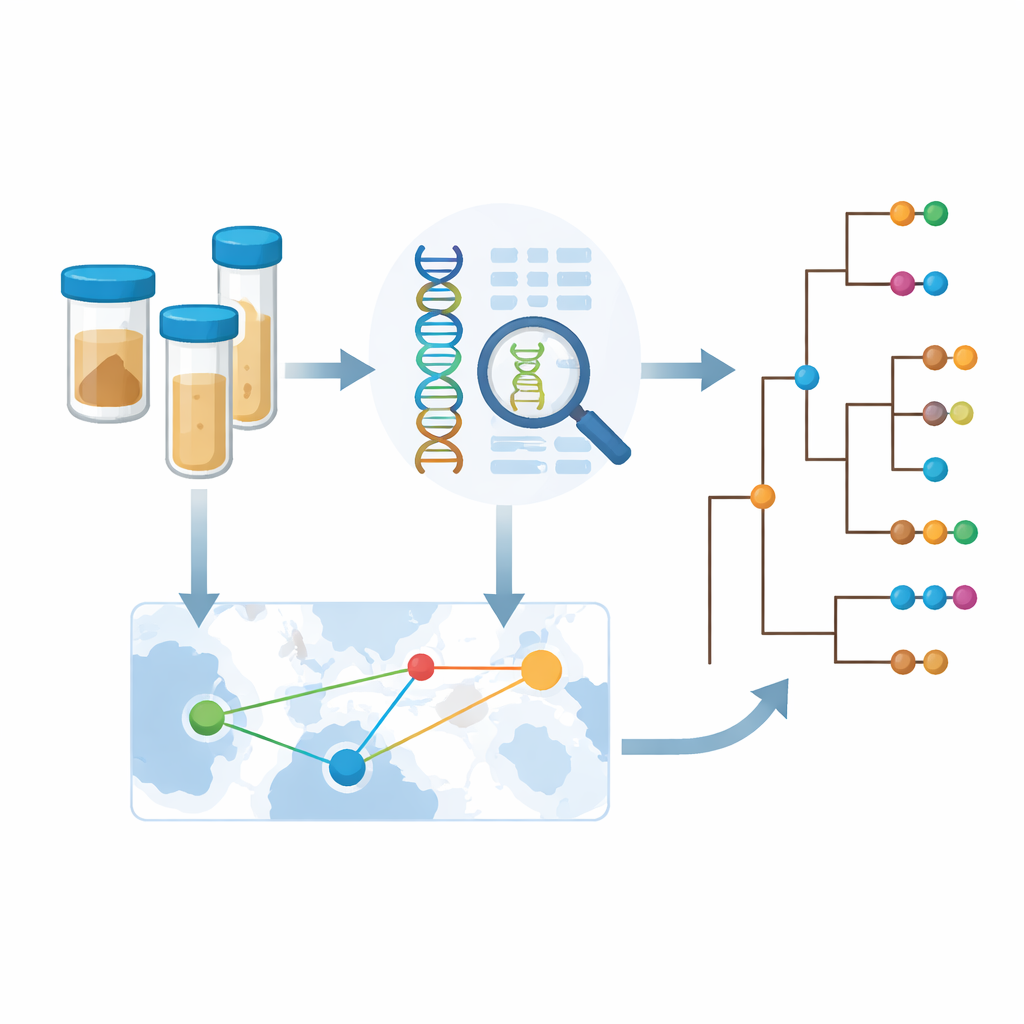
Utiliser la génomique pour orienter des mesures de contrôle plus intelligentes
Les auteurs concluent que, pour le choléra en Afrique aujourd’hui, la façon et les lieux de propagation importent davantage que tout changement spectaculaire de la bactérie elle-même. Les résultats plaident pour une surveillance génomique de routine, coordonnée au niveau régional, afin que les pays voisins puissent détecter rapidement les épidémies partagées, en tracer les sources et cibler plus efficacement des interventions telles que les campagnes de vaccination, les améliorations de l’eau et de l’assainissement, et les actions dans les zones frontalières. En développant la capacité de séquençage au sein des laboratoires de santé publique africains et en partageant les données au-delà des frontières, des initiatives comme CholGEN offrent une feuille de route pratique pour utiliser la génétique moderne et se rapprocher de l’objectif ambitieux d’éliminer le choléra comme menace pour la santé publique d’ici 2030.
Citation: Mboowa, G., Matteson, N.L., Tanui, C.K. et al. Multicountry genomic analysis underscores regional cholera spread in Africa. Nat Commun 17, 2539 (2026). https://doi.org/10.1038/s41467-026-68642-7
Mots-clés: choléra, surveillance génomique, Afrique, transmission transfrontalière, résistance aux antimicrobiens