Clear Sky Science · fr
Estimation de la stabilité du repliement des protéines avec prise en compte explicite des états dépliés
Pourquoi la stabilité des protéines compte
Chaque protéine de votre organisme est une minuscule machine moléculaire qui doit se replier en une forme tridimensionnelle précise pour fonctionner correctement. Si ce repli est trop fragile, la protéine peut mal fonctionner, s’agréger ou ne pas être produite du tout — des problèmes associés à des maladies et aux échecs dans la mise au point de médicaments et d’enzymes à base de protéines. Mesurer la stabilité d’une protéine en laboratoire est lent et délicat, aussi les chercheurs cherchent-ils des méthodes informatiques capables de dire, à partir de la seule séquence, à quel point une protéine se dépliera facilement.
Un regard renouvelé sur les états repliés et dépliés
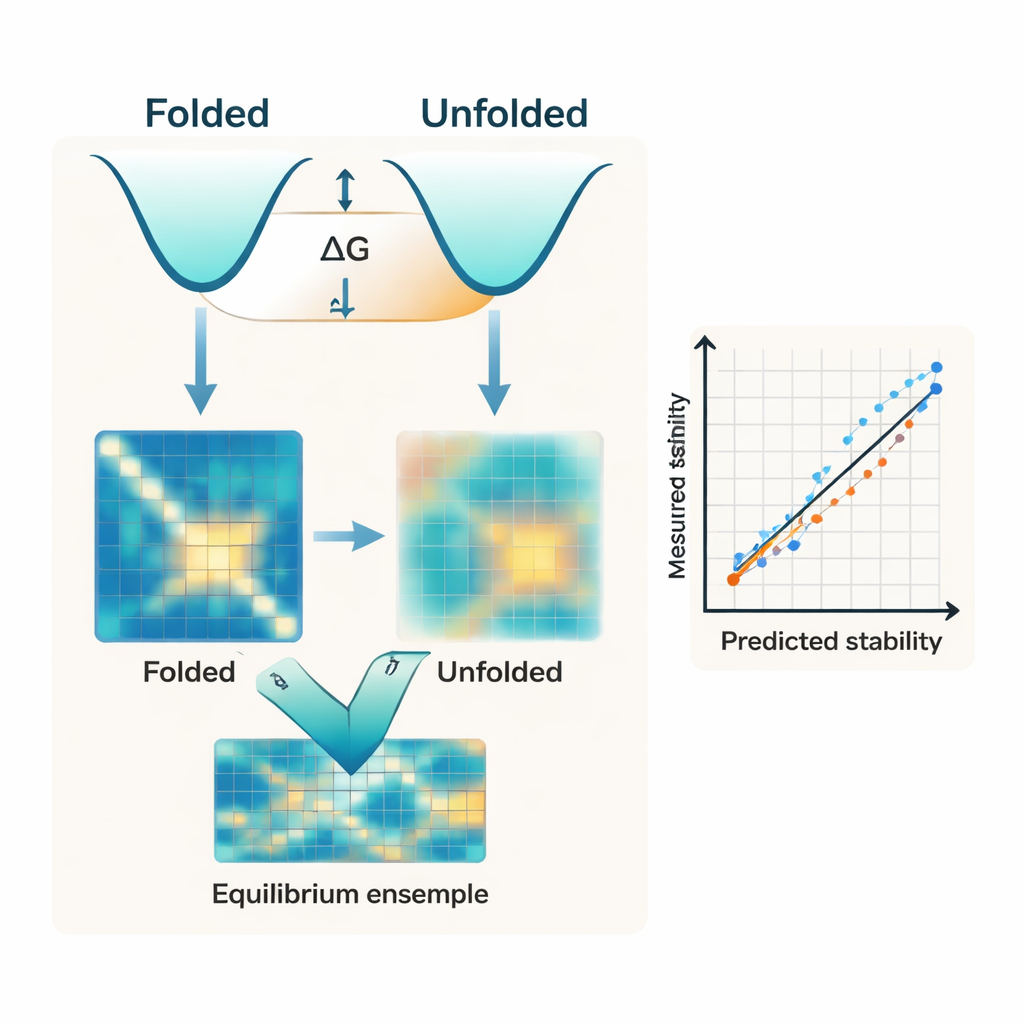
La plupart des algorithmes modernes se concentrent presque entièrement sur la forme repliée d’une protéine. Ils partent souvent d’une structure prédite par IA, comme celles d’AlphaFold, et traitent cette unique structure comme le principal déterminant de la stabilité. Or la stabilité est en réalité le gap énergétique entre deux grands ensembles : l’état compact replié et les nombreuses conformations lâches qui composent l’état déplié. Les auteurs soutiennent que l’ignorance du côté déplié de cet équilibre est une des raisons majeures pour lesquelles les outils existants peinent à reproduire les mesures expérimentales de l’énergie libre de repliement, connue sous le nom de ΔG.
Un nouveau modèle qui apprend les deux états
Les chercheurs présentent IFUM, un système d’apprentissage profond conçu pour estimer ΔG tout en apprenant également l’équilibre entre états repliés et dépliés pour chaque protéine. Plutôt que de traiter l’état déplié comme un arrière‑plan vague, IFUM utilise des idées de la physique des polymères pour le représenter comme une « bobine aléatoire » et encode les états replié et déplié sous forme de cartes de distances entre paires d’acides aminés. Le modèle intègre des informations provenant de réseaux de séquence et de structure préentraînés puissants, puis prédit conjointement la stabilité totale et une carte de probabilité décrivant la fraction de la population protéique repliée versus dépliée pour chaque paire de résidus. L’entraînement sur un très grand jeu de données composé de petites protéines caractérisées expérimentalement et de protéines désordonnées connues permet à IFUM de reconnaître à la fois les séquences bien structurées et celles plus flexibles.
De meilleurs chiffres et une couverture plus large des mutations
Testé sur un jeu de données soigneusement contrôlé de petites protéines, IFUM prédit les valeurs expérimentales de ΔG avec une erreur plus faible et une corrélation plus élevée que les méthodes IA précédentes qui ne se basent que sur la structure repliée ou sur des modèles de langage entraînés sur des séquences. Fait crucial, le modèle gère aussi une grande variété de modifications de séquence. Il capture avec précision les effets de mutations ponctuelles simples et doubles, ainsi que des insertions et suppressions modifiant la longueur de la protéine — des situations où de nombreux outils existants échouent complètement ou n’ont tout simplement pas été conçus pour opérer. Une comparaison interne montre que la suppression de l’objectif lié à l’état déplié dégrade sensiblement les performances, soulignant que modéliser explicitement l’ensemble déplié n’est pas qu’un détail conceptuel mais central pour l’exactitude des prédictions.
Du banc de conception aux tests en conditions réelles
Pour vérifier si IFUM peut guider l’ingénierie protéique pratique, les auteurs l’appliquent à trois problèmes de conception exigeants : stabiliser des interférons‑lambda, remodeler la protéine de signalisation immunitaire IL‑10 et améliorer une enzyme modifiant des sucres appelée UGT76G1. Dans les trois cas, les stabilities prédites par IFUM suivent bien les températures de dénaturation mesurées, qui indiquent la quantité de chaleur qu’une protéine peut supporter avant de se déplier. Le modèle aide aussi à filtrer des centaines de protéines entièrement nouvelles conçues par ordinateur pour sélectionner celles les plus susceptibles de se replier et de rester solubles dans les cellules, surpassant les scores de confiance couramment utilisés issus des réseaux de prédiction de structure. Ces résultats suggèrent qu’IFUM peut servir de « filtre de stabilité » pratique en complément des contrôles basés sur la structure dans les flux de travail modernes de conception de protéines.
Limites et pistes futures
Comme tout modèle, IFUM a des limites. Il est principalement entraîné sur de petites protéines solubles mono‑chaîne, et ses chiffres absolus de stabilité deviennent moins fiables pour des protéines beaucoup plus grandes ou présentant de longs boucles flexibles ou des régions transmembranaires. Sa description de l’état déplié reste un modèle statistique simplifié plutôt qu’un tableau entièrement réaliste de toutes les conformations possibles. Néanmoins, l’approche montre que former une IA à considérer conjointement les ensembles repliés et dépliés fournit des estimations de stabilité plus fiables. Pour les non‑spécialistes, la conclusion essentielle est qu’IFUM nous rapproche de la possibilité de demander à un ordinateur, avec une confiance quantitative, « Ce design de protéine tiendra‑t‑il réellement ? », accélérant potentiellement le développement de médicaments biologiques plus sûrs et d’enzymes industrielles plus robustes.
Citation: Lee, H., Cho, Y., Yun, J. et al. Protein folding stability estimation with explicit consideration of unfolded states. Nat Commun 17, 1883 (2026). https://doi.org/10.1038/s41467-026-68637-4
Mots-clés: stabilité des protéines, repliement des protéines, apprentissage profond, conception de protéines, mutations