Clear Sky Science · fr
Découverte à l’échelle du génome et phénotypage des transcrits non codants chez A. fumigatus révèle des lncARN impliqués dans la sensibilité aux antifongiques
Pourquoi un moisissure chez nous compte
La plupart d’entre nous perçoivent la moisissure comme une nuisance sur le pain ou dans les coins humides, mais une moisissure courante, Aspergillus fumigatus, est responsable de plus de deux millions de décès chaque année — plus que le paludisme et le VIH réunis. Les médecins disposent d’un arsenal limité d’antifongiques pour contenir ce pathogène, et la résistance à ces médicaments augmente rapidement. Cette étude explore une couche cachée du génome du champignon — les ARN longs non codants, ou lncARN — qui ne codent pas de protéines mais peuvent néanmoins influencer la réponse du champignon au traitement. Comprendre ces éléments génétiques « silencieux » pourrait ouvrir de nouvelles voies pour prédire, surveiller et éventuellement contrer la résistance aux antifongiques.
Messages cachés dans l’ADN fongique
Classiquement, on a considéré les gènes comme des segments d’ADN codant pour des protéines, les ouvriers de la cellule. Au cours de la dernière décennie, les chercheurs ont découvert que de vastes régions du génome sont transcrites en molécules d’ARN qui ne deviennent jamais des protéines. Ces ARN longs non codants peuvent cependant influencer le comportement des cellules, y compris leur réponse aux médicaments. Alors que les lncARN ont été cartographiés chez l’humain et chez la levure, ils restaient en grande partie inexplorés chez des moisissures pathogènes comme A. fumigatus. Les auteurs ont entrepris de changer cela en établissant un catalogue à l’échelle du génome de ces transcrits mystérieux et en demandant si l’un d’eux pouvait faire basculer l’équilibre entre sensibilité et résistance aux médicaments.
À l’écoute du champignon sous attaque médicamenteuse
Pour découvrir les lncARN, l’équipe a exposé A. fumigatus à six composés antifongiques différents, y compris des azolés largement utilisés qui ciblent la membrane cellulaire fongique, puis a séquencé tous les ARN produits. À l’aide d’un pipeline bioinformatique personnalisé, ils ont assemblé des dizaines de milliers de transcrits et ont systématiquement éliminé tout ce correspondant à des gènes codant pour des protéines connus ou à de courts ARN ménagers. Après plusieurs séries de filtrages et une curation manuelle, ils ont obtenu un jeu fiable de 1 089 nouveaux ARN longs non codants répartis dans le génome. La plupart se situaient entre des gènes connus ou les chevauchaient en sens opposé, et ensemble ils ont étendu la fraction du génome fongique connue pour être activement transcrite d’environ deux tiers à plus de quatre cinquièmes.
Réponses coordonnées et points chauds conservés
Quand les chercheurs ont comparé la manière dont ces lncARN variaient selon les doses de médicament, ils ont constaté que le champignon ne les mobilise pas au hasard. Les lncARN s’organisent plutôt en une quinzaine de schémas de réponse distincts, certains partagés par plusieurs médicaments et d’autres propres à un traitement particulier. Par exemple, des médicaments ciblant des voies biochimiques similaires avaient tendance à déclencher des signatures de lncARN qui se chevauchent, tandis qu’un inhibiteur de la synthèse protéique produisait de nombreuses réponses uniques. De nombreux lncARN se trouvaient très proches de gènes déjà connus pour influencer la sensibilité aux azolés, tels que ceux impliqués dans la capture du fer ou la biosynthèse de l’ergostérol, un composant clé des membranes fongiques. Dans plusieurs cas, un lncARN voisin et un gène de réponse médicamenteuse étaient activés ou réprimés conjointement, ce qui suggère que ces éléments non codants peuvent aider à coordonner des programmes de survie cruciaux.
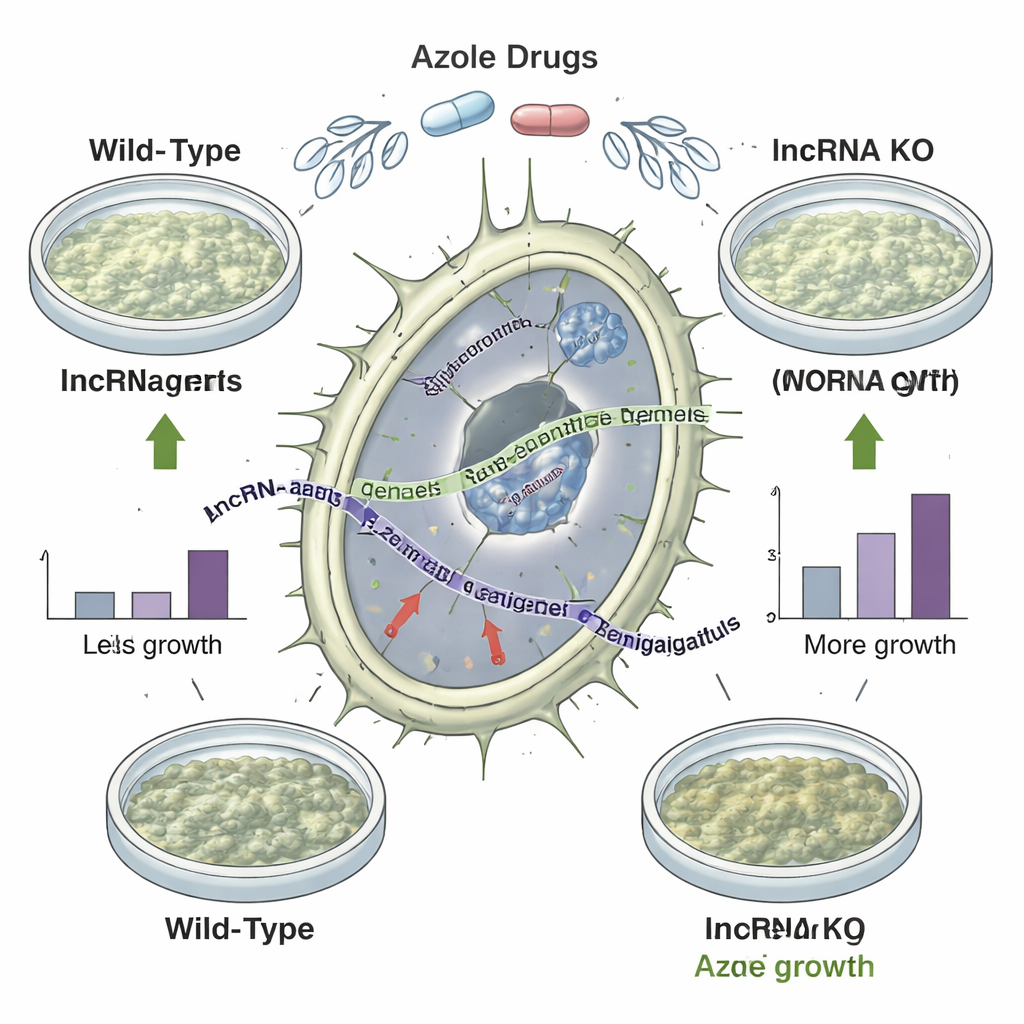
Supprimer des « gènes silencieux » modifie la sensibilité aux médicaments
Cataloguer les lncARN, c’est une chose ; prouver qu’ils ont un effet en est une autre. L’équipe a supprimé 92 régions lncARN sélectionnées du génome fongique et a comparé la croissance des mutants sous une série de stress, y compris température élevée, faible teneur en fer et exposition à trois azolés différents. Soixante mutants ont montré des changements de forme physique spécifiques à certaines conditions, et 35 ont en fait mieux poussé que la souche d’origine lorsqu’on les a exposés aux azolés. Une souche de délétion remarquable présentait une croissance améliorée face à tous les azolés testés sans simplement augmenter l’expression des gènes codant pour des protéines à proximité, suggérant fortement que le lncARN manquant freinait lui‑même la tolérance aux médicaments. En examinant de nombreux isolats cliniques et environnementaux avec des profils de sensibilité connus, les auteurs ont aussi trouvé que la présence ou l’absence de certains gènes lncARN corrélait avec la facilité d’inhibition de chaque souche par les azolés.
Ce que cela signifie pour la lutte contre les infections fongiques mortelles
Pour les non‑spécialistes, le message principal est que des parties du génome fongique autrefois qualifiées de « poubelle » façonnent activement le degré de dangerosité de A. fumigatus et l’efficacité de nos médicaments contre lui. En établissant la première cartographie complète des ARN longs non codants de ce pathogène majeur et en reliant des dizaines d’entre eux à des changements mesurables de la réponse médicamenteuse, ce travail ouvre une nouvelle classe de marqueurs génétiques et de cibles potentielles. À long terme, les lncARN pourraient aider à expliquer pourquoi certaines souches sont naturellement plus difficiles à traiter, orienter la conception de diagnostics plus efficaces et inspirer des thérapies qui désarment la résistance non pas en tuant directement le champignon, mais en silencant les régulateurs « silencieux » qui l’aident à survivre.
Citation: Weaver, D., Qi, T., Chown, H. et al. Genome-wide discovery and phenotyping of non-coding transcripts in A. fumigatus reveals lncRNAs with a role in antifungal drug sensitivity. Nat Commun 17, 1832 (2026). https://doi.org/10.1038/s41467-026-68543-9
Mots-clés: Aspergillus fumigatus, résistance aux antifongiques, ARN longs non codants, médicaments azolés, génomique fongique