Clear Sky Science · fr
Af-CUT&Tag : une méthode sensible et sans anticorps pour le profilage de la chromatine utilisant des étiquettes génétiquement codées et des liaisons à haute affinité fusionnées à Tn5
Un coup d’œil dans notre salle de contrôle de l’ADN
Chaque cellule de votre corps décide en permanence quels gènes activer ou réprimer, influençant tout, de la réparation du foie au risque de cancer. Les scientifiques étudient ces décisions en cartographiant où des protéines clés se placent sur notre ADN, mais les meilleurs outils pour cela reposent depuis longtemps sur des anticorps fragiles et coûteux qui ne fonctionnent pas toujours bien. Cet article présente une nouvelle méthode sans anticorps pour dresser ces interactions ADN–protéine, nommée Af-CUT&Tag, qui est plus sensible, plus fiable et suffisamment puissante pour fonctionner sur de petits échantillons et même des cellules individuelles.
Pourquoi les anticorps nous freinent
Les méthodes classiques de cartographie de la chromatine nécessitent des anticorps — de grosses protéines en forme de Y qui reconnaissent une protéine cible spécifique — pour guider une enzyme vers les bons endroits sur l’ADN. Quand les anticorps sont parfaits, ils permettent de voir où facteurs de transcription et autres régulateurs sont fixés sur le génome. Mais en pratique, les anticorps peuvent être difficiles à obtenir, de qualité variable, et leur liaison peut être gênée par des modifications chimiques courantes des protéines, comme la phosphorylation ou l’acétylation. Ces problèmes peuvent brouiller les cartes obtenues, limiter les protéines étudiables et rendre les comparaisons entre laboratoires ou expériences difficiles.
De petites étiquettes et des liaisons intelligentes remplacent les anticorps
Af-CUT&Tag évite complètement les anticorps en donnant à la protéine d’intérêt une toute petite étiquette génétique. À l’aide de l’édition génomique CRISPR, les chercheurs fusionnent de courts peptides-étiquettes, tels que HiBiT ou ALFA, à la protéine naturelle dans les cellules ou les tissus. Ils utilisent ensuite des protéines partenaires conçues — des liaisons à haute affinité qui reconnaissent ces étiquettes — directement fusionnées à l’enzyme Tn5, qui coupe l’ADN et y ajoute des adaptateurs de séquençage. Lorsque la fusion liaison–Tn5 se fixe sur l’étiquette de la protéine d’intérêt, elle coupe l’ADN à proximité et marque ces sites pour le séquençage. Comme les étiquettes sont très petites et que la fusion liaison–Tn5 est bien plus compacte qu’un anticorps, ce système pénètre facilement dans les cellules et les noyaux, se lie avec une précision exceptionnelle et n’est pas perturbé par les modifications chimiques de la protéine cible. 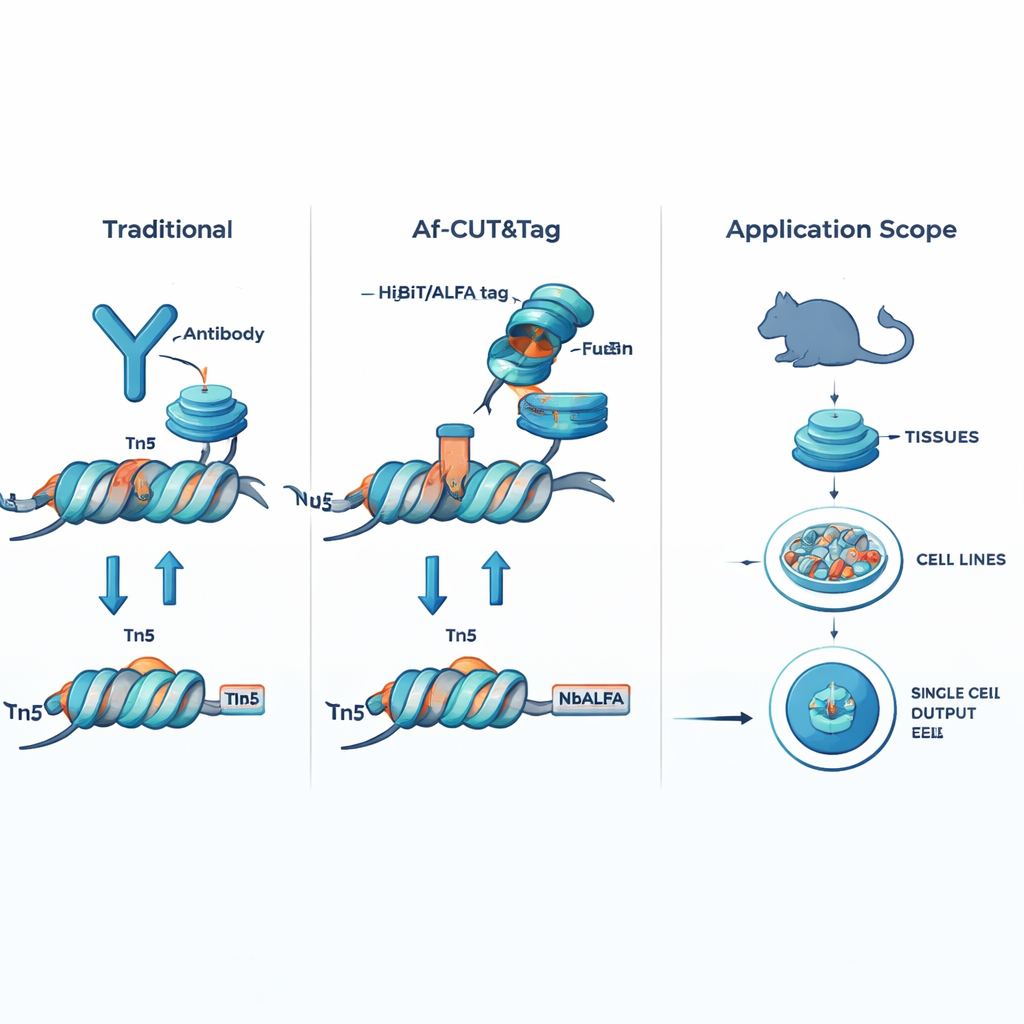
Des cartes plus nettes à partir de moins de cellules
L’équipe a d’abord montré que leurs fusions liaison–Tn5 saisissent toujours les étiquettes avec une grande affinité et coupent efficacement l’ADN. Ils ont ensuite comparé Af-CUT&Tag aux méthodes à base d’anticorps de pointe pour cartographier l’ARN polymérase II, l’enzyme qui lit les gènes codant pour des protéines, et la protéine CTCF, un grand organisateur de la structure du génome. Dans des lignées cellulaires humaines, Af-CUT&Tag a produit un signal plus propre aux points de départ des gènes, moins de coupures hors cible dans des régions d’ADN ouvertes mais non pertinentes, et des bibliothèques de séquençage de meilleure qualité. De façon remarquable, elle a généré des cartes robustes à partir d’à peine ~500 cellules, et la même stratégie peut être adaptée à de nombreux liaisons différents ciblant des caractéristiques distinctes de l’ADN. La méthode a également été étendue aux cellules uniques en indexant les fragments de chaque cellule, permettant la construction de cartes détaillées, cellule par cellule, de la chromatine.
Suivre la réparation du foie en temps réel
Pour montrer ce que cette technologie peut révéler chez des animaux vivants, les auteurs ont appliqué Af-CUT&Tag à la régénération hépatique de souris. Ils ont utilisé des virus et CRISPR pour ajouter des étiquettes HiBiT à deux régulateurs clés de la voie Hippo, YAP1 et TAZ, qui contribuent à contrôler la taille des organes et la réparation. Après ablation partielle du foie, ils ont isolé des noyaux de cellules hépatiques avant l’intervention et 24 heures après, puis utilisé Af-CUT&Tag pour voir où YAP1 et TAZ se fixaient sur le génome. Les cartes ont montré qu’au début après la lésion, ces protéines réduisent leur présence sur les gènes qui pilotent le métabolisme et la synthèse des lipides, tandis que les cellules du foie accumulent temporairement des gouttelettes de graisse. En parallèle, YAP1/TAZ augmentent leur liaison sur des gènes impliqués dans l’élimination de l’hème, un composant potentiellement toxique du sang, et sur Mir122, un gène qui produit un microARN fortement enrichi dans le foie.
miR-122, gardien de la régénération
miR-122 est un petit ARN qui aide à régler finement l’activité de nombreux autres gènes. Avec Af-CUT&Tag, les chercheurs ont observé un renforcement de la liaison YAP1/TAZ près de la région Mir122, associé à une chromatine plus ouverte et à des marques chimiques accrues liées à l’activation génique. Des expériences ont confirmé que les niveaux de miR-122 augmentent durant la fenêtre précoce de régénération. Quand l’équipe a spécifiquement supprimé miR-122 dans les cellules hépatiques de souris, les animaux ont présenté davantage d’accumulation lipidique, des réponses inflammatoires plus fortes et moins de cellules hépatiques entrant dans le cycle cellulaire après la chirurgie. Ensemble, ces résultats suggèrent que YAP1/TAZ aident le foie à trouver un équilibre délicat durant la réparation : stocker temporairement des lipides pour l’énergie, limiter les dommages dus à l’hème et à l’inflammation, et utiliser miR-122 pour tempérer le stress excessif tout en favorisant la repousse tissulaire. 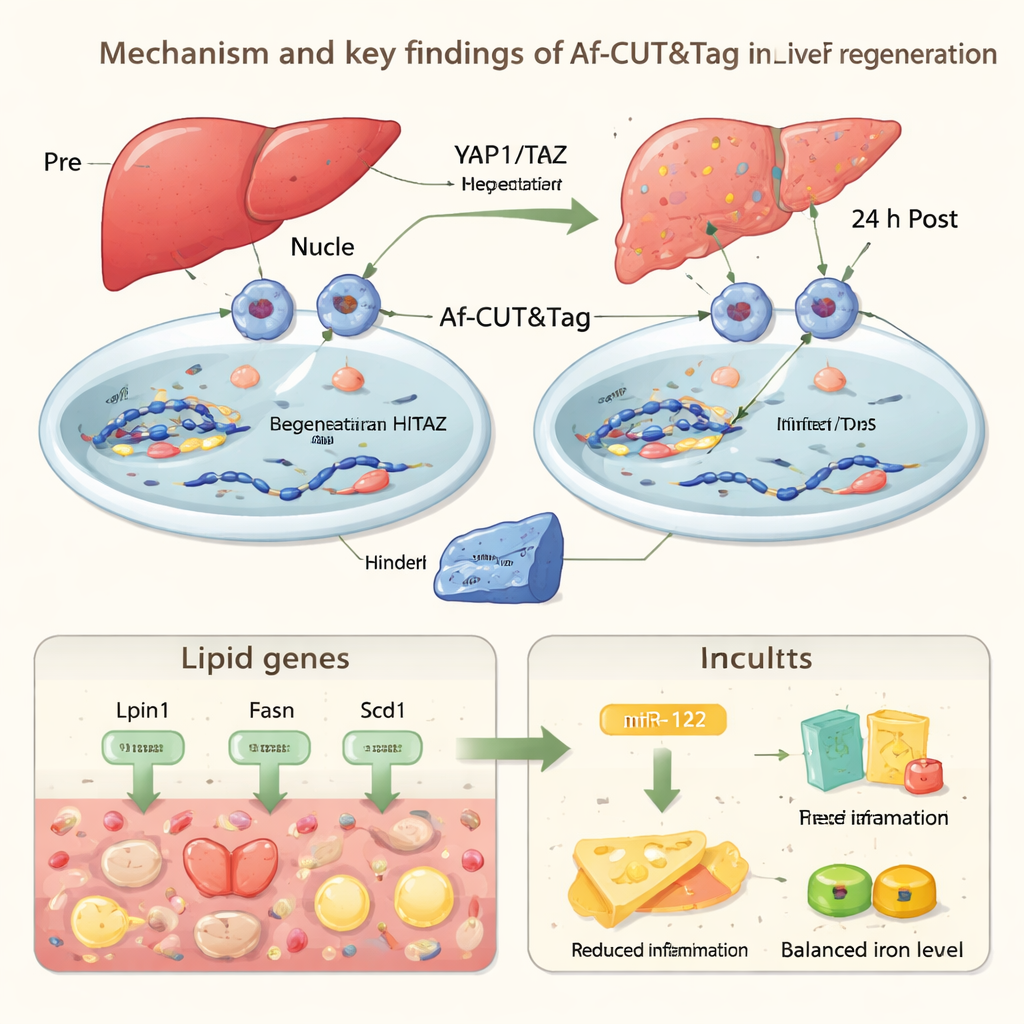
Un nouveau regard polyvalent sur le contrôle des gènes
Af-CUT&Tag offre une approche modulaire et sans anticorps pour visualiser où des protéines clés se trouvent sur l’ADN dans des lignées cellulaires, des tissus et même des cellules individuelles. En remplaçant des anticorps imprévisibles par de petites étiquettes génétiques et des liaisons conçues, elle fournit des cartes plus nettes et plus reproductibles à partir d’un bien plus petit nombre de cellules. Appliquée à la régénération hépatique, elle a révélé comment YAP1 et TAZ coordonnent le métabolisme, la gestion du fer et le microARN miR-122 pour soutenir la réparation précoce. À mesure que l’édition du génome et les liaisons conçues s’amélioreront, cette stratégie pourrait devenir un outil standard pour disséquer comment la régulation génique fonctionne normalement au cours du développement et de la régénération — et comment elle déraille dans des maladies comme le cancer et l’insuffisance hépatique.
Citation: Wang, X., Deng, X., Qiu, L. et al. Af-CUT&Tag: a sensitive and antibody-free chromatin profiling method using genetically encoded tags and high-affinity binders fused to Tn5. Nat Commun 17, 1746 (2026). https://doi.org/10.1038/s41467-026-68454-9
Mots-clés: profilage de la chromatine, épigénétique, régénération hépatique, YAP1 TAZ, microARN-122