Clear Sky Science · fr
Réduction des images médicales volumineuses via des réseaux neuronaux profonds séparant forme et texture
Pourquoi réduire la taille des images médicales est important
Les hôpitaux modernes produisent d'énormes quantités de scans 3D détaillés issus d'appareils CT et IRM. Ces images sont essentielles pour le diagnostic et la recherche, mais elles sont très volumineuses : un seul jeu de données peut occuper des centaines de gigaoctets, ce qui rend leur stockage, leur partage et leur analyse lents et coûteux. Cet article présente une nouvelle approche permettant de réduire drastiquement ces fichiers volumineux tout en conservant quasiment intact le détail diagnostique, ce qui pourrait accélérer le travail clinique, les consultations à distance et les études médicales à grande échelle.
Deux types d'information dans un même scan
Quand on regarde un scan corporel, on voit en réalité deux types d'information superposés. Le premier est la forme générale des organes et des os : où la colonne vertébrale se courbe, la taille du foie, l'organisation de l'abdomen. Le second est la texture fine : de petites variations d'intensité qui suggèrent des types de tissu ou des signes subtils de maladie. Les auteurs soutiennent que la plupart des outils de compression actuels traitent ces deux ingrédients comme s'ils étaient mélangés, ce qui rend la compression plus lente et moins efficace. Leur idée principale est de séparer forme et texture et de compresser chacun avec une stratégie adaptée.
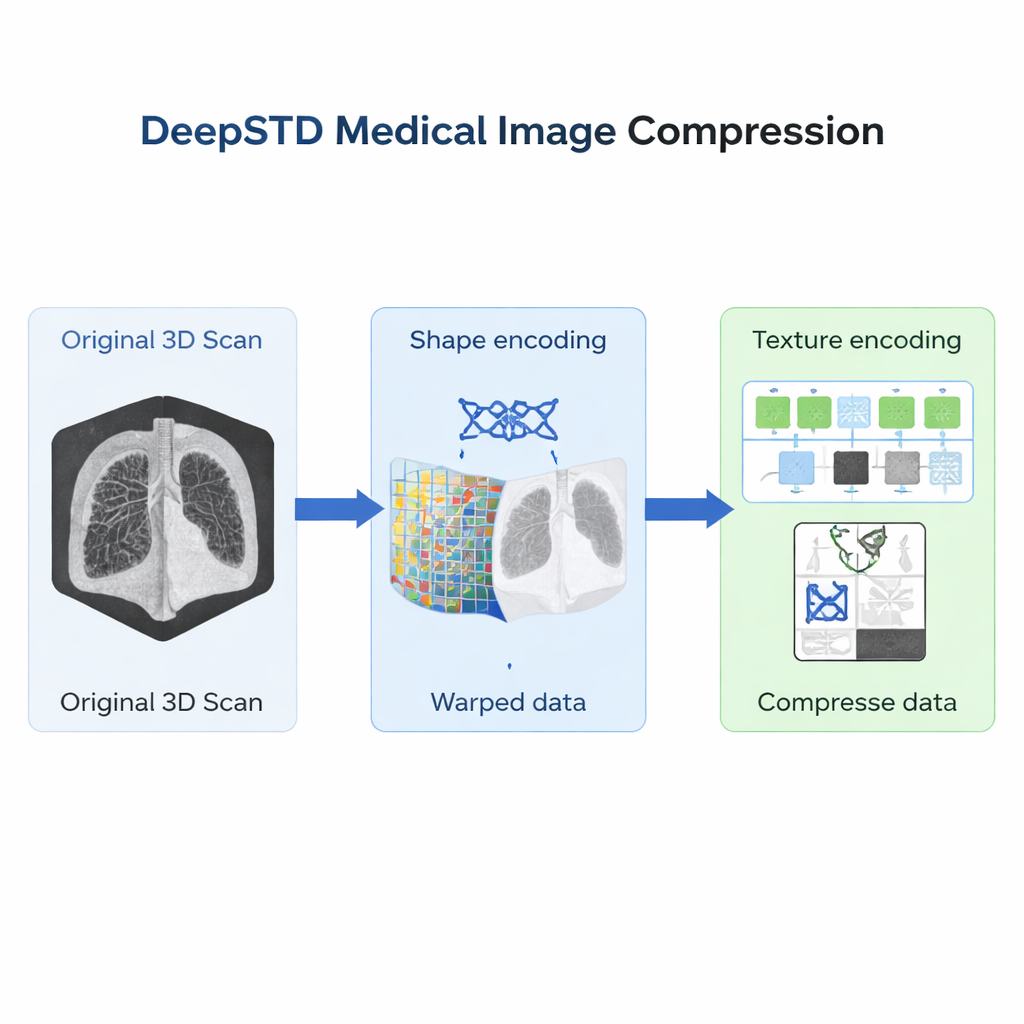
Un plan type anatomique
La nouvelle méthode, appelée Shape-Texture Decoupled Compression (DeepSTD), commence par choisir un « modèle » (template) pour une région corporelle et un type d'imagerie donnés, comme un CT du thorax ou une IRM abdominale. Ce modèle fait office de carte standard de cette anatomie. Pour chaque nouveau scan, DeepSTD détermine d'abord comment le corps de la personne doit être déformé de manière lisse pour se superposer au modèle. Ce champ de déformation décrit les différences de forme : par exemple un patient plus grand, un foie légèrement déplacé, ou une colonne vertébrale avec une courbure différente. Les auteurs représentent ce champ de déformation à l'aide d'un type compact de réseau neuronal particulièrement adapté à l'encodage de déformations 3D lisses, afin de stocker efficacement l'information de forme.
Capturer les textures subtiles après alignement
Une fois un scan transformé pour correspondre à la forme du modèle, il ne reste principalement que des différences de texture : les motifs d'intensité subtils qui distinguent les patients. Puisque tous les scans sont maintenant dans la même géométrie, ces textures sont plus faciles à modéliser et à compresser. DeepSTD alimente les données alignées dans un second réseau neuronal qui combine des couches convolutionnelles (pertinentes pour le détail local) et des blocs Transformer (pertinents pour la structure à plus longue portée) en 3D complète. Ce réseau apprend, à partir de nombreux exemples, quelles textures sont communes et lesquelles sont uniques, lui permettant de ne stocker que l'essentiel sous la forme d'un « code latent » compact. Le fichier compressé final se compose simplement du code de forme et du code de texture.
Tests sur des collections CT et IRM réelles
L'équipe a testé DeepSTD sur de grands ensembles de données publiques, incluant des scans CT détaillés de la colonne vertébrale et des volumes IRM abdominaux. Ils l'ont comparé à la fois à des outils classiques (comme JPEG, HEVC et des standards vidéo plus récents) et à des méthodes neuronales de pointe. À des niveaux de compression atteignant jusqu'à 256 fois plus petits que les fichiers originaux, DeepSTD a mieux préservé la similarité au niveau pixel et les caractéristiques médicalement importantes, comme les segmentations d'organes automatiques, que les alternatives. Parallèlement, il a encodé les scans des dizaines à plus d'une centaine de fois plus vite que le meilleur système neuronal antérieur reposant uniquement sur des représentations neuronales implicites. En termes pratiques, un jeu de données CT qui nécessitait autrefois des jours pour être téléchargé sur une connexion lente pourrait être transféré en moins d'une demi-heure avec DeepSTD, avec une perte pratiquement invisible.
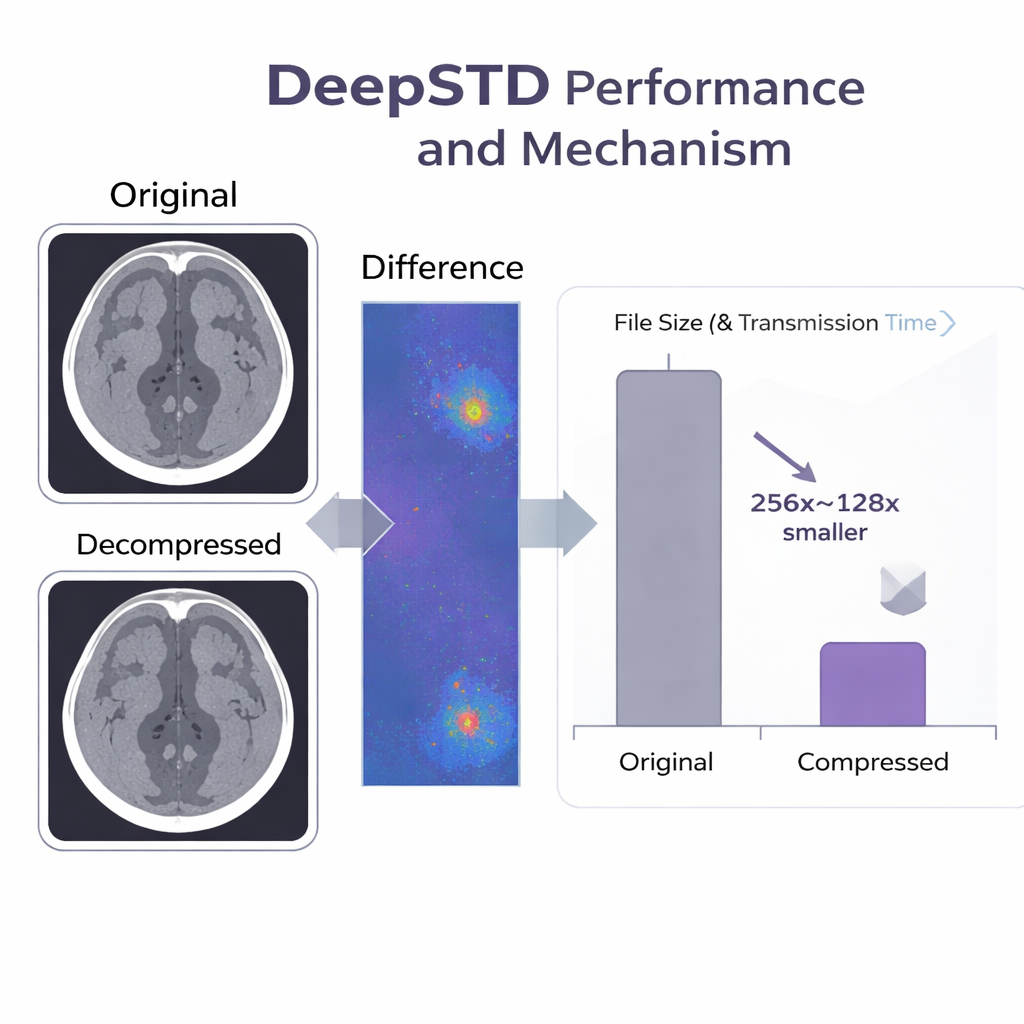
Conçu pour l'usage clinique quotidien
Au-delà des chiffres bruts, les auteurs ont conçu DeepSTD en tenant compte des contraintes du monde réel. La méthode peut utiliser plusieurs cartes graphiques en parallèle, réduisant encore les temps d'encodage et de décodage pour de grandes collections. Elle permet un contrôle précis du ratio de compression, afin que les hôpitaux puissent adapter la taille des fichiers au stockage disponible ou à la bande passante réseau. Le système fonctionne aussi lorsque les données d'entraînement sont limitées, grâce à des techniques astucieuses d'augmentation des données et de « distillation des connaissances » qui transfèrent ce qui a été appris depuis des ensembles plus riches. Des tests supplémentaires sur des radiographies thoraciques et des IRM du cerveau et du genou suggèrent que l'approche est largement applicable à différents types d'imagerie.
Ce que cela signifie pour les patients et les médecins
Pour un non-spécialiste, la conclusion est simple : DeepSTD est une manière plus intelligente de compresser les images médicales. En encodant séparément la forme du corps d'un patient et l'apparence de ses tissus, il réduit les scans de plus d'un facteur cent tout en préservant les informations sur lesquelles médecins et algorithmes s'appuient. Cela pourrait faciliter grandement le stockage à long terme des dossiers d'imagerie, le partage de données entre hôpitaux et la réalisation d'études IA à grande échelle, sans sacrifier la qualité diagnostique.
Citation: Yang, R., Xiao, T., Cheng, Y. et al. Reducing bulky medical images via shape-texture decoupled deep neural networks. Nat Commun 17, 1573 (2026). https://doi.org/10.1038/s41467-026-68292-9
Mots-clés: compression d'images médicales, apprentissage profond, données CT et IRM, représentation neuronale, stockage des données de santé