Clear Sky Science · es
Expansión global de cinco décadas de Staphylococcus argenteus ST2250 modela la dinámica de la resistencia a los antimicrobianos
Por qué importa un germen poco conocido
La mayoría de las personas ha oído hablar de la “MRSA”, el Staphylococcus aureus resistente a fármacos que acecha hospitales y titulares. Mucho menos conocidos son su pariente cercano, Staphylococcus argenteus. Este estudio muestra que una familia concreta de S. argenteus, denominada ST2250, se ha propagado silenciosamente por todo el mundo en los últimos 50 años mientras acumulaba un conjunto de genes de resistencia a los antibióticos. Entender cómo ha ocurrido esto ayuda a médicos y responsables de salud pública a prepararse para la próxima oleada de infecciones difíciles de tratar.
Un nuevo agente problemático en la familia del estafilococo
S. argenteus solo fue reconocido como especie propia en 2015, tras años de ser confundido con S. aureus en el laboratorio. Sin embargo, puede causar muchos de los mismos problemas: intoxicación alimentaria, infecciones de piel y tejidos blandos, infecciones sanguíneas, enfermedades óseas y articulares, e infecciones en animales y productos alimentarios. Dado que las pruebas de rutina a menudo lo etiquetan erróneamente como S. aureus, su impacto real probablemente se ha subestimado. Los autores reunieron 379 genomas de alta calidad de S. argenteus procedentes de 28 países en seis continentes, mayoritariamente de pacientes humanos pero también de alimentos, animales y el medio ambiente, para obtener una visión global de cómo está evolucionando esta especie.
Un clon dominante circunda el globo
Cuando el equipo comparó el ADN de todos estos aislados, encontró que S. argenteus está compuesto por varias líneas genéticas distintas, cada una correspondiente a un “tipo de secuencia” genético específico. Una, ST2250, dominó el conjunto de datos, representando más de la mitad de todos los genomas. ST2250 se detectó en múltiples continentes y en muchos tipos de muestras, desde pacientes hospitalizados hasta alimentos. Usando un árbol evolutivo calibrado en el tiempo, los investigadores estimaron que el ancestro común de las cepas ST2250 actuales emergió alrededor de 1967. Desde entonces, su tamaño efectivo de población —un indicador de cuántas infecciones y transmisiones exitosas ocurren— se disparó durante décadas, alcanzando un pico alrededor de 2012 antes de mostrar indicios de un descenso reciente.
Cargado con herramientas de resistencia y virulencia
El estudio catalogó genes que ayudan a S. argenteus a causar enfermedad (genes de virulencia) y a resistir antibióticos (genes de resistencia a los antimicrobianos, o RAM). Cada genoma portaba docenas de genes de virulencia, y las cepas ST2250 tenían solo ligeramente menos de estos que otras líneas, lo que sugiere un potencial similar para causar enfermedad. La diferencia más notable residía en la resistencia. En todos los genomas, los autores encontraron 29 genes RAM distintos que abarcan 12 clases de antibióticos y desinfectantes. Las cepas ST2250 solían portar más genes de resistencia que otros tipos y con frecuencia compartían las mismas combinaciones. Muchas cepas ST2250 también llevaban fosB, un gen que protege frente a la fosfomicina, un antibiótico “antiguo” que ha sido reempleado contra infecciones estafilocócicas difíciles. El pariente cercano ST1850 también portó fosB, lo que sugiere que este gen pudo estar presente en su ancestro común.
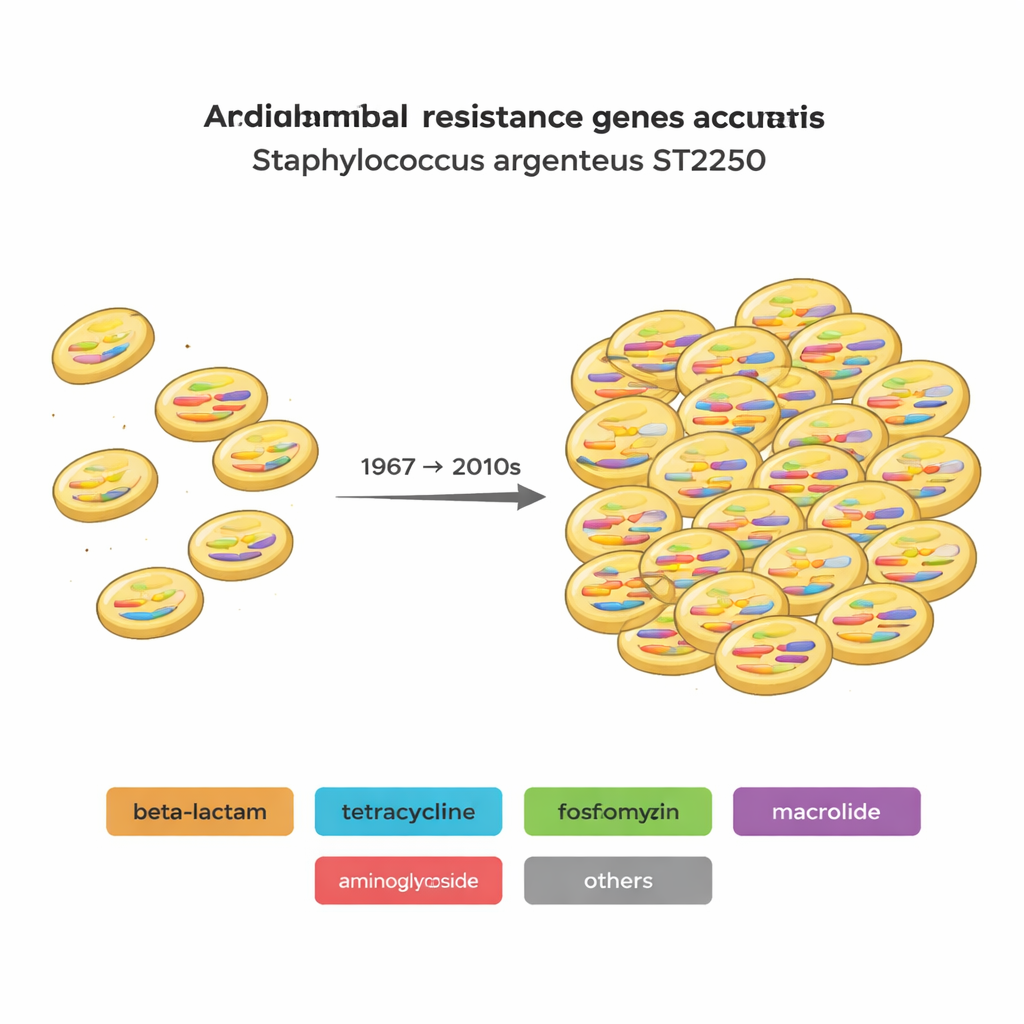
Cómo viajan juntas las características de resistencia
Los investigadores buscaron genes de resistencia que tienden a aparecer juntos en la misma cepa con más frecuencia de la que el azar predice. Encontraron emparejamientos fuertes, como genes de resistencia a tetraciclinas (tetL) con resistencia a aminoglucósidos (aph(3')-IIIa), y resistencia a trimetoprima (dfrG) con resistencia a meticilina (mecA). Estos agrupamientos probablemente reflejan eventos pasados en los que varios genes se adquirieron a la vez en elementos de ADN móviles como plásmidos, que luego se heredaron a medida que se propagaban las líneas bacterianas. De hecho, el equipo detectó docenas de tipos de “replicón” plasmídico y mostró que algunos plásmidos coocurren fuertemente con genes de resistencia específicos. Dentro de ST2250 surgieron dos sublinajes principales: uno en Asia y otro en Europa, cada uno marcado por su propio paquete característico de resistencia y, en Europa, por el cassette de resistencia a la meticilina conocido como SCCmec.
Qué significa esto para el futuro
Para no especialistas, el mensaje clave es que S. argenteus no es una curiosidad inofensiva sino un miembro en ascenso de la familia de estafilococos resistentes a fármacos. En aproximadamente cinco décadas, una única línea exitosa, ST2250, se ha extendido ampliamente y ha acumulado una mezcla rica de genes de resistencia, creando condiciones en las que las cepas multirresistentes pueden surgir con facilidad. Aunque hay indicios tempranos de que el crecimiento de ST2250 puede estar desacelerándose, otras líneas con sus propios rasgos de resistencia esperan en segundo plano. Los autores sostienen que una detección más precisa de S. argenteus, un muestreo más amplio fuera de los hospitales y una vigilancia genética estrecha serán esenciales para evitar que este patógeno silencioso se convierta en la próxima gran amenaza estafilocócica.
Cita: Costa, L.R.M., Marmion, M., Buiatte, A.B.G. et al. Five-decade global expansion of Staphylococcus argenteus ST2250 shapes antimicrobial resistance dynamics. npj Antimicrob Resist 4, 14 (2026). https://doi.org/10.1038/s44259-026-00188-6
Palabras clave: Staphylococcus argenteus, resistencia a los antimicrobianos, epidemiología genómica, clon ST2250, bacterias resistentes a los fármacos