Clear Sky Science · es
Paisaje genómico de la resistencia a los antimicrobianos en India: hallazgos de un estudio de vigilancia multispecies
Por qué los superbacterias en India nos importan a todos
Las “superbacterias” resistentes a los antibióticos son una preocupación global creciente, pero aún sabemos sorprendentemente poco sobre cómo evolucionan y se propagan estos gérmenes en muchas regiones del mundo. Este estudio examina detalladamente bacterias peligrosas de hospitales en India y lee su ADN completo para entender cómo burlan nuestros fármacos más potentes. Los resultados no solo revelan qué hace que estos microbios sean tan difíciles de eliminar, sino que también ponen a prueba si los métodos rápidos basados en ADN pueden sustituir con fiabilidad a las pruebas de laboratorio más lentas—un asunto que podría afectar el tratamiento de infecciones en cualquier lugar.
Una mirada más cercana a las infecciones hospitalarias
Investigadores recopilaron 266 muestras bacterianas de pacientes gravemente enfermos en hospitales grandes del norte y oeste de India entre 2022 y 2024. La mayoría de las muestras provenían de sangre, aunque también hubo de orina y de infecciones pulmonares, y la mayoría procedía de unidades de cuidados intensivos, donde los pacientes son más vulnerables. El equipo se centró en gérmenes problemáticos bien conocidos—como Escherichia coli, Klebsiella pneumoniae, Acinetobacter baumannii, Pseudomonas aeruginosa, Staphylococcus aureus resistente a meticilina (MRSA) y Enterococcus resistente a vancomicina (VRE). Para cada muestra, los médicos ya habían realizado pruebas estándar de susceptibilidad a antibióticos, que exponen las bacterias a fármacos en el laboratorio para ver qué medicamentos siguen siendo eficaces. Los científicos secuenciaron entonces los genomas bacterianos para cartografiar el conjunto completo de genes de resistencia y compararon lo que el ADN “predijo” con lo que realmente ocurrió en los tubos de ensayo.
Cuando los genes y los tubos de ensayo no coinciden
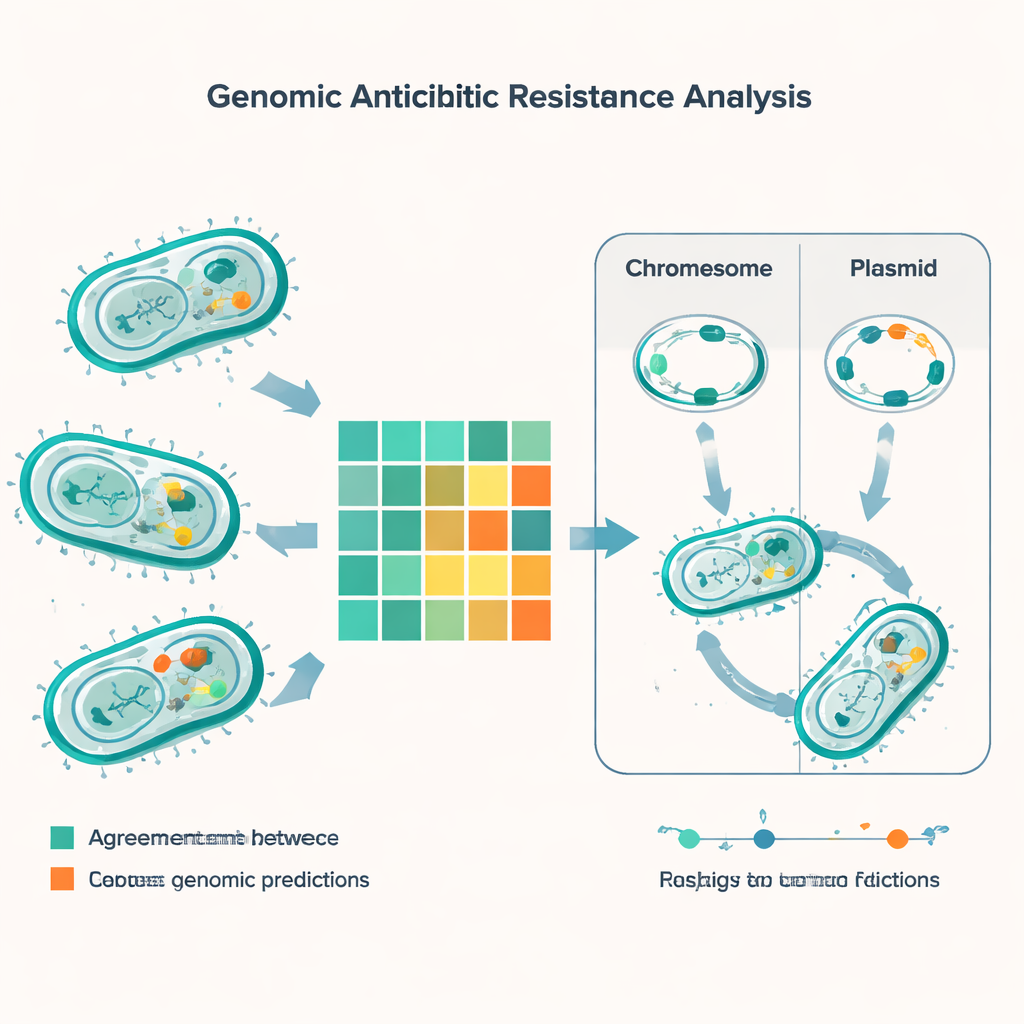
Al comparar las predicciones genómicas con los resultados de laboratorio para 56 antibióticos distintos, el estudio realizó más de 5.000 comparaciones. En la mayoría de los casos, el método basado en ADN y las pruebas tradicionales coincidieron, pero destacaron casi 600 discrepancias. El tipo de error más común fue que la herramienta genómica predijo que una bacteria sería resistente cuando la prueba de laboratorio indicó que aún era tratable. Esto ocurrió con frecuencia para fármacos como minociclina, colistina y gentamicina, especialmente en E. coli. El tipo opuesto de error—donde el laboratorio detectó resistencia pero los genes no la explicaron claramente—fue menos frecuente pero más preocupante, porque puede llevar a pasar por alto resistencias. Estas discrepancias “muy importantes” aparecieron de forma notable en bacterias intestinales llamadas enterococos, particularmente frente a fármacos tipo penicilina de uso generalizado y para la combinación trimetoprim‑sulfametoxazol.
Arsenales ocultos dentro del ADN bacteriano
La encuesta genómica descubrió un denso arsenal de genes de resistencia entre las principales especies. Cada uno de los patógenos Gram negativos comunes portaba al menos un gen de betalactamasa, que puede descomponer la penicilina y fármacos relacionados, y muchas cepas tenían varios de estos genes a la vez. Culpables notorios como las carbapenemasas tipo NDM—que neutralizan antibióticos de último recurso—eran generalizadas en E. coli, Klebsiella, Acinetobacter y Pseudomonas. El estudio también encontró genes que ayudan a las bacterias a sobrevivir a potentes antibióticos “peptídicos” como la colistina, junto con el clásico gen mecA que confiere a MRSA resistencia a la meticilina y conglomerados de resistencia a la vancomicina en enterococos. Al comparar huellas genéticas llamadas tipos de secuencia, el equipo vinculó algunos de estos genes de resistencia a linajes bacterianos de alto riesgo conocidos que ya se están propagando en India y en todo el mundo.
Intercambio de genes vía ADN móvil
Una parte crucial de la historia no reside solo en qué genes portan las bacterias, sino en dónde se ubican esos genes. Muchos genes de resistencia están en pequeños círculos de ADN llamados plásmidos, que las bacterias pueden intercambiar como si fueran cromos coleccionables. Usando software especializado, los investigadores predijeron alrededor de 1.400 plásmidos entre las muestras, con una diversidad especialmente alta en E. coli y Klebsiella. En estas especies, una gran parte de los genes de resistencia—incluidas varias betalactamasas críticas—estaban en plásmidos, lo que facilita su paso entre cepas e incluso entre especies. Otros rasgos de resistencia estaban integrados en los cromosomas bacterianos, lo que significa que pueden persistir aunque se pierdan los plásmidos. El equipo también catalogó elementos genéticos móviles—segmentos cortos de ADN que pueden saltar de sitio y llevar consigo genes de resistencia—subrayando otra vía para una propagación rápida.
Qué significa esto para los tratamientos futuros
Para el público general, el mensaje central es que leer el ADN bacteriano puede ayudar mucho en la lucha contra las superbacterias, pero la tecnología aún no es perfecta. Las herramientas genómicas tendieron a “sobrediagnosticar” la resistencia, lo que es más seguro que pasar por alto una cepa peligrosa pero podría llevar a que los médicos usen fármacos más potentes de lo necesario. Al mismo tiempo, un número menor de casos mostró que las pruebas de laboratorio detectaron resistencias que los catálogos de genes actuales no pudieron explicar por completo, lo que pone de manifiesto lagunas importantes en nuestro conocimiento. Al construir un mapa detallado de genes de resistencia, plásmidos y elementos móviles en hospitales indios, este estudio crea una base para diagnósticos basados en ADN más rápidos y mejores y para un uso de antibióticos más informado—no solo en India, sino en cualquier lugar donde las superbacterias amenacen la medicina moderna.
Cita: Gheewalla, N., Karthikeyan, V., Jadhav, Y. et al. Genomic landscape of antimicrobial resistance in India: findings from a multi-species surveillance study. npj Antimicrob Resist 4, 13 (2026). https://doi.org/10.1038/s44259-026-00185-9
Palabras clave: resistencia a los antimicrobianos, secuenciación genómica, infecciones hospitalarias, bacterias resistentes a fármacos, resistencia mediada por plásmidos