Clear Sky Science · es
Análisis de la expresión génica del hospedador para detectar la etiología bacteriana y viral en niños hospitalizados con sospecha de infección grave
Por qué esta investigación importa para los niños con infecciones graves
Cuando un niño llega al hospital con fiebre alta y aspecto muy enfermo, los médicos deben decidir con rapidez si la causa es una infección bacteriana, que suele requerir antibióticos, o una infección viral, que a menudo remite por sí sola. Las pruebas actuales están lejos de ser perfectas y muchos niños reciben antibióticos “por si acaso”. Este estudio exploró si leer las señales del propio cuerpo en la sangre —específicamente, patrones de actividad génica— puede distinguir con mayor precisión entre infecciones bacterianas y virales en niños con sospecha de enfermedad grave.
Mirar el sistema de alarma del cuerpo en lugar del germen
Las pruebas tradicionales intentan encontrar el germen directamente, por ejemplo cultivando bacterias a partir de la sangre o detectando material genético viral mediante PCR. Estos enfoques pueden ser lentos, pueden no detectar al causante real y con frecuencia identifican virus “espectadores” inocuos, sobre todo en niños pequeños que con frecuencia portan virus respiratorios. Los investigadores se centraron en cambio en la respuesta del hospedador: qué genes en las células sanguíneas del niño están activados o silenciados durante la infección. Dado que el sistema inmunitario reacciona de forma distinta a bacterias y virus, el patrón de genes activos puede funcionar como una huella dactilar del tipo de infección, incluso cuando resulta difícil encontrar o interpretar el germen en sí.
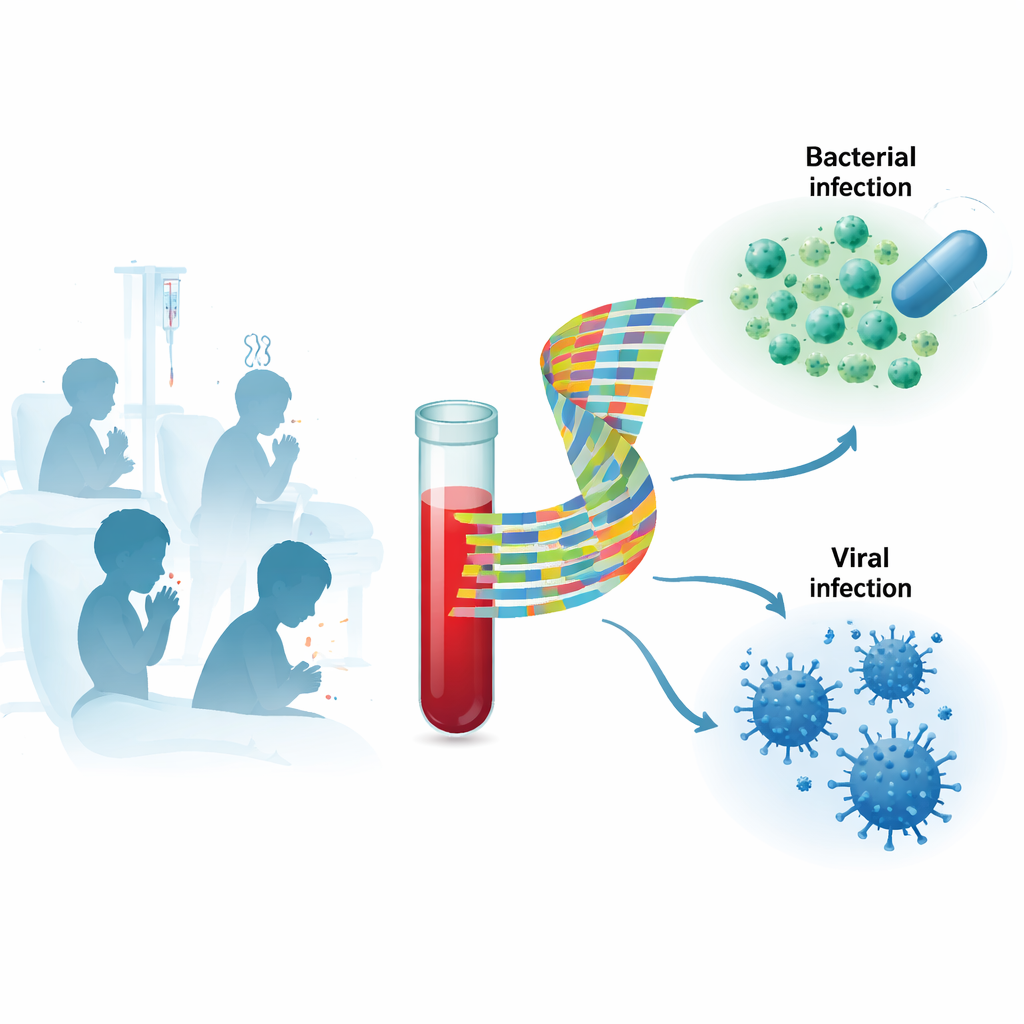
Estudiando una mezcla real de niños enfermos
El equipo reclutó a 268 niños de entre 4 semanas y 16 años en Finlandia. La mayoría fue hospitalizada con sospecha de infecciones graves; un grupo más pequeño tenía infecciones virales confirmadas y más leves tratadas como ambulatorias, y algunos eran controles sanos. Los médicos recogieron datos clínicos detallados, pruebas de laboratorio estándar como proteína C reactiva y procalcitonina, y hisopos nasales para virus respiratorios. Se utilizaron muestras de sangre para medir la actividad de miles de genes mediante secuenciación de ARN. La enfermedad de cada niño se clasificó cuidadosamente como bacteriana, viral, mixta bacteriana–viral, incierta o no infecciosa, y luego se agrupó de forma más simple como “bacteriana” o “viral” para los análisis clave.
Encontrando una señal simple de dos genes
Cuando los científicos examinaron de forma amplia la actividad génica en sangre de todos los niños, observaron que las muestras se agruparon en varios clústeres, pero estos clústeres no se correspondían de forma nítida con las etiquetas “bacteriana” frente a “viral”. Los niños sanos eran claramente distintos de los casos de infección bacteriana definida, mientras que los patrones génicos en las infecciones virales definidas eran más variados. Para clarificar esta complejidad, los investigadores dividieron a los pacientes en dos conjuntos: un grupo de descubrimiento con niños con infecciones respiratorias y un grupo de validación con otros tipos de infecciones, como renales o cutáneas. En el grupo de descubrimiento buscaron combinaciones muy pequeñas de genes que mejor distinguieran entre enfermedad bacteriana y viral, y luego evaluaron qué tan bien funcionaban esas mismas combinaciones en el grupo de validación.
Identificaron un par de genes particularmente prometedor, llamados TSPO y SECISBP2. En conjunto, los niveles de actividad de solo estos dos genes pudieron separar las infecciones bacterianas (incluidas las mixtas bacteriana–viral) de las infecciones puramente virales con alta precisión. Medido como el área bajo la curva ROC, esta señal de dos genes alcanzó 0,93 en el conjunto de descubrimiento y 0,81 en el de validación; en ambos grupos combinados fue 0,87, con una sensibilidad de aproximadamente 77% y una especificidad de aproximadamente 87%. En otras palabras, la señal identificó correctamente la mayoría de los casos bacterianos y rara vez etiquetó erróneamente infecciones virales como bacterianas. También se comportó mejor que marcadores sanguíneos ampliamente utilizados, como la proteína C reactiva y la procalcitonina, en esta población de estudio.

Qué podrían estar haciendo estos dos genes
TSPO está implicado en cómo las mitocondrias —las fábricas de energía de la célula— manejan el estrés y ayudan a controlar la inflamación. Trabajos previos han vinculado una mayor actividad de TSPO con infecciones bacterianas más graves y sepsis, y experimentos sugieren que estimular células inmunitarias con componentes bacterianos puede aumentar TSPO y potenciar la liberación de moléculas inflamatorias que ayudan a eliminar microbios. En este estudio, TSPO tendió a estar más activo en infecciones bacterianas y menos activo en las virales. SECISBP2, por su parte, ayuda al organismo a fabricar proteínas que contienen selenio y que tienen funciones antioxidantes, inmunitarias y antivirales. Se sabe que el selenio apoya a las células inmunitarias y reduce la gravedad de algunas enfermedades víricas. Aquí, la actividad de SECISBP2 fue generalmente mayor en las infecciones virales, coherente con la idea de que el organismo aumenta las defensas relacionadas con el selenio al combatir virus.
Qué podría significar esto para la atención futura
Los autores subrayan que sus hallazgos son preliminares pero alentadores. Una prueba simple que lea solo estos dos genes a partir de una pequeña muestra de sangre podría algún día ayudar a los equipos de urgencias a decidir con más confianza si un niño muy enfermo necesita antibióticos. Dado que la señal de dos genes funcionó no solo en infecciones pulmonares sino también en otras infecciones graves, podría ser útil en una amplia gama de casos reales, incluidos aquellos en los que se detectan germenes bacterianos y virales juntos. Sin embargo, el estudio se realizó en un solo país y se basó en definiciones, aunque las mejores disponibles, que son imperfectas de enfermedad bacteriana frente a viral. Serán necesarios estudios más amplios en diferentes hospitales y versiones rápidas y aptas para la clínica antes de que pueda guiar decisiones cotidianas. Aun así, este trabajo muestra que la propia actividad génica del cuerpo puede contener la clave para un uso más inteligente de los antibióticos y una mejor atención a los niños con infecciones graves.
Cita: Piri, R., Valta, M., Lempainen, J. et al. Host gene expression analysis in the detection of bacterial and viral etiology in children hospitalized with a suspected severe infection. Commun Med 6, 204 (2026). https://doi.org/10.1038/s43856-025-01370-z
Palabras clave: infecciones pediátricas, expresión génica, bacteriana frente a viral, gestión de antibióticos, diagnósticos de la respuesta del hospedador