Clear Sky Science · es
Entropía de la jerarquía de la red para cuantificar la disimilitud de grafos
Por qué importan las pequeñas diferencias en las redes
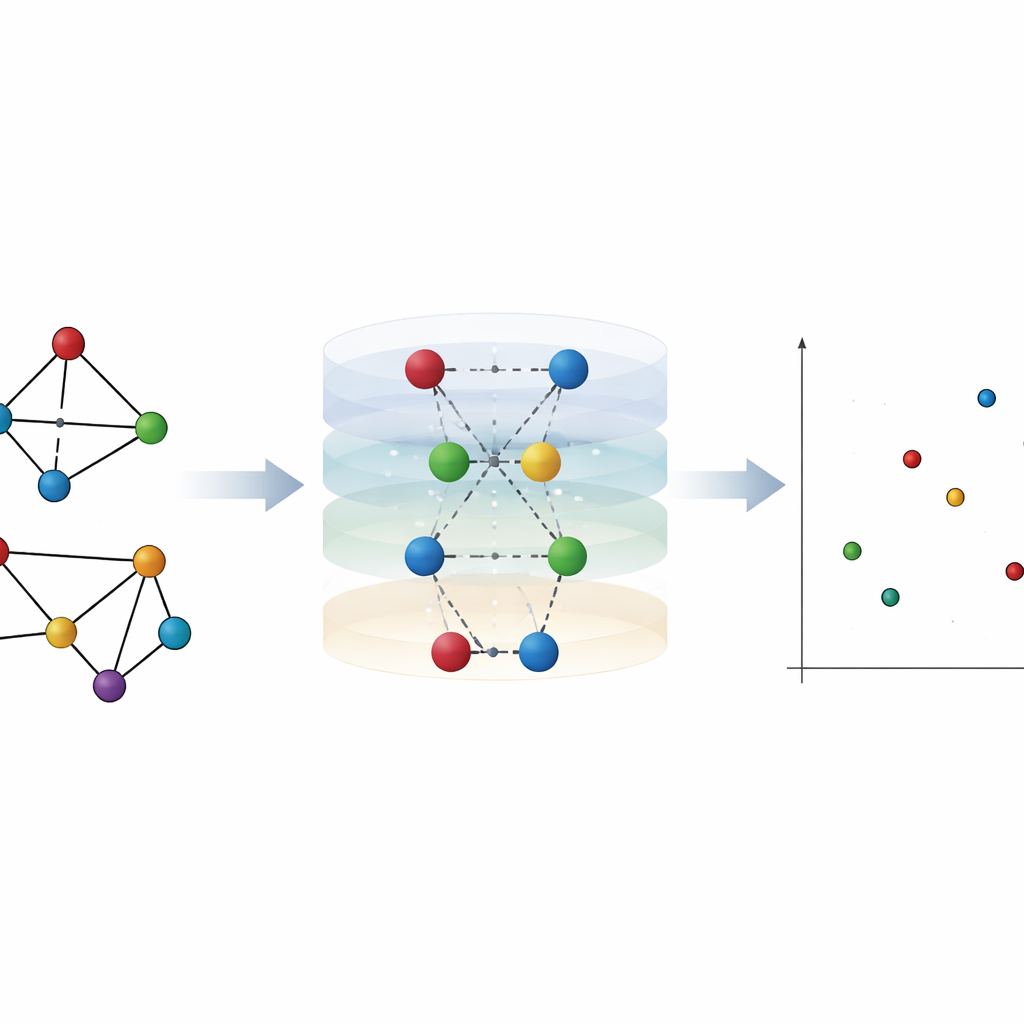
Desde amistades en redes sociales hasta rutas aéreas y estructuras proteicas, muchos sistemas a nuestro alrededor pueden representarse como redes de nodos y enlaces. Pero determinar cuándo dos redes son significativamente diferentes es sorprendentemente difícil, sobre todo cuando a primera vista parecen similares. Este artículo presenta una nueva forma de medir cuán diferentes son realmente dos redes, prestando atención no solo a puntos individuales (nodos) sino también a las conexiones (aristas) y a cómo actúan en conjunto. El método, llamado entropía de la jerarquía de la red, puede detectar cambios estructurales sutiles que otras herramientas pasan por alto e incluso ayuda a distinguir proteínas enzimas de no-enzimas.
Mirando las redes capa por capa
Para entender una red, los autores consideran primero qué tan lejos está cada nodo de todos los demás en términos de pasos a lo largo de las conexiones. Alrededor de cualquier nodo elegido, los demás nodos pueden agruparse en capas: vecinos inmediatos, vecinos de los vecinos, y así sucesivamente. Esta “jerarquía” alrededor de un nodo describe cómo la influencia o una infección podría propagarse hacia afuera a través de la red. La observación clave es que dos redes muy distintas pueden compartir la misma estructura de capas a nivel de nodo, por lo que esta vista por sí sola puede fallar al distinguirlas. El artículo muestra ejemplos clásicos, como los grafos de Desargues y el dodecaédrico, que comparten jerarquías de nodos idénticas aunque su cableado interno sea distinto.
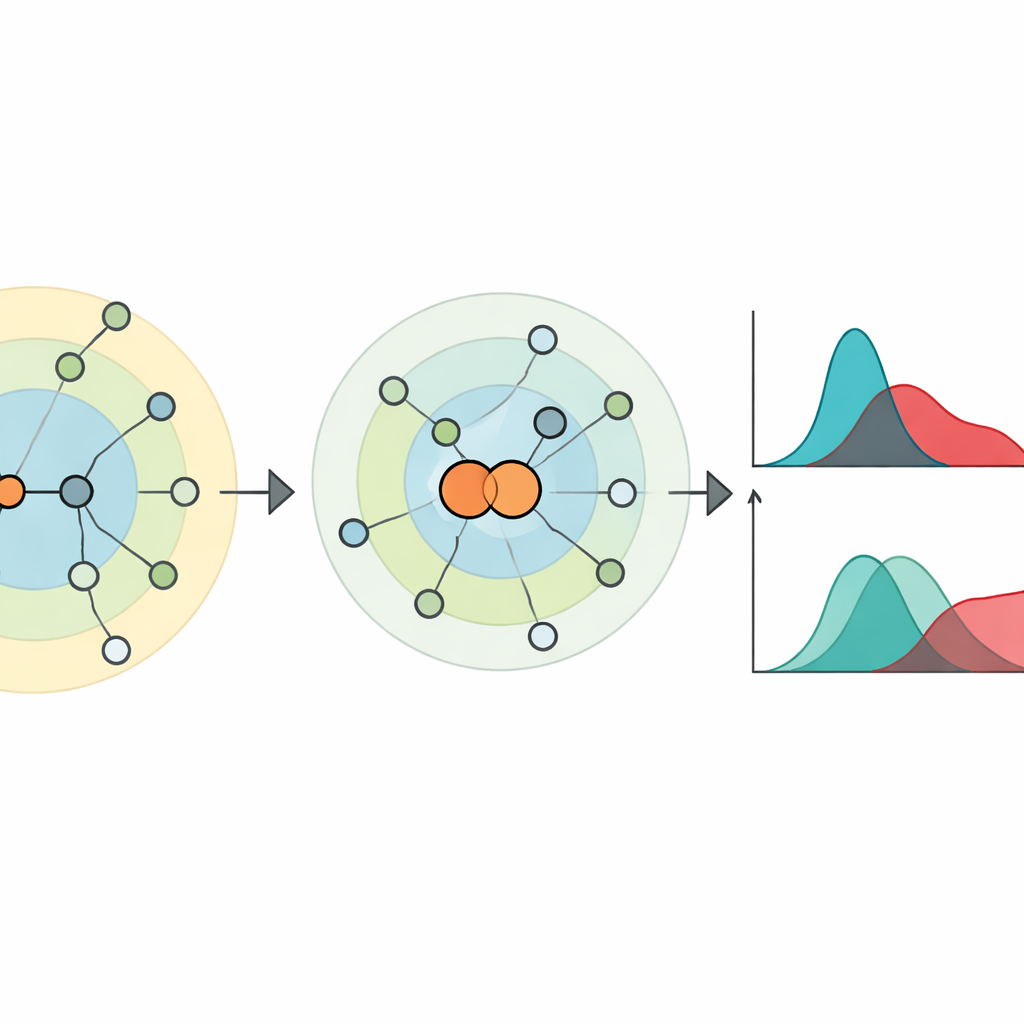
Dando voz a las aristas: contraer pares de nodos
Para captar lo que la visión a nivel de nodos no ve, los autores se centran en las aristas —las conexiones entre nodos— y en cómo reconfiguran las distancias en la red. Introducen una idea simple pero poderosa: “contracción de pares de nodos”. Aquí, dos nodos conectados se fusionan temporalmente en un único nodo nuevo, conservando sus vecinos combinados. Esto revela cuán cerca está cada otro nodo del par en comparación con cada extremo por separado. En términos de propagación, imita el efecto de infectar ambos extremos de una arista a la vez en lugar de comenzar desde un solo nodo. A partir de estos patrones de distancias por capas, definen la “centralidad de la jerarquía” tanto para nodos como para aristas, que resulta correlacionar fuertemente con la eficacia de nodos o aristas como agentes de propagación en simulaciones epidémicas sobre redes reales.
Medir la pérdida de información con entropía
Con base en estas centralidades, los autores definen dos tipos de entropía de la jerarquía. La entropía de la jerarquía de aristas pregunta: ¿cuánta información perdemos si intentamos aproximar la importancia de una arista simplemente promediando la importancia de los dos nodos que conecta? La entropía de la jerarquía de nodos formula la pregunta inversa para nodos y sus aristas circundantes. Ambas cantidades se normalizan para que no dependan del tamaño total de la red. Juntas forman una huella de dos números para cualquier red. La distancia entre dos redes es entonces simplemente la distancia geométrica entre sus huellas. Esta nueva métrica cumple las reglas estándar esperadas para una distancia y coincide con intuiciones, como penalizar en mayor medida cuando un cambio fragmenta la red.
Viendo estructura más fina y cambios temporales
Los autores prueban su medida tanto en redes artificiales como reales. En benchmarks sintéticos que imitan sistemas sociales o tecnológicos, la nueva métrica puede seguir cómo evolucionan las redes al cambiar parámetros del modelo, y separa claramente redes con comunidades fuertes de aquellas con comunidades más débiles, incluso cuando métodos competidores tienen dificultades. En experimentos controlados donde las redes se rebarajan cuidadosamente para conservar muchas estadísticas comunes —como secuencias de grado e incluso distribuciones de distancias—, la distancia de entropía de jerarquía aún detecta diferencias que otras medidas populares tratan como despreciables. También sobresale al agrupar versiones aleatorizadas de la misma red en las categorías correctas, indicando una sensibilidad aguda a la estructura de orden superior que va más allá de simples conteos de enlaces y caminos.
Usos en el mundo real: movilidad y proteínas
Para mostrar valor práctico, los autores aplican su medida de distancia a redes de movilidad diaria entre cientos de ciudades chinas durante los primeros meses de COVID-19. Usando comienzos de enero como línea base, la entropía de la jerarquía revela cómo los patrones de viaje cambian durante la agitación por el Año Nuevo lunar, la instauración de cuarentenas estrictas y el periodo de recuperación gradual, coincidiendo bien con los cambios de política conocidos y con patrones comunitarios de movilidad. En otra aplicación, tratan las estructuras proteicas como redes de aminoácidos conectados cuando están próximos en el espacio. Sin aprendizaje ni características hechas a mano, agrupar proteínas mediante la nueva distancia alcanza alrededor de un 75% de precisión en separar enzimas de no-enzimas —competitivo con enfoques modernos supervisados basados en redes neuronales.
Qué significa esto en términos simples
En esencia, este trabajo muestra que prestar atención a cómo nodos y enlaces configuran conjuntamente las distancias en una red ofrece una “huella” mucho más nítida que mirar solo los nodos. Al cuantificar cuánto se pierde cuando intentamos reemplazar aristas por sus extremos —o nodos por sus aristas circundantes—, la distancia de entropía de la jerarquía destaca diferencias estructurales sutiles que afectan de manera notable a la propagación, la movilidad y la función biológica. Para científicos y analistas que trabajan con cualquier tipo de datos de redes, esto ofrece una herramienta práctica y de uso general para comparar sistemas complejos de forma que es matemáticamente sólida y está estrechamente ligada a cómo los procesos realmente se desarrollan en esas redes.
Cita: Mou, J., Wang, L., Zhang, C. et al. Network hierarchy entropy for quantifying graph dissimilarity. Commun Phys 9, 83 (2026). https://doi.org/10.1038/s42005-026-02523-9
Palabras clave: similitud de redes, redes complejas, medidas de entropía, propagación epidémica, redes de estructura de proteínas