Clear Sky Science · es
Minería de enzimas basada en inferencia de ortólogos para la diversificación del esqueleto anticancerígeno de la evodiamina
Convertir los compuestos vegetales en mejores medicamentos
Muchos de los medicamentos actuales empezaron como compuestos defensivos en plantas. Estas moléculas naturales suelen mostrar efectos potentes contra el cáncer, las infecciones o el dolor, pero rara vez son «fármacos perfectos». Los químicos querrían ajustar sus estructuras con precisión para hacerlos más seguros y eficaces, sin embargo esas moléculas suelen ser tan complejas que incluso pequeños cambios son difíciles. Este estudio muestra cómo los científicos pueden reclutar enzimas vegetales como diminutas herramientas moleculares para introducir modificaciones dirigidas en un compuesto anticancerígeno llamado evodiamina, abriendo potencialmente nuevas vías hacia terapias mejoradas.
Por qué importa esta molécula vegetal
La evodiamina es un compuesto natural que se encuentra en los frutos de un árbol utilizado en la medicina tradicional china. Pertenece a una familia de moléculas en forma de anillo que ya sustentan fármacos importantes contra el cáncer, la hipertensión y las infecciones. La evodiamina en sí ha mostrado propiedades anticancerígenas, antiinflamatorias, analgésicas y antimicrobianas, y algunas de sus versiones modificadas parecen especialmente prometedoras como candidatos anticáncer multitarget. El reto es cómo añadir nuevos «mangos» químicos, como grupos que contienen oxígeno, en puntos muy concretos de este andamiaje tan congestionado sin recurrir a reactivos agresivos o a síntesis de múltiples pasos.
Dejar que las enzimas hagan la química difícil
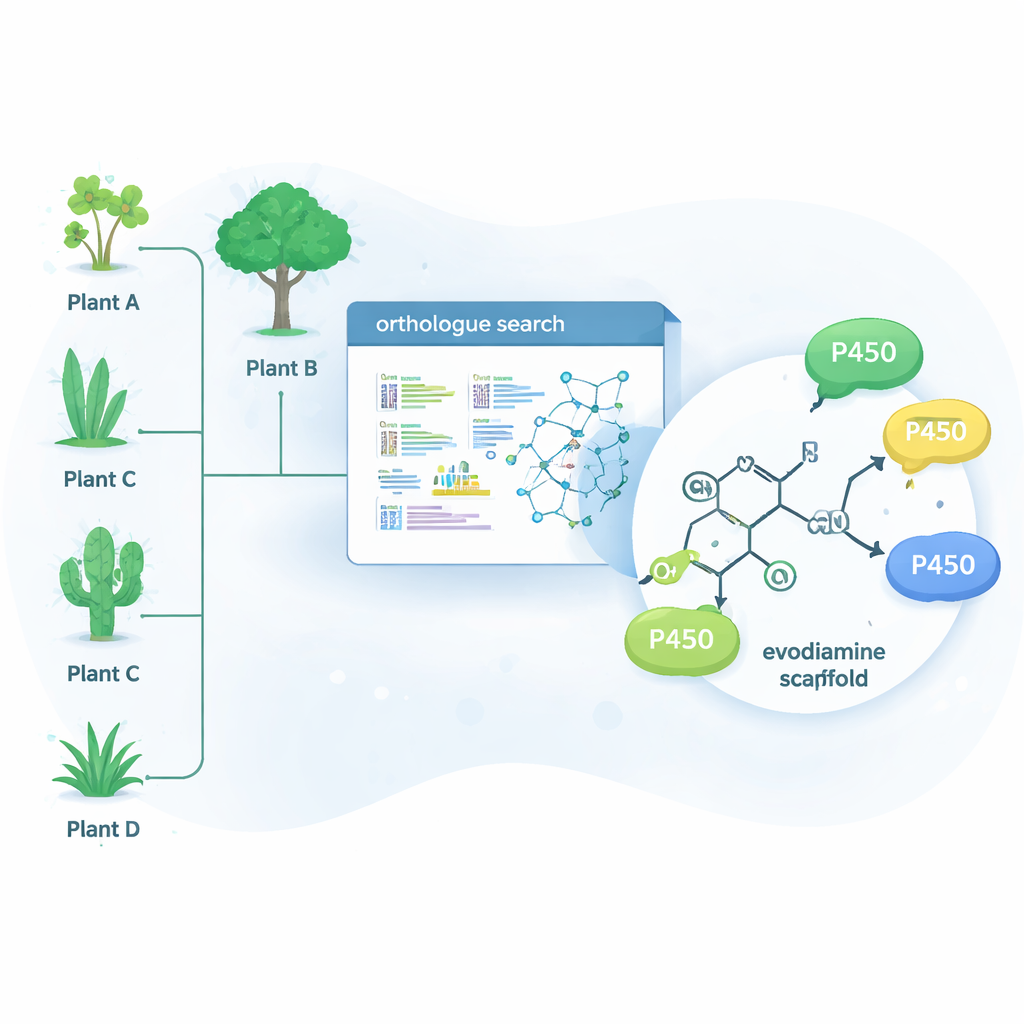
La naturaleza ya ha resuelto muchos de estos problemas químicos difíciles usando enzimas —proteínas que catalizan reacciones específicas. Una gran familia de enzimas, llamada citocromos P450, sobresale en la adición de oxígeno a enlaces carbono‑hidrógeno que de otro modo son poco reactivos. Ese único paso puede cambiar drásticamente el comportamiento de una molécula en el organismo y también crear un punto de partida para posteriores modificaciones químicas. En lugar de buscar solo en las plantas que producen naturalmente evodiamina, los investigadores utilizaron una herramienta bioinformática llamada OrthoFinder para escanear datos genéticos de 15 plantas productoras de alcaloides. Buscaron enzimas P450 que fueran «ortólogos» cercanos de enzimas conocidas por modificar alcaloides, razonando que los parientes de esas enzimas podrían también ser capaces de afinar moléculas relacionadas con potencial farmacológico.
Encontrar nuevas enzimas en plantas inesperadas
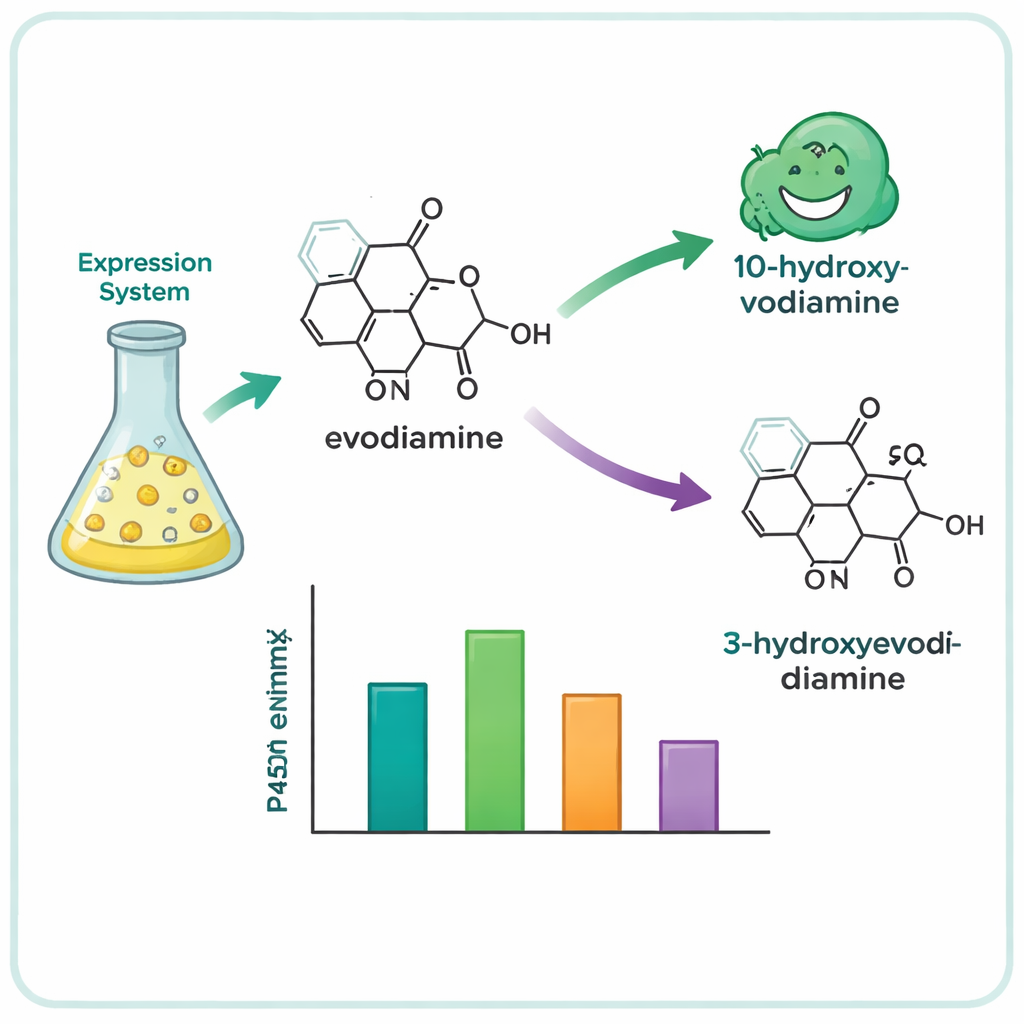
De cientos de genes candidatos, el equipo redujo la lista a 15 P450 prometedores y los expresó en células de levadura, que sirvieron como pequeñas fábricas de enzimas. A continuación alimentaron a estas levaduras con una colección de moléculas vegetales complejas y analizaron cuáles habían sido alteradas químicamente. Cuatro enzimas —tres del árbol Camptotheca acuminata y una del arbusto Tabernaemontana elegans— resultaron actuar sobre la evodiamina, pese a que ninguna de estas plantas es conocida por producirla. Estas enzimas insertaron selectivamente un átomo de oxígeno en una de dos posiciones del sistema de anillos de la evodiamina, generando dos productos principales: 10‑hidroxyevodiamina y 3‑hidroxyevodiamina. Tales versiones oxigenadas son más fáciles de transformar ulteriormente en candidatos farmacológicos más solubles en agua o más potentes, usando química más suave que las rutas sintéticas tradicionales.
Una mirada al kit de herramientas molecular
Para entender por qué estas enzimas tan relacionadas se comportaban de forma diferente, los investigadores construyeron modelos tridimensionales de la enzima más activa y de sus parientes usando herramientas modernas de predicción de estructuras proteicas. Luego emplearon acoplamiento por ordenador para ver cómo podría situarse la evodiamina dentro de los bolsillos activos de las enzimas, cerca del centro que contiene hierro del P450 donde ocurre la reacción. Los modelos destacaron varios aminoácidos voluminosos y repelentes al agua —especialmente residuos de fenilalanina— posicionados cerca de los anillos aromáticos de la evodiamina. Mediante la mutación cuidadosa de estas posiciones, el equipo demostró que cambiar el tamaño y la forma de este bolsillo puede debilitar la actividad, alterar el ajuste del sustrato o incluso cambiar el sitio de oxigenación favorecido de un anillo de la molécula a otro. En un caso, una sola mutación invirtió la preferencia de la enzima de producir el producto 10‑hidroxi al 3‑hidroxi.
Qué significa esto para futuros medicamentos
Para quienes no son especialistas, la idea clave es que los autores han demostrado una hoja de ruta práctica para descubrir y afinar enzimas vegetales capaces de hacer ediciones precisas y «quirúrgicas» en moléculas complejas con carácter farmacológico. Combinando la minería genética a gran escala con ensayos enzimáticos y modelado estructural, identificaron un conjunto de biocatalizadores que pueden remodelar selectivamente el andamiaje de la evodiamina en posiciones difíciles de alcanzar con la química estándar. Esto no solo ofrece una vía más limpia y sostenible para obtener versiones avanzadas de la evodiamina —como candidatos anticancerígenos solubles en agua— sino que también demuestra que enzimas útiles pueden encontrarse en plantas que ni siquiera fabrican el compuesto objetivo. La misma estrategia podría aplicarse ahora a muchos otros productos naturales, acelerando el diseño de la próxima generación de medicamentos derivados de plantas.
Cita: Kwan, B.D., Kim, T., Nguyen, H.H. et al. Orthologue inference-based enzyme mining for diversification of the anti-cancer evodiamine scaffold. Commun Chem 9, 73 (2026). https://doi.org/10.1038/s42004-025-01876-6
Palabras clave: evodiamina, enzimas vegetales, citocromo P450, biocatálisis, descubrimiento de fármacos