Clear Sky Science · es
Modelos generativos de la dinámica celular: de Neural ODEs a flow matching
Observando cómo cambian las células con el tiempo
Cada órgano de nuestro cuerpo se construye a partir de células que en un principio eran casi idénticas y que, con el tiempo, adoptaron diferentes funciones. A los biólogos les encantaría ver en tiempo real cómo cambia cada una de esas células, pero los métodos de medición actuales destruyen las células al medirlas. Este artículo de revisión explora cómo una nueva clase de herramientas de inteligencia artificial, llamadas Neural Ordinary Differential Equations, puede ayudar a reconstruir esas historias ocultas de cambio a partir de instantáneas estáticas, mejorando potencialmente nuestra comprensión del desarrollo, la enfermedad y el modo en que funcionan los tratamientos.

De instantáneas a películas vivas
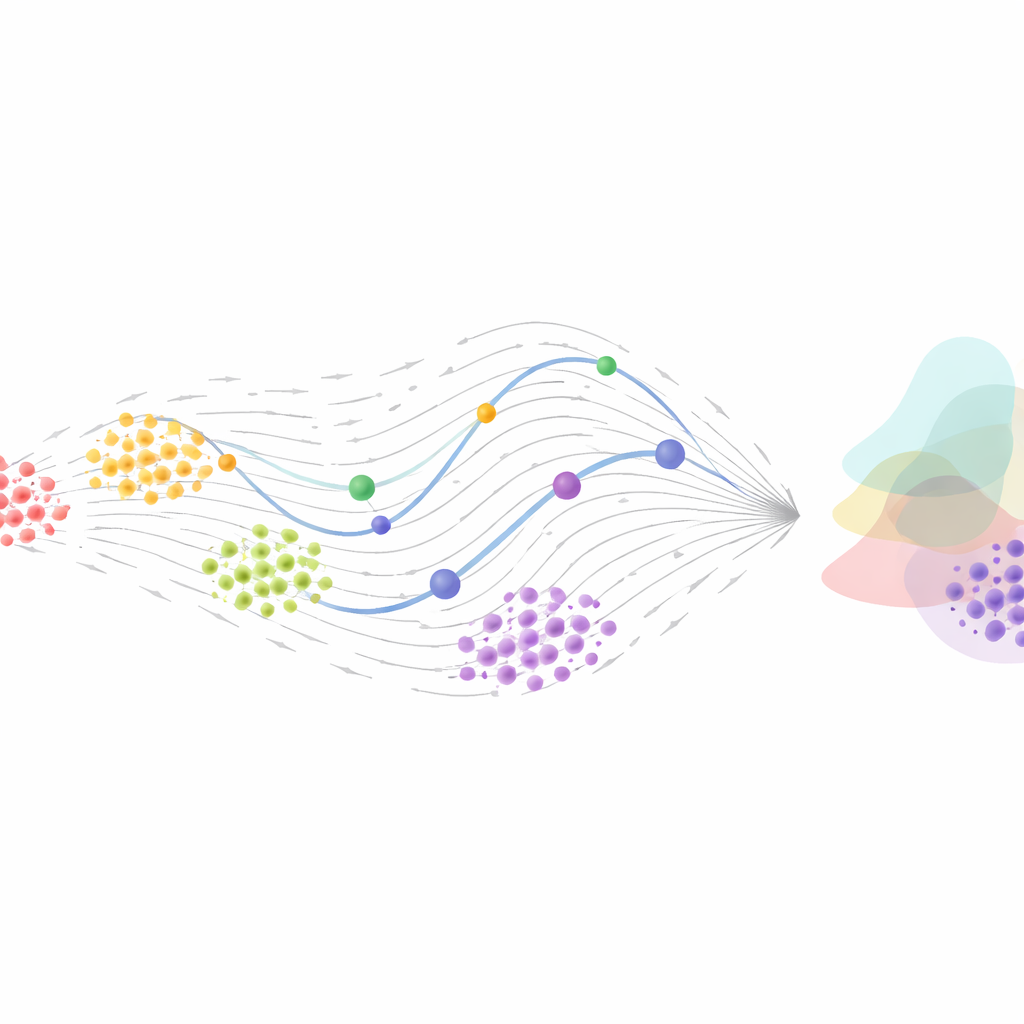
Las tecnologías modernas de secuenciación unicelular pueden medir la actividad de miles de genes en células individuales, generando enormes tablas de números. Cada fila corresponde a una célula y cada columna a un gen. Pero cada célula se mide solo una vez, así que los científicos acaban con una colección de fotos fijas en lugar de una película que muestre cómo cambia una célula a lo largo del tiempo. Los enfoques iniciales intentaron ordenar estas instantáneas en un «pseudotiempo» plausible, disponiendo las células a lo largo de trayectorias de desarrollo según la similitud de sus patrones de actividad génica. Esto ayudó a revelar rutas generales de diferenciación celular, pero tuvo dificultades cuando las células se ramificaban en múltiples destinos o seguían trayectorias complejas y cíclicas.
Describir el cambio celular como movimiento en un paisaje
Para ir más allá de los ordenamientos simples, los investigadores describen las células como puntos que se desplazan por un paisaje: la posición codifica el estado actual de actividad génica y el «momentum» refleja cómo cambia ese estado. Herramientas clásicas como la velocidad de ARN estiman hacia dónde se dirige una célula comparando distintas formas de ARN en su interior. Otros reconstruyen campos vectoriales: mapas de flechas que muestran, en cada punto de este espacio, la dirección probable del movimiento. Estos métodos empezaron a revelar cómo las redes génicas empujan a las células hacia destinos concretos y cómo regiones inestables en el paisaje pueden señalar decisiones próximas. Sin embargo, muchos de estos modelos realizan simplificaciones fuertes sobre las interacciones génicas y con frecuencia no pueden generar trayectorias completamente continuas que coincidan con datos poblacionales en varios puntos temporales.
Neural ODEs: aprender las reglas del cambio
Las Neural ODEs ofrecen una forma flexible de aprender las reglas subyacentes que gobiernan el movimiento celular en ese paisaje. En lugar de prescribir fórmulas de antemano, una red neuronal aprende una función que, para cualquier estado celular, indica cómo cambiará ese estado a continuación. Un solucionador de ecuaciones diferenciales ordinarias traza entonces trayectorias completas en el tiempo. Este marco se ha adaptado a varias tareas unicelulares: inferir rutas de desarrollo, destacar eventos de ramificación, identificar estados inestables o «preparados» e incluso recuperar redes de regulación génica—las relaciones de causa y efecto entre genes que se activan o inhiben mutuamente. Al incentivar que las reglas aprendidas sean simples y dispersas, algunos métodos pueden proponer diagramas regulatorios compactos que resultan más fáciles de interpretar y probar experimentalmente.
Flujos generativos: hacer corresponder poblaciones a lo largo del tiempo
Otra línea de trabajo trata el problema a nivel poblacional en lugar de rastrear células individuales. Aquí el objetivo es aprender cómo la distribución completa de estados celulares en un tiempo se transforma en la distribución en un tiempo posterior. Técnicas de transporte óptimo, originalmente desarrolladas para encontrar la forma más barata de mover masa de una forma a otra, se han combinado con Neural ODEs y modelos de «flujo» relacionados. Los continuous normalizing flows y los más recientes y eficientes métodos de «flow matching» aprenden directamente campos vectoriales que transforman una población celular en otra, sin tener que volver a ejecutar simulaciones costosas durante el entrenamiento. Estos enfoques pueden manejar muestreos irregulares, mediciones ruidosas e incluso dinámicas estocásticas (parcialmente aleatorias), ofreciendo modelos generativos capaces de simular poblaciones futuras realistas o reconstruir estados pasados probables.
Oportunidades y preguntas abiertas
A pesar de sus promesas, estos modelos enfrentan desafíos importantes. Distinguir la auténtica relación de causa y efecto de la mera correlación en las redes génicas es difícil, sobre todo cuando algunos factores influyentes no se observan. Los investigadores también están empujando a las Neural ODEs más allá de ajustar los datos que ven hacia el aprendizaje de leyes generales que puedan predecir respuestas a condiciones nuevas, como eliminaciones génicas o tratamientos farmacológicos. Manejar el ruido, la aleatoriedad y múltiples tipos de datos superpuestos—por ejemplo combinando actividad génica con ubicación espacial u otras capas moleculares—sigue siendo un área activa de investigación. Aun así, esas mismas ideas ya se aplican fuera de la genómica, por ejemplo a la dinámica cardíaca, al comportamiento de fármacos en el organismo y a series temporales médicas.
Por qué esto importa para la salud y la enfermedad
Para un público no especializado, el mensaje clave es que las Neural ODEs y los modelos de flow matching permiten a los científicos convertir mediciones celulares estáticas en historias dinámicas. En lugar de saber solo cómo se ven las células en unas pocas etapas aisladas, estas herramientas ayudan a inferir cómo es probable que las células se desplacen por su paisaje de desarrollo, qué conmutadores en sus circuitos génicos impulsan esos movimientos y cómo las intervenciones podrían redirigirlos. A largo plazo, estos modelos podrían permitir experimentos in silico que predigan cómo guiar una célula madre hacia un tipo deseado, cómo evolucionará la población celular de un tumor bajo tratamiento o cómo afectan las terapias complejas a ecosistemas celulares enteros—acercándonos a una comprensión mecanicista y predictiva de la vida a escala unicelular.
Cita: Richter, T., Wang, W., Palma, A. et al. Generative models of cell dynamics: from Neural ODEs to flow matching. Commun Biol 9, 352 (2026). https://doi.org/10.1038/s42003-026-09758-w
Palabras clave: dinámica unicelular, Neural ODEs, diferenciación celular, modelos generativos, transporte óptimo