Clear Sky Science · es
Un parche aromático en factores de transcripción tipo WhiB facilita la interacción con el factor sigma primario en Mycobacterium tuberculosis
Cómo las bacterias detectan el peligro
Mycobacterium tuberculosis, el germen que causa la tuberculosis, sobrevive dentro del cuerpo humano reprogramando con rapidez qué genes se activan o se silencian cuando las condiciones cambian, por ejemplo ante la exposición a antibióticos o un ataque inmunitario. Este estudio descubre una pequeña característica estructural—un "parche aromático"—en una familia de proteínas bacterianas que les ayuda a enganchar la maquinaria principal de conmutación génica de la célula. Entender este apretón microscópico revela cómo la tuberculosis y bacterias relacionadas se adaptan, y puede señalar nuevas vías para debilitar a este patógeno.
Una familia especial de proteínas reguladoras bacterianas
El trabajo se centra en las proteínas tipo WhiB (Wbl), un grupo que se encuentra solo en actinobacterias y sus virus, incluido Mycobacterium tuberculosis. Estas proteínas portan un pequeño clúster hierro–azufre, un cofactor metálico que les permite detectar cambios en el oxígeno y otros estreses. Se sabe que las Wbl controlan procesos clave como la división celular, la respuesta al estrés oxidativo y de nutrientes, y la resistencia a antibióticos. Sin embargo, la mayoría carecen de las formas clásicas que usan muchos reguladores para unirse directamente al ADN, lo que dejaba una pregunta sin resolver: ¿cómo controlan realmente la actividad génica?
Agarrando la máquina principal que lee los genes
Trabajos anteriores mostraron que varias proteínas Wbl activan genes uniéndose a una región conservada, llamada región 4, del factor sigma primario. El factor sigma es la parte de la ARN polimerasa—la enzima que lee el ADN—que reconoce dónde empezar a copiar los genes. En Mycobacterium tuberculosis, este factor sigma usa la misma región 4 para reclutar a muchos reguladores distintos. Los autores combinaron cristalografía de rayos X, ensayos bioquímicos de captura y calorimetría para mostrar que prácticamente todas las Wbl probadas de esta bacteria (con un caso especial) se enganchan en el mismo punto de la región 4 del sigma y lo hacen con una unión muy fuerte.
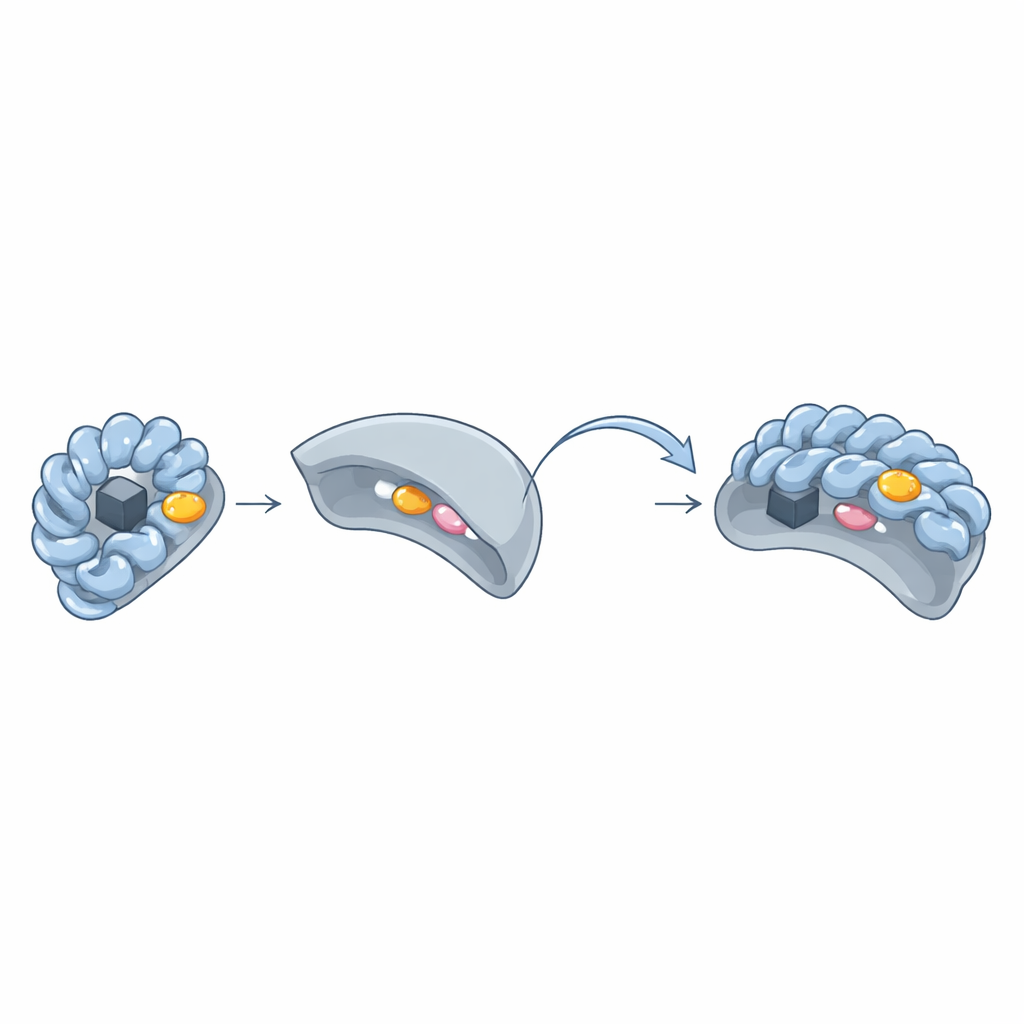
La cerradura y la llave ocultas: el "parche aromático"
Al comparar estructuras tridimensionales de pares Wbl–sigma, el equipo descubrió un cúmulo recurrente de aminoácidos voluminosos con anillos—triptófano, fenilalanina, tirosina o histidina—que forman un "parche aromático" en la superficie de las proteínas Wbl. Este parche rodea el clúster hierro–azufre y presiona directamente contra dos aminoácidos clave en la región 4 del sigma. Cuando los investigadores cambiaron estos residuos del parche aromático por otros más sencillos, las proteínas Wbl ya no pudieron formar complejos estables con el sigma, y sus clústeres hierro–azufre a menudo se volvieron inestables. Incluso en variantes de Wbl que parecían atípicas—como WhiB6 o WhiB5—residuos alternativos o cadenas laterales aromáticas cercanas compensaban para preservar el mismo modo de interacción.
Un diseño compartido entre bacterias y sus virus
Para ver cuán extendida está esta característica, los autores analizaron 995 secuencias de proteínas Wbl de muchas especies de actinobacterias y de sus virus infectantes (actinobacteriófagos). Agruparon estas proteínas en 29 subfamilias y encontraron que cinco ramas principales, representadas por cinco proteínas Wbl de Mycobacterium tuberculosis, abarcan alrededor del 80% de todas las secuencias. El modelado estructural con AlphaFold reveló que casi todas las Wbl—más del 98%—llevan al menos dos residuos aromáticos en posiciones que coinciden con el parche aromático, y casi todas tienen al menos uno en las posiciones centrales más críticas. Experimentos con varias Wbl codificadas por fagos confirmaron que estas versiones virales también se unen a la misma región del sigma de forma dependiente del parche, lo que indica que el mismo diseño molecular se reutiliza entre bacterias y sus fagos.
Una lucha evolutiva por el control
El árbol filogenético construido a partir de estas 995 secuencias muestra proteínas Wbl de fagos y bacterias entremezcladas, con señales claras de transferencia horizontal de genes en ambas direcciones. Algunas Wbl virales se sitúan en la base de grandes ramas bacterianas, lo que sugiere que los fagos pudieron haber regalado estos reguladores a bacterias ancestrales, que luego los adaptaron a sus propias necesidades. Otras Wbl virales aparecen incrustadas dentro de clústeres mayoritariamente bacterianos, lo que indica transferencias génicas posteriores de vuelta a los fagos. Dado que las Wbl controlan con firmeza respuestas al estrés, el desarrollo celular y la resistencia a fármacos mediante sus parches aromáticos de unión al sigma, estos intercambios de ida y vuelta probablemente moldearon cómo tanto bacterias como sus virus manipulan la maquinaria transcripcional del hospedador.
Qué significa esto para la tuberculosis y más allá
En términos sencillos, este estudio muestra que muchos reguladores de actinobacterias comparten un punto adhesivo pequeño pero crucial—el parche aromático—que les permite acoplarse a la misma parte del motor que lee los genes y afinar qué genes están activos bajo estrés. En Mycobacterium tuberculosis, este mecanismo de acoplamiento compartido ayuda a coordinar respuestas que sostienen la persistencia, la virulencia y la resistencia a antibióticos. Al revelar cómo funciona esta interfaz microscópica y cuán ampliamente está conservada, el trabajo destaca un posible punto débil que algún día podría ser atacado para interrumpir la capacidad del patógeno de adaptarse y sobrevivir dentro de su hospedador.
Cita: Guiza Beltran, D., Wan, T., Seravalli, J. et al. Aromatic patch in whiB-like transcription factors facilitates primary sigma factor interaction in mycobacterium tuberculosis. Commun Biol 9, 424 (2026). https://doi.org/10.1038/s42003-026-09698-5
Palabras clave: Mycobacterium tuberculosis, factores de transcripción, factor sigma, proteínas hierro-azufre, evolución de bacteriófagos