Clear Sky Science · es
DANST permite la deconvolución por tipo celular en transcriptómica espacial mediante redes neuronales adversariales de dominio profundo
Ver las células en su vecindario
Los tejidos humanos son ciudades densamente pobladas por muchos tipos celulares distintos, cada uno con su propia función. Las nuevas tecnologías de “transcriptómica espacial” pueden medir qué genes están activos a lo largo de un corte de tejido, pero cada medida a menudo mezcla señales de varias células vecinas. Este artículo presenta DANST, un método computacional inteligente que separa esas mezclas. Al indicarnos qué tipos celulares están presentes, y dónde, en órganos y tumores, ayuda a los científicos a comprender mejor cómo se construyen los tejidos, cómo se propagan las enfermedades y dónde podrían dirigirse mejor los tratamientos. 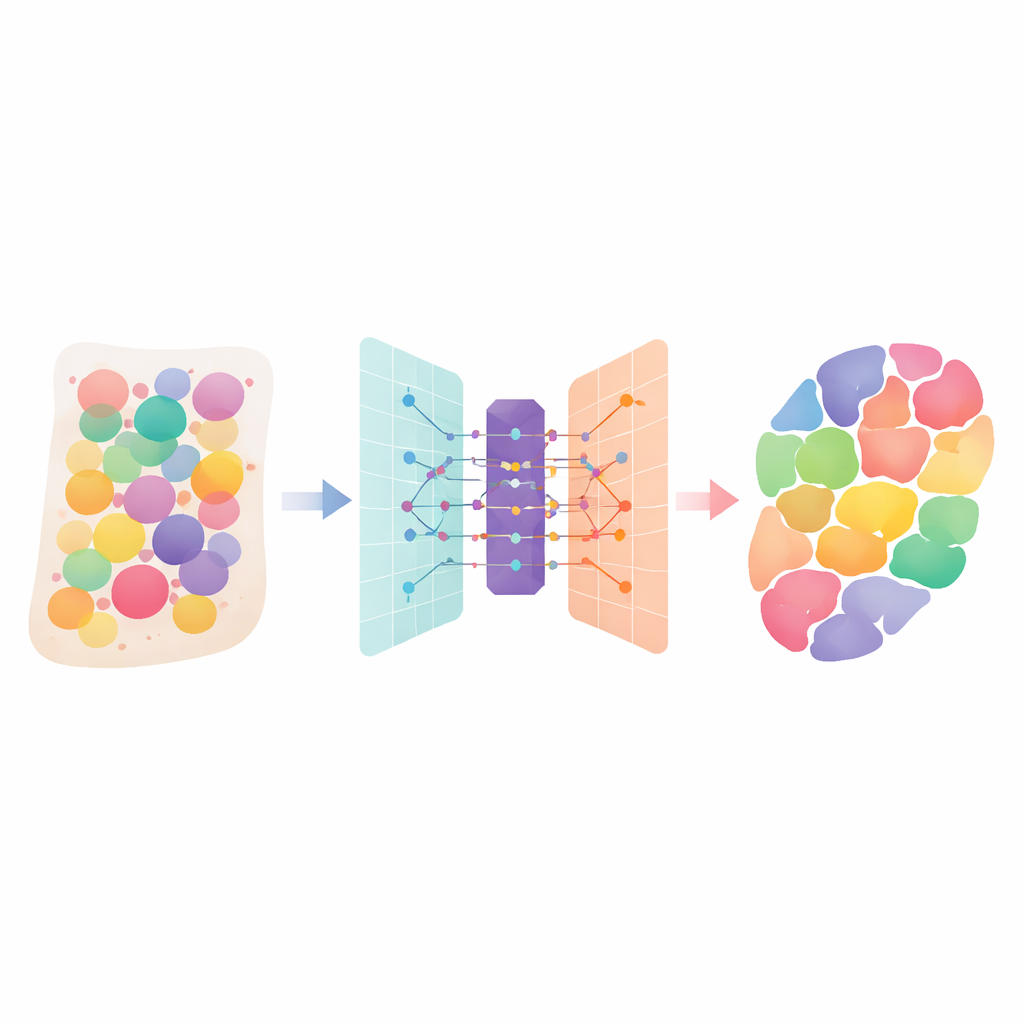
El reto de desenredar multitudes celulares
Las herramientas modernas de lectura génica pueden o bien observar con gran precisión células individuales o bien capturar la disposición completa de un tejido, pero rara vez ambas cosas a la vez. Las tecnologías espaciales más usadas registran la actividad génica en “puntos” relativamente grandes que pueden abarcar varias células. El resultado es parecido a escuchar un coro sin poder distinguir quién canta cada nota. Para interpretar esto, los investigadores necesitan métodos de “deconvolución” que estimen cuánto contribuye cada tipo celular a cada punto. Muchos enfoques existentes usan datos unicelulares como referencia, pero tienen dificultades porque los dos tipos de datos se recogen en experimentos distintos y no coinciden perfectamente en calidad, ruido o resolución.
Construyendo un puente entre mundos de datos
DANST afronta este desajuste creando un puente entre los datos unicelulares y los espaciales. Primero, utiliza los perfiles detallados de células individuales para simular muchos puntos mixtos artificiales con proporciones celulares conocidas. Al mismo tiempo, agrupa los puntos espaciales reales según su ubicación en el tejido y sus patrones de expresión génica, y emplea las distancias a esos grupos para asignar a cada punto simulado una posición “pseudo”. Este paso crea un mapa vinculado en el que puntos artificiales y reales comparten un marco espacial común, lo que permite al método aprender cómo deberían verse las señales mixtas en vecindarios específicos del tejido. 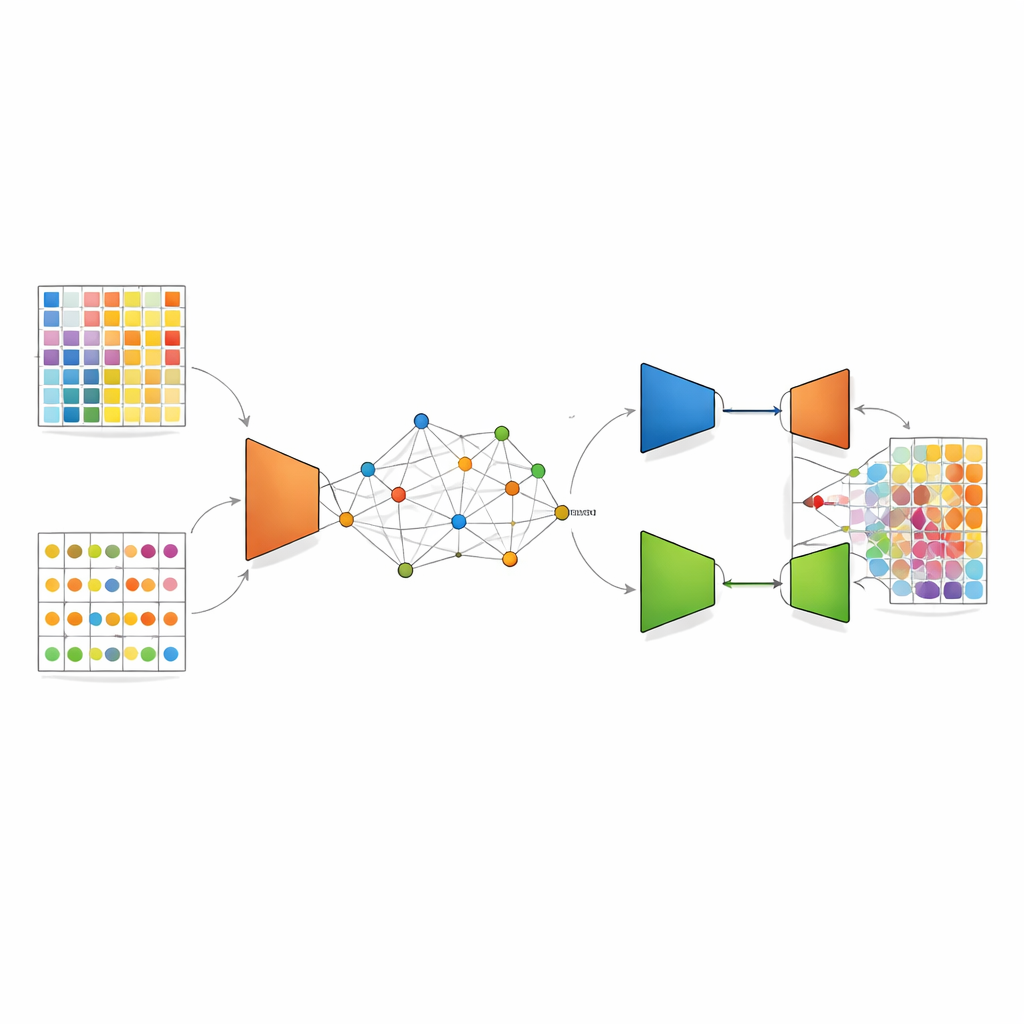
Limpiar señales y alinear dominios
Una vez que este mapa conjunto está en su lugar, DANST aplica un tipo de aprendizaje profundo llamado autoencoder variacional. Esta red comprime los patrones génicos tanto de puntos reales como simulados en una representación interna refinada y luego trata de reconstruirlos, lo que efectivamente reduce el ruido de los datos y destaca características importantes. Sobre esto, los autores añaden un componente adversarial: una segunda red intenta determinar si un patrón refinado proviene de datos espaciales reales o de datos simulados, mientras que el extractor de características aprende a engañarla. Este “tira y afloja” empuja el modelo hacia características útiles para ambas fuentes de datos, de modo que el conocimiento obtenido de los puntos simulados con fracciones celulares conocidas pueda transferirse de forma fiable a los puntos de tejido reales cuya composición se desconoce.
Pruebas en corazones, cerebros y tumores
El equipo evaluó DANST tanto en bancos de pruebas artificiales como en muestras biológicas reales de ratones y humanos. En comparación con varios métodos líderes, DANST recuperó con mayor precisión las proporciones de tipos celulares en conjuntos de datos sintéticos y mantuvo su ventaja en tejidos y plataformas muy diferentes. En un conjunto de datos de cerebro de ratón, reconstruyó claramente la organización en capas de la corteza y coincidió con regiones anatómicas definidas por expertos. En una rebanada separada de cerebro de ratón, capturó patrones finos en áreas como el hipocampo. Más notablemente, en tejido de cáncer de mama humano, DANST trazó cómo se disponen diversas células inmunitarias, células de soporte y células luminales sensibles a hormonas dentro y alrededor de las regiones tumorales. Estos mapas se alinearon con la biología conocida y sugirieron características clínicamente relevantes, como dependencia hormonal y un posible peor pronóstico donde ciertas células inmunitarias eran escasas.
Qué significa esto para la biología y la medicina
Para un no especialista, DANST puede verse como un intérprete potente que convierte señales borrosas y superpuestas en una imagen clara de qué células viven dónde en un tejido. Al separar de forma fiable los tipos celulares en el espacio, ofrece a los investigadores una visión más nítida de cómo se organizan los órganos sanos y cómo la enfermedad remodela esa organización. En cáncer, esto puede revelar cómo interactúan las células tumorales y las inmunitarias en regiones específicas, lo que puede orientar terapias dirigidas y ayudar a predecir la evolución de los pacientes. A medida que haya más conjuntos de datos espaciales y unicelulares disponibles, herramientas como DANST están llamadas a convertirse en esenciales para descifrar los vecindarios celulares que subyacen a la salud y la enfermedad.
Cita: Zhang, X., Wu, Z., Wang, T. et al. DANST enables cell-type deconvolution in spatial transcriptomics using deep domain adversarial neural networks. Commun Biol 9, 388 (2026). https://doi.org/10.1038/s42003-026-09659-y
Palabras clave: transcriptómica espacial, deconvolución por tipo celular, aprendizaje profundo, microambiente tumoral, secuenciación de ARN unicelular