Clear Sky Science · es
Evaluación de la calidad de modelos 3D de ARN mediante aprendizaje profundo y mapas 2D intermedios
Por qué importa juzgar las formas del ARN
Dentro de cada célula, las moléculas de ARN se retuercen y pliegan en intrincadas formas tridimensionales que ayudan a controlar qué genes se activan, guían reacciones químicas e incluso defienden contra virus. Hoy en día, programas informáticos potentes pueden predecir muchas de estas formas, pero los científicos siguen afrontando un problema básico: cuando el ordenador genera docenas o cientos de formas candidatas para el mismo ARN, ¿cuál de ellas se acerca realmente a la realidad? Este artículo presenta RNArank, una herramienta de inteligencia artificial diseñada para abordar esa pregunta calificando modelos 3D de ARN, como un inspector de calidad estructural, para que los investigadores puedan centrarse en las predicciones más fiables.
Un nuevo inspector para modelos de ARN
RNArank está diseñado para juzgar la calidad de una forma propuesta de ARN sin necesidad de saber cómo se generó esa forma. Tanto si el modelo procede de un sistema de aprendizaje profundo, de una simulación basada en física o de un experto humano, RNArank analiza únicamente las coordenadas 3D finales. Entonces plantea, en efecto, “¿Esta estructura parece un ARN realista?” Este tipo de evaluación de calidad independiente es esencial porque, a diferencia del mundo de las proteínas, donde herramientas como AlphaFold a menudo ofrecen respuestas muy fiables de serie, la predicción de ARN sigue beneficiándose de la combinación de múltiples métodos y del criterio humano, y de una forma inteligente de ordenar los modelos resultantes.
Enseñar a la IA cómo es un buen ARN
Para entrenar RNArank, los autores reunieron alrededor de 200 000 estructuras de ARN, que cubren un amplio espectro desde claramente erróneas hasta casi perfectas. Estas se construyeron a partir de estructuras experimentales conocidas empleando una gran variedad de enfoques, incluidos predictores modernos de aprendizaje profundo, simulaciones de dinámica molecular que imitan el movimiento atómico y deformaciones deliberadas de estructuras precisas para crear “señuelos”. Para cada modelo, el equipo calculó cuán estrechamente coincidía con el ARN real determinado experimentalmente, usando una puntuación de precisión refinada adaptada al ARN llamada lDDT_RNA. Esta puntuación se centra en cuánto se reproducen las distancias entre pares de nucleótidos, capturando tanto el plegamiento global como los detalles locales sin ser excesivamente sensible a la longitud de la molécula.
Cómo RNArank lee y puntúa un ARN
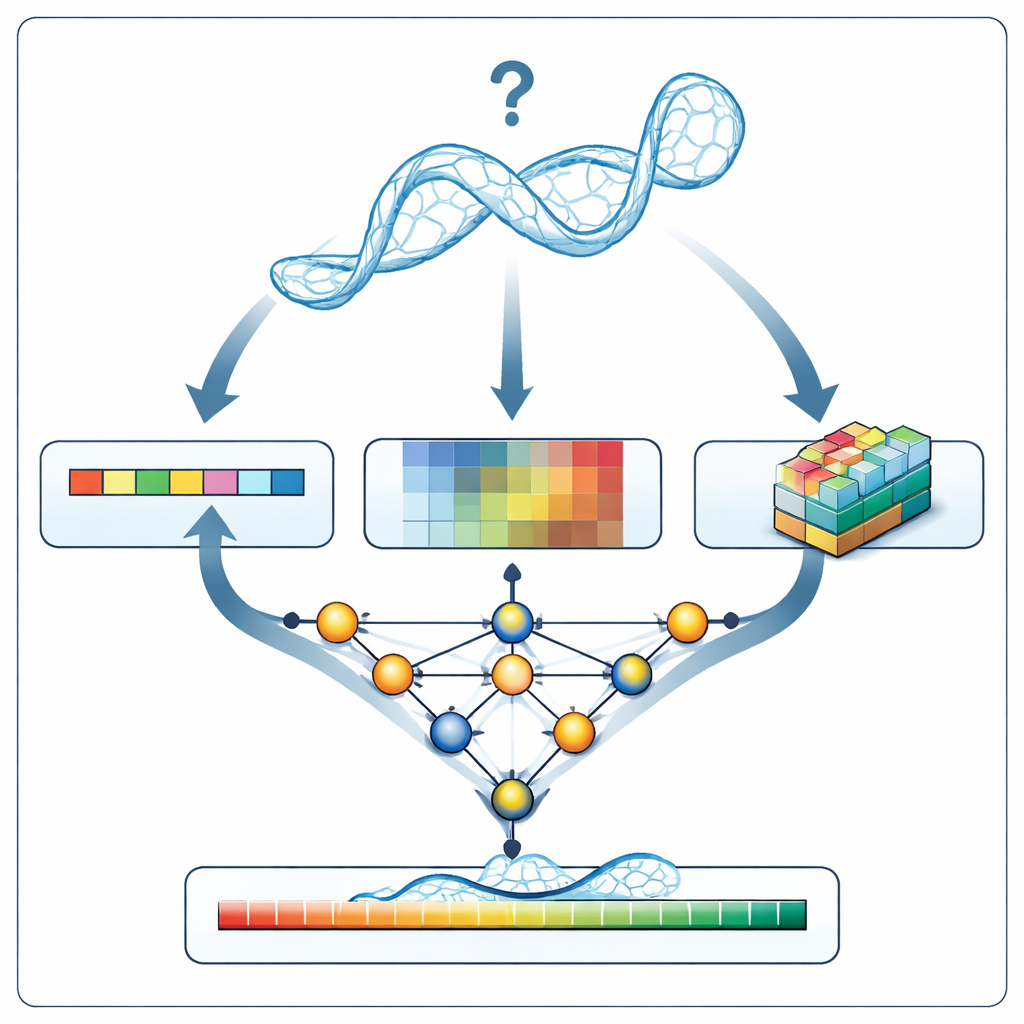
Cuando RNArank examina un nuevo modelo de ARN, primero traduce la estructura en tres tipos de información: una descripción 1D de la secuencia y la geometría de la columna vertebral a lo largo de la cadena, descripciones 2D de cómo se relaciona cada par de nucleótidos entre sí (sus distancias, energías de interacción estimadas y posibles choques atómicos) y “voxelizados” 3D, pequeñas rejillas que capturan la nube local de átomos alrededor de cada nucleótido. Una red neuronal multipartita entrelaza estas pistas en una imagen unificada y luego predice dos mapas 2D intermedios: qué nucleótidos probablemente estén en contacto y cuánto es probable que cada distancia modelada se desvíe de la estructura verdadera desconocida. A partir de estos mapas, RNArank reconstruye tanto una puntuación de confianza por nucleótido como una puntuación global para todo el modelo de ARN.
Poner el método a prueba
El equipo evaluó RNArank en tres conjuntos de datos exigentes: un conjunto de 24 ARN recién resueltos del Protein Data Bank y los objetivos de ARN de dos concursos internacionales de predicción a ciegas, CASP15 y CASP16, donde muchos grupos envían modelos sin conocer las respuestas de antemano. A lo largo de miles de estructuras candidatas, las puntuaciones de RNArank siguieron la calidad real de los modelos más de cerca que varios métodos consolidados basados en energía y otros enfoques de aprendizaje profundo. Fue especialmente eficaz a la hora de seleccionar los mejores o casi mejores modelos de un conjunto y de identificar qué partes de una estructura eran probablemente poco fiables. Los autores también mostraron que RNArank mantuvo su rendimiento incluso en ARN cuya secuencia era claramente distinta de las vistas durante el entrenamiento, señal de una generalización genuina más que de memorización.
Límites actuales y perspectivas futuras
RNArank no es perfecto: todavía tiene dificultades con ARN especialmente flexibles que adoptan muchas conformaciones y con ARN que cambian su forma cuando quedan inmovilizados por proteínas dentro de grandes máquinas moleculares. Sin embargo, es lo suficientemente rápido como para manejar muchos modelos de ARN de unos pocos cientos de nucleótidos en sólo segundos, y ya ayuda a servidores automatizados a elegir predicciones de mayor calidad en pruebas comunitarias. Al proporcionar un juez independiente del método y basado solo en la estructura de los modelos de ARN, RNArank ofrece a los biólogos un filtro más preciso para transformar la salida informática en bruto en hipótesis estructurales fiables, acercando el campo un paso más hacia la predicción rutinaria y de confianza de las formas del ARN y, a su vez, hacia una comprensión más profunda de cómo funcionan estas moléculas versátiles.
Cita: Liu, X., Wang, W., Du, Z. et al. Quality assessment of RNA 3D structure models using deep learning and intermediate 2D maps. Commun Biol 9, 293 (2026). https://doi.org/10.1038/s42003-026-09582-2
Palabras clave: Estructura 3D de ARN, aprendizaje profundo, evaluación de la calidad de modelos, bioinformática estructural, RNArank