Clear Sky Science · es
Plataforma de cribado virtual impulsada por IA identifica nuevos candidatos inhibidores de NSUN2 para terapia contra el cáncer dirigida: un enfoque computacional de descubrimiento de fármacos
Nuevas maneras de burlar cánceres resistentes
Muchos cánceres se vuelven letales no solo porque se desarrollan, sino porque aprenden a evadir nuestros mejores fármacos. Este estudio explora una vía prometedora para apagar a un ayudante clave del crecimiento tumoral, usando inteligencia artificial para analizar más de cien millones de posibles medicamentos en un ordenador antes de que ninguno se mezcle en un tubo de ensayo real.
Un interruptor oculto dentro de las células cancerosas
En el interior de nuestras células, una enzima llamada NSUN2 actúa como un marcador químico para el ARN, la molécula que ayuda a convertir genes en proteínas. Al añadir pequeñas marcas químicas al ARN, NSUN2 puede hacer que los mensajes relacionados con el crecimiento sean más estables y más fáciles de leer. Muchos tumores, incluidos los de pulmón, estómago, páncreas y mama, aumentan los niveles de NSUN2, lo que potencia su capacidad de dividirse, diseminarse y resistir fármacos dirigidos. Sin embargo, a pesar de su importancia, existen muy pocos candidatos farmacológicos que puedan reducir NSUN2 de forma segura, especialmente inhibidores reversibles que no dañen la enzima de manera permanente.
Permitir que la IA busque en un mar de moléculas
El descubrimiento de fármacos tradicional tendría dificultades para probar millones de moléculas contra NSUN2 en el laboratorio, porque cada experimento requiere mezclas complejas de ARN y reactivos auxiliares. En su lugar, los investigadores construyeron una canalización totalmente digital. Partieron de una forma tridimensional predicha de la NSUN2 humana generada por AlphaFold, un sistema de IA que ha revolucionado la predicción estructural. Para asegurar que este modelo fuera fiable, lo alinearon con una enzima estrechamente relacionada cuya estructura se conoce por estudios de rayos X. El bolsillo crítico donde NSUN2 se une a su molécula auxiliar natural resultó estar fuertemente conservado, lo que dio al equipo la confianza de que el acoplamiento virtual de posibles fármacos en este sitio sería significativo.
De cientos de millones a unos pocos
Con el bolsillo objetivo definido, el equipo recurrió a una vasta base de datos pública de moléculas comprables. Primero acoplaron un conjunto de entrenamiento de compuestos en el bolsillo de NSUN2 y usaron las puntuaciones resultantes para enseñar a un modelo de aprendizaje automático qué formas eran más prometedoras. Ese modelo luego cribó rápidamente alrededor de 350 millones de moléculas y marcó aproximadamente 101 millones como posibles “hits”. Para reducir aún más el campo, la fracción superior fue reacoplada con cálculos más cuidadosos, y solo se conservaron las mejores 12 000, con fuerte unión predicha. Estas se sometieron después a una batería de verificaciones de seguridad basadas en ordenador que estimaron cómo el cuerpo podría absorber, distribuir, metabolizar y tolerar cada candidato. Tras estos filtros, quedaron solo 34 moléculas que parecían tanto potentes como con características farmacológicas adecuadas.
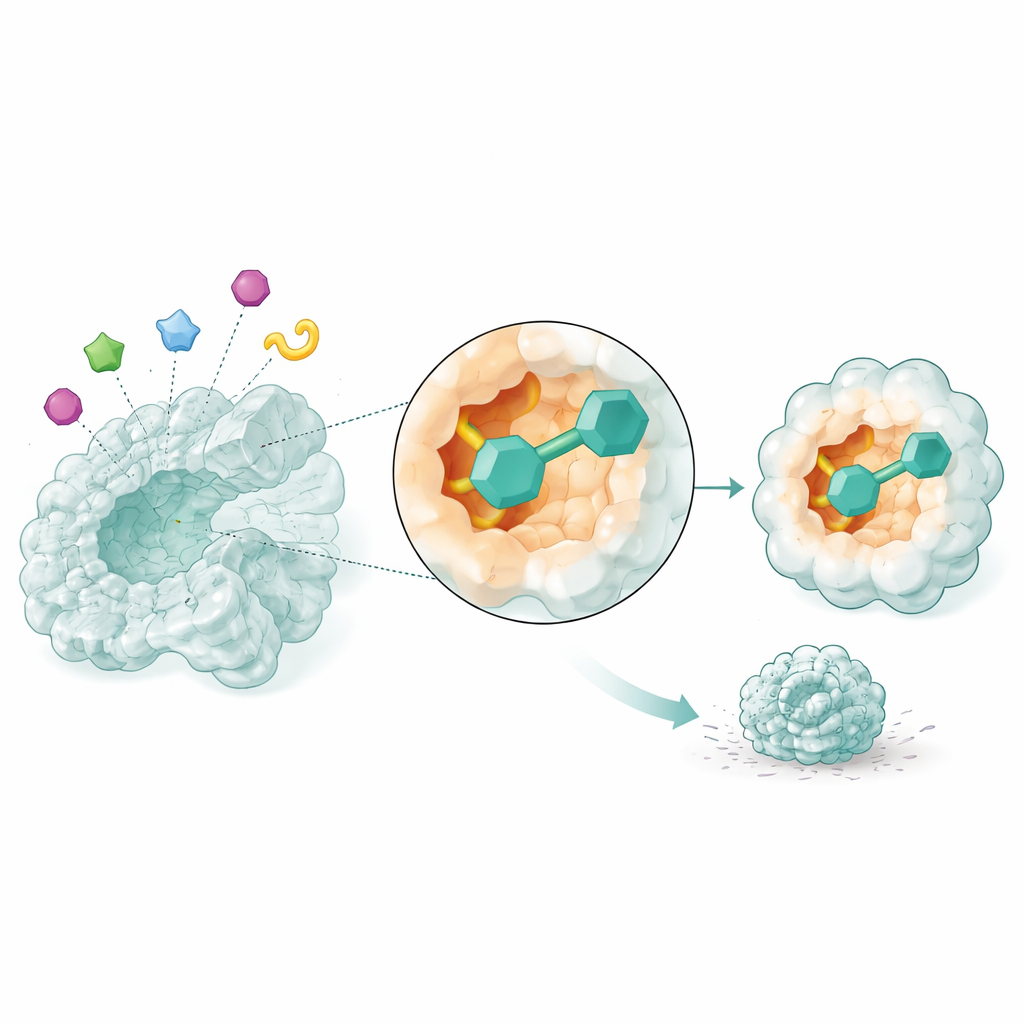
Observando los fármacos candidatos en movimiento
Las instantáneas estáticas no son suficientes para saber si un fármaco realmente se mantendrá unido a su objetivo. Por ello, los investigadores utilizaron simulaciones de dinámica molecular, que modelan cómo se mueven los átomos en el tiempo, para observar cómo interactuaban los tres candidatos más prometedores con NSUN2 durante 50 milmillonésimas de segundo. Dos compuestos, identificados solo por sus códigos de base de datos, formaron complejos especialmente estables: la estructura de la enzima se mantuvo compacta, sus regiones clave permanecieron firmes en lugar de flácidas, y las pequeñas moléculas conservaron un ajuste ceñido dentro del bolsillo mientras formaban contactos persistentes. Estas simulaciones sugieren que los dos compuestos podrían bloquear de forma fiable la actividad de NSUN2 en células reales.
Qué podría significar esto para tratamientos futuros
Aunque todos los resultados de este trabajo proceden de cálculos y aún deben demostrarse en el laboratorio, el estudio ofrece una lista breve de puntos de partida realistas para nuevos fármacos bloqueadores de NSUN2. Dado que NSUN2 ayuda a las células cancerosas a estabilizar señales de crecimiento y supervivencia, tales medicinas podrían debilitar los tumores y potencialmente volver a sensibilizarlos a las terapias dirigidas existentes, especialmente en cánceres de pulmón que han desarrollado resistencia. Igualmente importante, el estudio presenta una receta general para usar IA y modelos basados en la física para explorar espacios químicos enormes de modo rápido y económico, ofreciendo un atajo potente hacia la próxima generación de tratamientos oncológicos de precisión.
Cita: Yu, S., Peng, Q., Wei, W. et al. AI-driven virtual screening platform identifies novel NSUN2 inhibitor candidates for targeted cancer therapy: a computational drug discovery approach. npj Precis. Onc. 10, 98 (2026). https://doi.org/10.1038/s41698-026-01296-2
Palabras clave: NSUN2, epitranscriptómica, cribado virtual con IA, descubrimiento de fármacos contra el cáncer, metilación del ARN